Clear Sky Science · nl
Biochemische principes van miRNA-doelherkenning bij fruitvliegen
Kleine RNA-berichtjes die vliegencellen sturen
In elke cel van de fruitvlieg fungeren kleine moleculen, microRNA’s genaamd, als kwaliteitscontrole-inspecteurs: ze bepalen welke genetische boodschappen worden omgezet in eiwit en welke worden stilgezet. Deze studie stelt een deceptief eenvoudige vraag: hoe herkennen deze microRNA’s precies hun doelwitten in vliegen? Door die vraag te beantwoorden, komen de auteurs dichter bij het vermogen om op basis van sequentie alleen te voorspellen welke genen tijdens ontwikkeling, gedrag en ziekte omhoog- of omlaag worden bijgedraaid.
Hoe kleine RNA’s genen naar beneden bijstellen
MicroRNA’s zijn korte RNA-stukjes, ongeveer 22 bouwstenen lang, die in fruitvliegen samenwerken met een eiwit genaamd Argonaute 1 (Ago1). Gezamenlijk scannen ze veel langere boodschapper-RNA’s (mRNA’s), die instructies voor eiwitproductie dragen. Wanneer een microRNA een gedeeltelijk overeenkomend stukje op een mRNA vindt, kan het Ago1-complex het mRNA doorknippen of de translatie naar eiwit blokkeren, waardoor de genuitvoer vermindert. Bij zoogdieren hebben onderzoekers deze herkenningsregels uitgebreid in kaart gebracht en een verrassende verscheidenheid aan bindingsmodi ontdekt. In vergelijking daarmee waren de regels in vliegen minder duidelijk, hoewel microRNA’s daar sleutelprocessen regelen zoals groei, timing van ontwikkeling en slaap–waakcycli.
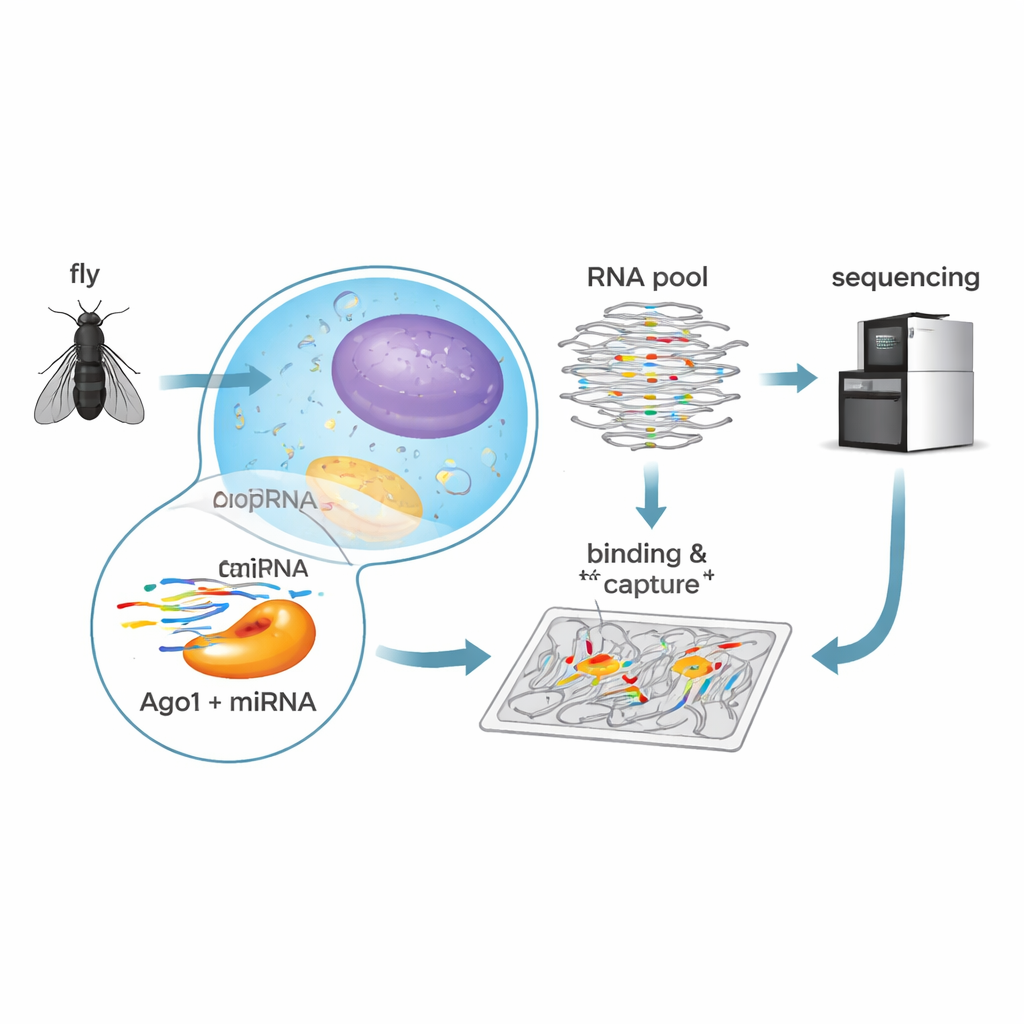
Een hoogdoorvoermeting van binding
Om deze regels in fruitvliegen te ontcijferen, gebruikten de onderzoekers een biochemische methode genaamd RNA Bind-n-Seq. Ze beladen zuiver Ago1 uit vliegen met een van vijf overvloedige microRNA’s — let-7, bantam, miR-184, miR-11 of miR-124 — elk met bekende rollen in vliegontwikkeling en hersenfunctie. Vervolgens mengden ze elk Ago1–microRNA-complex met een enorme bibliotheek synthetische RNA’s met willekeurige sequenties. Na binding scheidden ze gebonden van niet-gebonden RNA’s, sequentieerden de gebonden moleculen en gebruikten statistische modellering om te berekenen hoe sterk elk sequentietype werd herkend. Deze aanpak leverde kwantitatieve bindingssterkten voor honderden verschillende doelpatronen binnen één reeks experimenten op.
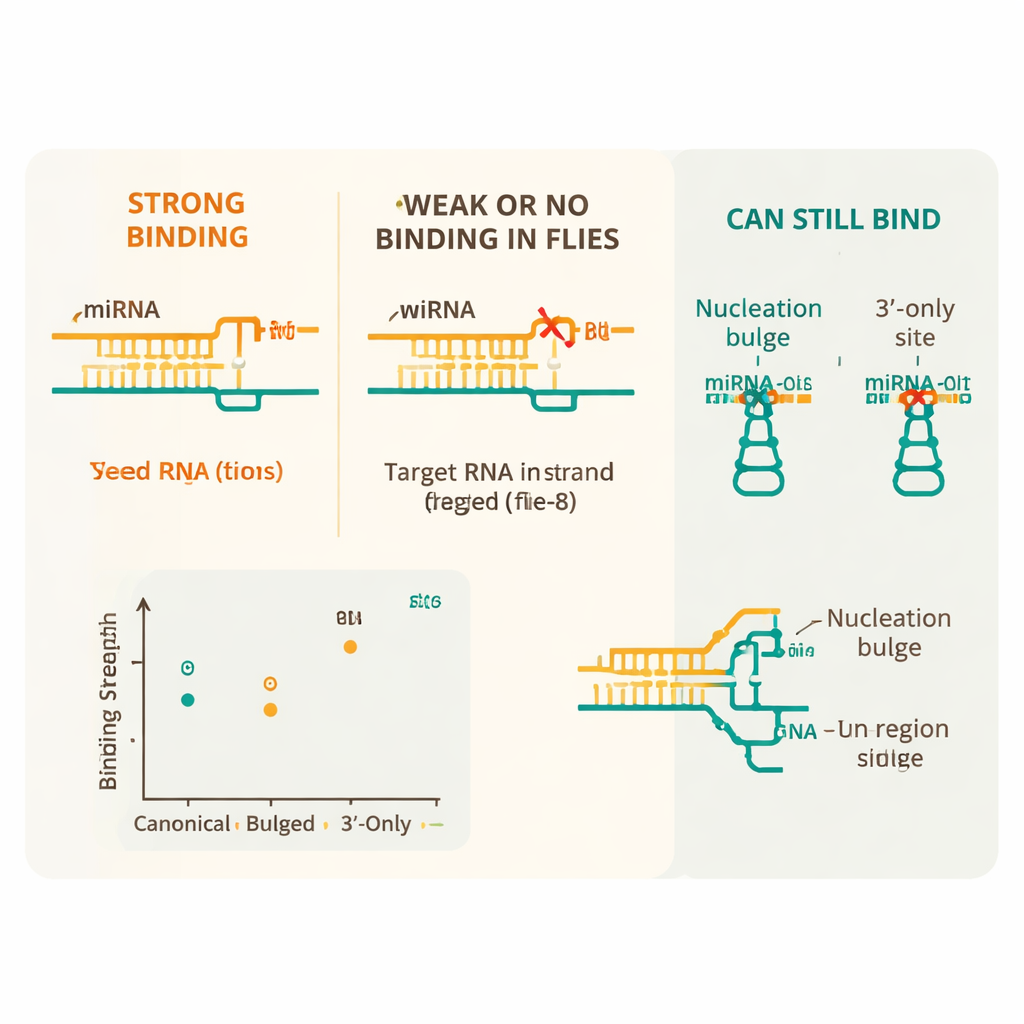
Eenvoudige regels met een paar slimme uitzonderingen
De resultaten tonen aan dat vlieg-microRNA’s een strikter regelboek volgen dan hun zoogdiertegenhangers. De belangrijkste eigenschap is een ‘‘seed’’-regio — posities 2 tot en met 8 van het microRNA — die bijna perfect moet paren met het mRNA voor sterke binding. Canonieke seed-overeenkomende sites, vooral die met acht overeenkomende basen en een bepaald aangrenzend nucleotide, binden met de hoogste affiniteit. Daarentegen verminderde zelfs één verkeerde wobbelbinding (een zogeheten G:U-paar) binnen deze seed de binding sterk, en twee of meer dergelijke imperfecties maakten de interactie niet meer onderscheidbaar van de achtergrond. Mismatches in het midden van de seed waren bijzonder schadelijk, wat benadrukt hoe gevoelig Ago1 dit kernsegment afleest.
Verborgen flexibiliteit buiten de kernmatch
Ondanks deze algemene rigiditeit onthulde de studie meerdere belangrijke ontsnappingswegen waardoor sommige imperfecte sites toch herkend worden. Extra paring tussen het staartige uiteinde van het microRNA en het mRNA kon een enkele fout in de seed compenseren en sterke binding herstellen. Bepaalde bijzondere rangschikkingen, genoemd nucleation-bulges — waarbij een extra nucleotide uitsteekt vlakbij de seed — binden ook bijna even goed als standaardsites. Het team toonde verder aan dat Ago1 ‘‘3′-only’’ sites kan binden, waarbij de seed niet betrokken is maar het staartje van het microRNA sterk pareert, en dat het efficiënt doelen kan knippen met lange centrale matches. Tenslotte bleek dat de omliggende sequentie uitmaakt: sites omgeven door A- en U-rijke regio’s, die RNA doorgaans minder gestructureerd en toegankelijk houden, sterker gebonden werden dan dezelfde sites ingebed in stijvere sequentiecontexten.
Waarom deze regels belangrijk zijn voor de biologie van vliegen
Samengevat laten deze bevindingen zien dat vlieg-microRNA’s over het algemeen bijna perfecte matches in hun seed-regio eisen, met slechts een beperkt aantal toegestane uitzonderingen. Dit eenvoudigere en strakkere regelsysteem contrasteert met de bredere flexibiliteit die bij zoogdieren wordt waargenomen. Door harde cijfers te leveren over hoe sterk verschillende doelpatronen binden, legt het werk de basis voor next-generation computertools die nauwkeuriger kunnen voorspellen welke vlieggenen door welke microRNA’s worden gereguleerd. Voor niet-specialisten is de hoofdboodschap dat genregulatie in vliegen, hoewel gestuurd door piepkleine RNA’s, volgens duidelijke biochemische principes verloopt — principes die nu gebruikt kunnen worden om complexe eigenschappen zoals ontwikkeling, gedrag en ziektebestendigheid te begrijpen en uiteindelijk te beïnvloeden.
Bronvermelding: Vega-Badillo, J., Zamore, P.D. & Jouravleva, K. Biochemical principles of miRNA targeting in flies. Nat Commun 17, 1641 (2026). https://doi.org/10.1038/s41467-026-68360-0
Trefwoorden: microRNA, Drosophila, Argonaute, RNA-binding, genregulatie