Clear Sky Science · nl
Een lange weg naar betrouwbare en volledige genomen van medicinale planten
Waarom DNA-kaarten van planten van belang zijn voor de menselijke gezondheid
Veel van de krachtigste geneesmiddelen van vandaag — van kankertherapieën zoals paclitaxel tot pijnstillers zoals morfine en het antimalariamiddel artemisinine — komen uit planten. Voor de meeste medicinale planten ontbreekt het onderzoekers echter nog aan een compleet "instructieboek" van hun DNA. Deze review verklaart hoe nieuwe genoomtechnologieën onze mogelijkheid om die handleidingen te lezen transformeren, waarom huidige plantgenomen vaak nog onvolledig of foutgevoelig zijn, en hoe echt nauwkeurige genomen betere medicijnen, duurzamere productie en verbeterde bescherming van waardevolle soorten kunnen ontsluiten.
De belofte van het lezen van de blauwdrukken van medicinale planten
Al millennia vertrouwen mensen op kruidenremedies, en de moderne farmacologie put nog steeds veel uit plantaardige natuurlijke producten. Deze gespecialiseerde moleculen — alkaloïden, terpenoïden, fenolische verbindingen en vele anderen — worden gemaakt via ingewikkelde metabole routes die in het plantengenoom gecodeerd zijn. Tot voor kort moesten wetenschappers deze routes stuk voor stuk reconstrueren met trage, arbeidsintensieve methoden zoals isotopen-tracing en het kloneren van één gen per keer. De komst van betaalbare, hoogdoorvoerse DNA-sequencing veranderde dat landschap. In februari 2025 waren genomen van 431 medicinale planten (over 203 soorten) gesequenced, wat onderzoekers een systematische manier gaf om naar routegenen te zoeken, te begrijpen hoe waardevolle verbindingen gereguleerd worden en te onderzoeken hoe deze chemieën evolueerden.
Een opleving in sequencen, maar veel onvolmaakte genomen
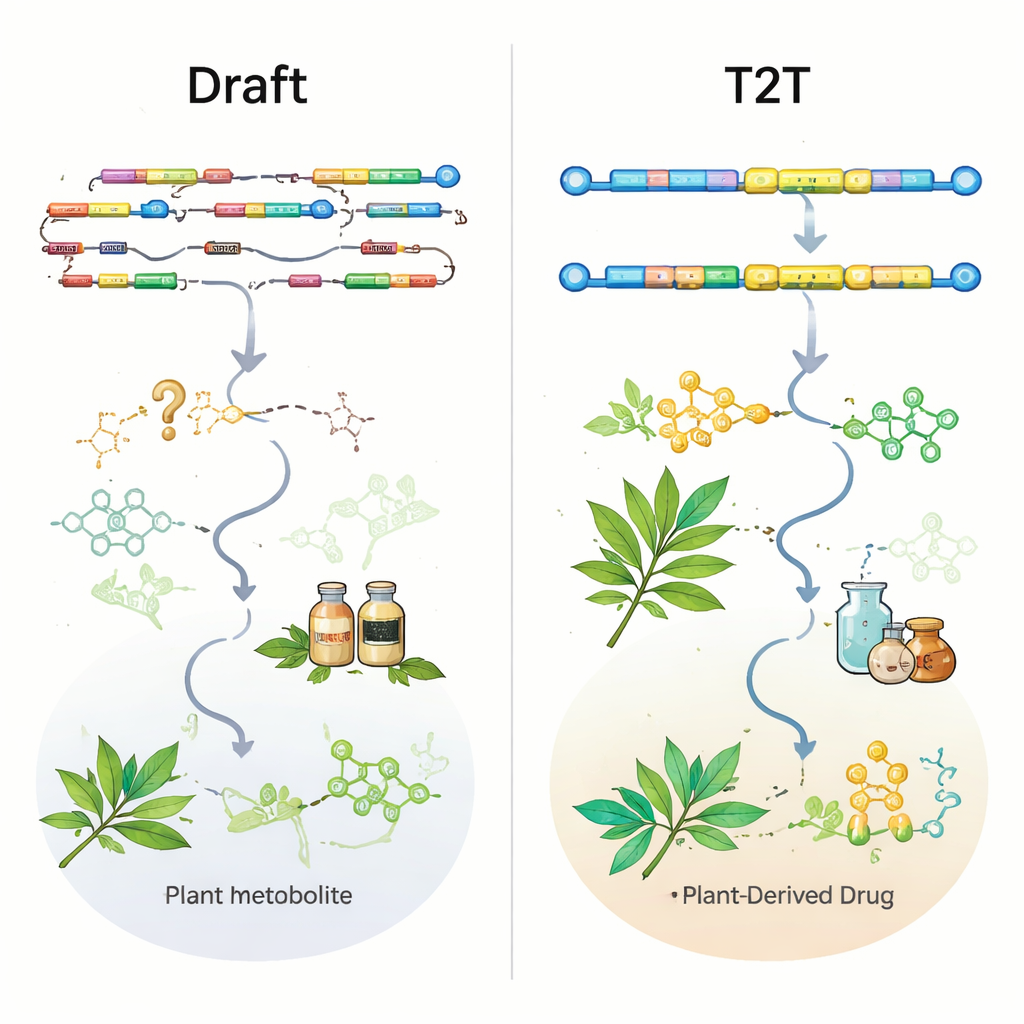
Long-read sequencing-technologieën van PacBio en Oxford Nanopore, gecombineerd met kortere Illumina-reads en chromosoom-niveau mappingmethoden zoals Hi-C, hebben de kwaliteit van plantgenomen sterk verbeterd. Bijna de helft van alle assemblages voor medicinale planten werd pas in de afgelopen drie jaar vrijgegeven, en de meeste recente genomen zijn nu op chromosoomschaal gebouwd. De review laat echter zien dat kwantiteit de kwaliteit heeft ingehaald. Meer dan de helft van de genomen bestaat alleen als een initiële versie, veel blijven op conceptniveau, en slechts 11 medicinale planten hebben "telomeer-tot-telomeer" (T2T) gapless assemblages die centromeren en andere repetitieve regio’s volledig vastleggen. Standaardmaten zoals N50 (een maat voor continuïteit) en BUSCO-scores (een maat voor geconserveerde genen) zien er over het algemeen veelbelovend uit, maar ze kunnen kritieke leemten verbergen precies daar waar belangrijke biosynthetische genen zitten.
Verborgen leemten waar de medicijngenen zouden moeten zijn
Om te testen hoe bruikbaar huidige genomen werkelijk zijn, bestudeerden de auteurs bekende, experimenteel gevalideerde routegenen in negen goed onderzochte medicinale planten. Zelfs in sommige chromosoom-niveau assemblages waren belangrijke enzymen voor verbindingen zoals ginsenosiden in ginseng of artemisinine in Artemisia annua ofwel volledig afwezig of slechts gedeeltelijk vastgelegd. In andere gevallen waren genen wel aanwezig in de ruwe genoomsequentie maar ontbraken ze of waren ze ingekort in de officiële genannotaties, waardoor ze moeilijk te vinden zijn. Een opvallend voorbeeld komt van het coumarine-producerende kruid Peucedanum praeruptorum: een oudere chromosoom-niveau genoom verbrak één sleutelgen en miste twee anderen; een nieuwere T2T-assemblage herstelde deze genen niet alleen maar toonde ook aan dat verschillende van deze genen bij elkaar zitten in een dicht opeengepakt biosynthetisch gencluster. Dergelijke clusterkaarten zijn precies wat onderzoekers nodig hebben om planten of microben te ontwerpen die medicijnen efficiënter produceren.
Waarom plantgenomen zo moeilijk te assembleren zijn
Medicinale planten vormen speciale uitdagingen die verder gaan dan die van veel teeltgewassen. Hun genomen bevatten vaak hoge niveaus van heterozygositeit (veel DNA-verschillen tussen de twee kopieën van elk chromosoom), frequente polyploïdie (meerdere sets chromosomen) en grote fracties repetitief DNA — kenmerken die assemblage-algoritmen verwarren en leiden tot breuken of foutieve samenvoegingen. Ongeveer een derde van de gesequencede medicinale planten heeft genomen met meer dan 70% repetitief materiaal, en meer dan een kwart toont zeer hoge heterozygositeit. Het fokken van sterk ingeburgerde lijnen of het isoleren van haploïde weefsels kan helpen, maar dat is traag, duur of biologisch moeilijk voor veel soorten. Nieuwe strategieën die elke ouderlijke haplotype afzonderlijk assembleren, en krachtigere algoritmen afgestemd op repeat-rijke, polyploïde genomen, beginnen deze hindernissen te verlichten maar zijn nog niet routinematig.
Van genomen naar nieuwe medicijnen en toekomstige richtingen
Wanneer genomen goed genoeg zijn, worden ze krachtige motoren voor ontdekking. Onderzoekers kunnen volledig genoomdata combineren met transcriptomica, metabolomica en synthetische biologie om enzymen, regulatorische genen en biosynthetische genclusters te pinpointen die de productie van hoogwaarde verbindingen controleren. Deze inzichten hebben al geleid tot reconstructie van complexe plantenroutes — zoals die voor vinblastine, paclitaxel en vele andere geneesmiddelen — in gist of modelplanten, wat een pad opent naar stabiele, grootschalige bioproductie. Vooruitkijkend pleiten de auteurs voor een verschuiving van "één ruwe genoom per soort" naar meerdere, hoogwaardige, T2T- en haplotype-opgelsoste assemblages die intrasoortelijke diversiteit vastleggen, vergelijkbaar met pan-genomen in gewasonderzoek. Het koppelen van deze referentiegenomen aan grootschalig resequencen, geavanceerde fenotypering en opkomende single-cell en ruimtelijke transcriptomica zou moeten verhelderen hoe milieu, celtype en gen-netwerken samenwerken om medicinale chemie vorm te geven.
Wat dit betekent voor patiënten en de planeet
De kernboodschap van de review is dat betrouwbare, volledige genomen van medicinale planten geen luxe zijn; ze vormen de basis om eeuwenoude kruidencatalogi om te zetten in precieze, moderne therapieën. Betere genomen helpen wetenschappers ontbrekende stappen in medicijnroutes te vinden, veiligere en overvloediger voorraden kritische geneesmiddelen te ontwerpen en alternatieve soorten te identificeren die dezelfde verbindingen kunnen produceren. Ze zullen ook het behoud en duurzaam gebruik van bedreigde medicinale planten begeleiden, van de meeste soorten ontbreekt nog steeds elke genomische bron. Kortom, het voltooien van het nauwkeurig in kaart brengen van deze genomen kan de geneesmiddelenontdekking versnellen, toeleveringsketens stabiliseren en de botanische diversiteit behouden — wat uiteindelijk de menselijke gezondheid ten goede komt.
Bronvermelding: Cheng, LT., Wang, ZL., Zhu, QH. et al. A long road ahead to reliable and complete medicinal plant genomes. Nat Commun 16, 2150 (2025). https://doi.org/10.1038/s41467-025-57448-8
Trefwoorden: genoom van medicinale planten, biosynthetische genclusters, telomeer-tot-telomeer genomen, biosynthese van natuurlijke producten, synthetische biologie