Clear Sky Science · ja
深層学習と中間2Dマップを用いたRNA三次元構造モデルの品質評価
なぜRNAの形を評価することが重要か
細胞内では、RNA分子が複雑な三次元形状にねじれて折りたたまれ、どの遺伝子がオンになるかを制御したり、化学反応を導いたり、ウイルスの防御に関与したりします。現在では強力な計算プログラムが多くの形を推定できますが、基本的な問題が残ります。コンピュータが同じRNAに対して数十〜数百の候補形状を出したとき、どれが実際の形に近いのかをどう判定するか、という点です。本論文はRNArankという人工知能ツールを紹介します。これはRNA 3Dモデルを構造の品質検査員のように評価して、研究者が最も信頼できる予測に集中できるようにするものです。
RNAモデルのための新しい検査員
RNArankは、その形状がどのように作られたかを知らなくても、提案されたRNA形状の品質を判定するよう設計されています。モデルが深層学習由来であろうと、物理ベースのシミュレーションであろうと、人間の専門家によるものであろうと、RNArankは最終的な三次元座標だけを見ます。そして実質的に「この構造は現実的なRNAに見えるか?」と問いかけます。独立した品質評価は重要です。タンパク質の世界ではAlphaFoldのようなツールがしばしば高い信頼性を出しますが、RNA予測は複数の手法や人間の洞察を組み合わせること、そして生成されたモデルを賢くランク付けする手段から依然利益を得るためです。
AIに「良いRNA」を教える
RNArankを訓練するために、著者らは約20万件のRNA構造を集め、明らかに誤ったものからほぼ完全なものまで幅広くカバーしました。これらは既知の実験構造から、最新の深層学習予測器、原子運動を模倣する分子動力学シミュレーション、正確な構造に意図的な歪みを加えた“デコイ”など多様な手法で作成されました。各モデルについて、著者らは実験的に決定された実際のRNAとどれほど一致するかを、RNA向けに調整された改良精度スコアlDDT_RNAを用いて算出しました。このスコアはヌクレオチド対間の距離がどれだけ再現されているかに焦点を当て、全体の折りたたみと局所的な詳細の両方を捉えつつ、分子長に対して過度に敏感にならないよう設計されています。
RNArankはRNAをどのように読み取り評価するか
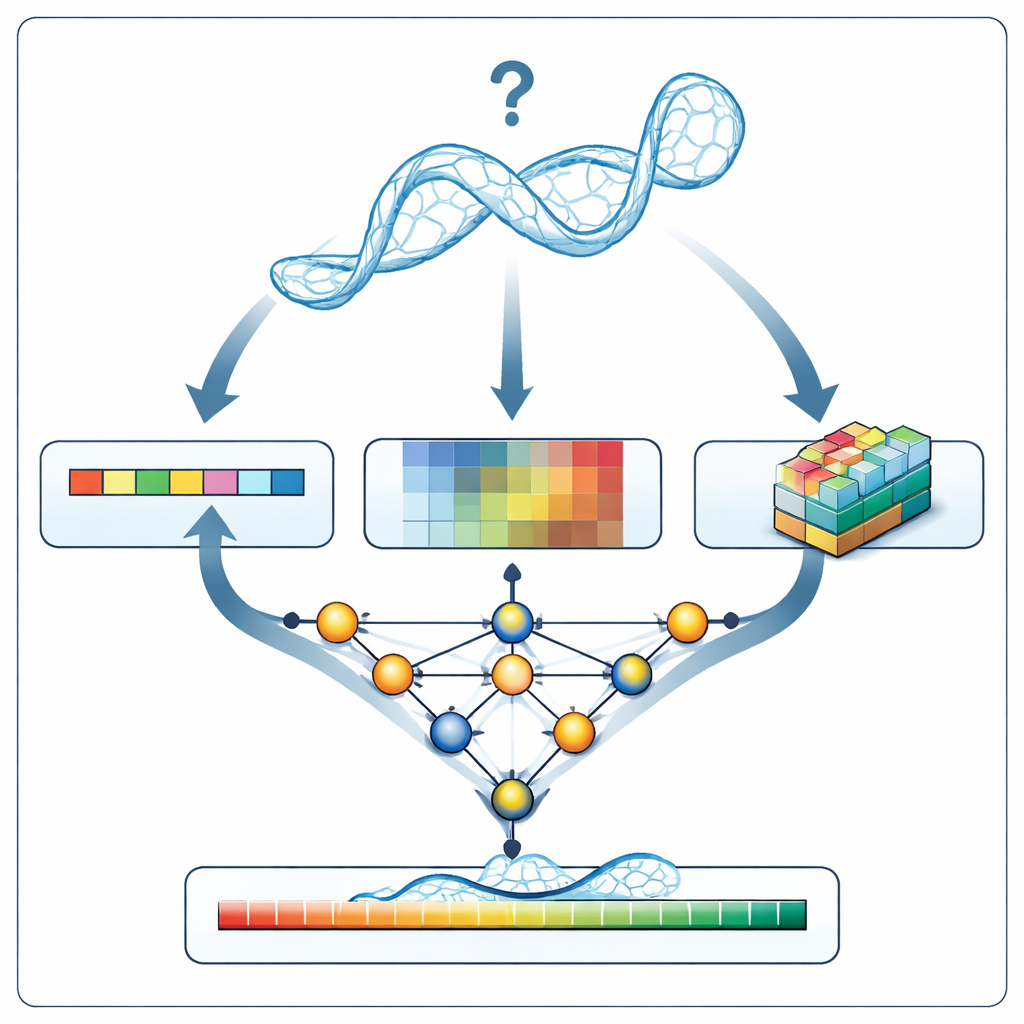
新しいRNAモデルを評価するとき、RNArankはまず構造を三種類の情報に変換します。鎖に沿った配列と主鎖の幾何を表す1D記述、各ヌクレオチド対の関係(距離、推定相互作用エネルギー、潜在的な原子衝突)を表す2D記述、そして各ヌクレオチド周辺の原子雲を捉えた小さなグリッド(3D“ボクセル”スナップショット)です。多段構成のニューラルネットワークがこれらの手がかりを統合して、二つの中間2Dマップ――どのヌクレオチドが接触する可能性があるか、各モデル化された距離が未知の真の構造からどれだけずれている可能性があるか――を予測します。これらのマップから、RNArankはヌクレオチドごとの信頼度スコアとRNAモデル全体の総合スコアの両方を再構築します。
手法の検証
著者らはRNArankを三つの厳しいデータセットでベンチマークしました:Protein Data Bankで新たに解かれた24件のRNA群、および多くのグループが事前に答えを知らずにモデルを提出する国際的なブラインド予測コンテストCASP15とCASP16のRNAターゲットです。何千もの候補構造にわたって、RNArankのスコアは既存のいくつかのエネルギーに基づくスコアリング法や他の深層学習アプローチよりも実際のモデル品質をより正確に追跡しました。特にプールから最良または準最良のモデルを選び出す点や、構造のどの部分が信頼できない可能性が高いかを特定する点で強みを示しました。さらに、訓練時に見た配列と明らかに異なるRNAについても性能を維持したことが示され、単なる暗記ではなく真の一般化を示す兆候となりました。
現状の限界と将来の展望
RNArankは完璧ではありません。多様な形をとる特に柔軟なRNAや、大きな分子機械内でタンパク質に拘束されることで形を変えるRNAに対しては依然苦戦します。しかし、数百ヌクレオチド程度のRNAについて多数のモデルを数秒で処理できるほど高速であり、コミュニティ全体のテストでは自動化サーバーがより高品質な予測を選ぶのに既に役立っています。手法に依存せず構造のみを基準にしたRNAモデルの判定を提供することで、RNArankは生物学者が生の計算出力を信頼できる構造的仮説に変えるための鋭いフィルターを与え、RNA形状の常套的かつ信頼できる予測に一歩近づけるとともに、これら多用途分子の働きに関するより深い洞察をもたらします。
引用: Liu, X., Wang, W., Du, Z. et al. Quality assessment of RNA 3D structure models using deep learning and intermediate 2D maps. Commun Biol 9, 293 (2026). https://doi.org/10.1038/s42003-026-09582-2
キーワード: RNA 3D 構造, 深層学習, モデル品質評価, 構造生物情報学, RNArank