Clear Sky Science · ja
大腸菌コリシンE9の免疫タンパク質と緑膿菌(Pseudomonas aeruginosa)のDNAジャイレースの相互作用を探る:新規抗菌戦略開発のための高度な計算的アプローチ
細菌の兵器を新たな薬へと転用する
抗生物質耐性が広がる中、医師たちは危険な感染を止める手段を失いつつあります。緑膿菌のような治療が難しい病原体は多くの薬剤に耐性を示すことがあります。本研究は新しい発想を得るために細菌自体に着目し、ある微生物が持つ保護用タンパク質を別の微生物の重要な酵素を無力化するために再利用できないかを探ります。高度な計算シミュレーションを用い、小さな“免疫”タンパク質が重要な細菌酵素にしっかり結合し得ることを示し、将来の抗菌薬の新たな可能性を示唆しています。
致命的な毒に対する小さな盾
特定の大腸菌株はコリシンと呼ばれる強力なタンパク質毒素を産生し、近隣の細菌を殺すことがあります。自己中毒を避けるため、これらの細菌は対応する免疫タンパク質も生産します。コリシンE9の免疫タンパク質(しばしばIm9と呼ばれる)は、この毒素の切断ドメインに結合して宿主のDNAを害するのを防ぎます。この結合は非常に特異的で強いため、詳細に理解すれば有害な細菌を制御する新たな手段が得られると以前から考えられてきました。本研究では、Im9がDNAのねじれや複製を管理する緑膿菌の必須酵素であるDNAジャイレースにも結合し得るかを検討しています。
治療が難しい病原体の脆弱な酵素を狙う
緑膿菌は主要な院内感染症原であり、過酷な環境下でも生存し多くの薬剤に耐性を示します。DNAジャイレースはその重要な酵素の一つで、長いDNA鎖のねじれを適切に維持して複製を可能にします。この酵素を阻害すれば細菌の増殖を止められるため、既にいくつかの抗生物質の標的となっています。著者らは深層学習ツールを用いて、緑膿菌のDNAジャイレースの三次元構造を走査し、結合に重要な表面上の「ホットスポット」—アミノ酸のクラスター—を特定しました。これらの領域は酵素の活性ポケットを形成し、通常のDNA処理が行われる場所であり、阻害剤が理想的に結び付くべき箇所です。
分子の握手をシミュレートする
Im9がこれらのホットスポットをつかめるかを確かめるため、研究者らは分子ドッキングプログラムを用いてタンパク質同士を3Dパズルのように仮想的に組み合わせました。まずIm9とDNAジャイレースの利用可能な構造を整え、酵素の欠損ループを修復し、応力のかかった領域を緩和するために短時間のシミュレーションを実行しました。続いてClusProとLightDockという二つの補完的なドッキングツールを用いて多数の候補複合体を生成し、有望な配座を選んで数百ナノ秒にわたる長時間の分子動力学シミュレーションにかけました。これらの時間分解の「ムービー」により、二つのタンパク質が結合時にどのように調整し、屈曲し、より安定した形に落ち着くかを観察できました。
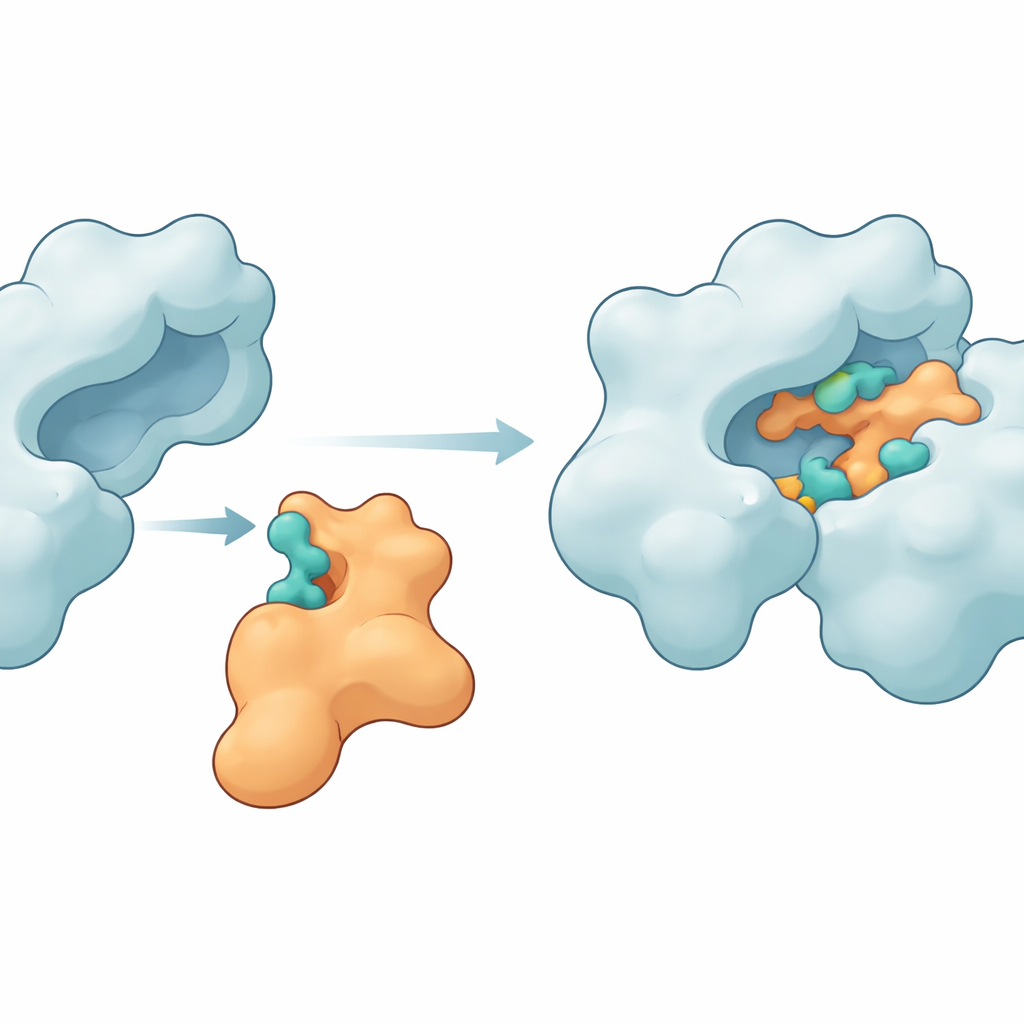
タンパク質を結び付ける主要な接触点
シミュレーションは、Im9が実際にDNAジャイレースと緊密で持続的な複合体を形成し得ることを明らかにしました。酵素側のいくつかのアミノ酸(例えばMET27、ASP47、LYS105、LEU198、ASN199、ARG191、GLU194など)がIm9上の対応する部位と繰り返し水素結合やその他の引力を形成しました。代表的なモデルでは、シミュレーションの大部分で6〜10本の水素結合が維持されており、強固でよく組織化された界面の兆候を示しました。タンパク質の凝縮度や形状のゆらぎといった他の構造指標も、酵素が安定を保ちつつ免疫タンパク質がジャイレース表面に合わせて適度に変形していることを示しました。MM-GBSA法によるエネルギー計算も、これらの接触が電気的相互作用やファンデルワールス寄与に支配される、好ましい(ただし穏やかな)結合自由エネルギーを生むという考えを支持しました。
計算モデルから将来の抗菌薬へ
総合すると、コリシンE9の免疫タンパク質は緑膿菌DNAジャイレースの活性領域に安定に結合し得て、酵素の通常のDNA取り扱い機能を理論上阻害する長寿命の複合体を形成し得ることが示唆されます。これらの知見はすべて計算モデルに基づくものであり、実験的検証がまだ必要ですが、タンパク質ベースの阻害剤がどこにどのように付着し得るかの詳細な設計図を提供します。専門外の読者向けに言えば、自然界の細菌が持つ攻撃と防御の仕組みは、治療が難しい感染症に対する新戦略の着想を与えてくれます。この微視的な“握手”を原子レベルで理解することで、研究者たちはヒト細胞に害を与えずに重要な細菌酵素を遮断する新しい抗菌剤の設計に一歩近づきます。
引用: Alfaraj, R., Alkathiri, F. & Chikhale, R. Investigating Escherichia coli Colicin E9 immunity protein interactions with DNA gyrase of Pseudomonas aeruginosa: advanced computational approach for developing novel antimicrobial strategies. Sci Rep 16, 10786 (2026). https://doi.org/10.1038/s41598-026-44427-2
キーワード: 抗生物質耐性, DNAジャイレース, タンパク質–タンパク質相互作用, 計算による創薬設計, Pseudomonas aeruginosa