Clear Sky Science · ja
Ribo‑Seqライブラリ中の汚染物質除去のための効率的なLNAブロッカーのデータ駆動設計
シーケンスデータのクリーン化が重要な理由
現代生物学では、細胞がどのようにタンパク質を合成しているかを理解するために、数百万に及ぶ小さなRNA断片を読み取ることがよく行われます。しかし、特にリボソームプロファイリング(Ribo‑Seq)と呼ばれる手法では、関連のないRNA断片が混入してシーケンシング容量とコストを浪費することがあります。本研究は、不要な断片を選択的に除去するための、単純でデータ駆動型の分子「ブロッカー」を設計する方法を示しており、同じ実験から得られる有用情報をほぼ倍増させます。
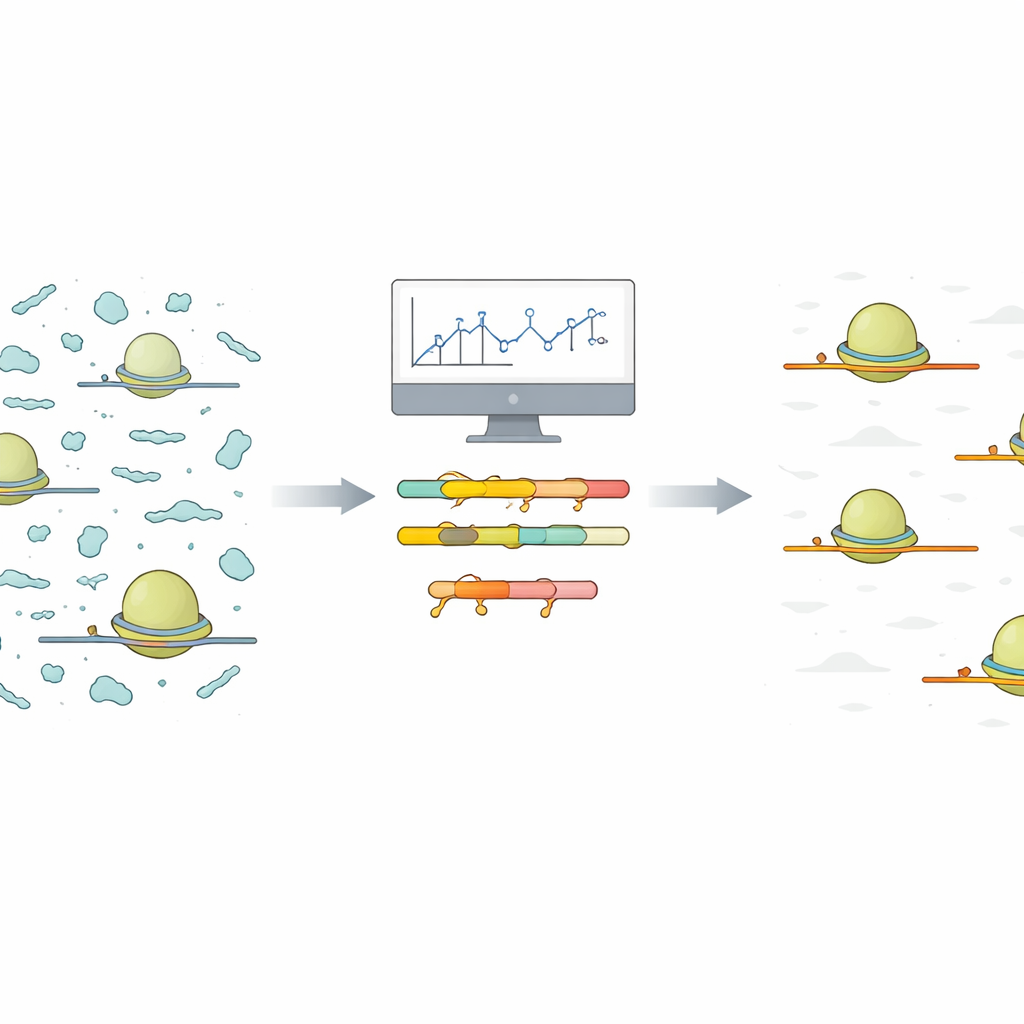
ノイズの多いリボソームスナップショットの問題点
Ribo‑Seqは、細胞内でどのメッセージが実際にタンパク質へ翻訳されているかを瞬時に捉える手法です。そのため、研究者はリボソームと、それが保護している短いメッセンジャーRNA(mRNA)断片を分離します。他は分解され、保護された断片がシーケンスされてゲノムへマッピングされます。しかし実際には、多くの非翻訳RNAの小断片がこの過程をすり抜けてしまいます。これらの汚染断片は量が多くかつ変動が大きいため、シーケンスリードの大部分を占め、本当に重要なタンパク質コードのシグナルに割けるリードが減ってしまいます。
既存のクリーンアップ法が不十分な理由
標準的な戦略は、事前に設計されたキャプチャプローブや酵素で高頻度のリボソームRNAやその他の非翻訳RNAを除去しようとします。これらはターゲットRNAが完全で予測可能な場合には有効ですが、Ribo‑Seqでは意図的にRNAを多種多様な長さに切断します。その断片化は固定プローブセットの標的部位を乱し、除去効率を低下させます。加えて、汚染の混合比は研究対象の種、増殖条件、使用するヌクレアーゼによって異なります。既存のクリーンアップワークフローは複数のインキュベーションや精製工程を伴いがちで、時間がかかり、サンプル損失やバイアスを引き起こすことがあります。
実データから設計するカスタムブロッカー
著者らは、まず本実験で用いるのと同じ条件下で小規模で低コストのパイロットシーケンスを行うスリムなアプローチを提案します。彼らは、そのパイロットから得られたアラインされたリードを取り込み、配列に基づいて類似した汚染断片を自動でグループ化するRスクリプトを提供します。各グループについて、スクリプトは断片全体に共通する最短の配列を報告します。これらの短い共有配列は、ロックドヌクレオチド(LNA)オリゴヌクレオチドと呼ばれる特殊分子の標的部位として理想的です。LNAは化学修飾により標的RNAに非常に強く結合する短い鎖です。スクリプトは直感的なヒートマップや要約プロットも生成し、どの汚染物が支配的か、および大幅なクリーンアップに必要なLNA標的数がわかるようにします。
増幅時のワンステップクリーンアップ
サンプルから物理的に汚染物を取り除く代わりに、この方法はシーケンシングライブラリを構築するDNA増幅ステップ中にLNAオリゴヌクレオチドをブロッカーとして用います。著者らは、これらのブロッカーを初期の逆転写ステップで加える場合と後のPCR増幅時に加える場合の両方を試しました。増幅時にLNAを加える方が効率的で必要濃度が低く、テスト対象の汚染物を千倍以上減少させ、鎖の向きに関係なく機能することがわかりました。実用的な設計上のヒントとしては、標準のDNAとLNA構成要素を交互に使うこと、植物のArabidopsisでは最小長さを14単位にすること、ブロッカー自身が誤って伸長されないよう末端を修飾することなどが挙げられます。
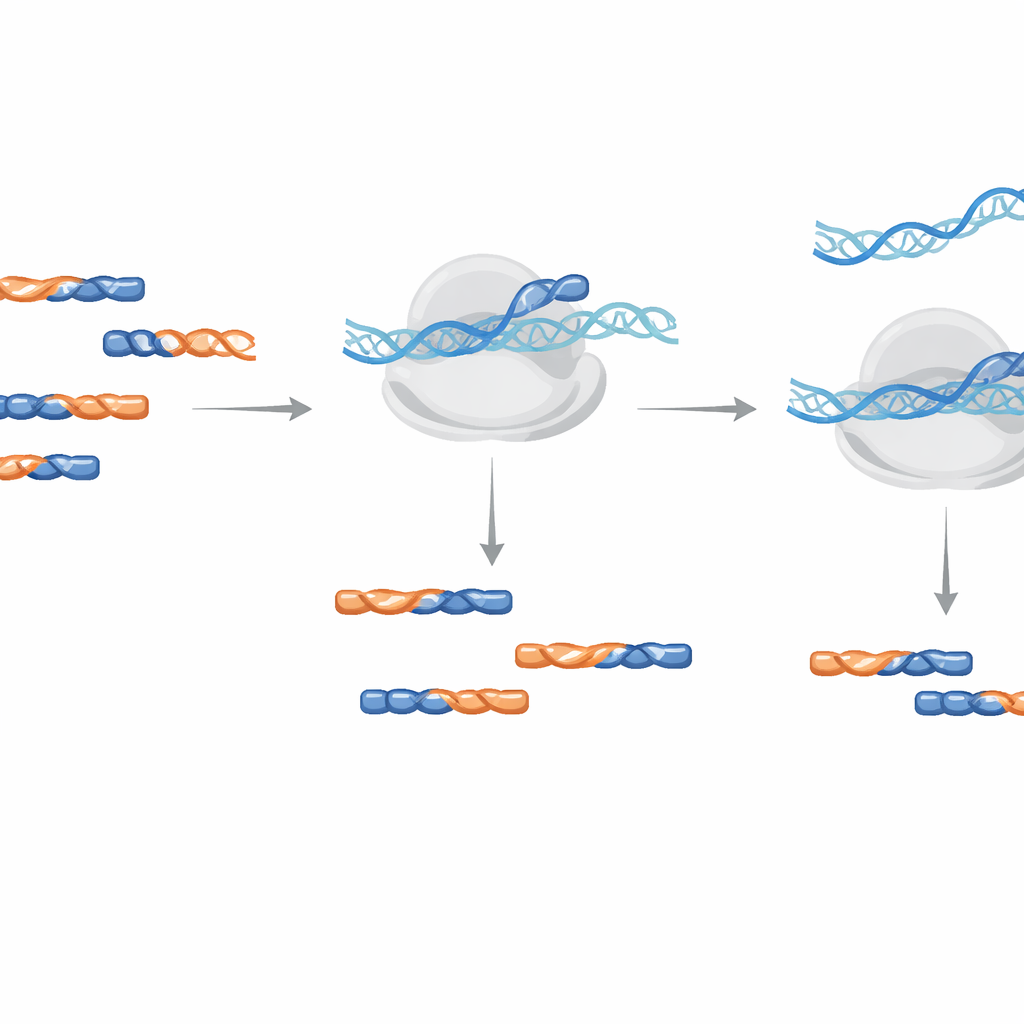
シグナルを歪めずに有用なリードを増やす
実世界での性能を示すために、チームはArabidopsisの典型的な増殖条件で観察される最も一般的な汚染物グループを標的とする5種類のLNAブロッカーを設計しました。ライブラリ増幅時にこの混合物を加えると、確認された汚染物の割合は30%以上減少し、有用なタンパク質コードのリード数はほぼ倍増しました。重要な点として、LNA処理の有無でライブラリ間の遺伝子レベルのリードカウントを比較したところ、値はほぼ完全に一致しました。これは、ブロッカーが本物のmRNAフットプリント由来の生物学的シグナルを歪めることなくジャンク断片を除去していることを示します。
今後の実験にとっての意味
この研究は、短いパイロット実験と使いやすい解析スクリプト、それに少数のカスタムLNAブロッカーを組み合わせることで、混雑したRibo‑Seqライブラリを単一のピペッティング操作でずっとクリーンで情報量の多いデータセットに変えられることを示しています。研究者はランごとにより意義のあるリードを得られ、コストを節約し実験設計を簡素化しつつ、遺伝子翻訳の正確な測定を保持できます。著者らは一般的な植物条件向けの汚染プロファイルとブロッカー設計も提供しており、同様のリソースは多くの生物種について作成可能であると示唆しています。これにより、高品質なリボソームプロファイリングが研究コミュニティ全体でより利用しやすくなる可能性があります。
引用: Ricciardi, D.A., Peter, F.E. & Böhmer, M. Data-driven design of LNA-blockers for efficient contaminant removal in Ribo-Seq libraries. Sci Rep 16, 8565 (2026). https://doi.org/10.1038/s41598-026-43117-3
キーワード: リボソームプロファイリング, RNA汚染物質, ロックドヌクレオチド(LNA), シーケンシングライブラリのクリーンアップ, 翻訳の制御