Clear Sky Science · ja
ヒッポファエ(Hippophae)の葉緑体ゲノム比較が描く系統関係と分類同定のための候補DNAマーカーの提示
なぜこの耐寒性低木が重要なのか
シーバックソーンは、多くの他の植物が育ちにくい場所—青海チベット高原の寒く乾いた風の強い斜面など—でよく育つ頑健な低木です。その鮮やかなオレンジ色の果実は世界的に「スーパーフルーツ」として宣伝され、土壌の安定化や荒れ地の修復にも広く利用されています。しかし、外見だけでは近縁の種や亜種を識別するのは専門家でも難しい場合が多い。本研究は単純だが重要な問いを投げかけます:種の同定のために、植物の内部にある説明書、つまりDNAを読み取ることで個体群を区別できるか、そしてその成果が育種家や保全関係者にとって有用な管理手段を提供できるか、という点です。
植物の緑色エンジンをのぞく
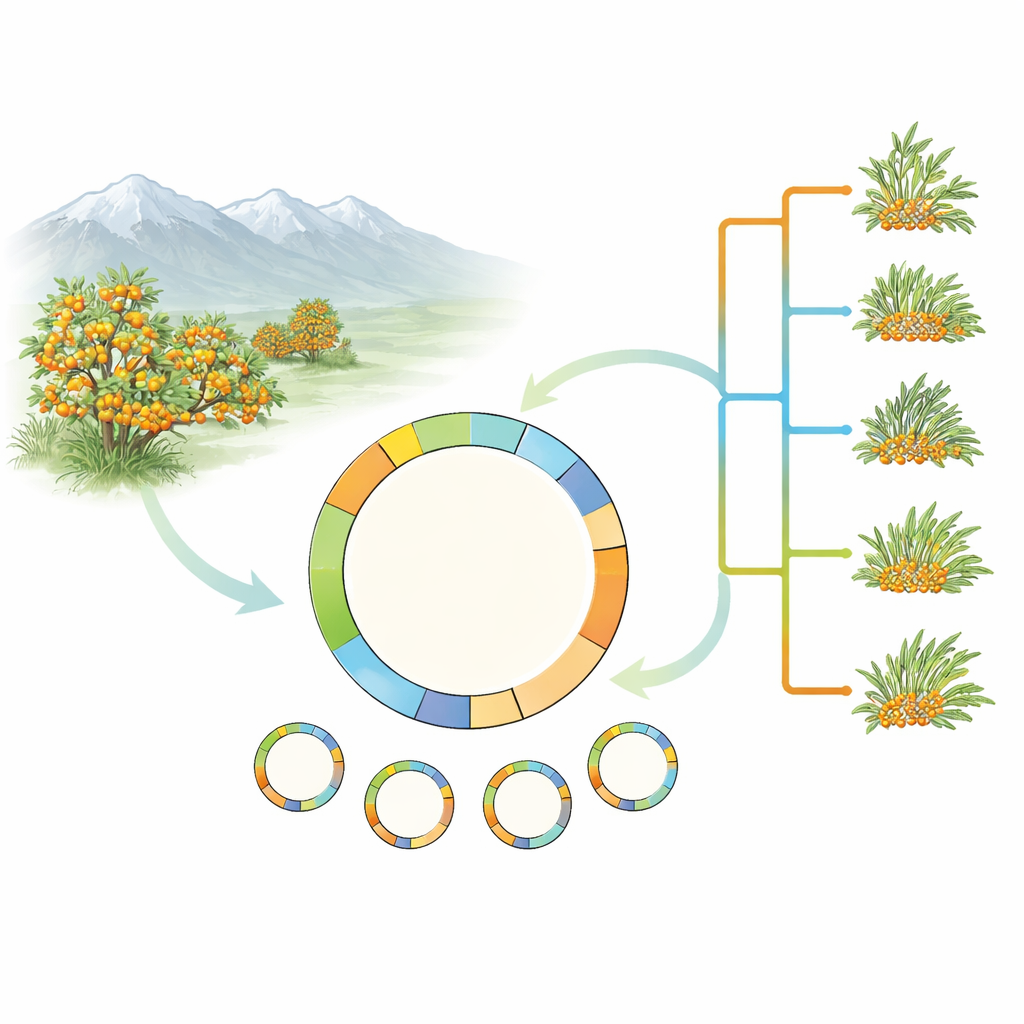
研究者たちはシーバックソーンの全ゲノムの複雑さに取り組む代わりに、光合成を担う細胞内の小さな緑色コンパートメントである葉緑体に注目しました。葉緑体は母系に由来する小さな環状DNAを持ち、植物の系統をたどるのに非常に有用であることが知られています。研究チームは、5種のシーバックソーンと広範に分布するH. rhamnoidesの複数の型を含む17試料から完全な葉緑体ゲノムを収集・配列決定しました。さらに、重要な栽培系統であるH. rhamnoides subsp. mongolica cv. Prevoskhodnayaの新たに組み立てた葉緑体ゲノムを追加し、既存データベースのエントリーを慎重に再検証して誤りを修正しました。
共通の設計図、しかし示唆に富む違い
一見すると、すべてのシーバックソーン試料の葉緑体DNAは非常によく似ていました。各ゲノムは約155,000〜156,000塩基長で、多くの被子植物に見られる四分割構造(2つの単一コピー領域が一対の複製領域に挟まれる)を踏襲していました。遺伝子のセットや配列順序も同一で、DNAを構成する4つの塩基の全体的な比率もほとんど変化がありませんでした。この構造的安定性は、ヒッポファエ属の葉緑体設計図が進化の過程で保存されてきたことを示唆します。しかし、研究者が特定のアミノ酸を記述するために使われるコドンの頻度のような細かな点に着目すると、系統ごとに特有の微妙なパターンが見つかり、属の異なる枝でコードがゆっくりと長期的に形成されてきたことを示唆しました。
系統樹を解きほぐす
葉緑体DNAの78個のタンパク質コード遺伝子を用いて、チームはシーバックソーンをバラ科を含む広い系統の中に置き、その後ヒッポファエ属内部の関係を詳述する系統樹を構築しました。解析は、シーバックソーン群が自然な単一の系統を形成していること、またH. rhamnoidesとその亜種群が密接に結びついていることを確認しました。興味深いことに、ある種であるH. tibetanaは葉緑体系統樹では一貫してH. rhamnoides群の内部に位置しますが、これまでの核DNAによる研究では属の基部に近い位置に置かれていました。核ゲノムと葉緑体ゲノムの履歴が一致しないこの不一致は、過去の雑種化や他の複雑な進化的出来事を示唆しており、今後は核ゲノムと葉緑体ゲノムの全体データを組み合わせた研究が必要であることを示しています。
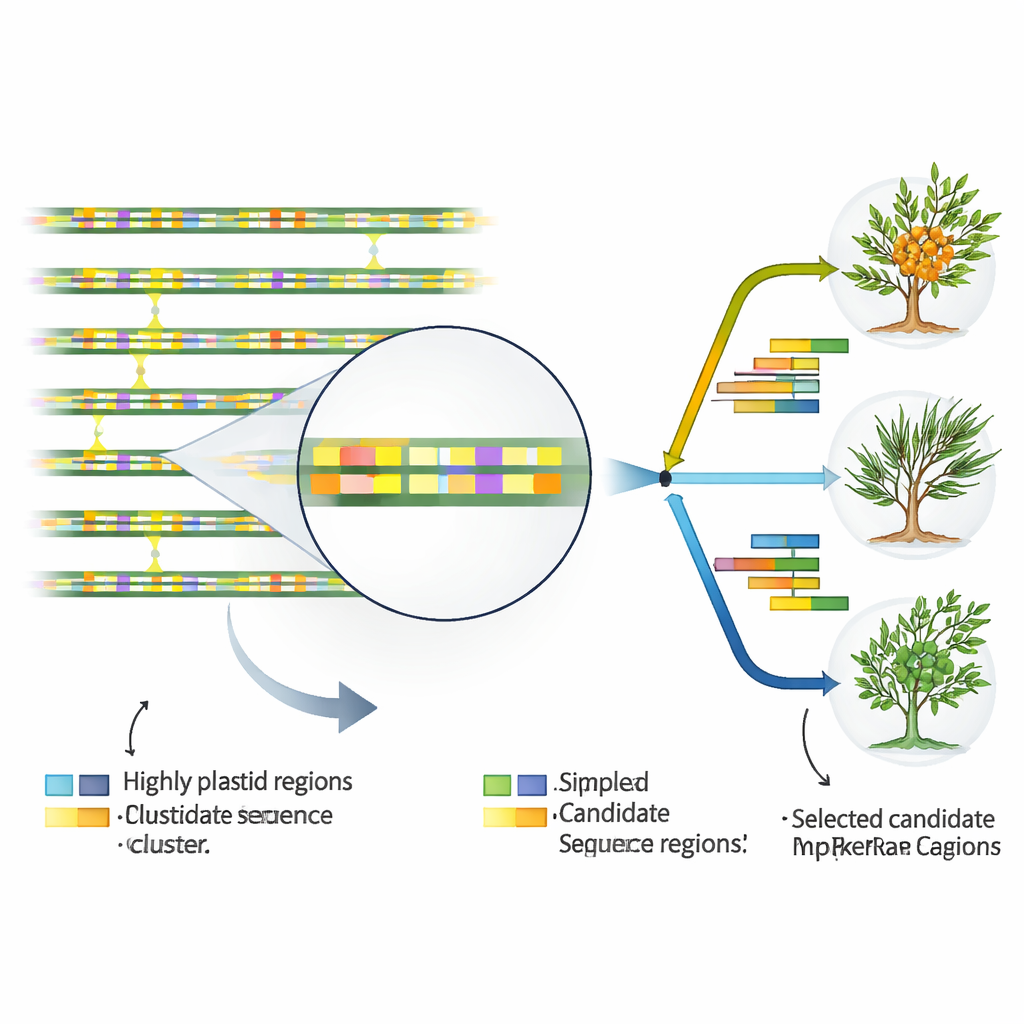
同定の目印となるゲノムのホットスポットを探す
葉緑体DNAを分類学者や育種家の日常的なツールにするため、著者らは他の領域よりも速く変化する配列領域を探索しました。17の葉緑体ゲノムを比較した結果、46の特に変動の大きい領域を特定しました。これらの多くは遺伝子間領域やイントロンといった非コード領域に位置し、遺伝子本体にはほとんどありませんでした。また、AとTに富む短い反復配列(単純繰り返し配列、SSR)を数十箇所にマップしました。これらの反復や変動領域のいくつかは種間、さらにはH. rhamnoidesの亜種間でも明確な差異を示しました。種レベルと亜種レベルの比較の両方でホットスポットとして際立つ領域がいくつかあり、それらは簡便な実験で狙える実用的なDNAマーカーの有力候補です。
DNAパターンから実用へ
シーバックソーンの葉緑体ゲノムにおける安定した枠組みと、小さいが情報量のある差異の両方を可視化することで、本研究は信頼できるDNA同定のための道具箱を提供します。提案されたマーカー領域は、外見が似た種の識別、商業用果実製品の産地確認、野生遺伝資源の保護、栄養・医療・土地復元を目指す育種プログラムにおける親の選定などに役立つ可能性があります。平たく言えば、慎重に読み解かれた葉緑体の説明書は、この耐寒性低木の拡大家族の中で誰が誰であるかを明らかにし、より賢明な保全とより狙いを定めた利用への道を開くことを示しています。
引用: Asakura, N., Noda, M., Takahashi, Y. et al. Comparative plastid genomics of Hippophae reveals phylogenetic relationships and provides candidate DNA markers for taxonomic identification. Sci Rep 16, 7943 (2026). https://doi.org/10.1038/s41598-026-40776-0
キーワード: シーバックソーン, 葉緑体ゲノム, DNAマーカー, 植物分類学, 遺伝的多様性