Clear Sky Science · ja
注意に導かれた強化逆畳み込みにより参照不要で空間トランスクリプトミクスの細胞型推定を実現
その場で見る細胞
現代生物学は、孤立した細胞だけでなく薄切り組織の内部で同時に何千もの遺伝子の発現を読み取ることができます。この「空間トランスクリプトミクス」的な視点は、異なる細胞がどこに存在し相互作用するかを明らかにしますが、各測定値はしばしば近接する多数の細胞からの信号が混ざったものになります。本研究はAGEDと呼ばれる新しい計算手法を導入し、これらの混合を解きほぐしてどの細胞型がどこに存在するかを推定します—別途慎重に整合された単一細胞参照データセットを必要とせずに。 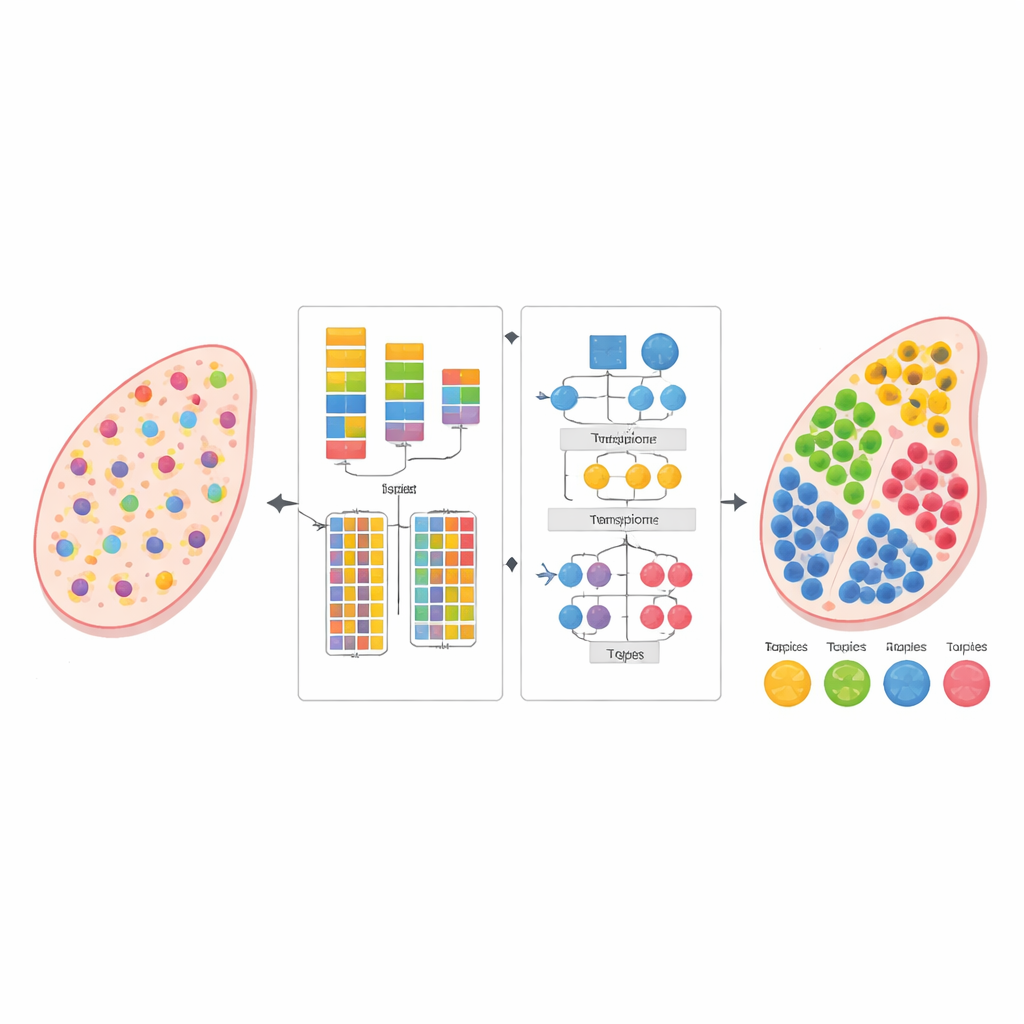
組織内の細胞マッピングが難しい理由
空間トランスクリプトミクスのプラットフォームは、組織切片上に敷かれたスポットの格子に沿って遺伝子発現を計測します。多くのスポットが同時に複数の細胞を捉えるため、研究者は混合された信号を数学的に分解して、基になっている細胞型とその割合を復元する必要があります。既存のツールは同一組織の外部単一細胞参照アトラスに依存することが多く、希少な組織、特殊な病態、または実験条件によってはこれらのアトラスが存在しないことがあり、存在しても完全には一致せずバイアスを生じさせる可能性があります。参照不要の手法はこの依存を避けますが、現在のアプローチは複雑な空間パターン、微妙な遺伝子間関係、そしてそもそも何種類の細胞型を探すべきかを決める難しさに苦しんでいます。
混合を解くための二段階戦略
著者らはAGEDを、統計学と最新の深層学習のアイデアを組み合わせた二段階フレームワークとして設計しました。第一段階では、組織内にどれだけの細胞型が存在する可能性があるかを幅広く試します。Performerとして知られる高速な注意機構ベースのニューラルネットワークを用いて候補となる分解を学習し、観測された遺伝子カウントの再構成の良さ、推定された細胞群の分離の鮮明さ、群の多様性といった複数の基準でそれらを評価します。曲線当てはめの手続きにより、細胞型を増やしてもほとんど利益が得られなくなる「肘点」を見つけ、ユーザーの推定に頼ることなく適切な数を自動選択します。
生物学を捉えるための誘導された注意
細胞型の数が決まると、AGEDの第二段階はより豊かな注意機構アーキテクチャで解を洗練します。まず各スポットを隠れた「テーマ」の混合として扱う統計的トピックモデルを出発点とし、ここでのテーマが細胞型に相当し、各細胞型は特徴的な遺伝子パターンとして表現されます。これらの初期テーマがグローバルな構造を提供します。その上に複数の注意機構を重ねます:一つは統計的テーマとニューラルネットワークを結びつけ、別のものは物理空間で隣接するスポットから情報をプールし、三つ目はテーマを遺伝子に直接結びつけます。ゲーティングシステムにより、モデルは各ケースで事前の統計パターンをどれだけ信頼するかと局所データをどれだけ重視するかを判断できます。さらに、ほとんどの組織部位がごく少数の主要な細胞型によって支配されるという生物学的現実を反映して、疎な解を促す制約も導入されています。 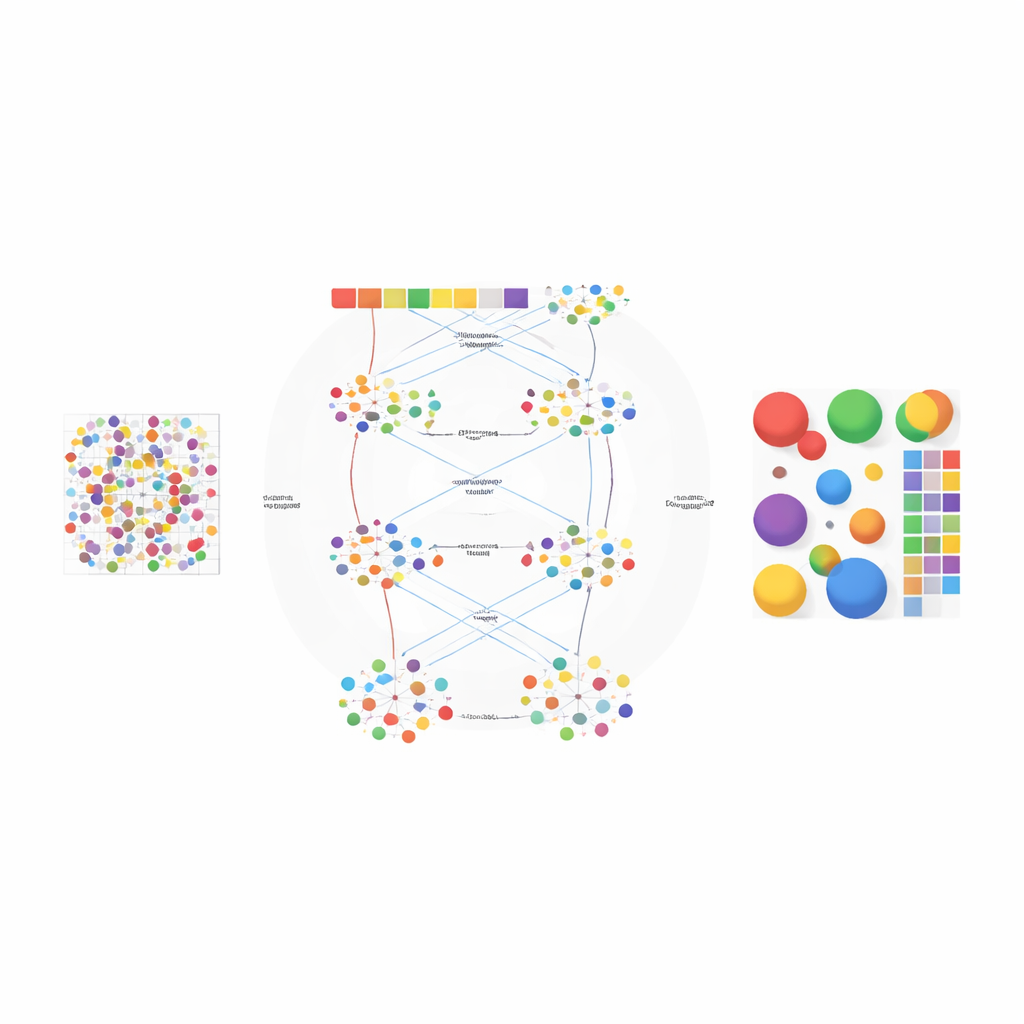
手法の実証
研究者らは複数のデータタイプでAGEDを評価しました。シミュレートしたマウス嗅球組織では、本手法は既知の4つの解剖学的層を復元し、広く使われる参照ベースおよび参照不要のツールよりも真の細胞組成により近い結果を出し、真値との高い相関と低い再構成誤差の両方を達成しました。ヒト膵管癌(膵管腺がん)では、AGEDは自動的に20種類の細胞型解を選び、腫瘍、管、正常膵など病理医が注釈した領域と整合し、推定マップを可視の組織構造と比較する構造的類似性の尺度で他手法を上回りました。ヒト胸腺組織では、AGEDは主要な細胞集団を正確に分離し、2つの特殊な上皮細胞型間に生物学的に期待される負の関係を捉えました—競合するアプローチでは再現できなかったパターンです。単一細胞に近い解像度や他のデータセットでの追加解析も本手法の頑健性を支持しました。
今後に向けての意義
非専門家の観点から見ると、AGEDは複雑な組織を解きほぐすスマートなエンジンと考えられます:空間データだけから、存在する異なる細胞コミュニティの数、それらの位置、そしてそれらを定義する遺伝子を学習します。解釈可能な統計モデルと柔軟な注意機構ベースのニューラルネットワークを織り交ぜることで、適切な参照アトラスが存在しない場合でも、精度と洞察の双方を提供します。これは脳の層から腫瘍や免疫器官まで、健康と病態における組織構造を探る実用的な道具となり得るとともに、生物学において強力だが不透明な機械学習モデルを事前知識で導くより広い戦略を示唆します。
引用: Yang, X., Wang, Y. & Chen, X. Attention-guided enhanced deconvolution enables reference-free cell type estimation in spatial transcriptomics. Sci Rep 16, 8097 (2026). https://doi.org/10.1038/s41598-026-39703-0
キーワード: 空間トランスクリプトミクス, 細胞型デコンボリューション, 深層学習, 組織アーキテクチャ, 参照不要解析