Clear Sky Science · ja
CiCLoDS: 単一細胞空間トランスクリプトミクスのための細胞クラスタリングと遺伝子選択の同時最適化
細胞の街で近隣を見つける
現代の顕微鏡は、組織内で各細胞の元の位置を保ちながら、数十万の細胞におけるどの遺伝子が活性化しているかを読み取れるようになりました。この「空間トランスクリプトミクス」の革命は、ぼんやりした都市地図を各家の前まで見られるストリートビューに変えるようなものです。しかし問題があります:これらのマップは細胞ごとに何千もの遺伝子の測定値を含み、研究者が容易に解釈したり、追試実験で測定するには多すぎます。本研究は CiCLoDS を提示します。これは意味のある細胞の「近隣」を見つけると同時に、それらの近隣を定義する小さく解釈しやすい遺伝子リストを選び出す新しい手法です。
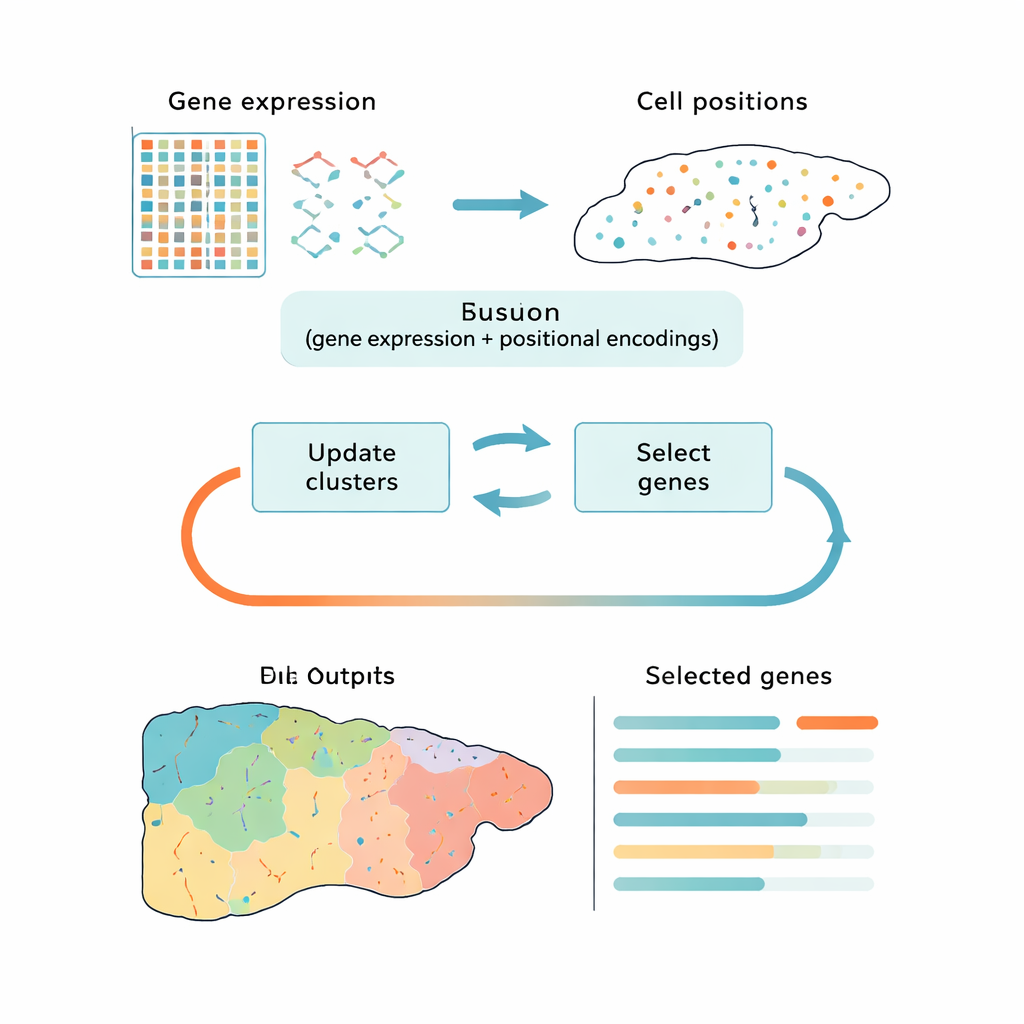
大規模データを縮約する賢い方法
現在の多くのツールはこの課題を二段階で切り離して扱います:まずデータを単純化し、その後で細胞をクラスタに分けます。主成分分析(PCA)のような一般的な手法は全体的な変動を保ちますが、技術的ノイズや一般的な細胞周期信号に注目してしまい、生物学的に重要な違いをとらえ損ねることがあります。他の方法は深層学習でパターンを見つけますが、ブラックボックスとして振る舞い、どの遺伝子が重要かを明確に示しません。CiCLoDS は異なる道を採ります。遺伝子選択とクラスタリングをユーザーが定める「遺伝子予算」の下で一つの同時問題として扱います。言い換えれば、限られた遺伝子数の中で、細胞の遺伝子発現と(利用可能であれば)組織内の位置情報の両方を考慮したとき、どの遺伝子群が細胞のグループ分けを最もよく説明するかを問うわけです。
数学から実際の組織地図へ
著者らは、サブスペースクラスタリングと呼ばれる数学的に透明性の高い手法群を、細胞数が百万を超えることもある空間トランスクリプトミクスの現実に適合させました。CiCLoDS は単純な細胞×遺伝子の表で動作し、細胞をクラスタに割り当てると同時に各遺伝子がクラスタ分離にどれほど寄与するかをスコア化します。位置情報は、組織内で各細胞がどこにいるかを記述する位置「エンコーディング」を追加する形で組み込め、コアの最適化問題自体は変わりません。高解像度イメージングプラットフォームで得られた大規模なマウス肝臓およびヒト結腸のデータセット上で、CiCLoDS は標準的なコンピュータで数分で動作し、元のデータの豊かな構造を保持しつつ数十〜数百程度のコンパクトな遺伝子パネルを生成します。
隠れた区域と血管の顕在化
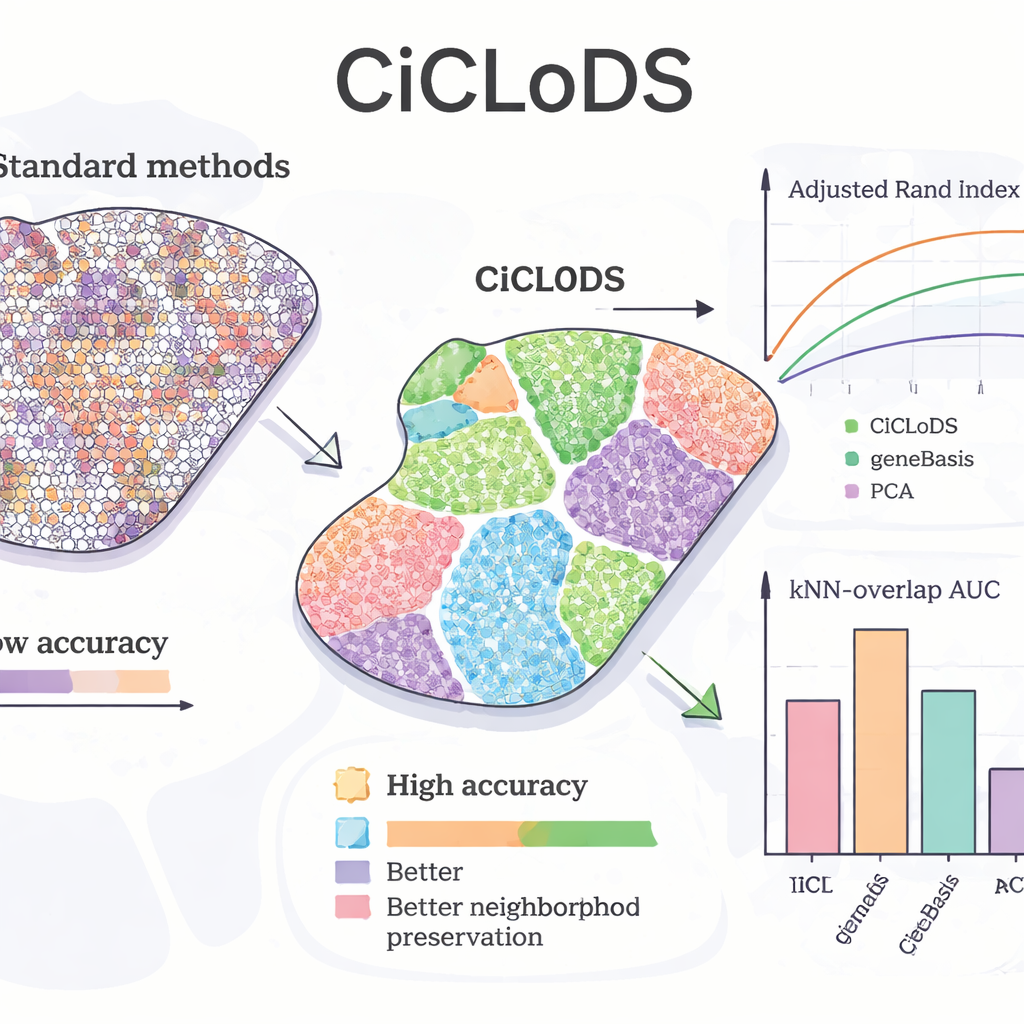
マウス肝臓に CiCLoDS を適用した際、研究チームはこの手法が既知の「ゾネーション」パターン――肝小葉の一方から他方への肝細胞機能の漸次的な変化――を再現できるかを調べました。PCA や geneBasis と呼ばれる主要な遺伝子選択ツールと比較して、CiCLoDS はより明瞭な空間的ゾーンを、より鋭い境界とはるかに少ない誤割り当て領域で生み出し、参照マップとの一致を測る定量的指標でも優れた結果を示しました。注目すべきことに、より多くの遺伝子を許容した場合、CiCLoDS は AXIN2 といった主要なバイオマーカー遺伝子や明示的な空間座標を与えられていなくても、専門家定義の参照クラスタと密接に一致する門脈周辺様(peri‑portal‑like)および中心静脈周辺様(peri‑central‑like)の肝細胞群を再発見しました。位置エンコーディングを追加すると、CiCLoDS は細胞表面や血管関連機能に富む遺伝子パネルを学習し、実際の血管をイメージングアーティファクトから正確に区別することができました――単純な手法では失敗したり、よりアドホックな手直しを要したタスクです。
脳を越えて一般化し、他手法を強化する
非常に異なる組織や個体間で CiCLoDS が有効かを試すため、著者らは3人のドナーから得たヒト背外側前頭前皮質(dorsolateral prefrontal cortex)のサンプルを解析しました。ここで CiCLoDS は、BayesCafe や BayesSpace といった専門的な空間手法と同等かそれ以上の性能を示し、特に他の手法が苦戦した難しいサンプルで良好でした。本研究はまた「ハイブリッド」な利用法も強調します:まず CiCLoDS を実行して安定したクラスタを得てから、それを BayesSpace に入力する方法です。このウォームスタート戦略は全体的な精度を高め、専門家の注釈と最も一致する脳層パターンを生み出し、CiCLoDS が単独でも機能し、下流の確率的モデルをより信頼できるものにできることを示しました。
生物学と医学にとっての意義
非専門家にとっての主要なポイントは、CiCLoDS が圧倒的な細胞地図を簡潔で生物学的に意味のある要約に変えることです。何千ものノイズを含む測定値に苦労する代わりに、研究者は扱いやすい遺伝子リストと、実際の組織配置を反映した明確な空間クラスタ(肝臓の代謝ゾーン、血管とそのニッチ、脳の層構造など)を得られます。遺伝子予算がユーザー制御であり計算負荷が軽いことから、CiCLoDS は将来の実験のためのターゲット遺伝子パネルの設計、複雑な空間データセットの解釈支援、より精緻なモデリングのための堅牢な出発点の提供に役立ちます。データ収集がボトルネックではなく理解が問題となる時代にあって、CiCLoDS のようなツールは高次元の組織地図を実用的で洞察に富んだものにする可能性を秘めています。
引用: Wang, N., He, Y., Ray, E. et al. CiCLoDS: Joint cell clustering and gene selection for single-cell spatial transcriptomics. Sci Rep 16, 5356 (2026). https://doi.org/10.1038/s41598-026-39168-1
キーワード: 空間トランスクリプトミクス, 細胞クラスタリング, 遺伝子パネル選択, 組織アーキテクチャ, 単一細胞解析