Clear Sky Science · ja
rhinotypeRはVP4/2配列から再現可能なライノウイルス遺伝子型割り当てを可能にする
小さな風邪ウイルスがいまでも重要な理由
多くの人は一般的な風邪を厄介ごと程度に捉えますが、風邪の原因となるヒトライノウイルスは重篤な肺感染症、ぜんそく発作、慢性肺疾患の急性増悪とも関連しています。これらのウイルスの進化や拡散を追跡するには、製品にバーコードを付けるように、正確な遺伝学的「型」に分類する必要があります。本稿では、遺伝的ラベリングをより正確で一貫性があり再現可能にする無料のオープンソースソフトウェアパッケージ、rhinotypeRを紹介します。これにより公衆衛生チームは、見過ごされがちな呼吸器ウイルス群をより明瞭に監視できます。
一般的な風邪に潜む多様性
ヒトライノウイルスは極めて頻繁に検出され、急性呼吸器疾患の患者検体のうち最大60%に現れることがあります。単一のウイルスではなく、A、B、Cの三つの主要群に分かれ、少なくとも169種類の認識された遺伝子型があります。型ごとに振る舞いが異なり、ある型は小児の重症感染やぜんそくの増悪とより強く関連する一方、他の型は重症疾患では稀にしか見られません。これらの型は独立に進化し、表面特性が異なるため、学校や家庭、地域社会での流行の動きを追うには信頼できる識別法が必要です。
散在するツールから一つの明確な流れへ
これまでは、ライノウイルスの型を遺伝子配列から割り当てる作業は寄せ集めでした。研究者は通常、ウイルスゲノムの短い領域であるVP4/2領域に注目し、既知の参照株と配列を整列させ、配列間の差異を測り、閾値を適用して各検体の型を決定してきました。しかしこれらの手順は複数のソフトウェアや手作業、個人の判断を混ぜて行われることが多く、同様のデータを用いても研究間で比較や再現が難しいことがありました。rhinotypeRは、この多段階で誤りが入りやすいプロセスを誰でも実行・共有できる一つのスクリプト化されたワークフローにするために作られました。
新しいソフトウェアが実際に行うこと
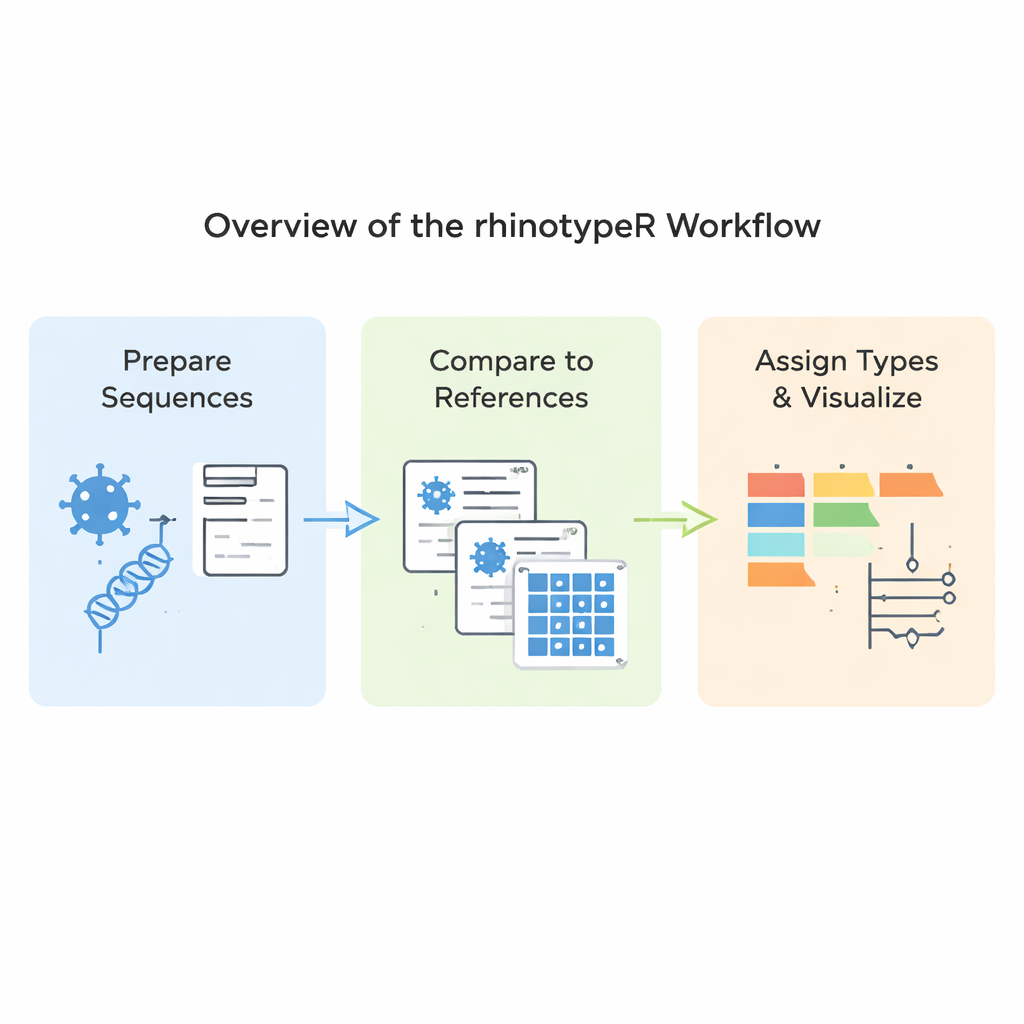
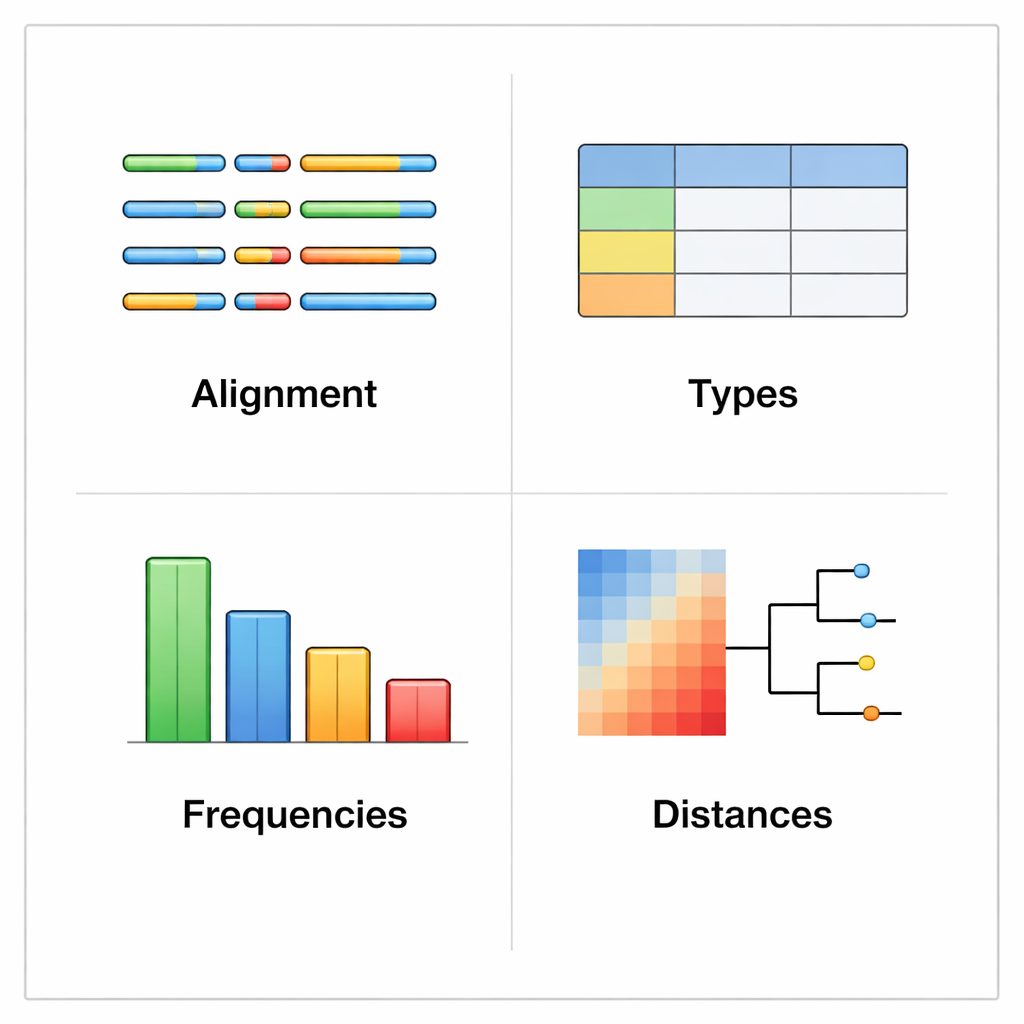
rhinotypeRは、データ解析で広く使われるRおよびBioconductor環境内で動作します。ライノウイルスのVP4/2配列群を入力として受け取り、配列の準備と整列、キュレーションされた参照型との間の距離計算、それぞれのサンプルを最も近い既知型に割り当てるか、差が大きすぎる場合は「未割当」としてフラグを立てる、という三つの主要段階を順に実行します。同じツールで、遺伝的差異を色分けしたマップ、簡易な系統樹、データセット内の各型の頻度を示す図表などの視覚出力も生成できます。ユーザーは好みに応じて外部プログラムで配列整列を行うことも、最大限の再現性を得るためにrhinotypeR内ですべて処理することもできます。
ツールの検証
rhinotypeRの距離測定が信頼できるかを確かめるため、著者らは同一の入力ファイルとモデルを用いて、既存の二つのプログラム(apeとMEGA X)と比較しました。その結果はほぼ完全に一致し、わずかな差異はコンピュータ計算における四捨五入の違いに起因するもので、方法論の実質的な差ではありませんでした。次に、90%超の既知型を網羅する過去の複数研究から集めた2,300以上のライノウイルス配列の大規模データセットに対してrhinotypeRを実行したところ、およそ5件中4件で従来の型ラベルと完全に一致しました。大半の不一致は、型を分けるために事前に合意された閾値のちょうど境界付近で発生しており、境界判定での差は予想されるものです。重要なのは、自信をもって既知型に割り当てられなかったサンプルが単に品質が低いまたはウイルス量が少ないためではなく、実際のウイルス多様性を反映している可能性が高い点です。
公衆衛生にとっての意義
専門外の方への要点は、rhinotypeRが風邪ウイルスの分類方法を根本的に変えるのではなく、そのプロセスをより明瞭で透明性が高く再現可能にするということです。配列整列、距離計算、型割り当てを一つのオープンソースパッケージにまとめ、分かりやすい視覚的要約を付けることで、研究者や監視プログラムが数千の検体を一貫した方法で処理できるようになります。その一貫性により、異なる場所や時期の研究を比較しやすくなり、異常あるいは新興のウイルス系統を早期に検出し、遺伝的パターンを実際の疾病傾向と結びつけることが向上します。長期的には、rhinotypeRのようなツールが、見た目にはありふれた風邪の定期的な監視を強化し、多くの人にとって深刻な病気を引き起こす可能性を持つ事象に備える助けとなります。
引用: Luka, M.M., Nanjala, R., Rashed, W.M. et al. rhinotypeR enables reproducible rhinovirus genotype assignment from VP4/2 sequences. Sci Rep 16, 6149 (2026). https://doi.org/10.1038/s41598-026-37050-8
キーワード: ライノウイルス遺伝子型判定, 分子監視, VP4/2シーケンシング, バイオインフォマティクスツール, 呼吸器ウイルス