Clear Sky Science · ja
因果グラフ学習を用いたアルファルファ(Medicago sativa L.)のSNPの直接効果と多面発現効果の分離
農場と食にとってなぜ重要か
アルファルファは現代農業の働き手であり、乳牛の飼料となり健全な土壌づくりにも寄与します。しかし、冬越しの強さ、損傷耐性、高品質の飼料を備えた優れたアルファルファの育種は、その遺伝の複雑さによって阻まれてきました。本研究は、長く混乱したDNAマーカーのリストから、どのゲノム領域が重要な茎形質を実際に駆動しているのか、どれが単に相関しているだけなのかを明確に示す、因果関係の地図へと移す新しい方法を提示します。
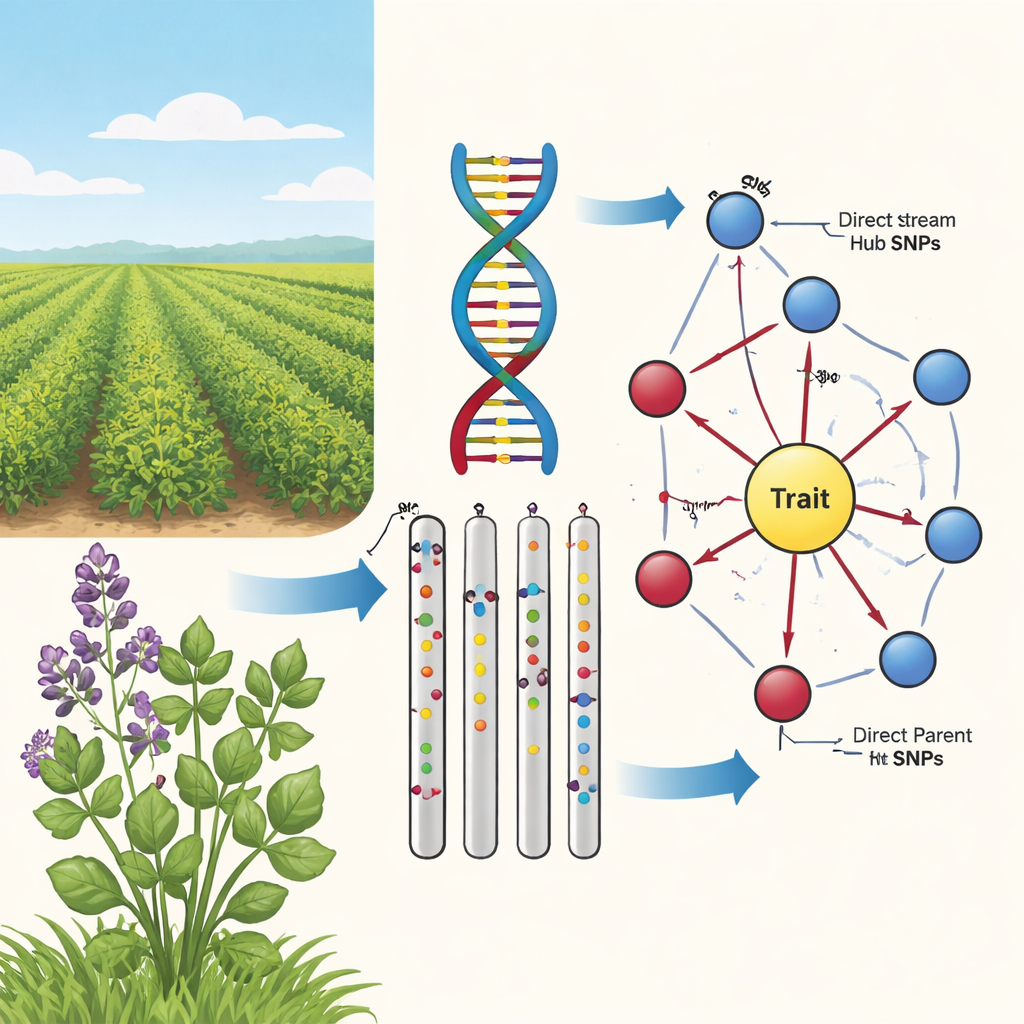
ゆるい相関から因果へ
従来のゲノムワイド関連解析(GWAS)は、茎の色や冬越しといった形質とともに現れやすいSNPと呼ばれるDNA変異をゲノム全体でスキャンします。しかしアルファルファでは状況が特に入り組んでいます:各染色体が4コピー存在し、大きなDNA領域が一緒に動き、個体の遺伝的混合度が高い。このため、多くのマーカーが重要に見えても実際に形質に影響を与えるのはごく一部という「相関の霧」が生じます。著者らは、育種家には単なる統計的関連以上のものが必要であり、どのマーカーが遺伝子型から目に見える形質への実際の因果経路上にあるかを知る必要があると主張します。
新しいフレームワークの仕組み
研究者らは、最新の機械学習と因果グラフ理論の考えを組み合わせた2段階のフレームワークを構築しました。まず、Double Machine Learningと呼ばれる手法で、約2,400個のSNPを500系統のアルファルファでスクリーニングしました。この段階では、系統背景や地理などの隠れた要因の影響を、ゲノムの主成分を代理変数として取り除きます。その結果、これらの交絡因子を考慮した後でも形質に対して直接的な効果を示すマーカーのよりクリーンな像が得られました。このフィルタリング後のビューでは、強く安定した信号のピークが主に染色体2と4に現れ、主要なマーカーは効果の信頼区間が明確にゼロを除外しており、実際の因果的影響を示唆しました。
マーカーを遺伝の道路地図に変える
第2段階では、PCアルゴリズムとして知られる因果グラフ学習アルゴリズムを用いて、有望なマーカーを方向性のあるネットワークにつなげました。これらの図ではノードがSNPと形質を表し、矢印が影響の最も可能性の高い向きを示します。基本的な生物学と矛盾する辺(例えば、形質が基礎となるDNAを変えることはありえない)を切り落とし、形質に流入するSNPのみを残すことで、著者らはコンパクトで生物学的に妥当な地図を得ました。これらの「ひまわり」ネットワークは層構造を明らかにします:形質に直接つながる内部リングのDirect Parent SNPsと、複数の親を介して影響を与えるが形質には直接触れない外側リングのUpstream Hub SNPsです。
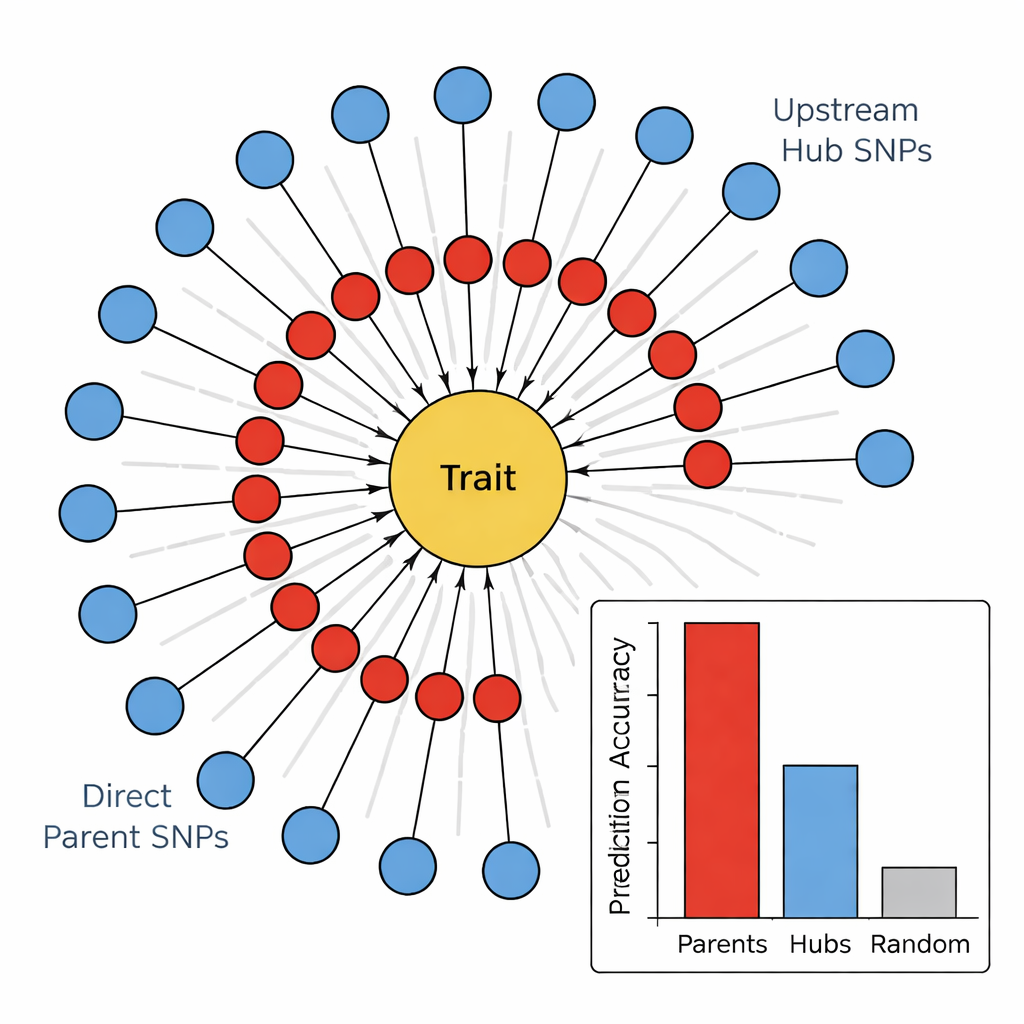
ゲノムにおける実行者と指揮者
この階層が意味を持つかを検証するために、著者らは異なるマーカー群が4つの茎関連形質(茎の色、茎の充実度、茎の強度、冬傷害)をどれだけ予測できるかを比較しました。すべての形質において、Direct Parent SNPsは一貫して最良の予測子であり、ランダムなマーカーやUpstream Hubsよりも何倍もの分散を説明することがありました。対照的に、ハブはネットワーク上で高い結合性を持っているにもかかわらず、予測力は弱いか場合によっては負でした。これらのSNPを既知の遺伝子に結びつけるとパターンが浮かび上がりました:Direct Parentsは細胞壁、色素、あるいは損傷応答に直接作用する酵素や構造タンパク質と一致することが多く、Hubsは多くの経路を広く調整する転写因子や調節タンパク質に対応する傾向がありました。
将来のアルファルファ育種にとっての意味
育種家や遺伝学者にとって、本研究はノイズの多い関連解析の結果を切り崩し、特定の形質を実際に動かすDNA変化に焦点を当てる方法を提供します。著者らは、交絡を取り除くスクリーニングと因果グラフの組合せが過学習に対する組み込みの防護策となり、長い候補リストを既知の生物学と整合する小さく解釈可能なネットワークに変えることを示しました。実用的には、Direct Parent SNPsはより良い茎や冬越しを持つ個体を選抜するための高精度マーカーとなり、Upstream Hubsは広範なストレス応答を再構築する可能性のあるマスタースイッチを示す一方で、トレードオフの可能性もあります。このゲノムの構造的な見方は、複雑な作物におけるより信頼できるゲノム選抜の基盤を築き、将来的に遺伝子発現や代謝などのデータ層を因果的で統合的な植物性能モデルに組み込むための土台を提供します。
引用: Lee, Y., Medina, C.A. & Xu, Z. Disentangling direct and pleiotropic SNP effects in alfalfa (Medicago sativa L.) using causal graph learning. Sci Rep 16, 5216 (2026). https://doi.org/10.1038/s41598-026-35876-w
キーワード: アルファルファの遺伝学, 因果グラフ学習, ゲノム選抜, 植物育種, 多倍体作物