Clear Sky Science · ja
CO₂固定経路予測のための化学合成独立栄養微生物ゲノムとマーカー遺伝子の精選リソース
地球の炭素収支を支える微生物たち
土壌や海洋、極限環境の奥深くにひそむいくつかの微生物は、二酸化炭素(CO₂)を主要な炭素源として自らの生体物質を合成する能力を持ちます。これらの微生物は地球の炭素循環の均衡を保つうえで重要であり、工業的なCO₂回収の新たな手法に着想を与える可能性もあります。しかしこれまで、微生物のDNA配列からどのCO₂固定戦略を用いるかを簡便かつ確実に判定する方法は欠けていました。本研究は、これを埋めるために精選された遺伝子カタログと、新しいコンピューターツール「AutoFixMark」を提示します。
空気を生体へ変える多様な経路
CO₂を固定する生物が皆同じやり方をするわけではありません。微生物は少なくとも7つの自然な経路を進化させ、CO₂を有機物に変換します。植物や多くの細菌に一般的なカルビン–ベンソン–バッシャム(Calvin)回路のようによく知られた経路もあれば、2020年に発見された還元グリシン経路のようにまだ十分に解明されていない経路もあります。これらの経路は系統樹の多くの枝に散在し、類似した酵素を再利用することが多いため、ゲノム配列だけで見分けるのは意外に難しいのです。既存のソフトウェアは広範な代謝能力を予測できますが、正確なCO₂固定経路を特定するよう最適化・十分検証されているわけではありません。
CO₂固定微生物のクリーンな参照地図を構築
研究者らはまず、慎重に検証した2つのゲノムコレクションを組み立てました。まず、CO₂固定経路が詳しく解明されている15種の良く研究された微生物を選びました。これらの参照生物は複数の細菌・古細菌群にまたがり、それぞれの経路を特徴づける主要酵素を定義するための設計図となりました。次に、化学合成独立栄養微生物(無機化学物質からエネルギーを得てCO₂から生体を合成する微生物)347件のベンチマーク集合を作成しました。この大きな集合の各ゲノムは文献に基づいて手作業で特定のCO₂固定経路に紐づけられており、予測を検証するための確かな真理セットを提供します。
ブラックボックスではなくマーカー遺伝子と単純ルール
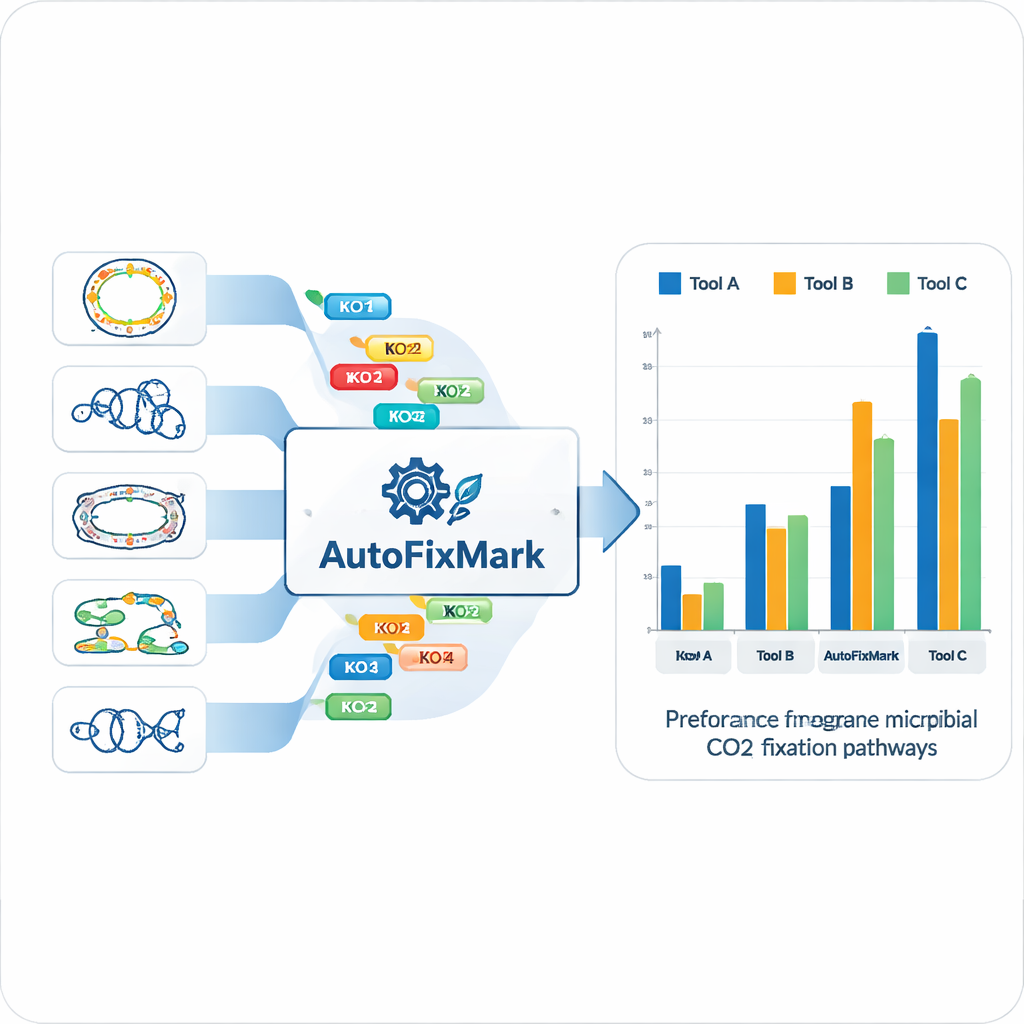
15の参照ゲノムを用いて、研究チームは7つのCO₂固定経路ごとに「マーカー遺伝子」を特定し、これらを標準化されたKEGG Orthology(KO)識別子にマッピングしました。不可視な機械学習に頼る代わりに、これらのマーカーがどのように組み合わさるかを示す透明なルールを符号化しました。ある反応は複数の代替酵素のいずれかで実行可能であり、これは「one_of」ルールで扱います。別の反応は多量体複合体に依存し、定義されたKO群の「all_of」を必要とします。還元グリシン経路のように全ての構成要素が完全には解明されていない場合は、最低限のサブユニット数を要求する「at_least」ルールを使います。これらの論理ルールは機械可読なJSONファイルに格納され、AutoFixMarkの中核知識ベースを構成します。
既存ソフトを上回る軽量ツール
AutoFixMark自体はPythonで書かれた小さなルールベースのプログラムです。入力としては通常、KofamScanという別ツールが生成するゲノム中の遺伝子のKO IDリストを受け取り、7つの経路それぞれについてどのマーカールールが満たされているかを判定します。著者らはAutoFixMarkを、METABOLICとgapseqという2つの広く用いられる代謝注釈ツールと、347ゲノムのベンチマーク集合を用いて比較しました。3つのツールはいずれもカルビン回路、還元トリカルボン酸回路、ウッド–ラングダール経路といった古典的経路では良好に機能しました。しかし、AutoFixMarkは3-ヒドロキシプロピオン酸/4-ヒドロキシブチル酸サイクル、ジカルボキシレート/4-ヒドロキシブチル酸サイクル、還元グリシン経路などの新しいまたは稀な経路に関して、明らかに他を凌駕しました。これらの一部は競合ソフトが扱っていないことすらあります。
気候・生態学研究への意義
精選された遺伝子セット、AutoFixMarkプログラム、完全なベンチマークゲノムコレクションは公開されています。これにより、研究者は単離微生物やメタゲノム組み立てゲノムの両方をスクリーニングし、それらが遺伝的にどのCO₂固定戦略を備えているかを判定できるようになります。重要なのは、AutoFixMarkが予測するのは遺伝学的な潜在能力であり、実際の環境下でその経路が活性化しているかどうかを示すものではないという点です。多くの生化学経路は細胞のエネルギー収支に応じて逆に働くこともあります。それでも、CO₂固定微生物を確実かつ透明に検出する手段が得られたことは、どこでどのように生物が大気中の炭素を取り込んでいるかの地図化、新興経路に関する実験の誘導、将来のCO₂ベースのバイオテクノロジー設計の支援に役立ちます。
引用: Kawashima, S., Okabeppu, Y., Miyazawa, S. et al. A curated resource of chemolithoautotrophic genomes and marker genes for CO₂ fixation pathway prediction. Sci Data 13, 121 (2026). https://doi.org/10.1038/s41597-026-06655-z
キーワード: 微生物による炭素固定, 独立栄養代謝, ゲノム注釈, CO2回収, メタゲノミクス