Clear Sky Science · ja
オプサリヒス・エヴォランス(コイ目:コイ科)の端から端までギャップのない全染色体ゲノムアセンブリ
遡行する渓流魚が語るゲノムの物語
中国南東部と台湾の急流に生息する小型で色彩豊かな魚がOpsariichthys evolansです。地域外ではあまり知られていませんが、この種は生態系で重要な役割を果たし、鮮やかな縞模様や繁殖期の派手な体色といった自然の芸術品のような外見を持ちます。1世紀以上にわたり、分類や淡水魚の系統樹上での位置づけを巡って議論が続いてきました。本研究はその謎を解く重要な一片を提供します:染色体の端から端まで連続した、初の完全かつギャップのないO. evolansのゲノムです。
なぜこの魚が重要なのか
O. evolansは透明で流れの速い渓流に住み、食物網のバランス維持に寄与するとともに水質の敏感な指標種にもなります。オスは繁殖期に側方の鮮明な縞や頭部や眼の周りの粒状突起、暗い黒みがかった紫色の吻を発達させます。これらの目を引く形質と速い流れを好む生態は、動物が環境に適応する仕組みを研究するうえで理想的なモデルにします。一方で汚染や生息地の断片化、外来種といった人為的変化により個体群は縮小しており、保全のためにその生物学を理解することが重要です。
長年続いた名前の混乱
何十年にもわたり、生物学者たちはO. evolansを属としてOpsariichthysに入れるべきか、あるいはZaccoに置くべきかで苦慮してきました。初期の分類学者はヒレの形や体の縞模様といった外見的特徴に基づき本種をZacco evolansと記述しました。後の詳細な研究は、その縞模様や繁殖性の突起がよく似たZacco platypusとは異なることを示しました。ミトコンドリアDNAの研究はO. evolansがOpsariichthysに最も適合すると示唆しましたが、核遺伝子の一部はZaccoとの近縁性を示す兆候を与えていました。完全なゲノムがなければ進化的な全体像は曖昧なままであり、系統上の正確な位置をめぐる議論は続いていました。

ゲノムの一文字一句を読む
これらの疑問を解決するため、研究者たちは中国安徽省の河川から野生の雄個体を採集し、九種類の異なる組織を慎重に保存しました。次に、それぞれに強みを持つ最先端の複数のDNAシーケンシング技術を組み合わせて遺伝情報を読み取りました。短く高精度なリードで配列を磨き上げ、PacBioやOxford Nanoporeの長〜超長リードが困難領域を越えて染色体を端から端まで繋ぎました。さらに細胞内でDNAが折りたたまれる様子を捕えるHi-C技術を用いて断片を完全な染色体に配置しました。最終的に得られたのは約8.9億塩基対、39本の染色体に一連の連続したDNA配列として整然と配列されたテロメア間(telomere-to-telomere)のギャップのないゲノムです。
ゲノムが明かすこと
完成したゲノムは厳格な品質検査をクリアし、期待される保存遺伝子の99%以上を捕捉し、関連種から知られている配列と高い一致を示しました。ゲノムのほぼ半分は繰り返し配列で占められており、その多くは進化の過程で移動してゲノムを再構築する「ジャンプ遺伝子」です。研究チームは約3万個のタンパク質をコードする遺伝子と数千の非コードRNAを同定し、大部分は主要な生物学データベースと結び付けて既知の機能に関連付けることができました。新しいこのゲノムを近縁種であるOpsariichthys bidensおよびZacco platypusのゲノムと比較したところ、全体的な染色体構造は非常に類似しており強い進化的結びつきを裏付けました。その枠組みの中で、体の縞模様や急流適応に関与すると考えられる候補遺伝子や経路を特定し、独特の外観や生活様式がどのように進化したかについての手がかりを提供しています。
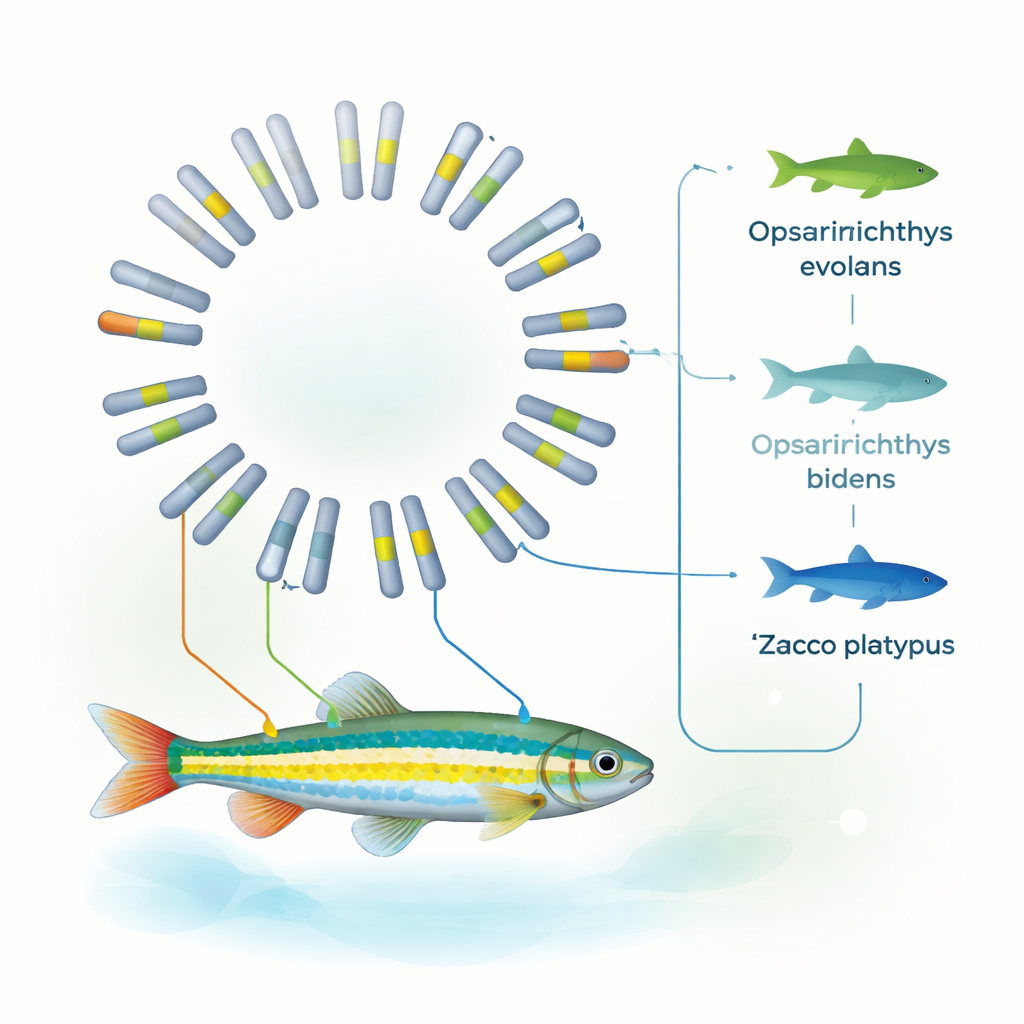
魚類の系統樹上での位置づけの明確化
10種の魚に共通する遺伝子ファミリーを用いて研究チームは詳細な進化樹を再構築しました。その解析はO. evolansがZ. platypusとおよそ800万〜1900万年前に分岐し、そのゲノム構造が特にO. bidensに近いことを示しています。これらのパターンは先行するミトコンドリアの証拠と合わせて、O. evolansをZaccoではなく確実にOpsariichthys属に位置づけることを支持します。言い換えれば、縞模様や吻の色、繁殖構造の注意深い形態学的観察が示唆していたことを、完全なゲノムが裏付けたのです:外見は誤解を招くこともありますが、形態と完全なゲノムが一致すると分類がずっと明確になります。
なぜ完全なゲノムが意味を変えるのか
専門外の人にとって、この成果はぼやけて裂けた地図から高解像度の完璧な地図帳に移行したようなものです。完全でギャップのないゲノムにより、研究者はO. evolansの鮮やかな色彩や急流に適した流線型の体型、東アジアの小型コイ類との関係をこれまでになく正確にたどることができます。この資源は魚類の分類を精緻化し、脆弱な渓流生態系の保全を導き、淡水魚に見られる多様性がDNAの小さな違いからどのように生じるかの理解を深める助けとなるでしょう。
引用: Wang, P., Wang, X., Yin, D. et al. Telomere-to-telomere gap-free genome assembly of the Opsariichthys evolans (Cypriniformes: Cyprinidae). Sci Data 13, 263 (2026). https://doi.org/10.1038/s41597-026-06588-7
キーワード: ゲノムアセンブリ, 淡水魚, テロメアからテロメアへ, 魚類の進化, 比較ゲノミクス