Clear Sky Science · ja
力とノイズから学ぶデータ効率の高い粗視化分子動力学
分子を縮めることが重要な理由
タンパク質とその周囲の水分子のすべての原子の絶え間ない運動をシミュレートすることは、分子スケールで生命の働きを理解するための最良の手段の一つです。しかし、これらの全原子シミュレーションは計算負荷が非常に大きく、タンパク質が折りたたまれる、ほどける、あるいは相互作用する様子を生物学的に意味のある時間スケールで追うにはスーパーコンピュータ上で何カ月もかかることがあります。本稿は、全原子シミュレーションに振る舞いが近いまま、はるかに少ない学習データと計算資源で動作する高速な簡略モデルを構築する新しい方法を紹介します。
全原子から簡潔な像へ
従来の分子動力学は各原子を追跡し、毎回の微小な時間刻みで原子間の力を計算します。計算を高速化するために、研究者は多くの原子を少数の「ビーズ」にまとめる粗視化モデルを用いることが多いです。こうした縮約モデルは実行がはるかに速い一方で、とくに複雑な折りたたみ挙動を示すタンパク質については、全原子シミュレーションの精度に匹敵させるのが難しいという問題がありました。近年では、より良い粗視化力場を自動発見するために機械学習が用いられるようになりましたが、これらのモデルの学習には通常、各原子の力がラベル付けされた何百万もの詳細なスナップショットが必要であり、膨大なデータと計算コストが問題でした。
物理的な力と有益なノイズの融合
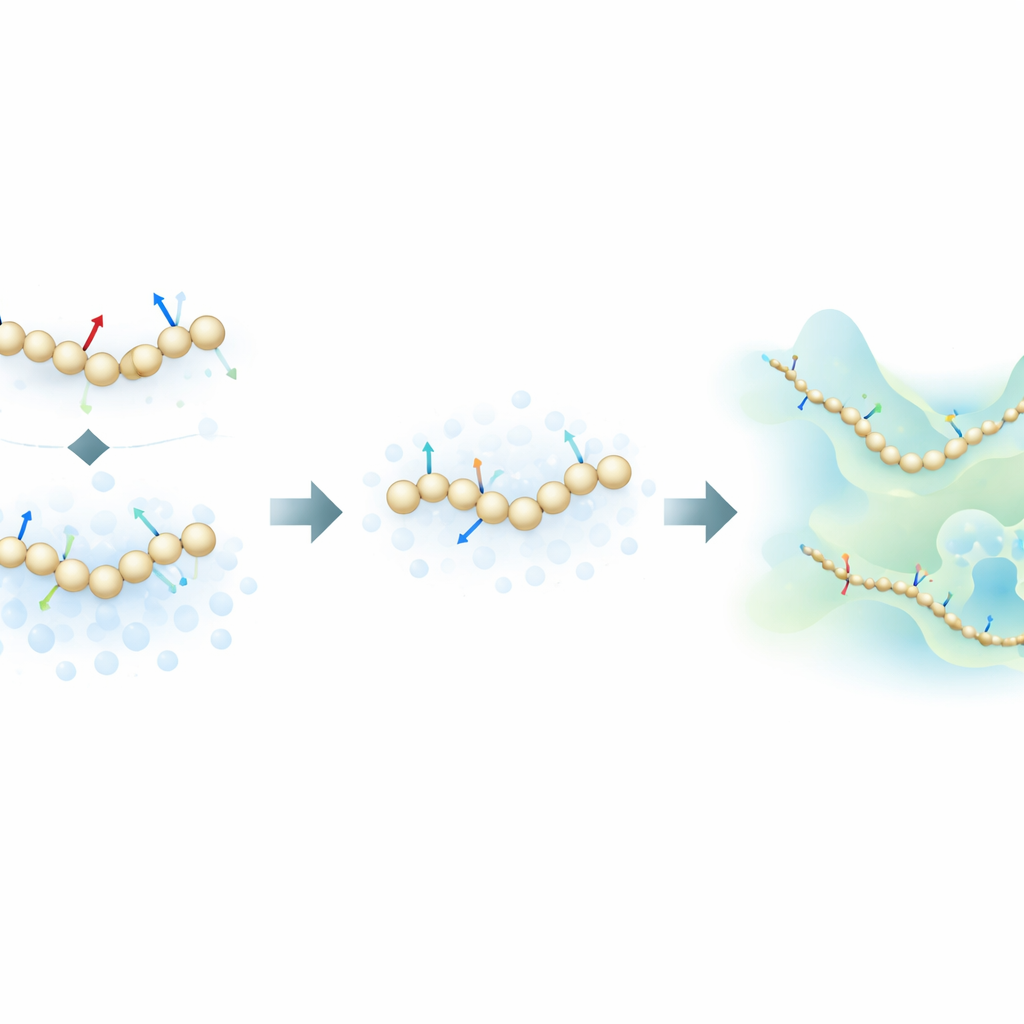
著者らは、生成的拡散モデルに触発された新しい学習戦略を提案します。これは多くの現代的なAI画像生成器の背後にあるアルゴリズム群と同じクラスの考え方です。全原子シミュレーションで計算される物理的な力からのみ学習する代わりに、この手法では粗視化された構成に制御されたノイズを意図的に加えることで、分子構造の空間分布からも学習します。この枠組みでは、ノイズは単なる除去すべき邪魔者ではなく、追加の情報源となります。従来の「力一致(force matching)」アプローチと拡散モデル由来の復元(denoising)技術を数学的に統合することで、この方法ははるかに少ないラベル付き例からタンパク質の潜在的なエネルギー景観を推定できます。
単純なモデルに複雑なタンパク質を模倣させる
アイディアを検証するため、研究者たちは複雑さが増すいくつかのタンパク質についてニューラルネットワークによる粗視化モデルを学習させました。対象は小さなミニタンパク質のChignolinとTrp-Cage、やや大きいNTL9、そして76残基のユビキチンです。学習モードは、原子力のみ、ノイズ由来の情報のみ、両者の組み合わせの三つを比較しました。小さなタンパク質については、新しい両者併用のアプローチが、折りたたみとほどけた状態の相対的安定性や中間状態の存在といった折りたたみ景観の主要な特徴を、標準的な力一致法よりも最大で100倍少ない学習データで再現できることを示しました。驚くべきことに、データが乏しい状況では、ノイズのみで学習したモデルが力のみで学習したモデルと同等かそれ以上の精度を示すことも多くありました。
より大きく困難なタンパク質系への到達
ユビキチンはより手強いテストケースです:その折りたたみ・ほどけを現実的な温度で捉えるには、従来は専用ハードウェアと非常に長い全原子走査が必要でした。本研究では、折りたたんだ状態の周辺での短い平衡シミュレーションと、タンパク質を強制的に引き伸ばす非平衡の「プル」シミュレーションを組み合わせた控えめなデータセットを用いて粗視化モデルを学習させました。この偏った学習セットと同一条件での完璧な原子参照が欠けているにもかかわらず、力とノイズの両方で学習したモデルは、折りたたんだ状態とほどけた状態が共存し、折りたたんだ状態が安定性の面で優勢であるという現実的な像を回復しました。これに対して力のみで学習したモデルは折りたたんだ状態をまったく安定化できず、ノイズのみのモデルはほどけた構造を好む傾向を示しました。注目すべきは、どの粗視化モデルも訓練データ中の極端に引き伸ばされた形状を単に記憶しているわけではなく、学習されたエネルギー景観が入力軌跡の単なる写しではなく物理的に意味のあるものになっている点です。
今後のシミュレーションが意味するもの
ノイズを学習信号に変え、それを物理的な力と統合することで、本研究は、タンパク質の精度の高い粗視化モデルが、従来考えられていたよりもずっと小さく質の劣るデータセットから構築できることを示しました。実用面では、研究者が機械学習による粗視化ダイナミクスで生体分子の挙動を探る前に、専用のスーパーコンピュータ上でミリ秒級の全原子シミュレーションを行う必要がなくなる可能性を意味します。代わりに、より手頃なハードウェア上での比較的控えめなシミュレーションで、主要な折りたたみ経路や熱力学的バランスを捉える強力な縮約モデルを学習できるかもしれません。追加するノイズの選び方と解釈、さらに本手法がより大きく複雑な生体分子集合体でどのように機能するかについては依然として課題が残りますが、このアプローチはデータ駆動型粗視化シミュレーションを分子科学の標準ツールにするための障壁を大幅に下げます。
引用: Durumeric, A.E.P., Chen, Y., Pasos-Trejo, A.S. et al. Learning data-efficient coarse-grained molecular dynamics from forces and noise. Nat Commun 17, 2493 (2026). https://doi.org/10.1038/s41467-026-70818-0
キーワード: 粗視化分子動力学, 機械学習フォースフィールド, タンパク質の折りたたみシミュレーション, 化学における拡散モデル, データ効率の高いシミュレーション