Clear Sky Science · ja
修正ガウス混合モデルによるDNA-PAINTの分子マッピング
分子の見えない世界を可視化する
現代生物学は、細胞だけでなくその内部の個々の分子を観察できる顕微鏡にますます依存しています。しかし、こうした分子からのかすかな点滅する光を、それぞれの分子がどこにあるかを示す信頼できる“地図”に変換するのは意外に難しい。 本研究はG5Mと呼ばれる新しい計算手法を紹介します。G5Mはこれらの分子地図をより正確かつ詳細にし、タンパク質が実際の細胞内でどのように配置・集合しているかを、ナノメートルスケール、場合によっては数ナノメートル以下の精度で理解する助けになります。
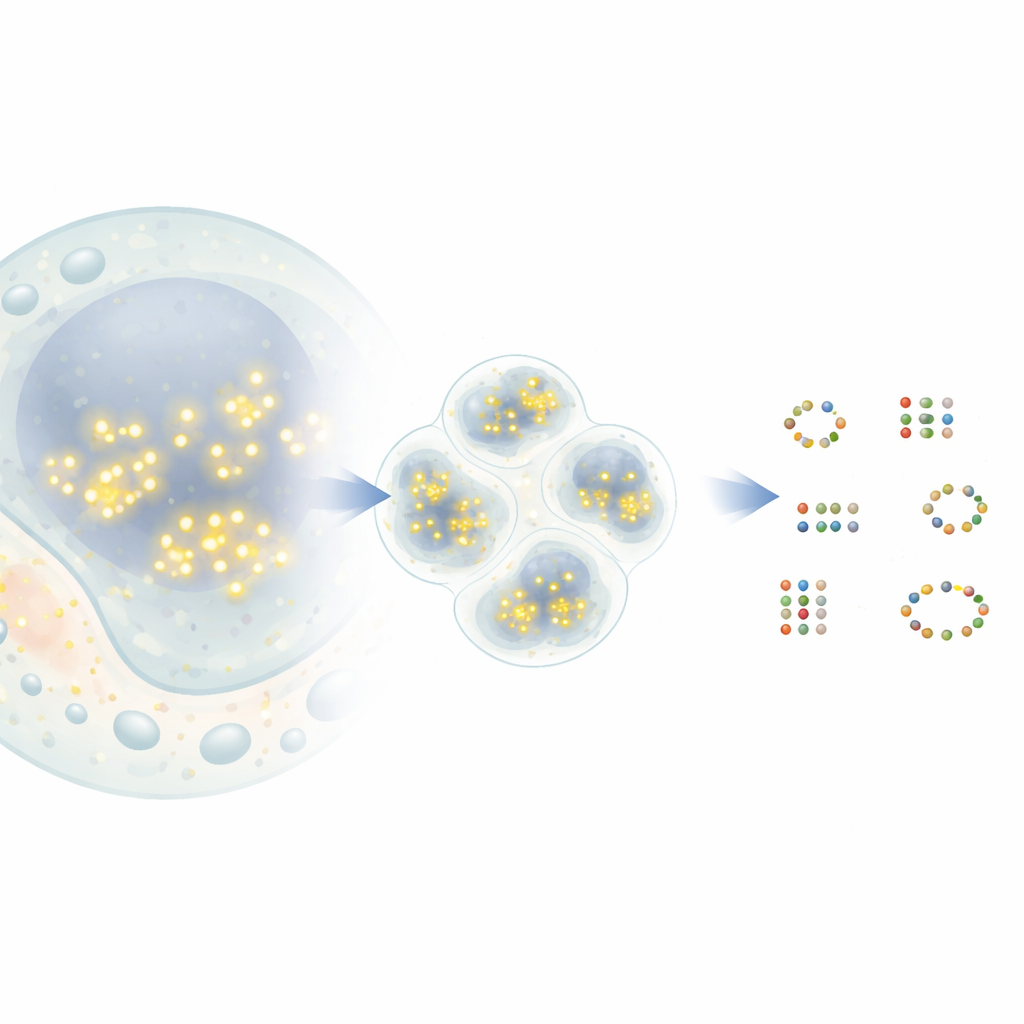
点滅する点から分子マップへ
DNA‑PAINTと呼ばれる一般的な超解像手法では、蛍光色素を持つ短いDNA鎖が標的タンパク質に取り付けられた相補的なDNAタグに一時的に結合・解離します。色素が結合するたびに顕微鏡上では明るい点として現れ、すぐに消えます。時間をかけて多数のイベントが蓄積されると、各タンパク質の周りに点の雲が形成されます。理論上は各雲の中心がナノメートル精度でタンパク質の真の位置を示しますが、実際には近接するタンパク質由来の点が重なったり、ランダムな背景信号からの点が混入したりします。既存の解析ツールは近接する点を1つのタンパク質として統合してしまったり、逆に存在しないタンパク質を誤検出したりしやすく、生物学的洞察の抽出を制限します。
実在する分子を見つける賢い方法
新しい手法G5Mは、点の群れを単純な鐘形の雲の混合として扱い、それぞれが一つの実在する分子に対応するとみなします。単に密度で近傍の点をまとめるのではなく、G5Mは確率モデルを用い、測定位置の精度、DNA鎖の結合解離の速度、顕微鏡による2次元あるいは3次元でのぼかしなど、実験について既に分かっている情報を取り込みます。続いて、異なる個数や形状の雲という複数の可能な説明を検討し、フィットの良さと単純さのバランスが最も良い解を自動的に選びます。さらに、点の数が少なすぎる、幅が狭すぎる・広すぎる、互いに十分に分離していないなど、疑わしい解を排除する追加の安全策も備えています。
シミュレーションとDNAナノ構造で実力を証明
G5Mを検証するために、著者らはまず現実的なコンピュータシミュレーションを用いて単純な場面を再現しました:近接した分子の対や、わずか数ナノメートル間隔で配列した12分子の小さな格子などです。現在の主要手法であるGradient Ascentと比較して、G5Mは理論的な解像限界で可視であるはずの分子をはるかに多く検出し、一方で存在しない分子をほとんど報告しませんでした。重要なケースでは、従来法より27倍多くの密接ペアを回復し、実効解像度を半分以上向上させました。次にDNAオリガミ構造(ドッキング部位が正確に配置された人工的なDNA形状)を用いた実験でこれらの利点を確認し、G5Mがさまざまなイメージング条件下で期待されるほとんどすべての部位を確実に数え、位置を特定できることを示しました。
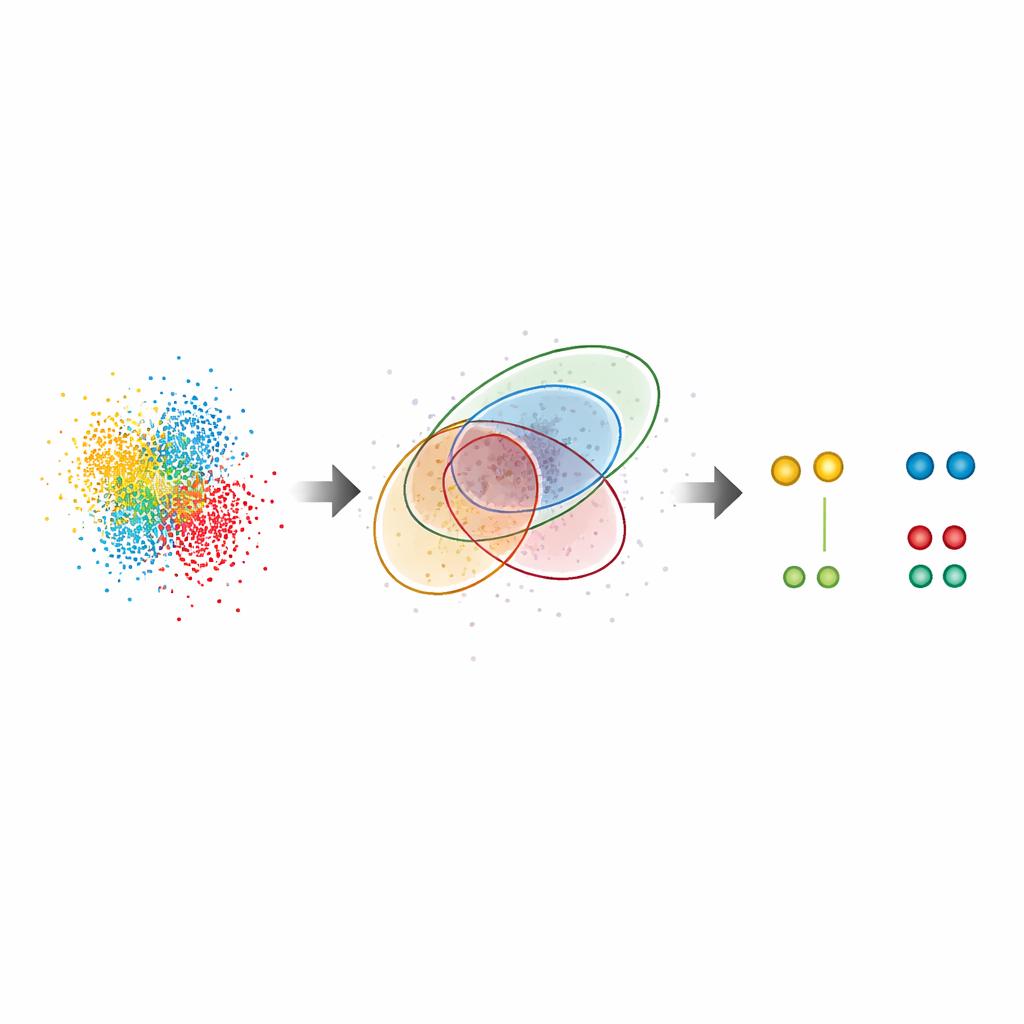
実細胞で隠れたパターンを明らかにする
試料を超えて、G5Mは複雑な生物学的システムにも適用されました。細胞核の巨大な出入り口である核膜孔複合体では、主要タンパク質Nup96の既知のリング状配列を、パートナー間が約10ナノメートルしか離れていない場合でも回復しました。標準的手法に比べほぼ倍のタンパク質ペアを検出し、標識効率の独立した推定とも一致しているため、多くの分子を見逃したり誤って追加したりしていないことが示唆されます。著者らは血液がんに関与し治療用抗体の標的でもある表面受容体CD20も調べました。ここではG5Mが細胞膜上のCD20の小さなクラスター(ダイマー、トリマー、テトラマー)を有意に多く明らかにし、抗がん抗体や関連する薬剤フォーマットがこれらの受容体をどのように再編成するかを解明しました。複数ラウンドのイメージングで信号を分離するRESIという超高解像アプローチの性能も向上させました。
今後の顕微鏡法にとっての意義
既存のDNA‑PAINTデータからより信頼できる情報を引き出すことで、G5Mは顕微鏡や色素を変更せずにソフトウェアだけで新たな生物学的詳細を明らかにできることを示しました。アルゴリズムは誤検出を極めて低く抑えつつ、ほとんど接触している分子を分解可能にし、複合体に何個のタンパク質が含まれるか、それらがどのように間隔を取っているか、薬剤が配置をどのように変えるかといった問いに不可欠です。オープンソースのPicassoプラットフォームに組み込まれ、一般的な設定に対して頑健なG5Mは、点滅する蛍光信号を信頼できる分子地図に変える標準的なツールになる位置にあり、細胞内のナノスケール組織を描き出す研究を支援します。
引用: Kowalewski, R., Reinhardt, S.C.M., Pachmayr, I. et al. Molecular mapping in DNA-PAINT via modified Gaussian Mixture Modeling. Nat Commun 17, 2315 (2026). https://doi.org/10.1038/s41467-026-70198-5
キーワード: 超解像顕微鏡法, DNA-PAINT, 分子マッピング, タンパク質のオリゴマー化, 画像解析アルゴリズム