Clear Sky Science · ja
ForkMLを用いたヒト細胞におけるDNA複製フォーク進行の自動マッピング
なぜDNAコピー速度の追跡が重要か
ヒトの細胞が分裂するたびに、30億以上の塩基配列を迅速かつ正確に複製する必要があります。この複製過程が遅くなったり停止したりすると、ゲノムが損傷を受け、がんや発達障害の原因になり得ます。しかしこれまで、個々のDNA「コピー機械」がヒトゲノムの特定領域をどれだけの速さで移動するかを直接的に観察する簡便な方法はありませんでした。本稿は、ナノポアDNAシーケンシングと機械学習を組み合わせ、前例のない規模でこの課題を自動化する新手法、ForkMLを紹介します。
細胞のコピー機械を間接的に観察する
DNAは複製フォークと呼ばれる微小な分子機械によって二重らせんに沿って移動し、新しい鎖を合成します。ForkMLでは、無害な化学標識であるBrdUを新しく合成されたDNAに短時間のパルスで2回導入することで、これらのフォークを間接的に観察します。BrdUは単一のDNA分子上でナノポアシーケンサーにより検出できるため、フォークが2回のパルスの間に通過した位置に沿って各DNA鎖上に2つの標識「ストライプ」が現れます。ストライプ間の距離を既知の時間差で割ることで、そのゲノム領域における各フォークの移動速度を算出できます。 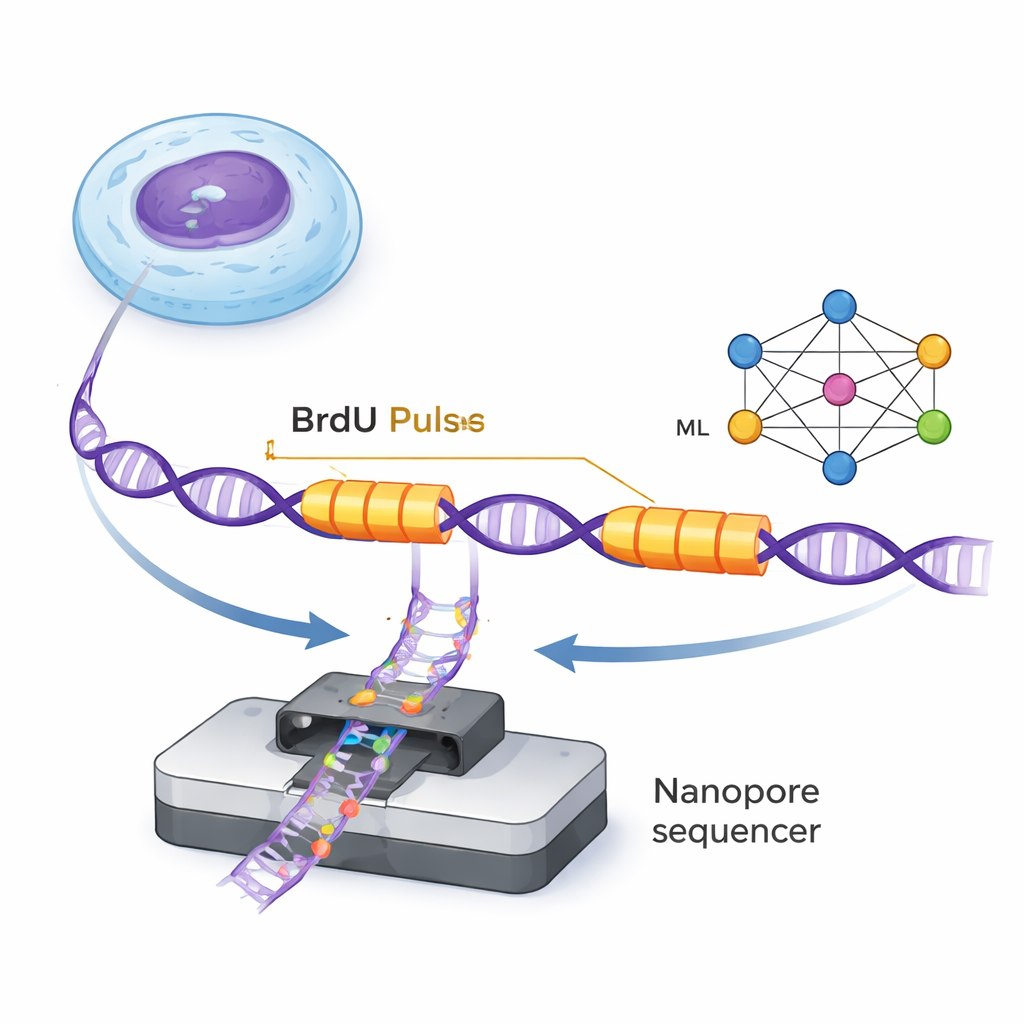
化学的な痕跡を読むようにコンピュータを訓練する
酵母での以前の研究では、著者らは単純なルールでBrdUトラックを検出できましたが、ヒト細胞では信号がより弱く複雑になります。人間の専門家であれば、パルス開始時のBrdUの急上昇と洗い流し後の緩やかな減少という特徴的なパターンを認識できますが、数百万のDNA断片を手作業で解析するのは不可能です。ForkMLは数千件の手動注釈例を用いてニューラルネットワーク(機械学習の一種)を訓練することでこの問題を解決します。モデルは各DNA区間を背景、右向きフォーク、左向きフォークに分類し、各BrdUパルスの開始点を高精度で特定することを学びます。これにより、単一のシーケンス実行から得られる数千の個別フォーク速度を完全に自動でマッピングできます。
ストレスやゲノム全体の差異を測る
ヒトの大腸がん細胞株でForkMLを適用したところ、実験ごとに2,000件以上のフォーク速度測定を得られ、典型的なフォーク速度は約1.2キロベース/分であり、従来の低スループット法と一致しました。複製を遅くすることが知られている薬剤で処理すると、ForkMLは明瞭に速度低下を検出し、複製ストレスを高感度に測定できることを示しました。各フォークは参照ゲノム上の位置にマッピングされるため、著者らは速度を複製タイミング、クロマチンの凝集度、転写活性などの他の特徴と関連付けることができました。 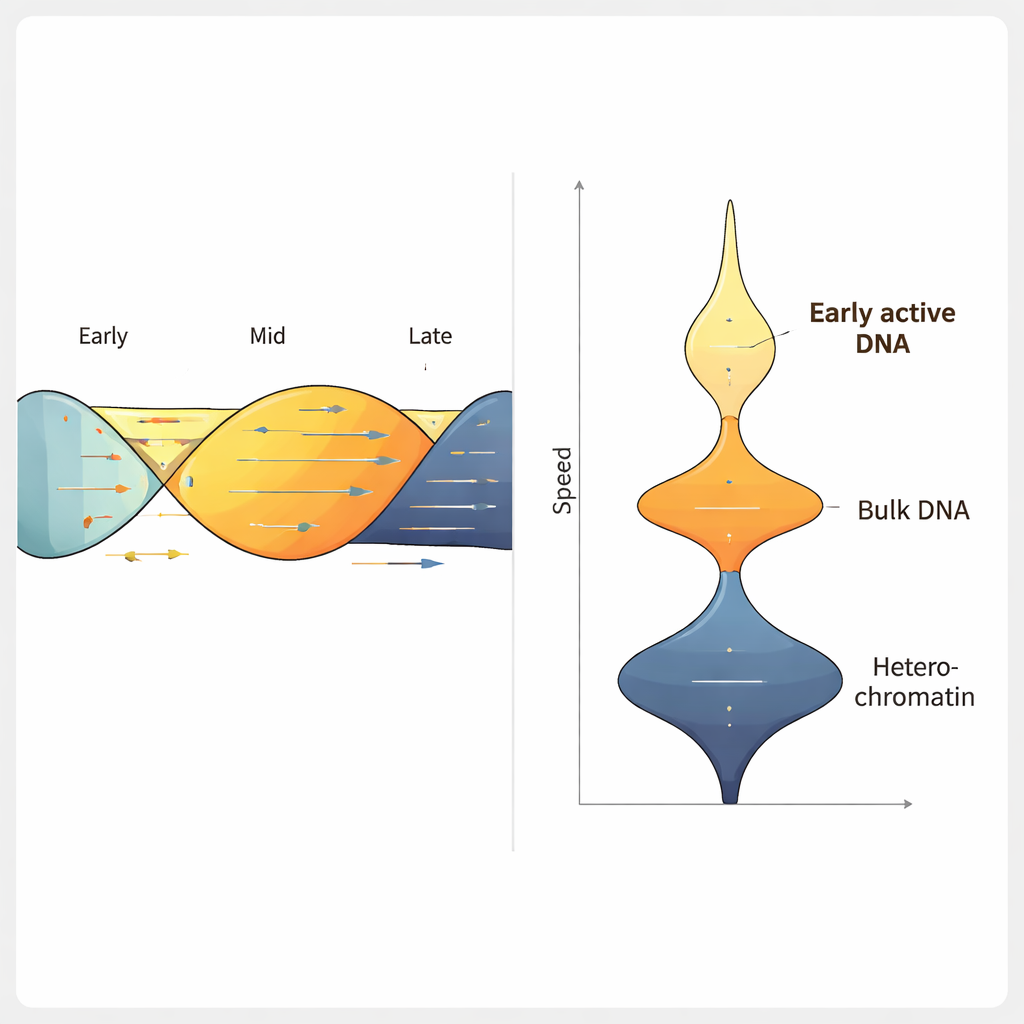
複製開始点と鎖ごとの差を明らかにする
速度に加えて、ForkMLは同一分子上でフォークが発散・収束する点を検出することで、複製がどこで始まりどこで終わるかも特定します。2万件を超える開始部位をマッピングした結果、ヒト細胞は混合戦略を採用しており、いくつかは明確な開始ゾーンで始まる一方で、多くはゲノム全体に散在していることが確認されました。さらに、フォークの進行方向とシーケンサーが読み取ったDNA鎖を組み合わせることで、従来のファイバー法では不可能だった先行鎖と遅延鎖の合成速度の違いも区別できます。正常およびがん由来を含む6種類のヒト細胞株での検証により、単純なBrdU標識条件が広く適用可能であり、各ケースで堅牢な速度推定が得られることが示されました。
古典的手法のデジタル化
専門外の人にとって、ForkMLは古典的なDNAファイバーアッセイを現代的にデジタル化したものと見なせます。類似の標識スキームを用いながら、手動顕微鏡観察を長読長シーケンシングと機械学習に置き換えています。これによりスループットが大幅に向上し、各測定値をゲノム上に直接配置でき、DNAがどこでどれだけ速く複製されるかについてより詳細な情報が得られます。プロトコルは単純で現行のナノポア機器と互換性があり、他の生物種にも適応可能なため、ForkMLはDNA複製研究の標準ツールになることが期待されます。実務的には、局所的なDNA複製速度(正常時およびストレス時)を遺伝子発現、クロマチン状態、疾患関連のゲノム変化と結び付ける強力な手段を研究者に提供します。
引用: Rojat, V., Ciardo, D., Tourancheau, A. et al. Automated mapping of DNA replication fork progression in human cells with ForkML. Nat Commun 17, 1975 (2026). https://doi.org/10.1038/s41467-026-68750-4
キーワード: DNA複製, 複製フォーク速度, ナノポアシーケンシング, BrdU標識, ゲノミクスにおける機械学習