Clear Sky Science · it
Colorazione virtuale dell'intera vetreria senza marcatori mediante microscopia PARS a doppia eccitazione ultravioletta
Osservare i tessuti senza distruggerli
Quando i medici diagnosticano malattie come il cancro o danni renali, spesso si basano su sottili sezioni di tessuto impregnate di coloranti chimici. Queste colorazioni rivelano strutture nascoste ma alterano in modo permanente o consumano il campione, il che può essere un problema quando la biopsia disponibile è minima. Questo studio presenta un metodo per «colorare digitalmente» i tessuti usando la luce e l'intelligenza artificiale, creando immagini di patologia dall'aspetto familiare senza applicare alcun colorante.
Perché le colorazioni tradizionali sono un’arma a doppio taglio
I coloranti chimici come ematossilina e eosina, o tinte speciali per collagene, carboidrati e strutture renali, sono gli strumenti fondamentali della patologia moderna. Rendono visibile il tessuto trasparente e sono indispensabili per diagnosticare cancro, infezioni e danni d’organo. Ma queste colorazioni sono distruttive: la stessa sezione di solito non può essere nuovamente colorata o impiegata per test avanzati, e più colorazioni consumano rapidamente materiale di biopsia prezioso. Ogni colorazione richiede inoltre procedure di laboratorio controllate, personale addestrato e può aggiungere ore o giorni al tempo necessario per ottenere una diagnosi.
Imaging a luce che legge il tessuto stesso
I ricercatori hanno usato un microscopio specializzato chiamato Photon Absorption Remote Sensing (PARS), che misura come le molecole dei tessuti assorbono e rilasciano energia dalla luce ultravioletta. In questo lavoro hanno combinato due lunghezze d’onda ultraviolette, una più corta e una leggermente più lunga, sparandole in un pattern intrecciato nello stesso punto del tessuto. Ogni impulso produce sia segnali legati al calore sia emissioni deboli simili a luminescenze, fornendo quattro canali distinti di informazione dalla stessa posizione. Una lunghezza d’onda è particolarmente sensibile al DNA nei nuclei cellulari, mentre l’altra evidenzia collagene, elastina, globuli rossi e pigmenti scuri come la melanina. Insieme mappano nuclei, tessuto di supporto, sangue e pigmento in modi che assomigliano e persino estendono ciò che i patologi vedono con le colorazioni tradizionali. 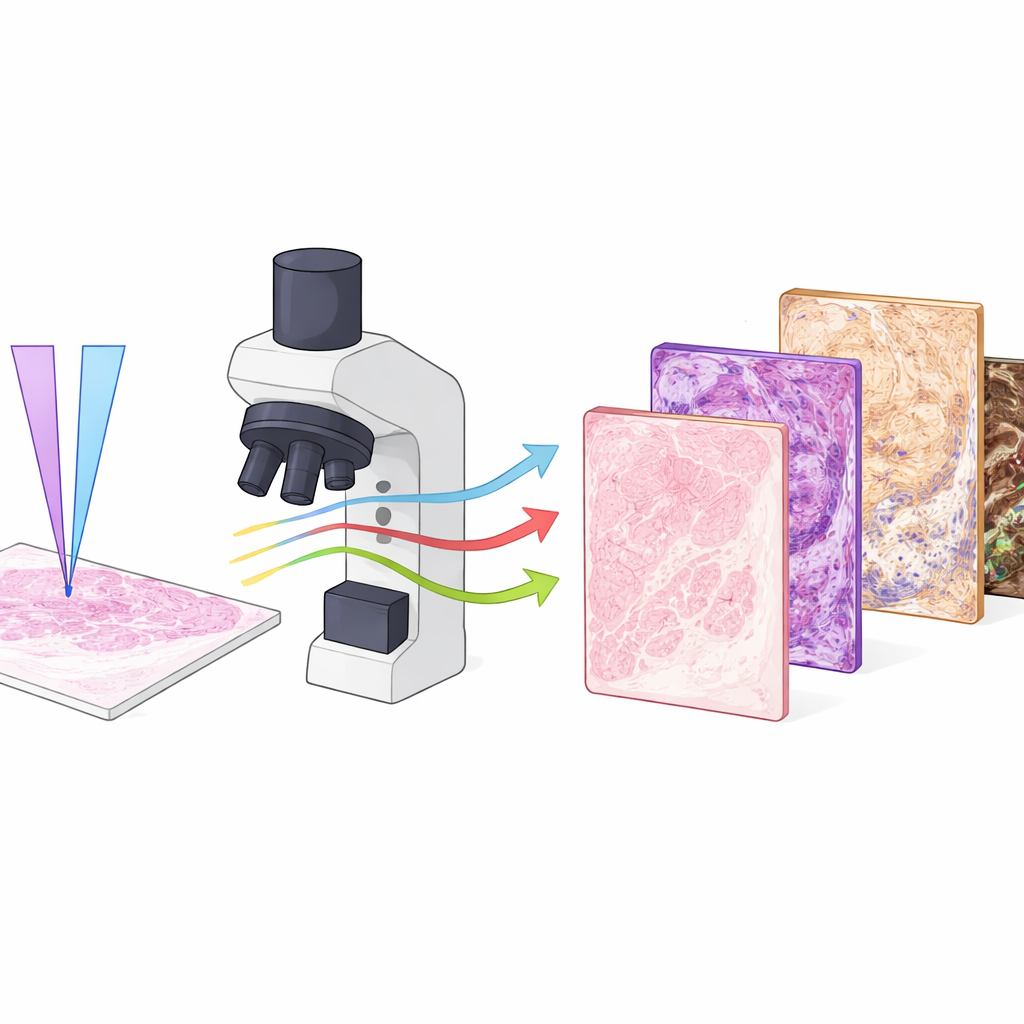
Insegnare ai computer a dipingere colorazioni virtuali
Raccogliere segnali ottici ricchi è solo metà della storia; l’altra metà è trasformarli in immagini che somiglino alle vetrini colorati standard. Per fare ciò, il team ha usato un framework di deep learning chiamato RegGAN. Hanno prima immagineato tessuti non colorati con PARS, poi hanno colorato chimicamente lo stesso vetrino e lo hanno scandito con uno scanner a campo chiaro convenzionale. Dopo aver allineato accuratamente queste immagini accoppiate, hanno addestrato reti neurali a trasformare le immagini PARS multicanale in versioni che imitano specifiche colorazioni, inclusi l'ematossilina-eosina di routine così come il tricromo di Masson, PAS e il metodo Jones con argento metenamina. Sono stati addestrati modelli separati per ogni colorazione, in modo che un singolo vetrino senza marcatori possa poi essere «ri-colorato virtualmente» in diversi modi su richiesta.
Cosa rivelano i vetrini virtuali
Su tessuti umani e murini — inclusi tumori renali, melanoma, infezioni fungine cutanee e organi normali — le colorazioni virtuali hanno seguito da vicino le controparti chimiche. I confini tumorali, le forme nucleari, il tessuto cicatriziale ricco di collagene, i globuli rossi, i filamenti fungini e le sottili strutture renali sono comparsi con elevata fedeltà quando entrambe le lunghezze d’onda ultravioletto sono state usate insieme. Misure quantitative di qualità dell’immagine hanno confermato che la combinazione delle due eccitazioni supera l’uso di ciascuna singolarmente, in particolare per strutture come collagene, cellule del sangue ed elementi fungini che beneficiano del contrasto aggiunto dalla lunghezza d’onda più lunga. In un piccolo studio in cieco, tre patologi esperti hanno valutato sia le immagini reali sia quelle virtuali principalmente come buone o eccellenti per qualità diagnostica visiva, e non sono riusciti a distinguere in modo affidabile quali immagini fossero chimicamente colorate e quali virtuali.
Punti di forza, limiti e potenziale futuro
Sebbene promettente, il metodo non è ancora pronto a sostituire gli scanner di routine. L’attuale sistema PARS è lento, impiegando ore per coprire l’area che uno scanner clinico può acquisire in minuti, e tutti i dati provengono da un unico setup di imaging e da un unico laboratorio di colorazione. La valutazione si è concentrata sulla somiglianza visiva e su alcune caratteristiche misurabili, piuttosto che sul processo decisionale clinico completo su molti pazienti e centri. Tuttavia, l’approccio offre un vantaggio unico: poiché l’imaging senza marcatori non danneggia il tessuto, lo stesso vetrino può in seguito essere colorato con coloranti tradizionali o usato per test molecolari, e da una singola scansione si possono generare più colorazioni virtuali. 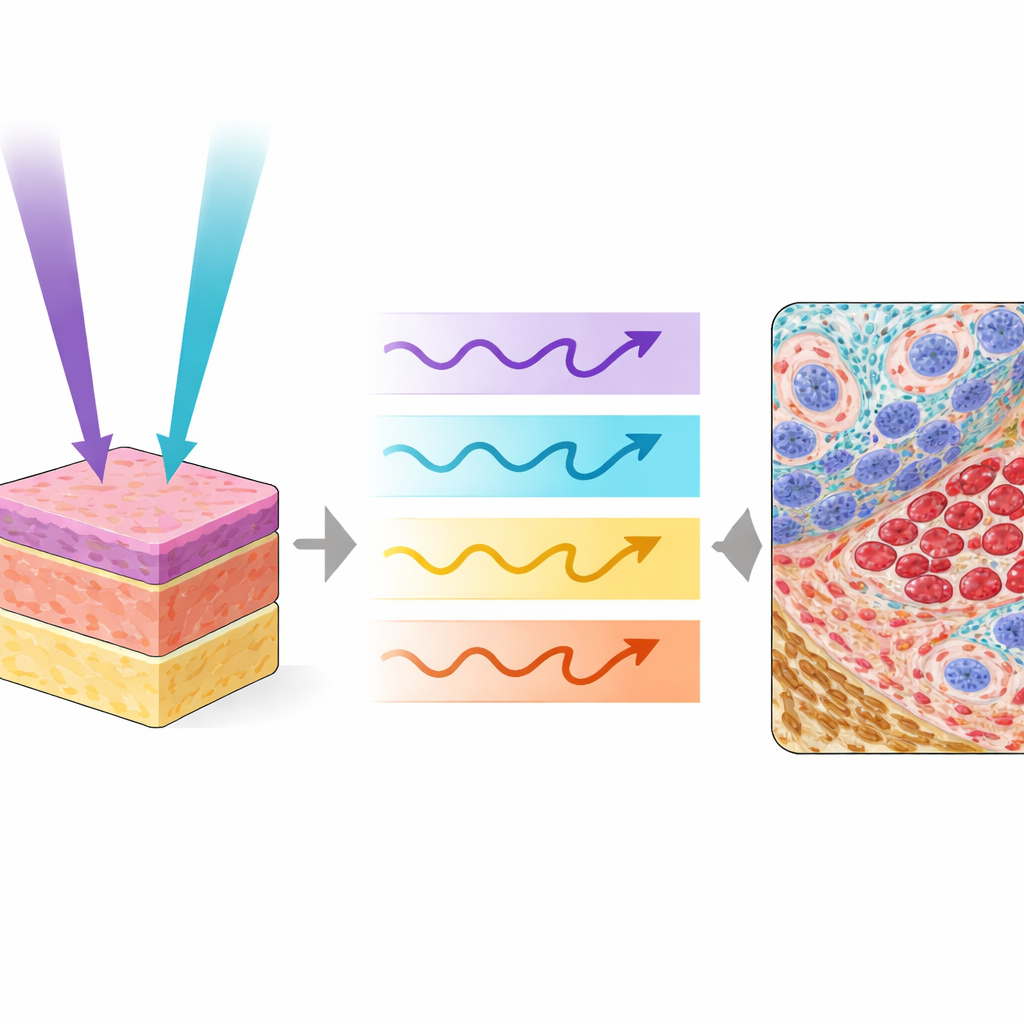
Cosa significa per pazienti e medici
In termini semplici, questo studio dimostra che è possibile «leggere» i tessuti usando solo la luce e poi impiegare l’intelligenza artificiale per ricreare i colori e i motivi familiari su cui i patologi fanno affidamento, incluse diverse colorazioni a partire da una singola sezione. Il sistema PARS a doppio colore fornisce informazioni sufficienti per evidenziare virtualmente nuclei, tessuto di supporto, sangue, pigmento e strutture renali specializzate senza toccare una goccia di colorante. Con hardware più veloce e studi più ampi multicentrici, questa tecnologia potrebbe diventare un valido complemento alla patologia standard, preservando preziose biopsie e offrendo ai patologi una visione più ricca e non distruttiva della malattia.
Citazione: Tweel, J.E.D., Ecclestone, B.R., Tummon Simmons, J.A. et al. Label-free whole slide virtual multi-staining using dual-excitation photon absorption remote sensing microscopy. npj Imaging 4, 22 (2026). https://doi.org/10.1038/s44303-026-00154-x
Parole chiave: colorazione virtuale, microscopia senza marcatori, patologia digitale, imaging ultravioletto, deep learning in istologia