Clear Sky Science · it
Un quadro genomico completo per identificare geni predisponenti al carcinoma mammario o ovarico con carenza di riparazione per ricombinazione omologa
Perché alcune famiglie affrontano rischi tumorali più elevati
Molte donne con carcinoma mammario o ovarico presentano una forte storia familiare della malattia, ma i test genetici spesso non forniscono una spiegazione chiara. Questo vuoto, talvolta definito «ereditabilità mancante», lascia le famiglie senza risposte e può limitare l’accesso a programmi di screening personalizzati o a terapie mirate. Questo studio ha cercato di costruire un nuovo approccio, più potente, per cercare nel nostro DNA geni nascosti che aumentano il rischio di cancro combinando diversi tipi di informazioni genomiche e cliniche invece di analizzarle separatamente. 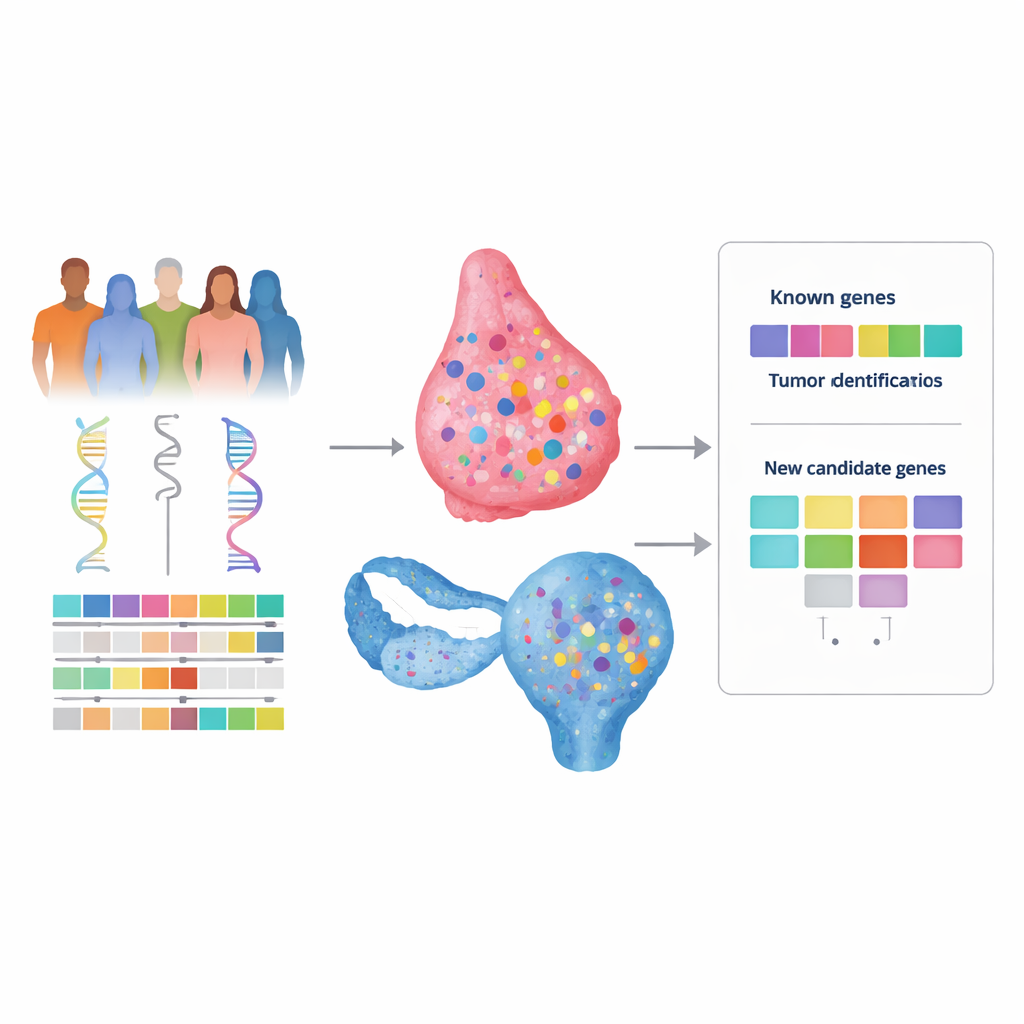
Cercare l’impronta di una riparazione del DNA difettosa
I ricercatori si sono concentrati su una particolare modalità di riparazione del DNA, nota come riparazione per ricombinazione omologa, che normalmente sistema rotture pericolose nel nostro materiale genetico. Quando questo sistema fallisce, le cellule accumulano una «firma mutazionale» rivelatrice — un pattern caratteristico di alterazioni nel DNA del tumore che funziona come un’impronta molecolare. Questo pattern è particolarmente comune in alcuni tumori mammari e ovarici difficili da trattare. Il gruppo ha ipotizzato che se un tumore mostra questa impronta, è probabile che abbia perso entrambe le copie funzionanti di qualche gene per la riparazione del DNA, noto o sconosciuto, e che ciò possa derivare da varianti ereditarie in quel gene.
Costruire un quadro combinato genetico e clinico
Per verificare questa idea, gli autori hanno analizzato il DNA di centinaia di pazienti con tumore al seno e all’ovaio presente in The Cancer Genome Atlas, che fornisce sia dati genetici del sangue (ereditarî) sia del tumore (acquisiti), insieme a informazioni cliniche. Hanno esaminato l’intero esoma — la parte codificante delle proteine del genoma — alla ricerca di varianti ereditarie rare potenzialmente dannose che presentassero anche un «secondo colpo» nel tumore, come la perdita della copia sana residua. Per ogni gene hanno poi chiesto se tali eventi a due colpi fossero più frequenti nei tumori con la firma di difetto di riparazione rispetto a quelli senza. Fondamentale è stato il fatto che non si sono limitati a un pannello predefinito di geni, permettendo così l’emergere di candidati inattesi.
Verificare che il metodo funzioni e trovare nuovi sospetti
Come controllo di realtà, il quadro ha correttamente evidenziato i noti geni BRCA1 e BRCA2 come fortemente associati alla firma di difetto di riparazione in entrambi i tipi di tumore, confermando che l’approccio si comporta come previsto. Nel tumore mammario ha inoltre segnalato un gene aggiuntivo, THBS4, e suggerito possibili ruoli per i geni KIF13B e TESPA1. Tuttavia, revisioni dettagliate caso per caso hanno mostrato che le alterazioni in THBS4 spesso comparivano insieme ad altri eventi correlati alla riparazione più consolidati, rendendolo un candidato meno convincente come guida principale. 
Approfondire i tumori ad alto rischio non spiegati
Per andare oltre la statistica, i ricercatori hanno sovrapposto dettagli clinici come il sottotipo tumorale, l’età alla diagnosi e l’ascendenza. Si sono concentrati sui pazienti i cui tumori mostravano chiaramente la firma di difetto di riparazione e appartenevano a gruppi clinici già legati a questa biologia — tumori mammari di tipo basal-like e carcinomi sierosi di alto grado dell’ovaio — ma che non presentavano eventi noti di tipo BRCA. In questi pazienti hanno cercato di nuovo varianti ereditarie con secondi colpi, questa volta all’interno di una lista ampia e curata di geni del cancro e della riparazione del DNA. Questa visione «clinico‑genomica» ha messo in luce diversi geni coinvolti nella riparazione delle rotture a doppio filamento del DNA e nella via correlata dell’anemia di Fanconi, inclusi RAD51B, RAD54B, RAD54L, FANCD2 e altri, come plausibili nuovi contributori al rischio ereditario.
Cosa significa per i pazienti e per la ricerca futura
Lo studio non pretende di aver dimostrato in modo definitivo nuovi geni di rischio tumorale; il numero di pazienti interessati per ciascun gene candidato è ancora limitato e saranno necessarie coorti più ampie e diversificate per confermarne il ruolo. Piuttosto, gli autori forniscono un modello riutilizzabile: un metodo per combinare DNA ereditario e tumorale, firme mutazionali caratteristiche e caratteristiche cliniche per dare priorità in modo sistematico a geni che potrebbero spiegare casi familiari inspiegati. Con il tempo, l’applicazione di questo quadro a dataset più grandi e ad altri tipi di cancro potrebbe ridurre il divario dell’«ereditabilità mancante», affinare i pannelli di test genetici e aiutare più pazienti a comprendere il proprio rischio e le opzioni di prevenzione e trattamento mirato.
Citazione: Camacho-Valenzuela, J., Matis, T., Roca, C. et al. A comprehensive genomic framework for identifying genes predisposing to homologous recombination repair-deficient breast or ovarian cancer. BJC Rep 4, 15 (2026). https://doi.org/10.1038/s44276-026-00218-w
Parole chiave: carenza di ricombinazione omologa, genetica del cancro al seno, cancro ovarico, geni della riparazione del DNA, sensibilità al cancro