Clear Sky Science · it
Paesaggio genomico della resistenza antimicrobica in India: risultati di uno studio di sorveglianza multispecie
Perché i superbatteri in India ci riguardano tutti
I “superbatteri” resistenti agli antibiotici sono una preoccupazione globale in crescita, ma sappiamo ancora sorprendentemente poco su come questi germi evolvono e si diffondono in molte aree del mondo. Questo studio esamina da vicino batteri pericolosi provenienti da ospedali indiani e legge il loro intero DNA per comprendere come eludono i nostri farmaci più potenti. I risultati non solo rivelano ciò che rende questi microrganismi così difficili da eliminare, ma testano anche se i metodi rapidi basati sul DNA possono sostituire in modo affidabile i test di laboratorio più lenti — una questione che potrebbe influenzare il trattamento delle infezioni ovunque.
Uno sguardo ravvicinato alle infezioni ospedaliere
I ricercatori hanno raccolto 266 campioni batterici da pazienti gravemente malati in grandi ospedali del nord e dell’ovest dell’India tra il 2022 e il 2024. La maggior parte dei campioni proveniva dal sangue, ma anche da urine e infezioni polmonari, e la maggioranza era proveniente da reparti di terapia intensiva, dove i pazienti sono più vulnerabili. Il team si è concentrato su noti germi problematici — come Escherichia coli, Klebsiella pneumoniae, Acinetobacter baumannii, Pseudomonas aeruginosa, Staphylococcus aureus meticillino‑resistente (MRSA) ed Enterococcus resistente alla vancomicina (VRE). Per ogni campione, i medici avevano già eseguito i test standard di sensibilità agli antibiotici, che espongono i batteri ai farmaci in laboratorio per vedere quali medicine funzionano ancora. Gli scienziati hanno quindi sequenziato i genomi dei batteri per mappare l’insieme completo dei geni di resistenza e hanno confrontato ciò che il DNA "prevedeva" con quello che effettivamente è accaduto nelle provette.
Quando geni e provette non concordano
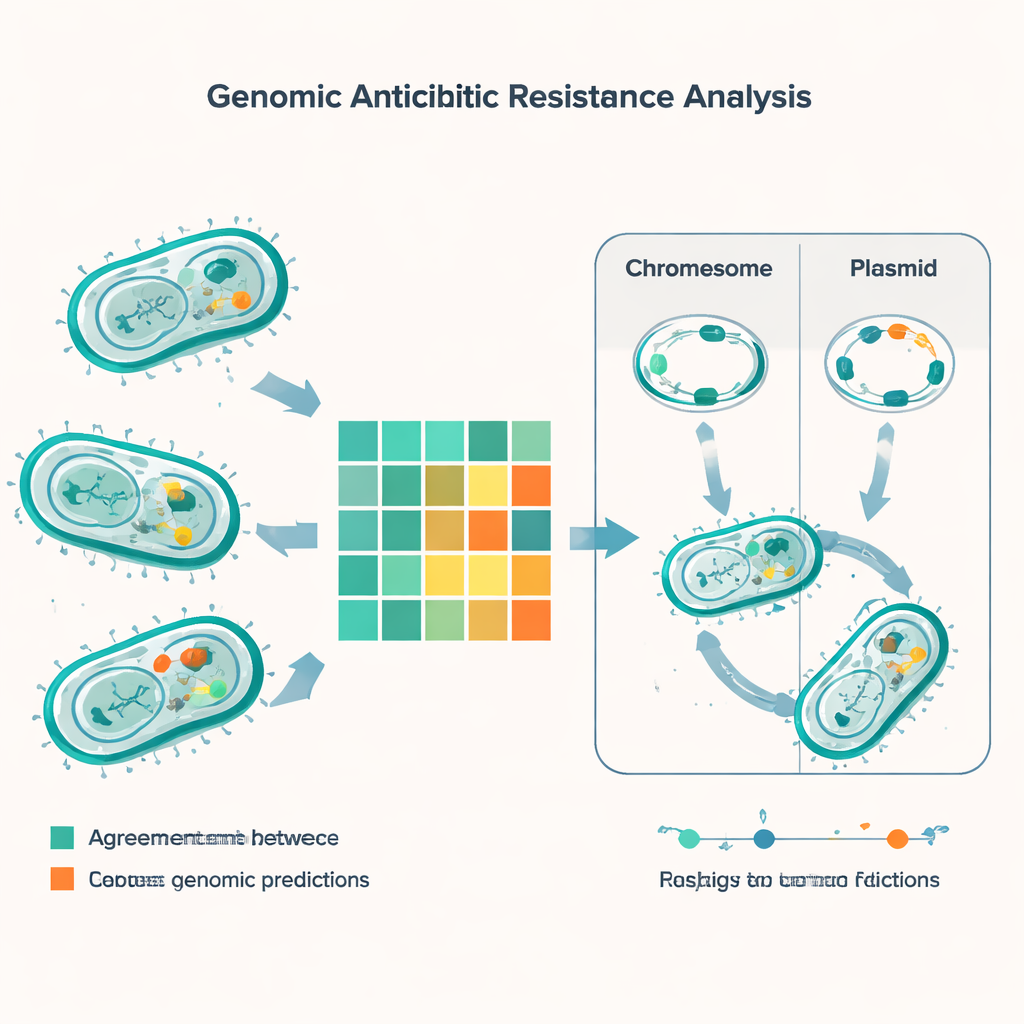
Confrontando le predizioni genetiche con i risultati di laboratorio per 56 diversi antibiotici, lo studio ha effettuato oltre 5.000 confronti. Nella maggior parte dei casi il metodo basato sul DNA e i test tradizionali concordavano, ma sono emersi quasi 600 disallineamenti. L’errore più comune è stato che lo strumento genomico prevedeva che un batterio fosse resistente quando il test di laboratorio indicava che era ancora trattabile. Questo è avvenuto spesso per farmaci come minociclina, colistina e gentamicina, specialmente in E. coli. L’errore opposto — dove il laboratorio osservava resistenza ma i geni non la spiegavano chiaramente — è stato meno frequente ma più preoccupante, perché rischia di far passare inosservata una resistenza. Queste discrepanze “molto maggiori” sono apparse in modo notevole in batteri intestinali chiamati enterococchi, in particolare per antibiotici simili alla penicillina e per la combinazione trimetoprim‑sulfametossazolo.
Arsenali nascosti nel DNA batterico
La indagine genomica ha scoperto un fitto arsenale di geni di resistenza nelle principali specie. Ognuno dei comuni patogeni Gram‑negativi portava almeno un gene beta‑lattamasi, che può degradare penicilline e farmaci correlati, e molti ceppi avevano diversi di questi geni contemporaneamente. Colpevoli noti come le carbapenemasi di tipo NDM — che neutralizzano antibiotici di ultima risorsa — erano diffuse in E. coli, Klebsiella, Acinetobacter e Pseudomonas. Lo studio ha anche rilevato geni che aiutano i batteri a sopravvivere ad antibiotici potenti di tipo “peptide” come la colistina, insieme al classico gene mecA che rende il MRSA resistente alla meticillina e ai cluster di resistenza alla vancomicina negli enterococchi. Confrontando le impronte digitali del DNA chiamate tipi di sequenza, il team ha collegato alcuni di questi geni di resistenza a linee batteriche ad alto rischio note che si stanno già diffondendo in India e nel resto del mondo.
Condivisione di geni tramite DNA mobile
Una parte cruciale della storia non riguarda solo quali geni i batteri portano, ma dove risiedono questi geni. Molti geni di resistenza si trovano su piccoli cerchi di DNA chiamati plasmidi, che i batteri possono scambiarsi come fossero carte da collezione. Usando software specializzati, i ricercatori hanno previsto circa 1.400 plasmidi tra i campioni, con una diversità particolarmente elevata in E. coli e Klebsiella. In queste specie, una larga parte dei geni di resistenza — inclusi diversi beta‑lattamasi critici — era portata da plasmidi, rendendoli più facili da trasferire tra ceppi e persino tra specie. Altri tratti di resistenza erano integrati nei cromosomi batterici, il che significa che possono persistere anche se i plasmidi vengono persi. Il team ha inoltre catalogato elementi genetici mobili — brevi segmenti di DNA che possono saltare e trasportare con sé geni di resistenza — evidenziando un’altra via per una rapida diffusione.
Cosa significa per i trattamenti futuri
Per i non specialisti, il messaggio centrale è che leggere il DNA batterico può sostenere notevolmente la lotta contro i superbatteri, ma la tecnologia non è ancora perfetta. Gli strumenti genomici tendevano a “sovrastimare” la resistenza, il che è più sicuro che non rilevarla, ma potrebbe spingere i medici a usare farmaci più potenti del necessario. Allo stesso tempo, un numero minore di casi ha mostrato che i test di laboratorio hanno rilevato resistenza che gli attuali cataloghi genici non sono stati in grado di spiegare completamente, sottolineando punti ciechi importanti nella nostra conoscenza. Costruendo una mappa dettagliata di geni di resistenza, plasmidi ed elementi mobili negli ospedali indiani, questo studio crea una base per diagnostiche basate sul DNA migliori e più rapide e per un uso degli antibiotici più informato — non solo in India, ma in qualunque contesto in cui i superbatteri minaccino la medicina moderna.
Citazione: Gheewalla, N., Karthikeyan, V., Jadhav, Y. et al. Genomic landscape of antimicrobial resistance in India: findings from a multi-species surveillance study. npj Antimicrob Resist 4, 13 (2026). https://doi.org/10.1038/s44259-026-00185-9
Parole chiave: resistenza antimicrobica, sequenziamento del genoma, infezioni ospedaliere, batteri resistenti ai farmaci, resistenza mediata da plasmidi