Clear Sky Science · it
Caratterizzazione genomica e sottoclustering del complesso clonale 38 di Escherichia coli rivelano marcatori genetici associati all’ospite
Perché è importante nella vita di tutti i giorni
Le infezioni resistenti agli antibiotici non sono più un problema confinato agli ospedali: interessano sempre di più il cibo, gli animali, i viaggi e la vita comunitaria. Questo studio si concentra su un particolare gruppo di batteri Escherichia coli, chiamato complesso clonale 38 (CC38), che può causare gravi infezioni del sangue e delle vie urinarie e spesso resiste ai nostri antibiotici più importanti. Tracciando le origini di questi batteri e come si muovono tra esseri umani, animali e ambiente, i ricercatori evidenziano indizi che potrebbero aiutare le autorità sanitarie a fermare ceppi pericolosi prima che si diffondano ampiamente.
Uno sguardo più attento a una famiglia batterica problematica
Non tutti gli E. coli sono dannosi, ma alcune linee sono recidive nelle malattie severe. CC38 è emerso recentemente come uno di questi gruppi problematici, secondo solo a una nota linea ad alto rischio (ST131) nelle infezioni ematiche danesi. Il team ha esaminato 242 ceppi resistenti di E. coli CC38 provenienti da pazienti danesi, 83 da alimenti e animali d’allevamento e oltre 2.300 genomi correlati raccolti a livello mondiale. Hanno utilizzato il sequenziamento dell’intero genoma — sostanzialmente la lettura del DNA di ciascun batterio — per mappare come sono correlate le diverse ramificazioni di questa famiglia, quali geni di resistenza portano e in quali ospiti tendono a risiedere.
Seguendo la traccia dagli ospedali alle fattorie e ai cibi
Confrontando gli E. coli CC38 dei pazienti danesi con quelli provenienti da pollame, bestiame e alimenti, i ricercatori hanno individuato due principali gruppi danesi. Un gruppo era composto principalmente da infezioni umane, mentre l’altro comprendeva batteri da pollame, altri animali d’allevamento e prodotti alimentari. Importante, non sono state trovate corrispondenze di DNA quasi identiche tra isolati umani e animali, il che suggerisce l’assenza di chiari focolai di origine alimentare in Danimarca nel periodo dello studio. Tuttavia, modelli statistici che esaminano segmenti di DNA accessorio hanno indicato che alcuni sottogruppi associati all’uomo probabilmente hanno origini nel pollame, suggerendo episodi di spillover passati o indiretti dai polli alle persone.
Un albero genealogico globale con due grandi rami
Estendendo l’analisi a un dataset mondiale di 2.638 genomi, il team ha costruito un “albero familiare” globale per CC38. Sono emersi due rami principali. Uno era fortemente legato al pollame e portava livelli moderati di resistenza insieme a molti tratti associati a malattie gravi. L’altro era dominato da sottogruppi associati all’uomo che differivano per resistenza, potenziale patogeno e ospiti preferenziali. Alcuni sottogruppi erano chiaramente focalizzati sull’uomo e fortemente resistenti, mentre altri mostravano schemi misti, comparendo in esseri umani, pollame, fauna selvatica, acque e animali da compagnia. Questo mosaico riflette la capacità di CC38 di adattarsi a diversi ambienti e specie ospiti, complicando gli sforzi di controllo.
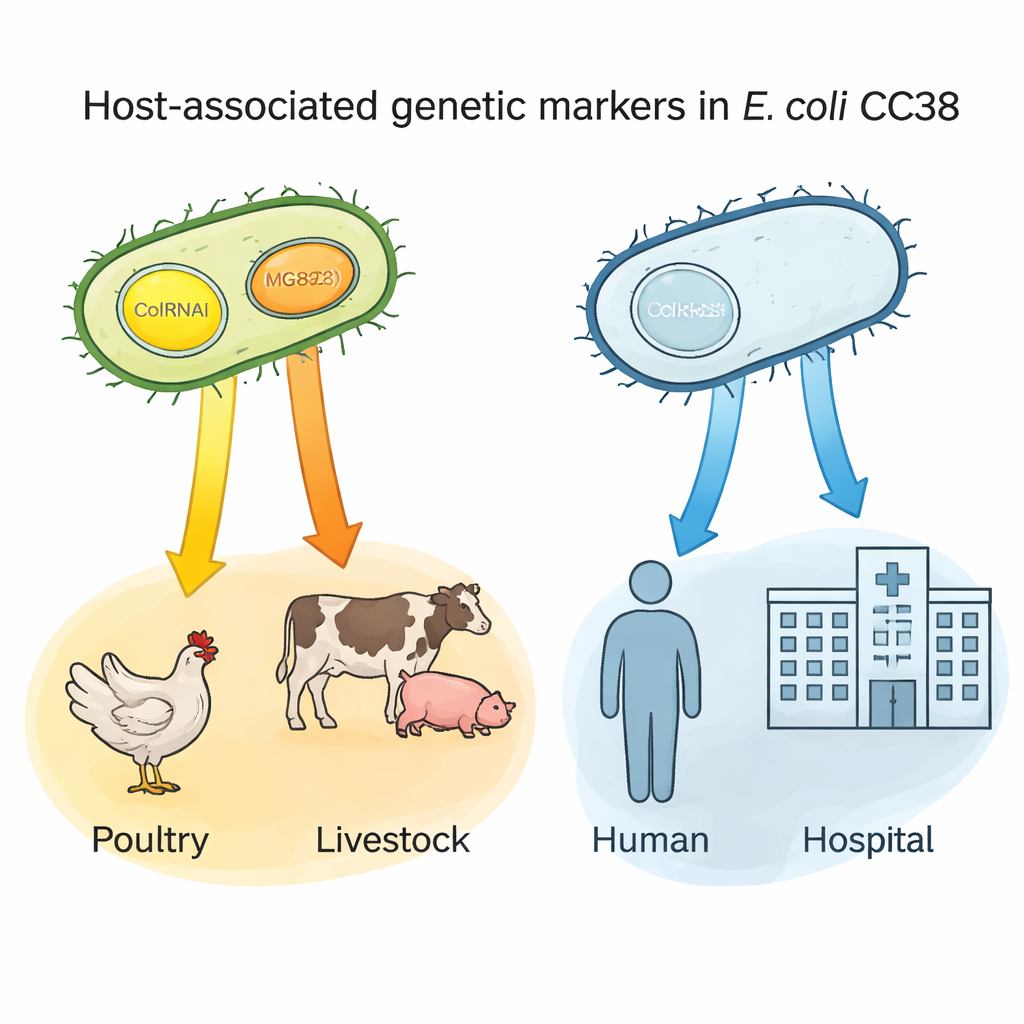
Piccoli cerchi di DNA come “etichette” dell’ospite
Una scoperta chiave ha riguardato due minuscoli frammenti di DNA — plasmidi chiamati ColRNAI e Col(MG828) — che possono spostarsi tra batteri. Questi plasmidi erano comuni in CC38 provenienti da pollame e altri animali d’allevamento ma rari nei sottogruppi centrati sull’uomo. Tramite analisi statistiche, gli autori hanno dimostrato che la presenza di uno di questi plasmidi prevedeva con forza un’origine avicola; il possesso di entrambi insieme era particolarmente caratteristico di linee legate al bestiame e a certe fonti alimentari. Poiché questi plasmidi spesso portano anche tratti di resistenza, possono agire come “etichette” genetiche che segnalano batteri probabilmente provenienti da serbatoi animali e aiutare a tracciare come ceppi resistenti entrano nella catena alimentare e raggiungono le persone.
Cosa significa per la protezione della salute
Per un lettore non specialista, il messaggio principale è che gli E. coli dannosi e resistenti ai farmaci non sono confinati agli ospedali o ai pazienti: costituiscono popolazioni interconnesse che attraversano esseri umani, pollame, bestiame, fauna selvatica, cibo e ambiente. Questo studio mostra che, all’interno di una linea importante come CC38, alcuni rami sono fortemente legati agli animali e altri all’uomo, e che specifici elementi di DNA mobili possono aiutare a rivelare l’origine probabile di un ceppo. L’uso di questi marcatori genetici nella sorveglianza di routine potrebbe fornire un allarme precoce quando batteri resistenti associati agli animali cominciano a comparire nelle persone. A sua volta, ciò supporta un approccio One Health — considerare la salute umana, animale e ambientale come parti di un unico sistema — per progettare strategie più intelligenti e mirate per prevenire le infezioni e rallentare la diffusione della resistenza agli antibiotici.
Citazione: Roer, L., Rasmussen, A., Hansen, F. et al. Genomic characterization and sub-clustering of Escherichia coli clonal complex 38 reveal host associated genetic markers. Commun Med 6, 126 (2026). https://doi.org/10.1038/s43856-026-01402-2
Parole chiave: resistenza antimicrobica, Escherichia coli, trasmissione zoonotica, pollame e bestiame, sorveglianza genomica