Clear Sky Science · it
Analisi dell’espressione genica ospite per la rilevazione di eziologia batterica e virale nei bambini ricoverati con sospetta infezione grave
Perché questa ricerca è importante per i bambini con infezioni gravi
Quando un bambino arriva in ospedale con febbre alta e un aspetto molto malato, i medici devono decidere rapidamente se la causa sia un’infezione batterica, che di solito richiede antibiotici, o un’infezione virale, che spesso migliora da sola. I test attuali sono ben lontani dall’essere perfetti e molti bambini ricevono antibiotici “per precauzione”. Questo studio ha esplorato se leggere i segnali del corpo nel sangue — in particolare i modelli di attività genica — possa distinguere con maggiore precisione le infezioni batteriche da quelle virali nei bambini con sospetta malattia grave.
Guardare il sistema d’allarme del corpo invece del germe
I test tradizionali cercano di trovare il germe direttamente, per esempio coltivando batteri dal sangue o rilevando materiale genetico virale con la PCR. Questi approcci possono essere lenti, possono non identificare il colpevole reale e spesso rilevano virus “di passaggio” non rilevanti, soprattutto nei bambini piccoli che portano frequentemente virus respiratori. I ricercatori si sono invece concentrati sulla risposta dell’ospite: quali geni nelle cellule del sangue del bambino sono attivati o disattivati durante l’infezione. Poiché il sistema immunitario reagisce in modo diverso a batteri e virus, il modello di geni attivi può funzionare come un’impronta digitale del tipo di infezione, anche quando è difficile trovare o interpretare il germe stesso.
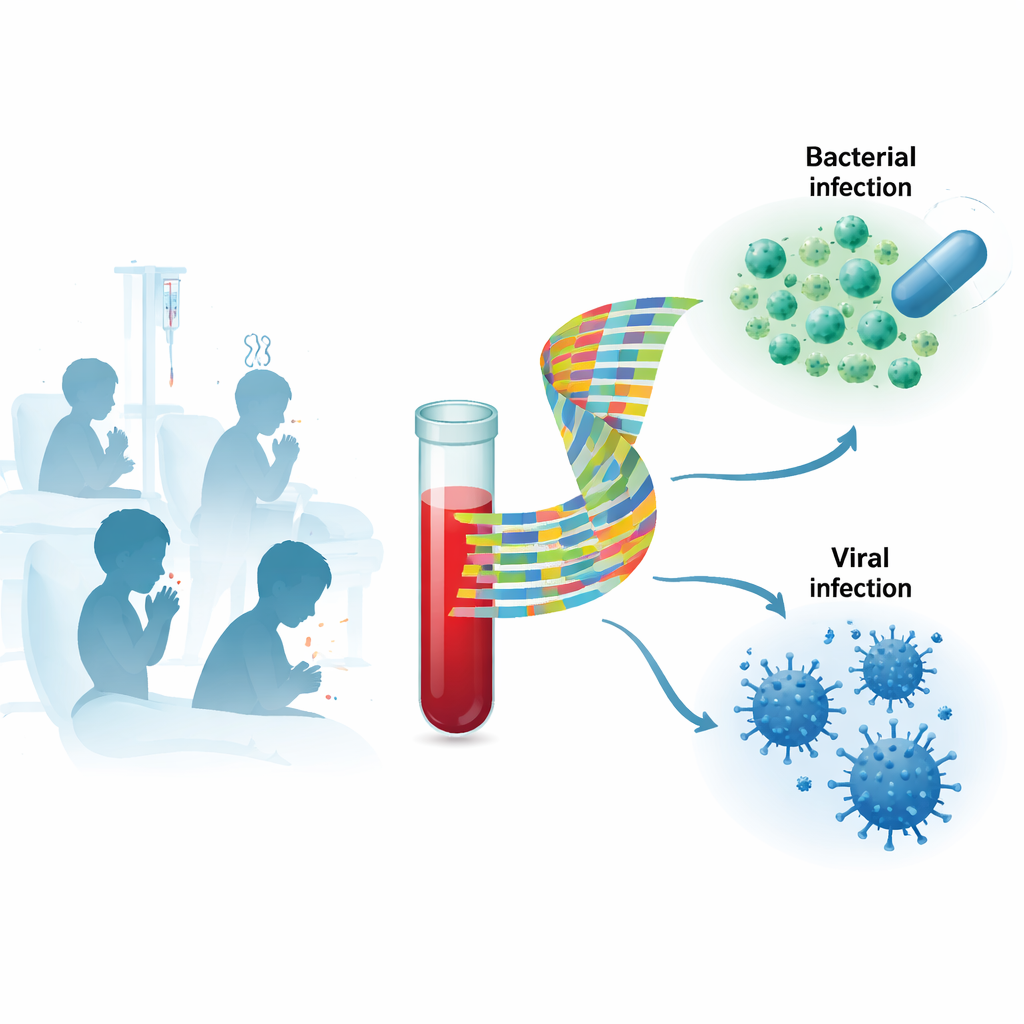
Studiare una combinazione reale di bambini malati
Il team ha arruolato 268 bambini di età compresa tra 4 settimane e 16 anni in Finlandia. La maggior parte è stata ricoverata con sospetta infezione grave; un gruppo più piccolo aveva infezioni virali confermate più lievi trattate in ambulatorio e alcuni erano controlli sani. I medici hanno raccolto dati clinici dettagliati, esami di laboratorio standard come la proteina C-reattiva e la procalcitonina, e tamponi nasali per i virus respiratori. Dai campioni di sangue è stata misurata l’attività di migliaia di geni tramite sequenziamento dell’RNA. La malattia di ciascun bambino è stata classificata con cura come batterica, virale, mista batterico–virale, incerta o non infettiva, e poi anche raggruppata più semplicemente come “batterica” o “virale” per le analisi principali.
Individuare un segnale semplice a due geni
Quando gli scienziati hanno esaminato in modo ampio l’attività genica nel sangue di tutti i bambini, hanno osservato che i campioni si raggruppavano in diversi cluster, ma questi cluster non corrispondevano nettamente alle etichette “batterico” o “virale”. I bambini sani erano chiaramente diversi da quelli con infezioni batteriche definite, mentre i modelli genici nelle infezioni virali definite erano più variabili. Per districarsi da questa complessità, i ricercatori hanno diviso i pazienti in due gruppi: un gruppo di scoperta composto da bambini con infezioni respiratorie e un gruppo di validazione con altri tipi di infezioni, come renali o cutanee. Nel gruppo di scoperta hanno cercato piccole combinazioni di geni in grado di distinguere meglio le infezioni batteriche da quelle virali, quindi hanno testato quanto bene le stesse combinazioni funzionassero nel gruppo di validazione.
Hanno identificato una coppia di geni particolarmente promettente, chiamata TSPO e SECISBP2. Insieme, i livelli di attività di questi due soli geni riuscivano a separare le infezioni batteriche (incluse quelle miste batterico–virale) dalle infezioni puramente virali con elevata accuratezza. Misurato come area sotto la curva ROC, questo segnale a due geni ha raggiunto 0,93 nel set di scoperta e 0,81 nel set di validazione; combinando entrambi i gruppi è stato 0,87, con una sensibilità di circa il 77% e una specificità di circa l’87%. In altre parole, il segnale identificava correttamente la maggior parte dei casi batterici evitando nella maggior parte dei casi di classificare erroneamente come batteriche le infezioni virali. Inoltre, in questa popolazione di studio ha mostrato prestazioni migliori rispetto a marcatori ematici largamente usati come la proteina C-reattiva e la procalcitonina.

Cosa potrebbero fare questi due geni
TSPO è coinvolto nel modo in cui i mitocondri — le “centrali energetiche” della cellula — gestiscono lo stress e aiutano a controllare l’infiammazione. Lavori precedenti hanno collegato un’attività più alta di TSPO a infezioni batteriche più severe e alla sepsi, e esperimenti suggeriscono che stimolare le cellule immunitarie con componenti batterici può aumentare TSPO e favorire il rilascio di molecole infiammatorie che aiutano a uccidere i microrganismi. In questo studio, TSPO tendeva a essere più attivo nelle infezioni batteriche e meno attivo in quelle virali. SECISBP2, invece, aiuta l’organismo a sintetizzare proteine contenenti selenio che hanno ruoli antiossidanti, immunitari e antivirali. Il selenio è noto per sostenere le cellule immunitarie e ridurre la gravità di alcune malattie virali. Qui, l’attività di SECISBP2 era generalmente più alta nelle infezioni virali, coerente con l’idea che il corpo innalzi le difese legate al selenio quando combatte i virus.
Cosa potrebbe significare per la cura futura
Gli autori sottolineano che i risultati sono preliminari ma promettenti. Un test semplice che legga solo questi due geni da un piccolo campione di sangue potrebbe un giorno aiutare i reparti di emergenza a decidere con maggiore sicurezza se un bambino molto malato ha bisogno di antibiotici. Poiché il segnale a due geni ha funzionato non solo nelle infezioni polmonari ma anche in altri casi gravi, potrebbe essere utile in un’ampia gamma di situazioni reali, incluse quelle in cui sono presenti contemporaneamente batteri e virus. Tuttavia, lo studio è stato condotto in un solo Paese e si è basato sulle migliori ma imperfette definizioni disponibili di malattia batterica o virale. Saranno necessari studi più ampi in ospedali diversi e versioni rapide e utilizzabili in clinica del test prima che possa guidare le decisioni quotidiane. Ciononostante, questo lavoro mostra che l’attività genica dell’ospite potrebbe contenere la chiave per un uso più intelligente degli antibiotici e una migliore cura dei bambini con infezioni gravi.
Citazione: Piri, R., Valta, M., Lempainen, J. et al. Host gene expression analysis in the detection of bacterial and viral etiology in children hospitalized with a suspected severe infection. Commun Med 6, 204 (2026). https://doi.org/10.1038/s43856-025-01370-z
Parole chiave: infezioni pediatriche, espressione genica, batterico versus virale, stewardship degli antibiotici, diagnostica della risposta dell’ospite