Clear Sky Science · it
Una patch aromatica nelle proteine WhiB-like favorisce l’interazione con il fattore sigma primario in Mycobacterium tuberculosis
Come i batteri percepiscono il pericolo
Mycobacterium tuberculosis, il germe che causa la tubercolosi, sopravvive all’interno dell’organismo umano riprogrammando rapidamente quali geni sono attivi o spenti quando le condizioni cambiano, ad esempio in presenza di antibiotici o durante l’attacco immunitario. Questo studio svela una piccola caratteristica strutturale — una «patch aromatica» — in una famiglia di proteine batteriche che le aiuta ad agganciarsi alla principale macchina di controllo genico della cellula. Comprendere questa stretta di mano microscopica rivela come la tubercolosi e batteri affini si adattino, e potrebbe indicare nuove strategie per indebolire questo patogeno.
Una famiglia speciale di proteine regolatrici batteriche
Il lavoro si concentra sulle proteine WhiB-like (Wbl), un gruppo presente solo negli actinobatteri e nei loro virus, compreso Mycobacterium tuberculosis. Queste proteine portano un piccolo cluster ferro–zolfo, un cofattore a base metallica che permette loro di percepire variazioni di ossigeno e altri stress. Le Wbl sono note per controllare processi chiave come la divisione cellulare, la risposta allo stress ossidativo e nutrizionale, e la resistenza agli antibiotici. Tuttavia molte di esse non possiedono le classiche strutture che permettono a molti regolatori di legarsi direttamente al DNA, lasciando un mistero di lunga data: come controllano davvero l’attività genica?
Aggrapparsi alla principale macchina di lettura dei geni
Studi precedenti avevano mostrato che diverse proteine Wbl attivano geni legandosi a una regione conservata, chiamata regione 4, del fattore sigma primario. Il fattore sigma è la parte della RNA polimerasi — l’enzima che legge il DNA — che riconosce dove iniziare la trascrizione dei geni. In Mycobacterium tuberculosis, questo fattore sigma usa la stessa regione 4 per reclutare molti regolatori differenti. Gli autori hanno combinato cristallografia a raggi X, saggi biochimici di pull-down e calorimetria per mostrare che praticamente tutte le Wbl testate in questo batterio (con un caso speciale) si attaccano allo stesso punto nella regione 4 del sigma e lo fanno con un legame molto stretto.
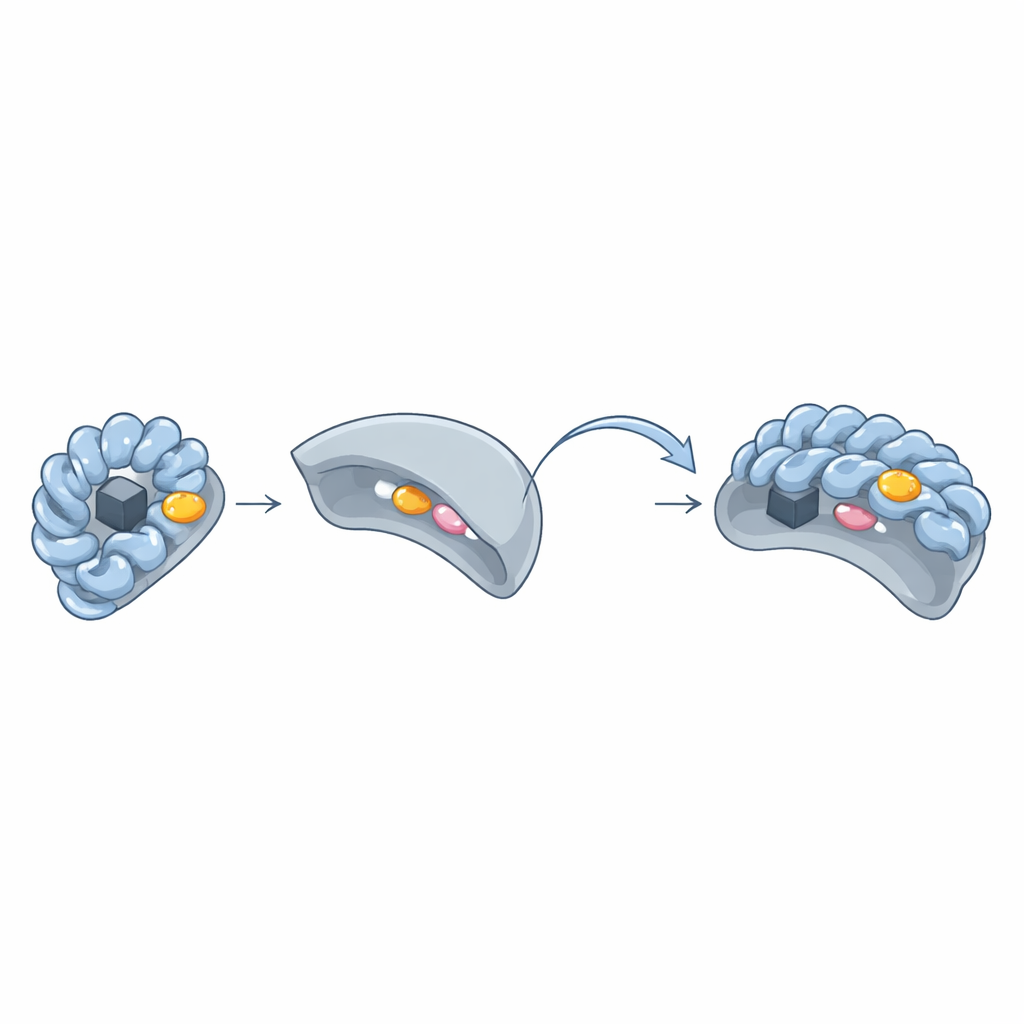
La serratura e la chiave nascosta: la «patch aromatica»
Confrontando le strutture tridimensionali delle coppie Wbl–sigma, il gruppo ha scoperto un ricorrente ammasso di amminoacidi ad anello voluminosi — triptofano, fenilalanina, tirosina o istidina — che formano una «patch aromatica» sulla superficie delle Wbl. Questa patch circonda il cluster ferro–zolfo e preme direttamente contro due amminoacidi chiave nella regione 4 del sigma. Quando i ricercatori hanno sostituito questi residui aromatici con altri più semplici, le Wbl non hanno più potuto formare complessi stabili con il sigma e i loro cluster ferro–zolfo spesso sono diventati instabili. Anche in varianti di Wbl che sembravano atipiche — come WhiB6 o WhiB5 — residui alternativi o catene laterali aromatiche vicine compensavano per preservare lo stesso tipo di interazione.
Un disegno condiviso tra batteri e loro virus
Per valutare quanto sia diffusa questa caratteristica, gli autori hanno analizzato 995 sequenze di proteine Wbl provenienti da molte specie di actinobatteri e dai loro virus infettanti (actinobacteriofagi). Hanno raggruppato queste proteine in 29 sottofamiglie e scoperto che cinque rami principali, rappresentati da cinque proteine Wbl di Mycobacterium tuberculosis, costituiscono circa l’80% di tutte le sequenze. La modellazione strutturale con AlphaFold ha rivelato che quasi tutte le Wbl — più del 98% — portano almeno due residui aromatici in posizioni corrispondenti alla patch aromatica, e quasi tutte hanno almeno uno dei residui nelle posizioni centrali più critiche. Esperimenti con diverse Wbl codificate dai fagi hanno confermato che anche queste versioni virali si legano alla stessa regione del sigma in modo dipendente dalla patch, indicando che lo stesso disegno molecolare è riutilizzato in batteri e fagi.
Una lotta evolutiva per il controllo
L’albero filogenetico costruito a partire da queste 995 sequenze mostra proteine Wbl di fagi e batteri intrecciate, con chiari segnali di trasferimento genico orizzontale in entrambe le direzioni. Alcune Wbl virali si trovano alla base di grandi rami batterici, suggerendo che i fagi possano aver donato questi regolatori a batteri ancestrali, che poi li hanno adattati per i propri scopi. Altre Wbl virali appaiono inglobate in gruppi in gran parte batterici, indicando trasferimenti genici successivi di ritorno nei fagi. Poiché le Wbl controllano strettamente risposte allo stress, sviluppo cellulare e resistenza ai farmaci tramite le loro patch aromatiche che legano il sigma, questi scambi reciproci probabilmente hanno plasmato il modo in cui sia i batteri sia i loro virus manipolano la macchina trascrizionale dell’ospite.
Cosa significa per la tubercolosi e oltre
In termini semplici, questo studio mostra che molti regolatori actinobatterici condividono un piccolo ma cruciale punto adesivo — la patch aromatica — che permette loro di agganciarsi alla stessa parte della macchina di lettura dei geni e modulare quali geni sono attivi sotto stress. In Mycobacterium tuberculosis, questo meccanismo di aggancio condiviso aiuta a coordinare risposte che favoriscono persistenza, virulenza e resistenza agli antibiotici. Rivelando come funziona questa interfaccia microscopica e quanto sia conservata, il lavoro mette in luce un potenziale punto debole che un giorno potrebbe essere preso di mira per interrompere la capacità del patogeno di adattarsi e sopravvivere all’interno dell’ospite.
Citazione: Guiza Beltran, D., Wan, T., Seravalli, J. et al. Aromatic patch in whiB-like transcription factors facilitates primary sigma factor interaction in mycobacterium tuberculosis. Commun Biol 9, 424 (2026). https://doi.org/10.1038/s42003-026-09698-5
Parole chiave: Mycobacterium tuberculosis, fattori di trascrizione, fattore sigma, proteine ferro-zolfo, evoluzione dei batteriofagi