Clear Sky Science · it
DANST abilita la deconvoluzione dei tipi cellulari nella transcriptomica spaziale usando reti neurali antagoniste deep domain
Vedere le cellule nei loro quartieri
I tessuti umani sono città affollate di molti tipi cellulari diversi, ciascuno con un ruolo specifico. Le nuove tecnologie di “transcriptomica spaziale” possono misurare quali geni sono attivi su una fetta di tessuto, ma ogni misura spesso mescola segnali provenienti da più cellule vicine. Questo articolo presenta DANST, un metodo computazionale intelligente che separa questi miscugli. Indicando quali tipi cellulari sono presenti e dove, negli organi e nei tumori, aiuta gli scienziati a comprendere meglio come i tessuti sono costruiti, come le malattie si diffondono e dove le terapie potrebbero essere più efficaci. 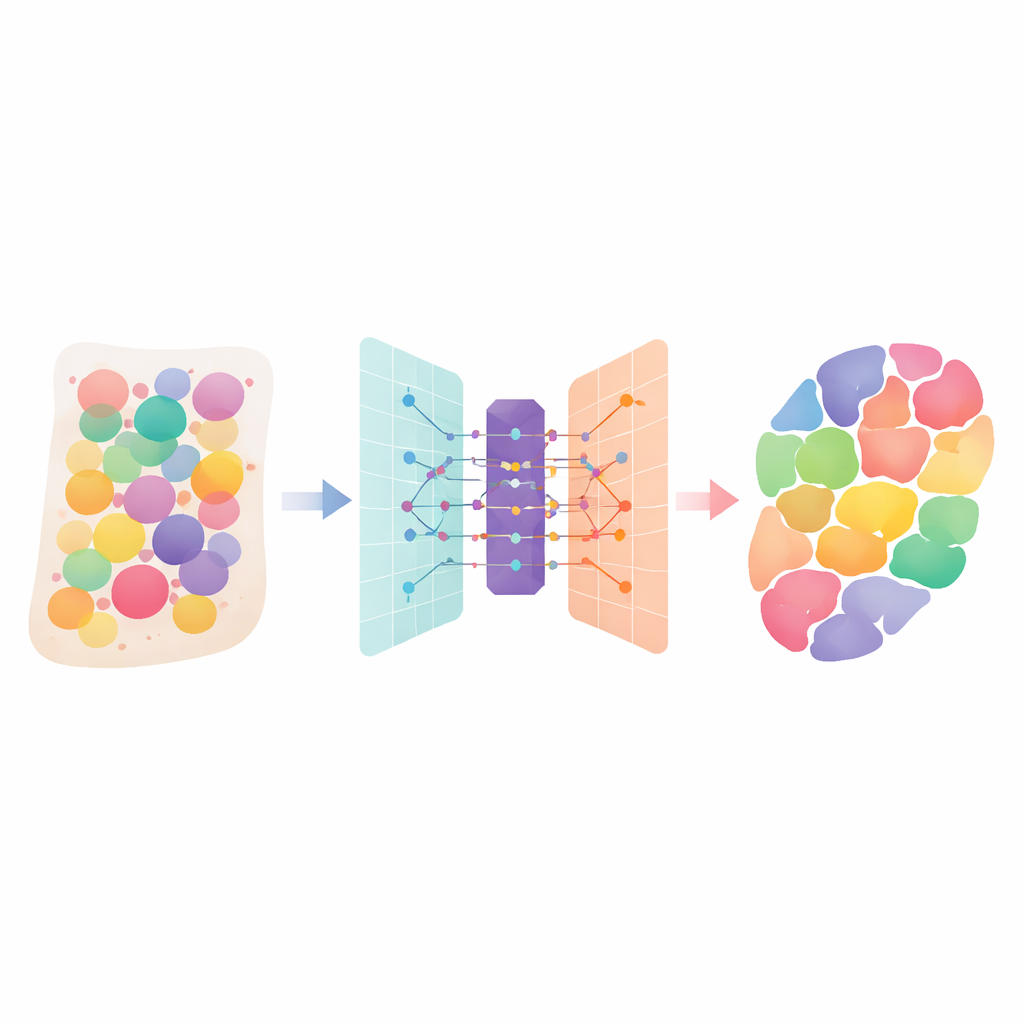
La sfida di districare folle cellulari
Gli strumenti moderni per leggere i geni possono osservare con grande precisione singole cellule oppure catturare la disposizione complessiva di un tessuto, ma raramente fanno entrambe le cose contemporaneamente. Le tecnologie spaziali più diffuse registrano l’attività genica in “spot” relativamente ampi che possono comprendere più cellule. Il risultato è come ascoltare un coro senza poter distinguere chi canta quali note. Per interpretare questi dati, i ricercatori hanno bisogno di metodi di “deconvoluzione” che stimino quanto ciascun tipo cellulare contribuisce a ogni spot. Molti approcci esistenti usano dati a singola cellula come riferimento, ma faticano perché i due tipi di dati sono raccolti con esperimenti diversi e non corrispondono perfettamente per qualità, rumore o risoluzione.
Costruire un ponte tra mondi di dati
DANST affronta questo disallineamento creando un ponte tra i dati a singola cellula e quelli spaziali. Innanzitutto utilizza i profili dettagliati a singola cellula per simulare molti spot misti artificiali con proporzioni di tipi cellulari note. Allo stesso tempo raggruppa gli spot spaziali reali in base sia alla loro posizione nel tessuto sia ai loro pattern genici, e usa le distanze da questi gruppi per assegnare a ciascuno spot simulato una posizione “pseudo”. Questo passaggio crea una mappa collegata in cui spot artificiali e reali condividono un quadro spaziale comune, permettendo al metodo di apprendere come dovrebbero apparire segnali misti in specifici quartieri del tessuto. 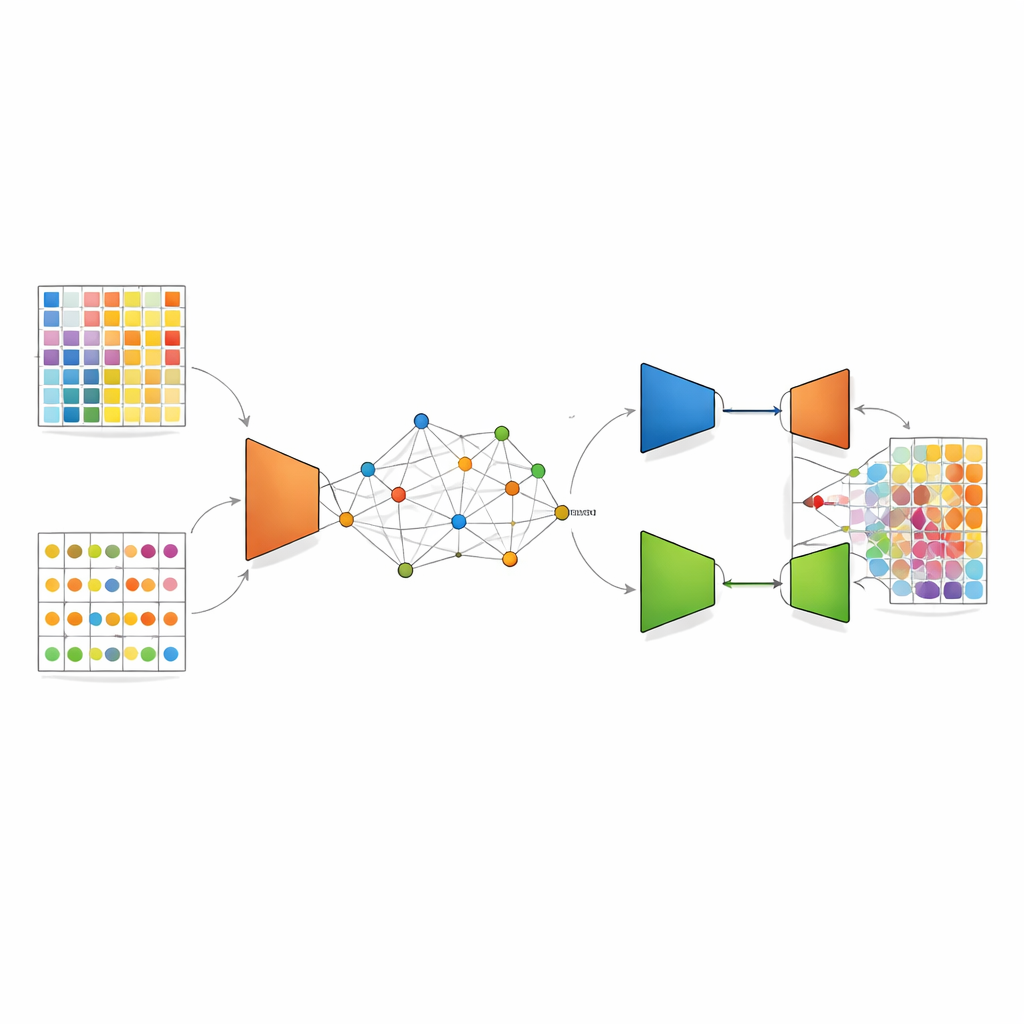
Pulire i segnali e allineare i domini
Una volta che questa mappa congiunta è stata costruita, DANST applica un tipo di deep learning chiamato autoencoder variazionale. Questa rete comprime i pattern genici sia degli spot reali sia di quelli simulati in una rappresentazione interna raffinata e poi cerca di ricostruirli, denoising effettivamente i dati e enfatizzando le caratteristiche importanti. Su questo strato i autori aggiungono un componente avversariale: una seconda rete cerca di capire se un pattern raffinato proviene da dati spaziali reali o da dati simulati, mentre l’estrattore di caratteristiche impara a ingannarla. Questo “tiro alla fune” spinge il modello verso caratteristiche utili per entrambe le fonti di dati, in modo che la conoscenza acquisita dagli spot simulati con frazioni di tipi cellulari note possa essere trasferita in modo affidabile agli spot reali il cui composizione è sconosciuta.
Test su cuori, cervelli e tumori
Il team ha testato DANST sia su benchmark artificiali sia su campioni biologici reali di topo e umano. Rispetto a diversi metodi di punta, DANST ha recuperato con maggiore accuratezza le proporzioni di tipi cellulari nei dataset sintetici e ha mantenuto il vantaggio su tessuti e piattaforme molto differenti. In un dataset di cervello di topo ha ricostruito chiaramente l’organizzazione stratificata della corteccia e ha corrisposto alle regioni anatomiche definite dagli esperti. In un’altra sezione di cervello di topo ha catturato pattern fini in aree come l’ippocampo. Più significativamente, nel tessuto di cancro al seno umano, DANST ha tracciato come varie cellule immunitarie, cellule di supporto e cellule luminali sensibili agli ormoni sono disposte all’interno e attorno alle regioni tumorali. Queste mappe si allineavano con la biologia conosciuta e suggerivano caratteristiche di rilevanza clinica, come la dipendenza ormonale e una possibile prognosi peggiore dove alcune cellule immunitarie erano scarse.
Cosa significa per biologia e medicina
Per un non specialista, DANST può essere visto come un interprete potente che trasforma segnali sfocati e sovrapposti in un quadro chiaro di quali cellule vivono dove in un tessuto. Separando in modo affidabile i tipi cellulari nello spazio, fornisce ai ricercatori una visione più nitida di come sono organizzati gli organi sani e di come le malattie rimodellano quell’organizzazione. Nel cancro, questo può rivelare come le cellule tumorali e le cellule immunitarie interagiscono in regioni specifiche, cosa che può indirizzare terapie mirate e aiutare a predire gli esiti dei pazienti. Man mano che saranno disponibili più dataset spaziali e a singola cellula, strumenti come DANST sono pronti a diventare essenziali per decodificare i quartieri cellulari che stanno alla base della salute e della malattia.
Citazione: Zhang, X., Wu, Z., Wang, T. et al. DANST enables cell-type deconvolution in spatial transcriptomics using deep domain adversarial neural networks. Commun Biol 9, 388 (2026). https://doi.org/10.1038/s42003-026-09659-y
Parole chiave: transcriptomica spaziale, deconvoluzione dei tipi cellulari, deep learning, microambiente tumorale, sequenziamento RNA a singola cellula