Clear Sky Science · it
I QTL molecolari sono arricchiti di varianti strutturali in una coorte bovina con sequenziamento long-read
Perché il DNA bovino può insegnarci sui tratti complessi
Allevatori, veterinari e genetisti vogliono capire perché alcuni animali crescono più velocemente, resistono alle malattie o producono più latte di altri. Gran parte della risposta sta nel DNA, ma i nostri strumenti abituali osservano per lo più piccole modifiche a singole «lettere» del genoma. Questo studio mostra che cambiamenti molto più grandi del DNA — le varianti strutturali — modulano silenziosamente il funzionamento dei geni nel bestiame, e che le nuove tecnologie di sequenziamento long-read ci permettono finalmente di percepirne l’impatto completo.
Guardare il genoma con una lente più nitida
La maggior parte degli studi genetici si basa su brevi porzioni di sequenza DNA, economiche e accurate ma in difficoltà nelle regioni ripetitive o complesse del genoma. Gli autori hanno usato una tecnica più recente, il sequenziamento long-read, su 120 tori di una razza legata alla produzione lattiera. Queste letture lunghe coprono tratte di DNA molto più estese, rendendo più semplice individuare grandi inserzioni, delezioni e riorganizzazioni note come varianti strutturali. Il gruppo ha confrontato queste letture lunghe con i dati short-read già disponibili per gli stessi animali e ha scoperto che le long-read hanno rivelato più varianti nel complesso e hanno migliorato in modo drastico la copertura di regioni difficili come i cromosomi X e Y.
Scoprire migliaia di riarrangiamenti del DNA nascosti
Con i dati long-read, i ricercatori hanno catalogato circa 24 milioni di piccole variazioni del DNA e oltre 79.000 varianti strutturali tra i tori. Molti di questi cambiamenti maggiori erano associati a elementi di DNA ripetitivo che si copiano e incollano in giro per il genoma. Circa una variante strutturale su dieci compariva in uno o due soli animali, rivelando un ricco serbatoio di varianti rare. Rispetto a un pangenoma bovino precedente costruito da assemblaggi di alta qualità, il nuovo dataset ha aggiunto decine di migliaia di varianti strutturali supplementari, in particolare inserzioni e duplicazioni complesse che sono difficili da rilevare con metodi più vecchi. Questo suggerisce che gli studi long-read stanno ancora portando alla luce strati di diversità genetica precedentemente invisibili negli animali da allevamento.
Collegare le modifiche del DNA all’attività genica
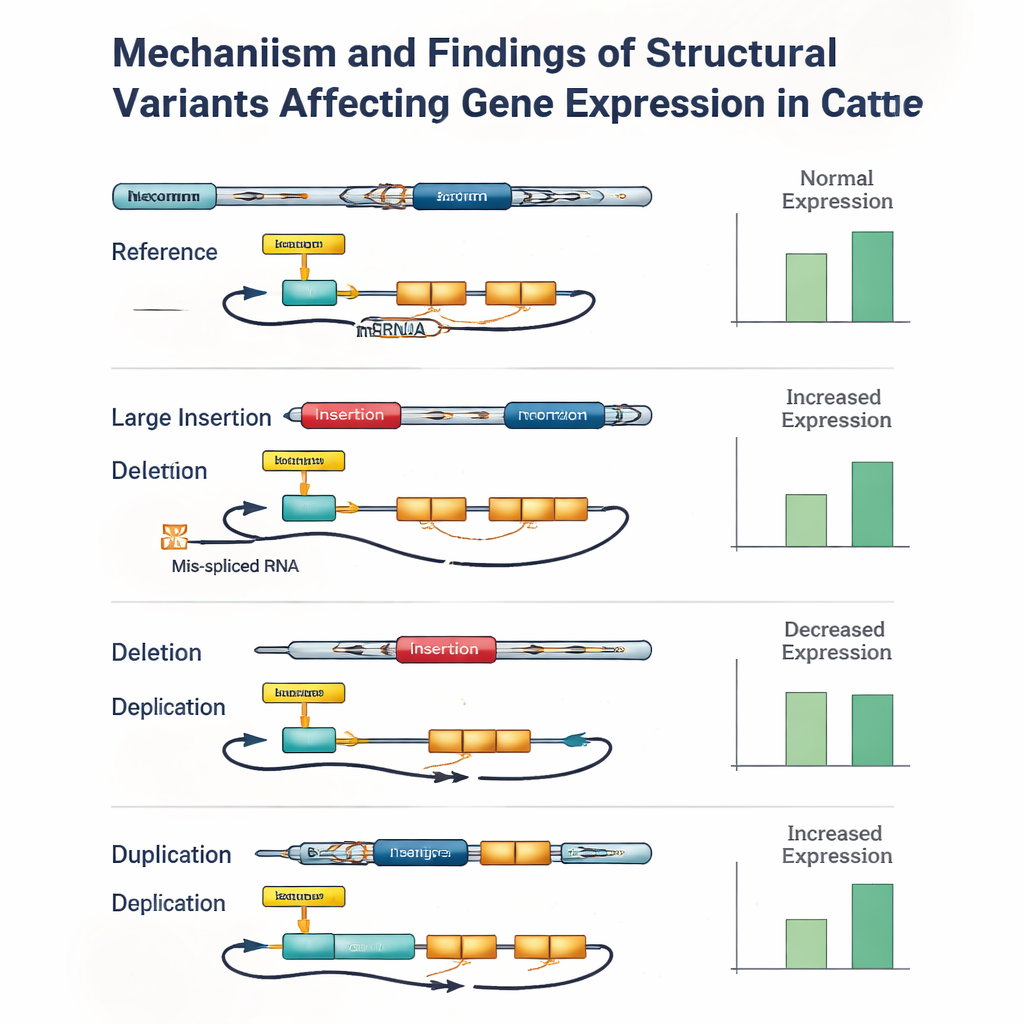
Per capire come queste differenze del DNA influenzino effettivamente la biologia, il team ha esaminato un tessuto rilevante per la fertilità maschile: il testicolo. Per 117 dei tori disponevano di sequenziamento RNA profondo che rivela quali geni sono attivi e come i loro trascritti vengono splicing-ati. Collegando statisticamente le varianti genetiche vicine a ciascun gene alla sua attività, hanno identificato oltre 27.000 «QTL molecolari» — siti genomici che modificano o la quantità di espressione di un gene o il modo in cui il suo RNA è assemblato. Le varianti strutturali sono emerse come attori chiave: erano più del doppio tra i segnali di espressione più forti e oltre cinque volte più comuni tra i segnali di splicing più importanti rispetto a quanto atteso per caso. In molti casi, la variante più influente era una grande inserzione, delezione o duplicazione collocata in un promotore, potenziatore, esone o sito di splicing piuttosto che una singola modifica letterale.
Quando errori di genotipizzazione nascondono segnali importanti
Tuttavia, lo studio ha messo in luce anche i limiti degli strumenti attuali. Anche con letture long-read di alta qualità, assegnare con precisione i genotipi delle varianti strutturali a ciascun animale è risultato impegnativo, specialmente per grandi inserzioni e duplicazioni estese. Piccoli errori — a volte che coinvolgevano uno o due tori soltanto — potevano rendere una variante strutturale leggermente meno significativa dal punto di vista statistico rispetto a una variante piccola vicina che fosse in perfetto blocco genetico con essa. Quando gli autori hanno controllato manualmente alcuni dei segnali più forti, hanno ripetutamente trovato casi in cui una variante strutturale all’interno di un gene o di una regione regolatoria chiave era il candidato più plausibile per guidare l’effetto, ma errori di genotipizzazione o dati mancanti facevano emergere come primo classificato una variante piccola collegata.
Cosa significa per l’allevamento bovino e oltre
Per i non specialisti, la conclusione è che le modifiche «grandi» del DNA contano molto. Questa indagine long-read nel bestiame mostra che le varianti strutturali sono fortemente arricchite tra i siti genetici che controllano come i geni vengono attivati e splicing-ati, in particolare nei tessuti riproduttivi. Eppure lo studio avverte anche che i metodi di analisi odierni continuano a perdere o a etichettare in modo errato molte di queste varianti, soprattutto quando la profondità di sequenziamento è modesta. Man mano che il sequenziamento long-read diventerà più economico e accurato, e che saranno sviluppati software migliori, allevatori e ricercatori potranno ricondurre tratti di importanza economica — come fertilità, resistenza alle malattie e produzione di latte — a varianti strutturali specifiche. Gli stessi principi si applicano alla salute umana e all’allevamento delle piante: per comprendere pienamente i tratti complessi dobbiamo guardare oltre le singole lettere e abbracciare i riarrangiamenti maggiori che rimodellano i genomi.
Citazione: Mapel, X.M., Leonard, A.S. & Pausch, H. Molecular QTL are enriched for structural variants in a cattle long-read cohort. Commun Biol 9, 290 (2026). https://doi.org/10.1038/s42003-026-09596-w
Parole chiave: varianti strutturali, sequenziamento long-read, genomica bovina, espressione genica, QTL molecolari