Clear Sky Science · it
MHC1-TIP consente il profiling multimodale dell’immunopeptidoma in una singola provetta e rivela eterogeneità intratumorale nella presentazione degli antigeni
Uno sguardo alle carte d’identità del cancro
Ogni cellula porta sulla propria superficie piccole “carte d’identità” molecolari che aiutano il sistema immunitario a decidere se quella cellula è sana o pericolosa. Nel cancro, queste carte d’identità—brevi frammenti proteici chiamati antigeni—possono rivelare cosa rende una cellula tumorale anomala e segnalarla per la distruzione da parte delle cellule immunitarie. Questo studio presenta un nuovo metodo di laboratorio, MHC1-TIP, che rende molto più semplice ed economico leggere queste carte d’identità a partire da quantità molto piccole di tessuto del paziente, aprendo la strada a immunoterapie contro il cancro più precise.
Perché i segnali di superficie cellulare sono importanti
Il nostro sistema immunitario ispeziona costantemente le cellule controllando gli antigeni esposti su molecole speciali chiamate MHC di classe I. Le cellule tumorali spesso mostrano antigeni anomali che, in linea di principio, possono essere riconosciuti dalle cellule T e presi di mira da terapie come i vaccini personalizzati. Tuttavia, misurare effettivamente quali antigeni sono presenti in campioni reali di pazienti è stato tecnicamente impegnativo. I metodi tradizionali richiedono enormi numeri di cellule, molti passaggi di lavorazione e anticorpi costosi, rendendoli poco adatti a minuscole biopsie o a campioni clinici scarsi. Allo stesso tempo, i tumori non sono uniformi: regioni diverse possono esprimere proteine differenti, il che fa pensare che anche la presentazione degli antigeni possa variare da zona a zona all’interno di un singolo tumore.
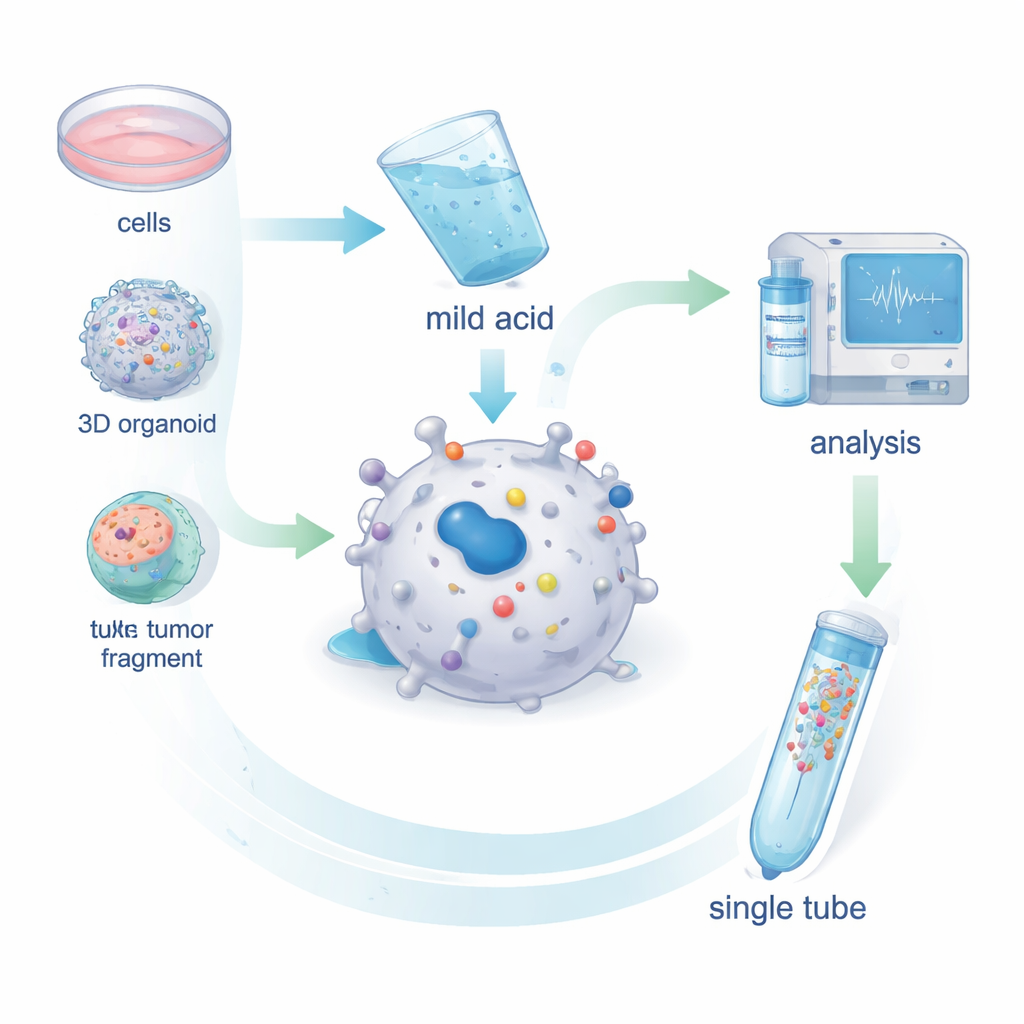
Un’unica provetta per estrarre gli antigeni del cancro
I ricercatori hanno sviluppato MHC1-TIP (MHC-I 1-Tube Immunopeptidomics) come un metodo snello per raccogliere gli antigeni da cellule vive. Invece di rompere le cellule ed estrarre le molecole MHC con anticorpi, lavano brevemente le cellule intatte—o minuscoli frammenti tumorali—con una soluzione acida blanda. Questo trattamento delicato provoca il distacco degli antigeni dalla tasca dell’MHC senza uccidere le cellule. I peptidi liberati passano quindi attraverso un piccolo filtro che rimuove detriti più grandi e vengono trattenuti su una minuscola colonna all’interno di una singola provetta. Da lì, vengono inseriti direttamente in uno spettrometro di massa che identifica le sequenze peptidiche. I test su cellule di melanoma hanno mostrato che questo passaggio con acido blando rimuove quasi tutti i complessi MHC–antigene di superficie e che i peptidi recuperati assomigliano agli antigeni realmente legati a MHC in termini di lunghezza e motivi di sequenza.
Più dati con meno campione
MHC1-TIP è stato progettato per funzionare con pochissime cellule e comunque fornire molti antigeni identificabili. Abbinando il nuovo workflow a una modalità moderna di spettrometria di massa chiamata acquisizione indipendente dai dati (data-independent acquisition), il team ha rilevato centinaia di antigeni a partire da appena 100.000 cellule e migliaia da pochi milioni di cellule—una profondità simile al metodo standard basato su anticorpi del campo, ma con meno materiale e costi inferiori. Il metodo ha funzionato anche su organoidi derivati da pazienti, che sono mini-tumori 3D coltivati in laboratorio, e su minuscoli frammenti tumorali ex vivo più piccoli di un millimetro cubo. È importante sottolineare che, poiché il lavaggio acido lascia le cellule in gran parte intatte, il materiale residuo può essere usato per un profiling proteico completo dello stesso campione, permettendo un confronto diretto tra quanto di una data proteina è presente e quanto di essa è effettivamente presentato come antigene.
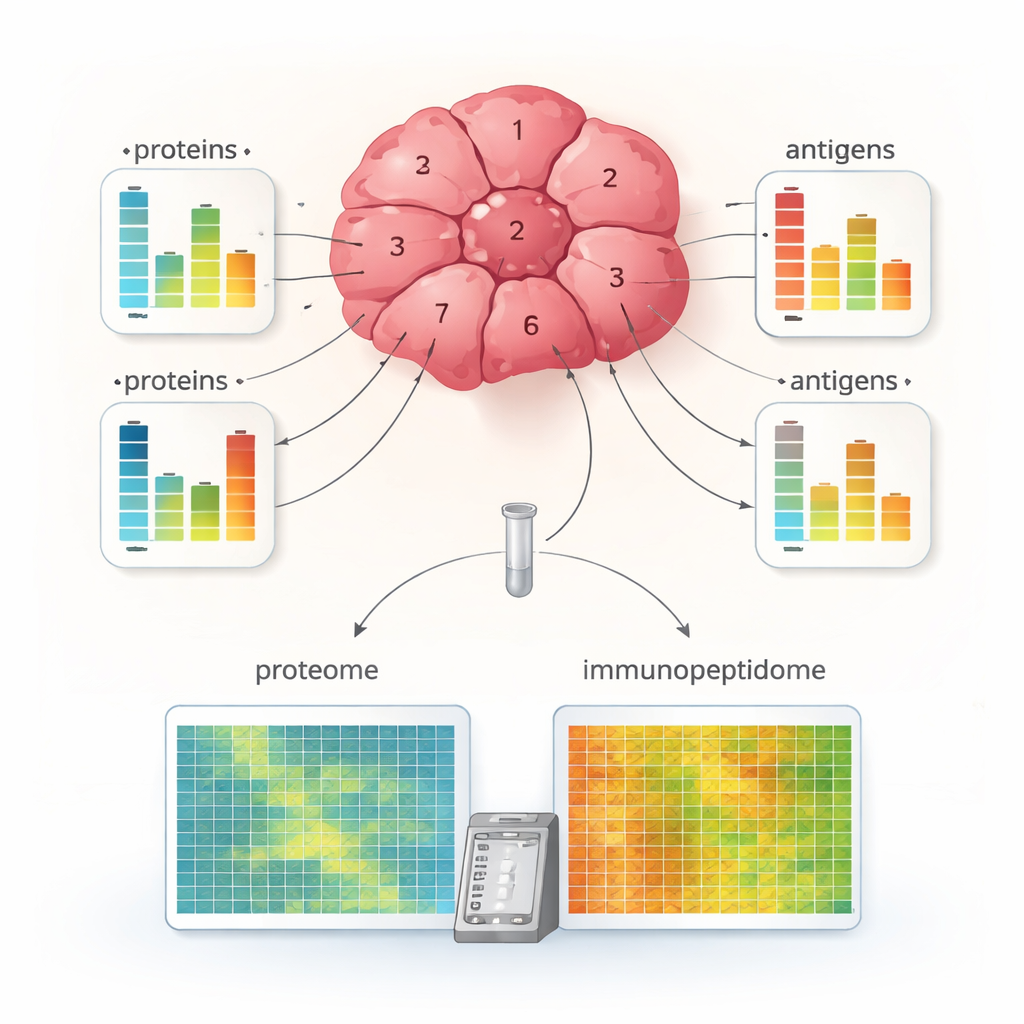
Differenze nascoste all’interno di un singolo tumore
Applicando MHC1-TIP a più piccoli frammenti prelevati da diverse regioni di un tumore di carcinoma renale, i ricercatori hanno rivelato una sorprendente diversità interna. Alcuni frammenti mostravano una ricca presentazione di antigeni, mentre altri ne esponevano pochissimi, nonostante il contenuto proteico complessivo potesse essere simile. Per molte proteine, le variazioni nei livelli di antigene non corrispondevano alle variazioni nella loro abbondanza proteica, suggerendo che il processamento degli antigeni e il caricamento sulle molecole MHC sono regolati indipendentemente da quanto della proteina parentale è presente. Il team ha inoltre combinato i dati sugli antigeni con marcatori delle cellule immunitarie e del macchinario MHC, identificando regioni tumorali “immune-hot”, con elevata esposizione di antigeni e segni di cellule T attive, e regioni “immune-cold”, con meno antigeni e minore evidenza di attacco immunitario. Questo livello di dettaglio è stato raramente possibile da pezzi di tessuto così piccoli.
Cosa significa per la cura del cancro in futuro
Per un non specialista, il messaggio principale è che misurare semplicemente quali proteine un tumore produce non è sufficiente per sapere cosa il sistema immunitario può effettivamente riconoscere. Il nuovo metodo MHC1-TIP offre un modo pratico per leggere la reale esposizione di antigeni a partire da campioni molto piccoli e clinicamente realistici, misurando allo stesso tempo il panorama proteico più ampio. La scoperta che la presentazione degli antigeni può variare notevolmente tra diverse parti dello stesso tumore, e non segue sempre i livelli proteici, mette in guardia dal scegliere bersagli per vaccini o per cellule T basandosi soltanto su espressione genica o proteica. In futuro, approcci come MHC1-TIP potrebbero aiutare a progettare immunoterapie più efficaci e personalizzate concentrandosi su antigeni realmente mostrati in superficie e presentati in modo più coerente attraverso il tumore.
Citazione: Bathini, M., Bocaniciu, D., Johnson, F.D. et al. MHC1-TIP enables single-tube multimodal immunopeptidome profiling and uncovers intratumoral heterogeneity in antigen presentation. Commun Biol 9, 296 (2026). https://doi.org/10.1038/s42003-026-09570-6
Parole chiave: presentazione degli antigeni, immunopeptidomica, immunoterapia oncologica, eterogeneità tumorale, spettrometria di massa