Clear Sky Science · it
Indice Kinic: un modello predittivo guidato dall’intelligenza artificiale e un framework di scoperta di farmaci multitarget per pazienti con carcinoma epatocellulare
Perché questa ricerca è importante
Il tumore del fegato è uno dei tumori più letali a livello mondiale, in parte perché i tumori variano molto da un paziente all’altro e spesso risultano resistenti ai farmaci attuali. Questo studio introduce un nuovo modo di classificare i pazienti con carcinoma epatocellulare in gruppi di rischio e, contemporaneamente, di cercare nuovi farmaci su misura per la loro malattia. Utilizzando avanzate tecniche di intelligenza artificiale (IA), i ricercatori hanno costruito uno strumento chiamato Indice Kinic che collega sottili marcature chimiche sulle proteine alla sopravvivenza dei pazienti e a promettenti bersagli farmacologici.
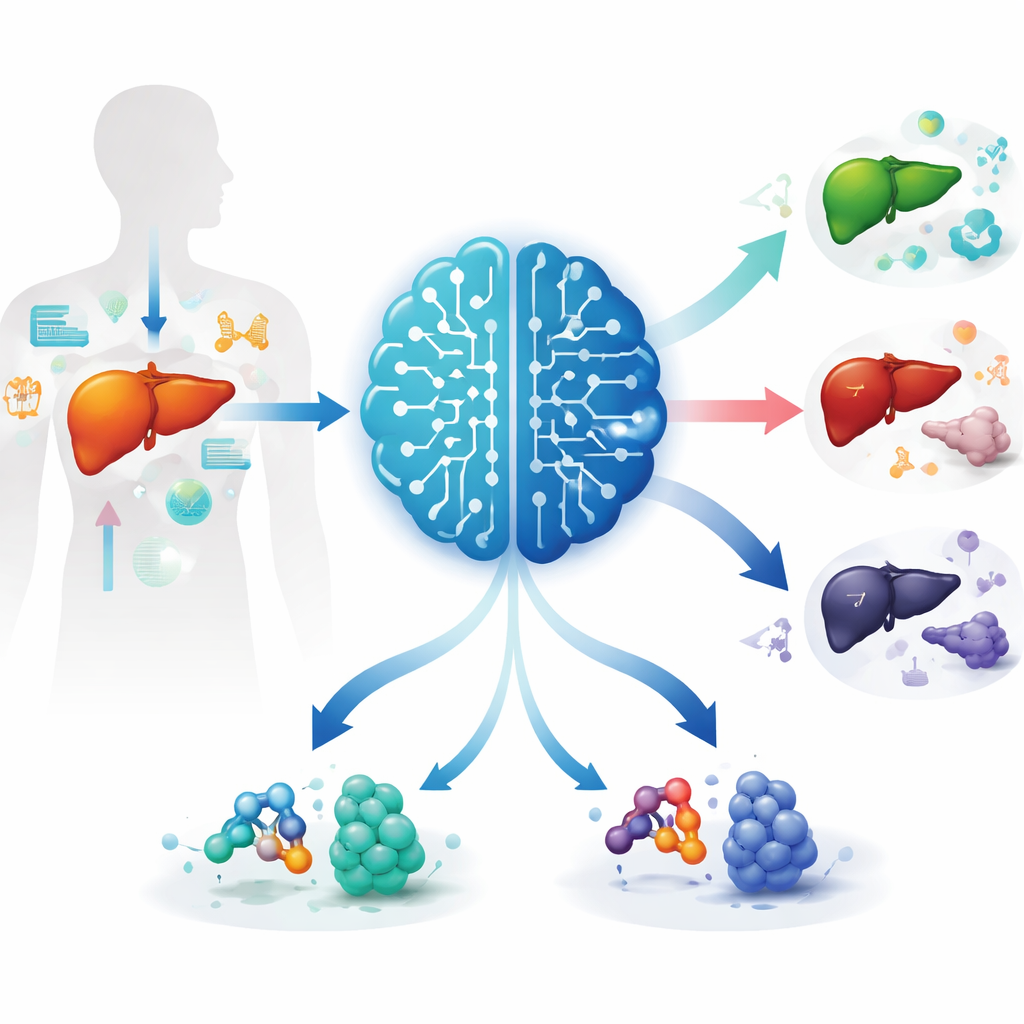
Una nuova marcatura chimica dalle grandi conseguenze
Negli ultimi anni gli scienziati hanno scoperto un nuovo tipo di tag chimico sulle proteine delle cellule del fegato, chiamato isonicotinilazione. Queste piccole marcature possono modificare il modo in cui il DNA è impacchettato e come i geni legati al cancro vengono attivati o disattivati. Il team ha raccolto ampi dataset da centinaia di tumori epatici e fegati sani, cercando geni la cui attività fosse legata a questa nuova modificazione. Hanno identificato decine di tali geni e dimostrato che molti di essi appartengono a vie biologiche che regolano il metabolismo dei lipidi, la detossificazione dei farmaci e altre sostanze chimiche, così come la crescita e la diffusione dei tumori.
Classificare i pazienti in rischio più elevato o più basso
Per trasformare questi risultati in uno strumento utile in clinica, gli scienziati hanno impiegato apprendimento automatico per raggruppare i pazienti con carcinoma epatocellulare in base all’attività dei geni correlati all’isonicotinilazione. Sono emersi due sottogruppi principali. Un sottogruppo mostrava maggiore attività di certi geni e presentava una sopravvivenza complessiva chiaramente peggiore. Questo gruppo ad alto rischio mostrava anche segni di un microambiente tumorale più aggressivo: divisione cellulare accelerata, maggiore instabilità genetica e un panorama immunitario che suggeriva la possibilità che i tumori eludano le difese dell’organismo. L’altro sottogruppo mostrava vie metaboliche e di detossificazione più attive e registrava risultati migliori, suggerendo che questi pattern molecolari potrebbero aiutare i medici a prevedere l’andamento clinico dei pazienti.
Un punteggio IA che mette in evidenza due geni chiave
Sulla base di questi pattern, i ricercatori hanno creato l’Indice Kinic, un punteggio guidato dall’IA che combina diversi metodi di machine learning per prevedere il rischio di morte di un paziente. Hanno testato oltre cento combinazioni di modelli e scelto quella che ha dato le migliori prestazioni sia in un grande database oncologico sia in una coorte indipendente di pazienti. Il punteggio si è dimostrato un predittore solido e indipendente di sopravvivenza, anche tenendo conto dell’età e dello stadio tumorale. Importante, una tecnica chiamata SHAP, che spiega le decisioni dei modelli di IA, ha indicato due geni — CYP2C9 e G6PD — come i più influenti. Analisi a singola cellula e spaziali hanno mostrato che entrambi i geni sono principalmente attivi nelle cellule epatiche maligne con alto potenziale di diffusione, e che la loro attività è strettamente collegata a come i tumori interagiscono con le cellule immunitarie e di supporto circostanti.
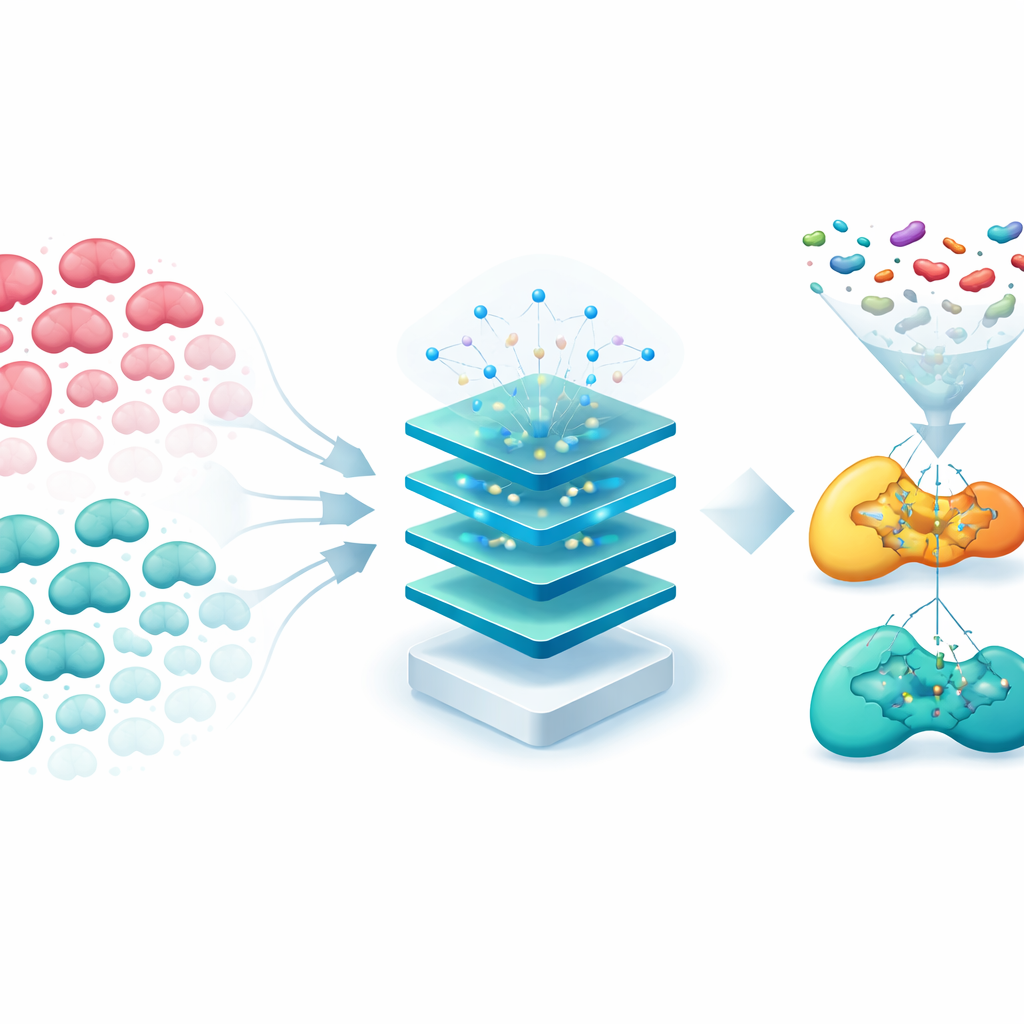
Dal punteggio di rischio ai farmaci candidati
Lo studio non si è fermato alla prognosi. Il team ha usato un framework di deep learning chiamato GraphBAN per selezionare oltre 200.000 composti chimici valutandone la capacità di legarsi a CYP2C9 e G6PD. Successivamente hanno applicato uno strumento di IA che predice l’assorbimento, il metabolismo e la tollerabilità dei composti nell’organismo, restringendo la lista a poche molecole con caratteristiche farmacologiche promettenti. Simulazioni di docking al computer hanno suggerito che due candidati, ognuno mirato a una delle proteine chiave, si inseriscono bene in tasche altamente favorevoli sui loro bersagli e formano complessi stabili nel tempo. Questi risultati propongono punti di partenza concreti per nuovi farmaci progettati per colpire i punti deboli metabolici dei tumori epatici evidenziati dall’Indice Kinic.
Cosa significa per la cura futura
In sintesi, questo lavoro mostra come l’IA possa collegare tre passaggi cruciali nella cura moderna del cancro: comprendere come una nuova marcatura proteica modelli il comportamento tumorale, tradurre tale conoscenza in un punteggio di rischio che separi i pazienti più fragili da quelli più stabili, e individuare rapidamente nuovi candidati farmacologici che colpiscano i giusti bersagli molecolari. Se confermato da studi successivi e trial clinici, l’Indice Kinic potrebbe aiutare i medici a identificare i pazienti con carcinoma epatocellulare che necessitano di terapie più intensive, a selezionare trattamenti in linea con la biologia del tumore e a guidare lo sviluppo di farmaci multitarget che anticipino e contrastino la resistenza farmacologica.
Citazione: Zhou, J., Jiang, Y., Yu, M. et al. Kinic index: an artificial intelligence-driven predictive model and multitarget drug discovery framework for hepatocellular carcinoma patients. npj Precis. Onc. 10, 132 (2026). https://doi.org/10.1038/s41698-026-01324-1
Parole chiave: carcinoma epatocellulare, oncologia di precisione, intelligenza artificiale, modificazione epigenetica, scoperta di farmaci