Clear Sky Science · it
Normalizzazione della colorazione in istopatologia: confronto di metodi usando un dataset multicentrico
Immagini tissutali più nitide per medici e computer
Quando i patologi osservano campioni tissutali al microscopio, si affidano a sottili sfumature di rosa e viola per decidere se le cellule sono sane o cancerose. Oggi quei colori possono variare notevolmente da un laboratorio ospedaliero all'altro, il che non solo complica la diagnosi umana ma mette anche in difficoltà gli strumenti di intelligenza artificiale addestrati su queste immagini. Questo studio si propone di misurare l'entità del problema cromatico e di testare quali tecniche computazionali funzionano meglio per rendere le immagini dei vetrini più simili tra loro senza perdere dettagli importanti.
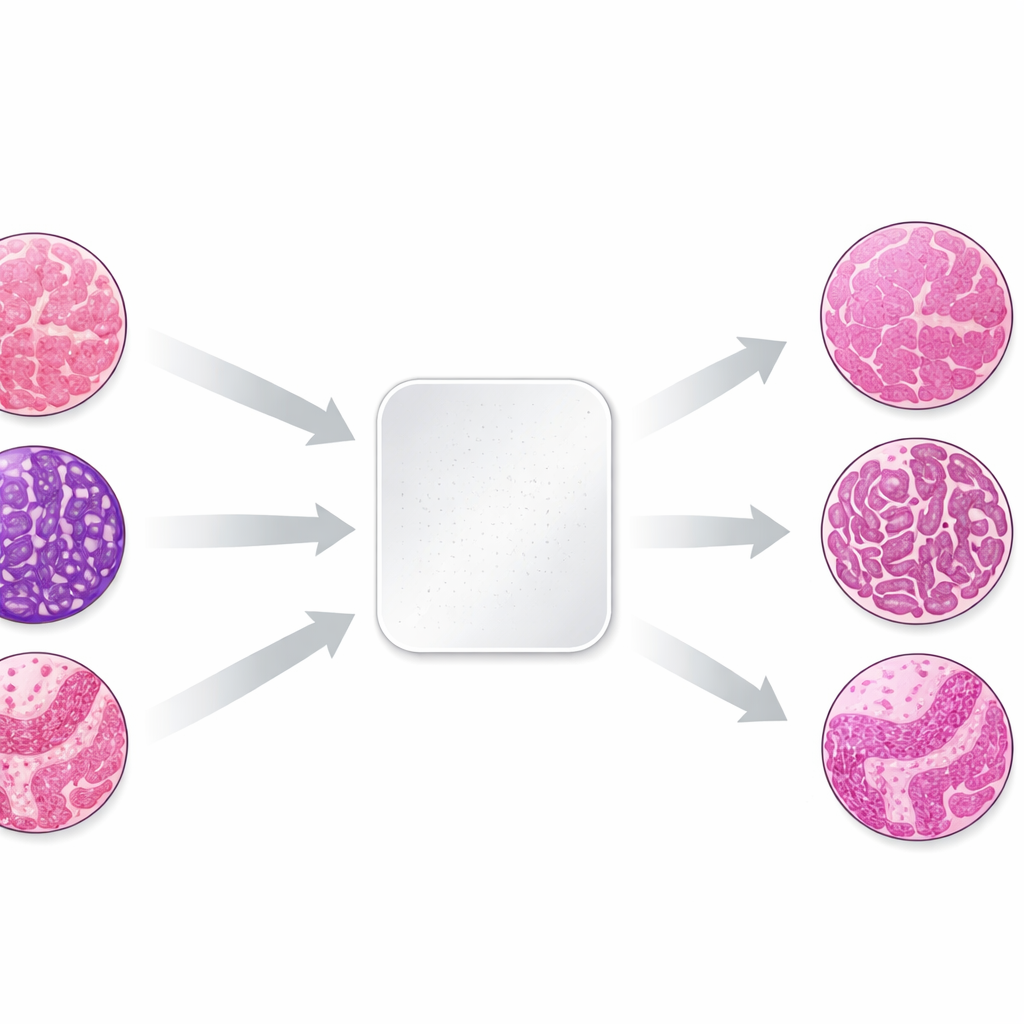
Perché il colore varia da laboratorio a laboratorio
Il lavoro si concentra sulla coppia di coloranti più comune in patologia, ematossilina ed eosina, che colora i nuclei cellulari di blu-viola e i tessuti circostanti di rosa. Piccole differenze nelle procedure di fissazione, lavorazione e colorazione, e nel modo in cui gli scanner acquisiscono le immagini, possono spostare questi colori in modo marcato. Per studiare l'effetto in modo controllato, gli autori hanno prelevato tre piccoli campioni tissutali—cute, rene e colon—dagli stessi blocchi donatori e hanno inviato sezioni identiche non colorate a 66 laboratori in 11 paesi. Ogni laboratorio ha utilizzato la propria procedura di colorazione di routine; poi i vetrini finite sono stati digitalizzati. Poiché il materiale biologico era quasi identico, qualsiasi differenza nell'aspetto rifletteva principalmente come ciascun laboratorio aveva colorato e acquisito il tessuto.
Costruire una piattaforma di test unica per la correzione del colore
La collezione di immagini risultante mostrava variazioni sorprendenti: i vetrini dello stesso blocco tissutale potevano andare da tonalità molto chiare a quasi nere, o scivolare da sfumature fredde a calde. Il team ha prima quantificato queste differenze misurando i livelli medi di rosso e blu in ogni vetrino. Ha quindi scelto un singolo vetrino ben bilanciato per ogni tipo tissutale come riferimento e ha applicato otto diversi metodi di normalizzazione della colorazione a tutti gli altri. Quattro metodi erano approcci tradizionali basati su formule matematiche che aggiustano le statistiche cromatiche globali o separano e riscalano i componenti di colorazione. Quattro erano basati su moderne tecniche di IA “generativa”, che apprendono a trasformare immagini da uno stile cromatico a un altro usando reti neurali.
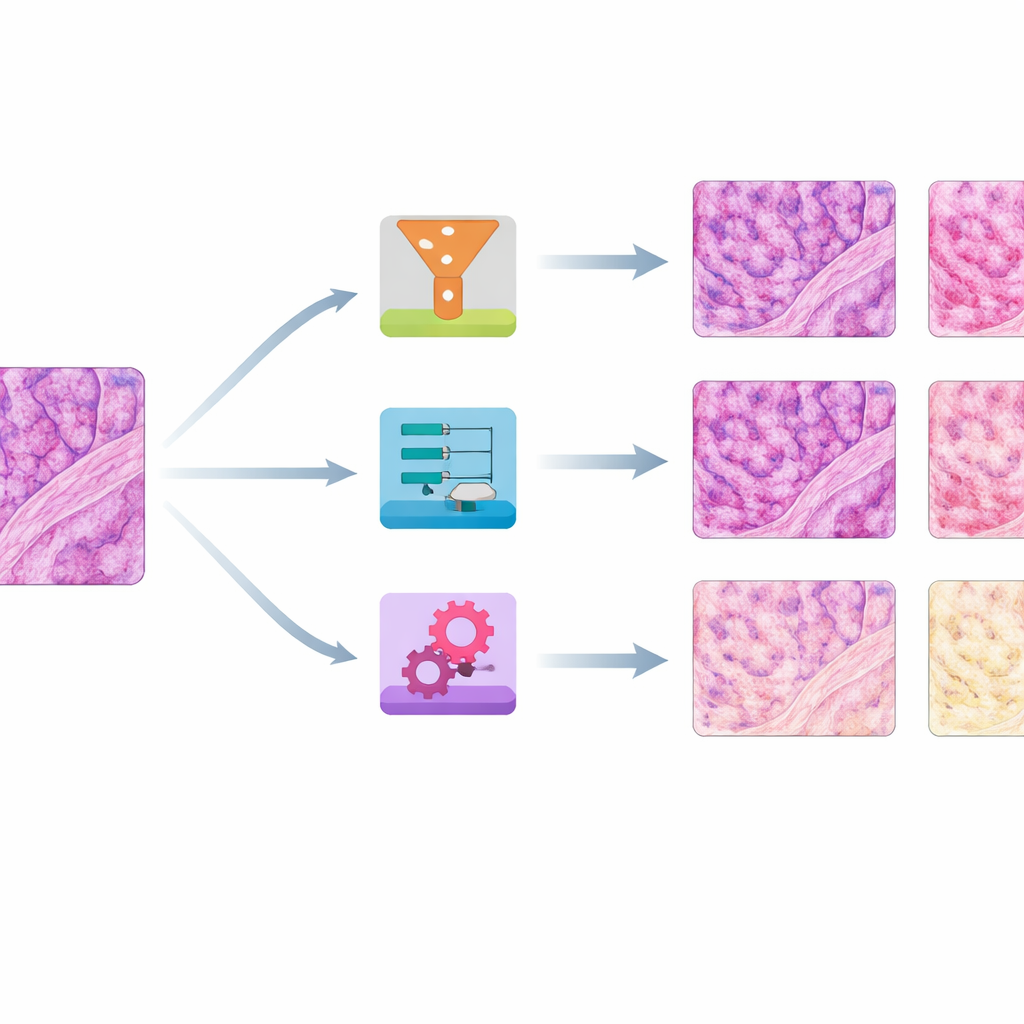
Quali metodi hanno funzionato meglio su colore e struttura
Per valutare le prestazioni, gli autori hanno posto due domande principali: quanto i vetrini corretti si avvicinavano ai colori di riferimento e quanto bene preservavano la struttura tissutale fine? Hanno utilizzato diversi punteggi numerici che confrontano le distribuzioni di colore, una misura di similarità immagine di alto livello mutuata dalla visione artificiale e un indice strutturale sensibile a sfocature o distorsioni. Su cute, rene e colon, un metodo semplice chiamato histogram matching—sostanzialmente rimodellare la distribuzione dei colori di ogni vetrino per imitare il riferimento—ha prodotto costantemente la corrispondenza cromatica più vicina pur mantenendo le strutture per lo più intatte. Un altro approccio tradizionale, la normalizzazione di Reinhard, spesso ha avuto prestazioni quasi comparabili. Un terzo metodo, Vahadane, si è distinto per preservare la struttura ma tendeva a spostare tutto verso toni rosa e a sopprimere la colorazione blu dei nuclei.
Come le immagini sono apparse a esperti umani e strumenti di IA
Patologi esperti hanno riesaminato i vetrini normalizzati del colon per valutare come i metodi influenzassero l'interpretabilità nel mondo reale. Hanno verificato se gli strati e i tipi cellulari importanti restavano facili da distinguere, se gli originali sovra- o sotto-colorati miglioravano e se comparivano artefatti digitali strani. Nessun metodo ha risolto ogni problema, ma l'histogram matching in generale ha fornito colori uniformi e simili al riferimento senza artefatti evidenti, specialmente nei campioni fortemente sovra-colorati. Alcuni metodi basati su IA, in particolare alcune versioni di CycleGAN e Pix2pix, hanno prodotto risultati dall'aspetto realistico ma a volte hanno introdotto sottili strutture false o anomalie di colore in cellule ematiche e aree di sfondo. Il team ha inoltre mostrato che la normalizzazione ha modificato il modo in cui un algoritmo all'avanguardia per il rilevamento delle cellule contava i nuclei e come un grande modello “fondazionale” rappresentava i vetrini, sottolineando che la correzione cromatica può influenzare profondamente il comportamento delle applicazioni downstream di IA.
Cosa significa questo per la diagnostica digitale futura
Nel complesso, lo studio rivela che le differenze cromatiche tra laboratori sono abbastanza grandi da essere rilevanti sia per i lettori umani sia per i sistemi automatizzati, e che rendere le immagini più uniformi è un passo importante verso una patologia digitale affidabile e condivisibile. Sorprendentemente, in questo dataset controllato con contenuto tissutale molto simile, metodi globali semplici come l'histogram matching hanno spesso superato tecniche deep-learning più complesse, che richiedono molti più dati di addestramento rispetto a una singola vetrino per laboratorio. Gli autori rilasciano apertamente il loro dataset a 66 centri in modo che altri possano confrontare nuovi metodi e progettare meglio dati di addestramento che riflettano la variazione del mondo reale. Per i pazienti, i progressi in quest'area potrebbero tradursi in sistemi di IA che si trasferiscono bene da un ospedale all'altro, offrendo diagnosi più coerenti indipendentemente dal luogo in cui viene analizzata una biopsia.
Citazione: Khan, U., Härkönen, J., Friman, M. et al. Staining normalization in histopathology: Method benchmarking using multicenter dataset. Sci Rep 16, 11097 (2026). https://doi.org/10.1038/s41598-026-40943-3
Parole chiave: patologia digitale, normalizzazione delle colorazioni, imaging istologico, IA medica, variazione di colore