Clear Sky Science · it
Genomica plastidiale comparativa di Hippophae rivela relazioni filogenetiche e fornisce marcatori di DNA candidati per l'identificazione tassonomica
Perché questo arbusto resistente è importante
L'olivello spinoso è un arbusto robusto che prospera dove molte altre piante falliscono: su pendii freddi, secchi e ventosi del Plateau Qinghai–Tibet e oltre. Le sue bacche arancioni brillanti sono promosse in tutto il mondo come “superfrutti” e la pianta è ampiamente utilizzata per stabilizzare i suoli e ripristinare terre degradate. Eppure anche gli esperti faticano a distinguere le specie e le sottospecie strettamente affini solo osservandole. Questo studio pone una domanda semplice ma importante: possiamo leggere il manuale di istruzioni interno della pianta — il suo DNA — per capire chi è chi e, nel processo, fornire a miglioratori e conservazionisti un nuovo strumento potente per gestire questa risorsa preziosa?
Guardare dentro i motori verdi della pianta
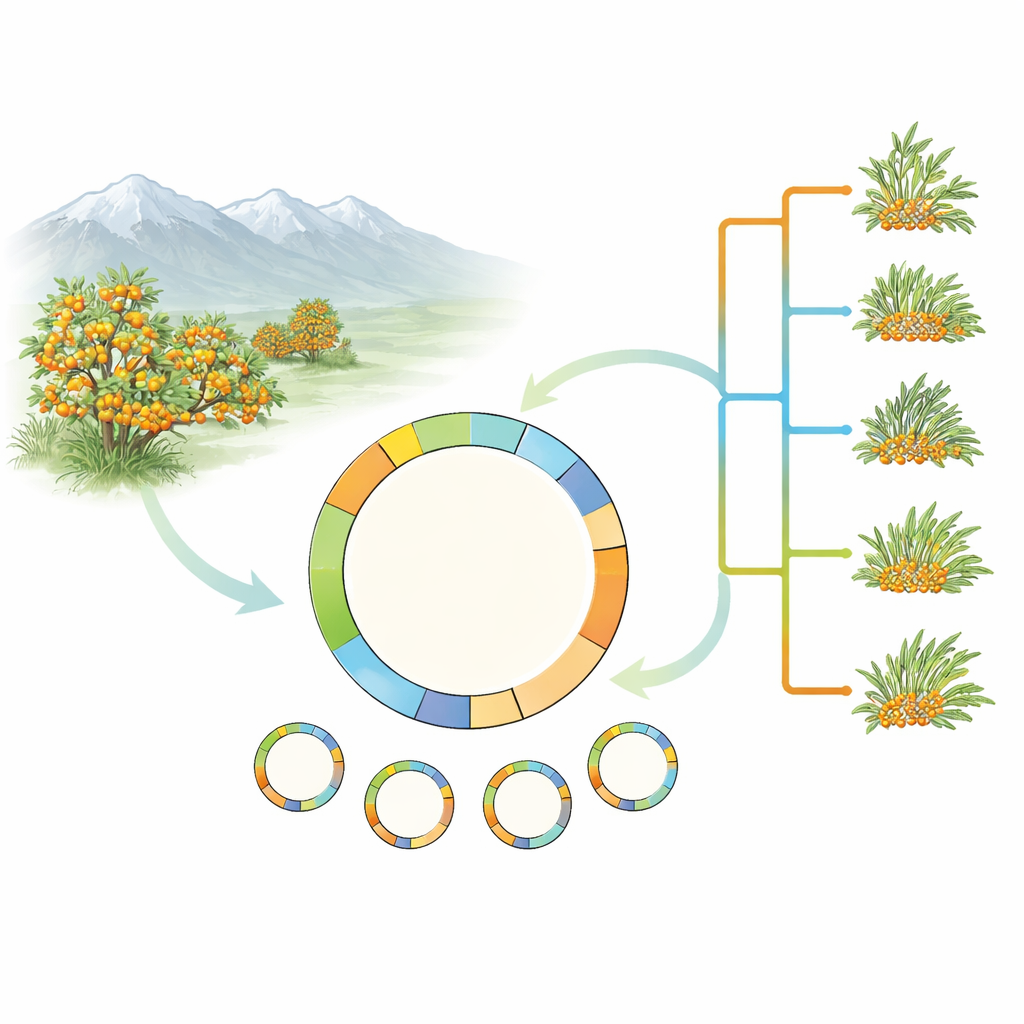
Piuttosto che affrontare la complessità dell'intero genoma dell'olivello spinoso, i ricercatori si sono concentrati sui plastidi della pianta — piccole compartimentazioni verdi all'interno delle cellule che eseguono la fotosintesi. I plastidi possiedono una loro piccola molecola di DNA circolare, ereditata per lo più dalla madre, che si è dimostrata estremamente utile per ricostruire gli alberi genealogici delle piante. Il gruppo ha raccolto e sequenziato genomi plastidiali completi da 17 campioni coprendo cinque specie di olivello spinoso e diverse forme dell'ampia Hippophae rhamnoides. Hanno inoltre aggiunto un genoma plastidiale appena assemblato da un importante tipo coltivato, H. rhamnoides subsp. mongolica cv. Prevoskhodnaya, e hanno ricontrollato con cura le voci di database precedenti alla ricerca di errori.
Un progetto condiviso con differenze significative
A prima vista, il DNA plastidiale di tutti i campioni di olivello spinoso sembrava sorprendentemente simile. Ogni genoma era lungo circa 155.000–156.000 “lettere” e seguiva la stessa struttura in quattro parti riscontrata in molte piante da fiore: due regioni a copia singola separate da una coppia di segmenti duplicati. Era presente lo stesso set di geni disposti nello stesso ordine e persino l'equilibrio complessivo delle quattro basi del DNA variava appena. Questa stabilità strutturale suggerisce che, nel corso dell'evoluzione, il progetto plastidiale in Hippophae sia stato conservato. Tuttavia, quando i ricercatori hanno esaminato più da vicino dettagli fini — come la frequenza d'uso di certi codoni per rappresentare lo stesso amminoacido — hanno trovato modelli sottili e specifici per linaggio che suggeriscono un lento e prolungato modellamento del codice in diversi rami del genere.
Districare l'albero genealogico
Usando 78 geni codificanti proteine dal DNA plastidiale, il team ha costruito alberi evolutivi che collocano l'olivello spinoso nella più ampia famiglia delle rosaceae e poi approfondiscono le relazioni all'interno di Hippophae. Le analisi hanno confermato che l'olivello spinoso come gruppo forma un unico lignaggio naturale e che H. rhamnoides e le sue sottospecie sono anch'esse strettamente correlate. In modo intrigante, una specie, H. tibetana, ricade costantemente all'interno del gruppo H. rhamnoides nell'albero plastidiale, sebbene studi precedenti basati sul DNA nucleare l'avessero collocata più vicino alla radice del genere. Questo disallineamento tra storie nucleari e plastidiali suggerisce antichi ibridazioni o altri eventi evolutivi complessi e indica la necessità di studi futuri che combinino set di dati nucleari e plastidiali completi.
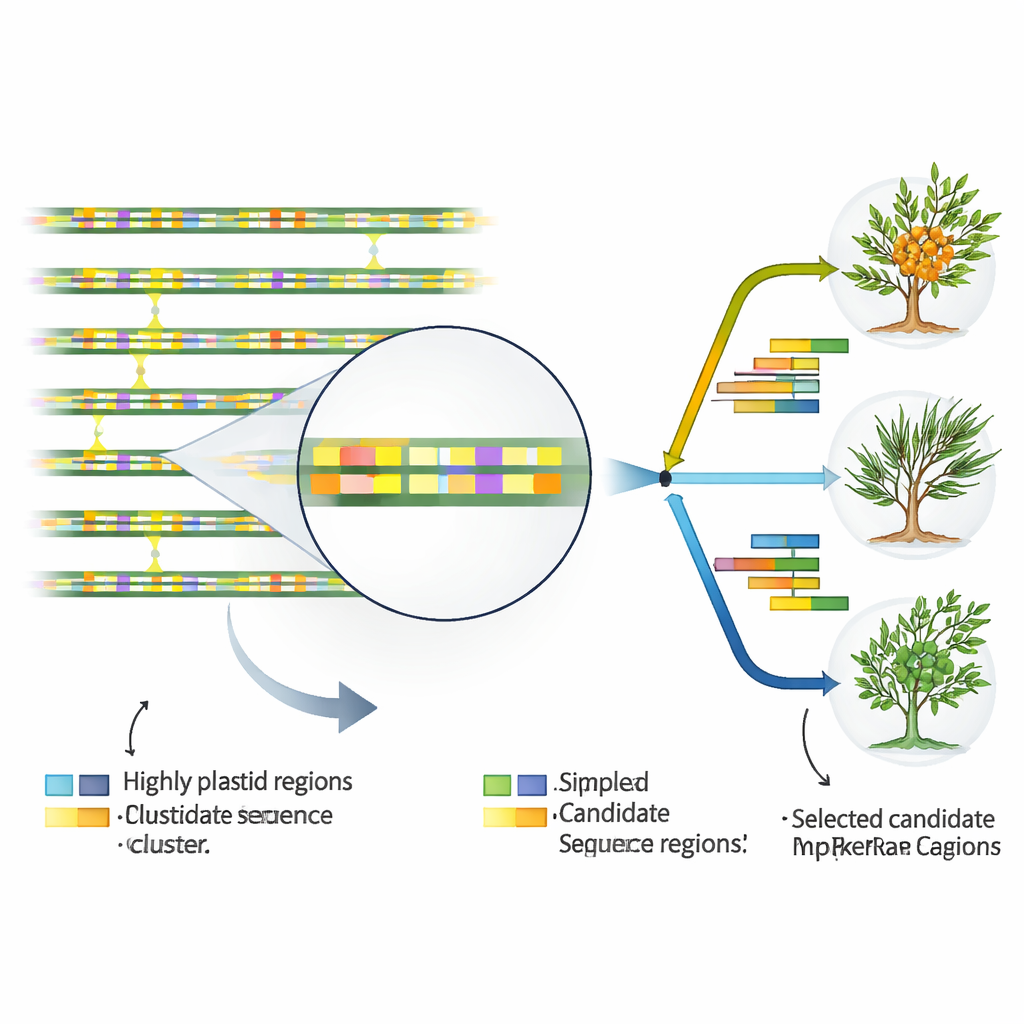
Individuare gli hotspot genomici che definiscono l'identità
Per trasformare il DNA plastidiale in strumenti di uso quotidiano per tassonomi e miglioratori, gli autori hanno cercato tratti di sequenza che mutano più rapidamente del resto. Confrontando tutti i 17 genomi plastidiali, hanno identificato 46 regioni particolarmente variabili, quasi tutte situate tra i geni o all'interno di introni non codificanti piuttosto che nei corpi genici stessi. Hanno inoltre mappato decine di piccoli motivi ripetuti noti come microsatelliti, ricchi soprattutto delle basi A e T e concentrati in regioni non codificanti. Alcune di queste ripetizioni e segmenti variabili mostravano differenze chiare tra specie e persino tra sottospecie di H. rhamnoides. Poche regioni si sono distinte come hotspot sia nei confronti a livello di specie sia a livello di sottospecie, rendendole candidate ideali per marcatori DNA pratici che possono essere rilevati con semplici test di laboratorio.
Dai pattern di DNA agli usi nel mondo reale
Mappando sia l'impalcatura stabile sia le differenze piccole ma informative nei genomi plastidiali dell'olivello spinoso, questo studio fornisce una cassetta degli attrezzi per un'identificazione affidabile basata sul DNA. Le regioni marcatore proposte potrebbero aiutare a distinguere specie simili, verificare l'origine di prodotti commerciali a base di bacche, proteggere la diversità genetica selvatica e guidare la selezione dei genitori in programmi di miglioramento volti a nutrizione, medicina e ripristino del territorio. In termini semplici, gli autori mostrano che un manuale di istruzioni del cloroplasto letto con cura può rivelare chi è chi nella famiglia allargata di questo arbusto resistente, spianando la strada a una conservazione più intelligente e a un uso più mirato di una delle colture di frutta più rustiche al mondo.
Citazione: Asakura, N., Noda, M., Takahashi, Y. et al. Comparative plastid genomics of Hippophae reveals phylogenetic relationships and provides candidate DNA markers for taxonomic identification. Sci Rep 16, 7943 (2026). https://doi.org/10.1038/s41598-026-40776-0
Parole chiave: olivello spinoso, genoma plastidiale, marcatori DNA, tassonomia delle piante, diversità genetica