Clear Sky Science · it
Caratterizzazione genomica di ceppi di Escherichia coli multiresistenti identificati in pazienti con infezione del tratto urinario in Egitto
Perché queste infezioni ostinate sono importanti
Le infezioni del tratto urinario sono tra i motivi più comuni per cui le persone si rivolgono a ospedali e ambulatori. Molte sono causate dal batterio Escherichia coli e di solito sono trattabili con antibiotici standard. Ma in tutto il mondo, incluso l’Egitto, alcuni ceppi di E. coli sono diventati così resistenti ai farmaci che i medici stanno esaurendo le opzioni. Questo studio analizza a fondo il patrimonio genetico di due di questi ceppi difficili da trattare provenienti da pazienti egiziane per capire come eludono più farmaci e quanto facilmente la loro resistenza possa diffondersi.
Due pazienti, due germi pericolosi
I ricercatori si sono concentrati su due ceppi di E. coli, denominati UPE7 e UPE139, isolati da donne con infezioni del tratto urinario in un ospedale di Mansoura, in Egitto. Testati rispetto a un ampio spettro di antibiotici, entrambi i ceppi hanno resistito a molti dei farmaci che i medici prescrivono normalmente, compresi alcuni farmaci di ultima istanza. Hanno mostrato resistenza a penicilline e cefalosporine comuni, a carbapenemi potenti, a fluorochinoloni di largo uso e ad altre classi di farmaci. Questo quadro li colloca saldamente nella categoria dei batteri multiresistenti, rendendo le infezioni difficili e costose da curare e aumentando il rischio di complicazioni.
Leggere il manuale genetico dei batteri
Per scoprire come questi ceppi siano diventati così robusti, il gruppo ha sequenziato i loro genomi completi utilizzando tecnologie di sequenziamento di nuova generazione. Ha poi impiegato strumenti informatici specializzati per scansionare i genomi alla ricerca di geni associati alla resistenza agli antibiotici e di caratteristiche che favoriscono la virulenza. Entrambi i ceppi portavano numerosi geni di resistenza che corrispondevano al loro comportamento in laboratorio. Per esempio, ospitavano molteplici geni “beta-lattamasi” che inattivano antibiotici chiave, oltre a geni che proteggono da farmaci come aminoglicosidi, tetracicline, macrolidi, sulfamidici e trimetoprim. Mutazioni negli enzimi centrali che interagiscono con il DNA, bersagli dei fluorochinoloni, erano coerenti con la forte resistenza al levofloxacina. Entrambi i ceppi possedevano anche un operone noto per modificare la superficie esterna in modo da attenuare l’azione dei polimixine.
Aiutanti nascosti che diffondono la resistenza
Oltre ai singoli geni di resistenza, lo studio mette in luce i veicoli genetici che trasferiscono questi tratti. Molti dei geni di resistenza erano adiacenti a elementi genetici mobili come sequenze di inserzione e trasposoni—piccole unità di DNA che possono spostarsi tra locazioni—e su plasmidi, molecole di DNA circolare che i batteri si scambiano tra loro. Per esempio, un gene ampia-diffusione per beta-lattamasi a spettro esteso, CTX-M-15, era associato a tali elementi mobili in entrambi i ceppi, mentre UPE139 portava anche OXA-244, un enzima che degrada i carbapenemi inserito tra segmenti di DNA mobili sul cromosoma. Gli stessi tipi di plasmidi riscontrati qui sono stati collegati altrove a cluster di geni di resistenza, sollevando preoccupazioni sul fatto che questi ceppi possano trasmettere le loro difese ad altri batteri in ospedali e nella comunità.
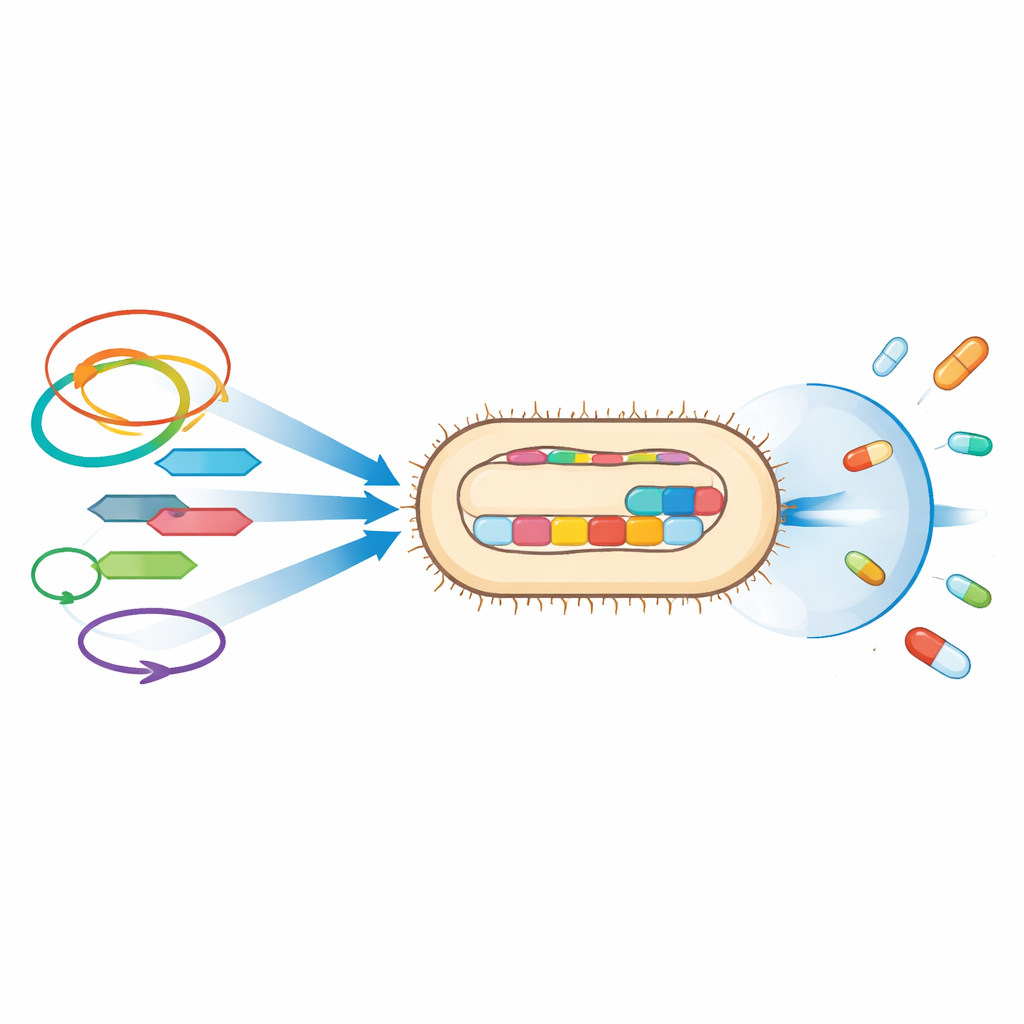
Strumenti per l’infezione e la sopravvivenza
L’analisi genetica ha inoltre rivelato numerosi tratti che aiutano questi ceppi di E. coli a colonizzare il tratto urinario e danneggiare i tessuti dell’ospite. Sia UPE7 sia UPE139 possedevano molteplici strutture di adesione che permettono loro di attaccarsi alle cellule e formare biofilm, comunità protettive più difficili da eliminare con farmaci o dal sistema immunitario. Codificavano tossine come l’emolisina, che può danneggiare le cellule dell’ospite, e sistemi di acquisizione del ferro che consentono ai batteri di prosperare nell’ambiente povero di ferro dell’organismo. UPE139, in particolare, possedeva geni aggiuntivi associati alla formazione della capsula, all’invasione e all’evasione immunitaria, suggerendo che potrebbe avere una capacità particolarmente elevata di persistere e diffondersi nei pazienti.
Cosa significa per pazienti e medici
Combinando i test tradizionali di sensibilità ai farmaci con il sequenziamento completo del genoma, questo studio mostra come un numero relativamente limitato di geni ed elementi mobili possa trasformare batteri urinari comuni in patogeni formidabili e multiresistenti. Rivela inoltre che questi tratti pericolosi sono su segmenti di DNA ben adatti al trasferimento ad altri ceppi, aumentando il rischio di una diffusione locale e regionale più ampia. Per i pazienti, ciò significa che alcune infezioni comuni potrebbero diventare più difficili da curare. Per i clinici e i responsabili della sanità, il lavoro sottolinea la necessità di un continuo monitoraggio genomico, di un uso prudente degli antibiotici e di studi più ampi su molti più isolati per tracciare cloni ad alto rischio, perfezionare le linee guida terapeutiche e rallentare l’avanzata della resistenza.
Citazione: El Halfawy, N.M., Gouda, M.K., Elgayar, F.A. et al. Genomic characterization of multidrug-resistant Escherichia coli strains identified from patients with urinary tract infection in Egypt. Sci Rep 16, 8958 (2026). https://doi.org/10.1038/s41598-026-40536-0
Parole chiave: resistenza agli antibiotici, infezione del tratto urinario, Escherichia coli, sequenziamento del genoma, elementi genetici mobili