Clear Sky Science · it
Evoluzione molecolare e diversità della RNA-dipendente RNA polimerasi del norovirus
Perché i virus intestinali continuano a sorprenderci
Il norovirus è il famoso virus della «influenza intestinale» che può mettere ko navi da crociera, scuole e ospedali in pochi giorni. Si trasmette facilmente, fa ammalare centinaia di milioni di persone ogni anno e genera continuamente nuovi varianti. Questo studio indaga i meccanismi di quell’evoluzione, concentrandosi su un singolo enzima virale — una «macchina di copia» interna chiamata RNA polimerasi — per capire come cambi nel tempo e quanto sia realmente stabile. Comprendere questo motore nascosto del cambiamento potrebbe aiutare a spiegare perché alcuni ceppi di norovirus dominano a livello globale e guidare la progettazione di futuri farmaci antivirali.
La macchina di copia interna del virus
Il norovirus porta il suo materiale genetico sotto forma di RNA e dipende da un enzima chiamato RNA-dipendente RNA polimerasi per copiare quell’RNA nelle cellule infette. Questo enzima, lungo circa 510 residui, somiglia a una mano ricurva con dita, palmo e pollice, formando un canale attraverso il quale passano l’RNA e i nuovi mattoni. All’interno di questa struttura si trovano sette piccoli «punti caldi» quasi identici tra i ceppi; queste regioni svolgono la chimica fondamentale della copia del genoma. Poiché la polimerasi è essenziale per la riproduzione del virus, anche piccole perturbazioni in questi punti critici possono essere disastrose per il virus, perciò l’evoluzione tende a preservarli con grande cura.
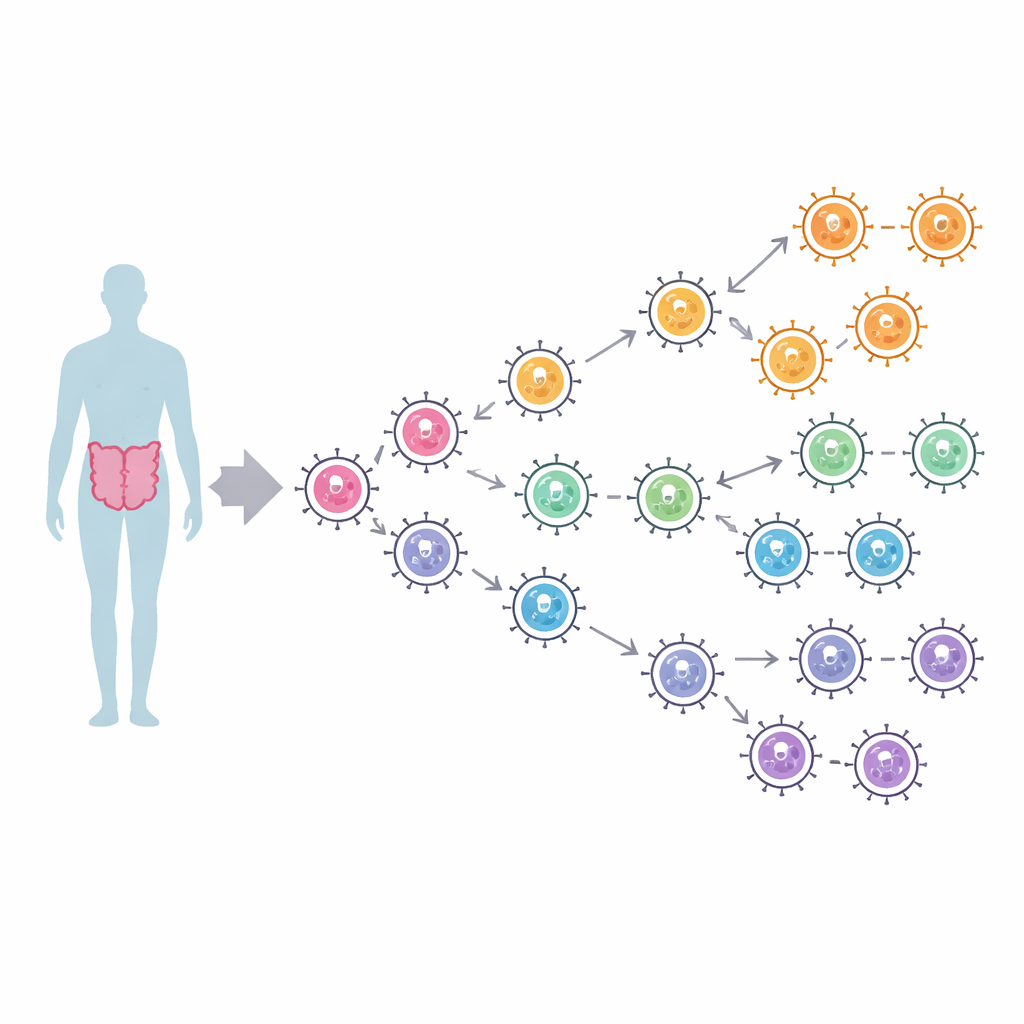
Centinaia di ceppi, poche famiglie chiave
I ricercatori hanno raccolto 1.094 sequenze complete della polimerasi provenienti da due principali gruppi umani di norovirus, chiamati GI e GII, campionati in tutto il mondo tra il 1972 e il 2024. Usando alberi filogenetici computazionali che incorporano date e luoghi di campionamento, hanno ricostruito come questi enzimi si siano ramificati in quasi quattro secoli. Le polimerasi GI si sono raggruppate in tre principali lignaggi che probabilmente si sono separati a partire circa dal 1600, mentre le polimerasi GII hanno formato quattro lignaggi, includendo un ramo distinto per un tipo noto come P16. Le infezioni moderne sono dominate da due tipi di polimerasi GII, P16 e P31, entrambi storicamente associati al genotipo di capside pandemico a lungo circolante GII.4. Tuttavia, nonostante la diffusione globale, gli alberi filogenetici mostrano scarso raggruppamento geografico — ceppi provenienti da continenti diversi si mescolano — suggerendo che il norovirus si muove rapidamente nel mondo senza restare confinato in regioni particolari.
Cambiamento lento e costante con nuclei ben protetti
Confrontando gli amminoacidi in ogni posizione della polimerasi, il team ha catalogato migliaia di cambiamenti tra i tipi. Hanno rilevato molte meno variazioni in GI rispetto a GII, riflettendo in parte un minor numero di sequenze disponibili, ma è emerso un modello chiaro: i sette punti caldi conservati e il sito di legame all’RNA vicino a essi sono rimasti quasi intatti. Quando si verificavano sostituzioni in queste aree, erano di solito scambi tra amminoacidi chimicamente simili, suggerendo che l’enzima tolleri solo piccole modifiche in queste zone cruciali. La maggior parte dei cambiamenti frequenti si è concentrata nelle «dita» e in altre regioni esterne dell’enzima, lontano dalla chimica centrale. Alcune posizioni hanno mostrato addirittura cambiamenti reversibili avanti e indietro tra diversi tipi di polimerasi, un segno di evoluzione convergente in cui ceppi non correlati convergono su soluzioni simili.
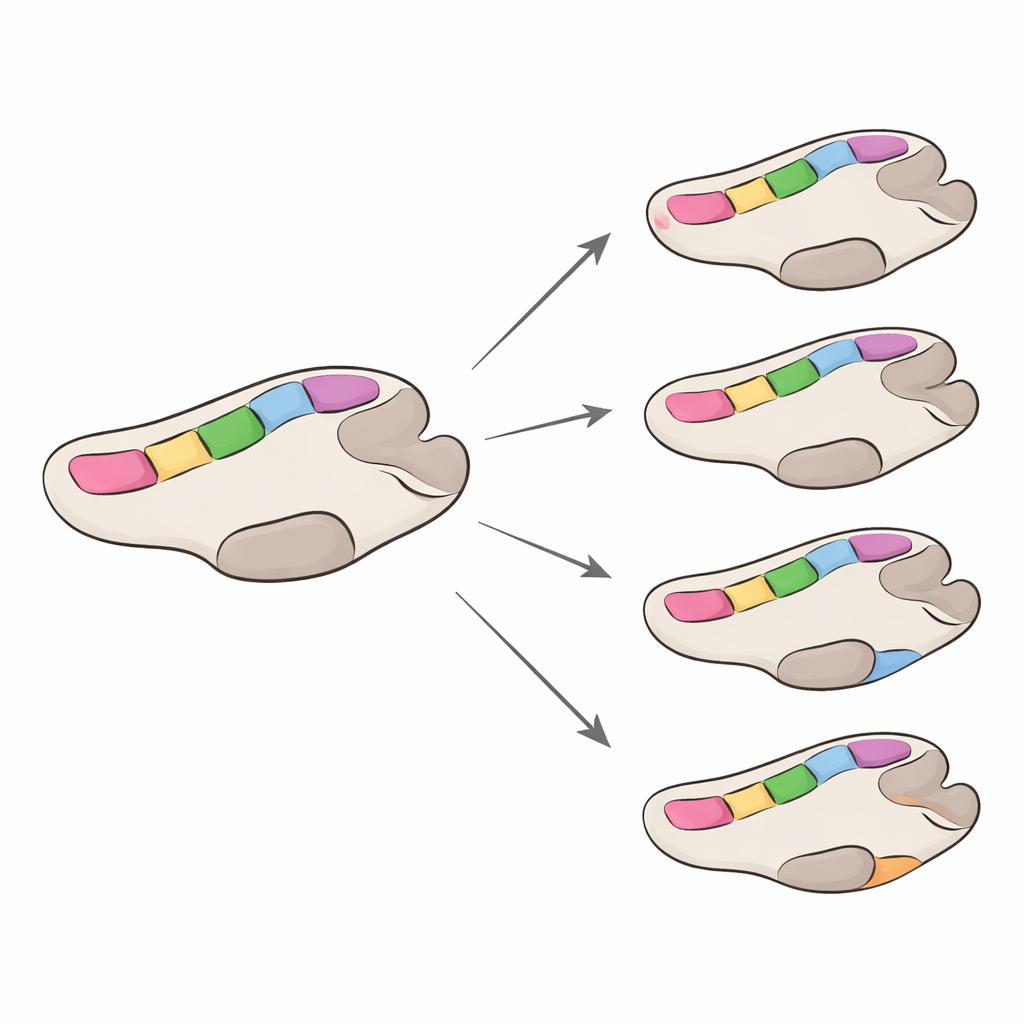
Velocità diverse per famiglie virali diverse
Il team ha quindi stimato la velocità con cui evolve la polimerasi, concentrandosi sui cambiamenti che alterano gli amminoacidi, più propensi a influire sulla funzione. Complessivamente, le polimerasi GII sono cambiate circa quattro volte più rapidamente delle GI, sebbene entrambe siano più lente rispetto alla proteina di rivestimento esterna del norovirus, nota per mutare rapidamente per sfuggire all’immunità. All’interno di ciascun gruppo, alcuni tipi di polimerasi evolvono leggermente più in fretta di altri, ma le differenze sono modeste. È importante notare che la maggior parte delle posizioni nell’enzima è soggetta a una forte pressione purificatrice — mutazioni che compromettono la funzione vengono eliminate — mentre solo un numero limitato di siti mostra segnali di selezione positiva. Quando questi siti sottoposti a selezione positiva sono stati mappati su modelli tridimensionali dell’enzima, risultavano quasi sempre esterni ai punti caldi più conservati, sebbene alcuni fossero abbastanza vicini da poter modulare il modo in cui la polimerasi lega l’RNA o si muove durante la copia.
Cosa significa per future epidemie e terapie
Nel complesso, questi risultati descrivono la polimerasi del norovirus come un nucleo sorprendentemente stabile avvolto da regioni più flessibili che consentono un adattamento graduale. Le polimerasi GII, in particolare quelle associate a ceppi storicamente pandemici, stanno evolvendo un po’ più rapidamente, il che potrebbe aiutare quei virus a tenere il passo con l’ospite in evoluzione e con varianti concorrenti. Tuttavia, la profonda conservazione delle regioni funzionali chiave per secoli suggerisce che questo enzima è un promettente bersaglio fisso per farmaci antivirali: perturbare la macchina di copia centrale lascia al virus poco margine di fuga senza auto-compromettersi. Per i non specialisti, la conclusione è che mentre le facce esterne del norovirus possono continuare a cambiare, rendendo inevitabili nuovi focolai, il motore interno che alimenta quei cambiamenti è sia strettamente vincolato sia scientificamente affrontabile — offrendo un bersaglio stabile per terapie future.
Citazione: Flint, A., Jawad, M. & Nasheri, N. Molecular evolution and diversity of the norovirus RNA-dependent RNA polymerase. Sci Rep 16, 9042 (2026). https://doi.org/10.1038/s41598-026-40248-5
Parole chiave: norovirus, evoluzione virale, RNA polimerasi, bersagli antivirali, epidemiologia molecolare