Clear Sky Science · it
L’integrazione trascrittomica guidata dal machine learning identifica GFM1 come potenziale biomarcatore legato alla lattilazione nella dissezione aortica
Perché questa minaccia nascosta nell’aorta è importante
La dissezione aortica è un’emergenza medica in cui una lacerazione all’interno dell’arteria principale del corpo può causare emorragie interne potenzialmente letali in poche ore. I medici spesso possono salvare i pazienti con un intervento chirurgico d’urgenza, ma non esistono ancora esami del sangue affidabili per segnalare il pericolo in fase precoce né farmaci che rallentino la malattia stessa. Questo studio esplora se spostamenti sottili nel modo in cui le cellule arteriose gestiscono l’energia e i segnali chimici possano rivelare nuovi segnali di allarme, concentrandosi su un gene poco noto chiamato GFM1 che potrebbe collegare il metabolismo cellulare all’indebolimento della parete aortica.
Decifrare il meccanismo di una lacerazione pericolosa
Nella dissezione aortica il sangue si insinua nella parete dell’aorta, separandone gli strati. Perché in alcune persone l’aorta fallisca in questo modo non è ancora del tutto chiaro. Gli autori hanno esaminato i modelli di attività genica in campioni prelevati da persone con dissezione aortica e da individui con aorte sane. Hanno prestato particolare attenzione ai geni legati alla “lattilazione”, un meccanismo recentemente scoperto tramite cui le cellule utilizzano il lattato — noto soprattutto come la sostanza che si accumula nei muscoli durante lo sforzo intenso — per modulare proteine e regolazione genica. Poiché la lattilazione è stata associata all’infiammazione e al rimodellamento dei tessuti, il gruppo ha ipotizzato che i geni correlati al lattato potessero essere coinvolti anche nel danneggiamento della parete aortica.
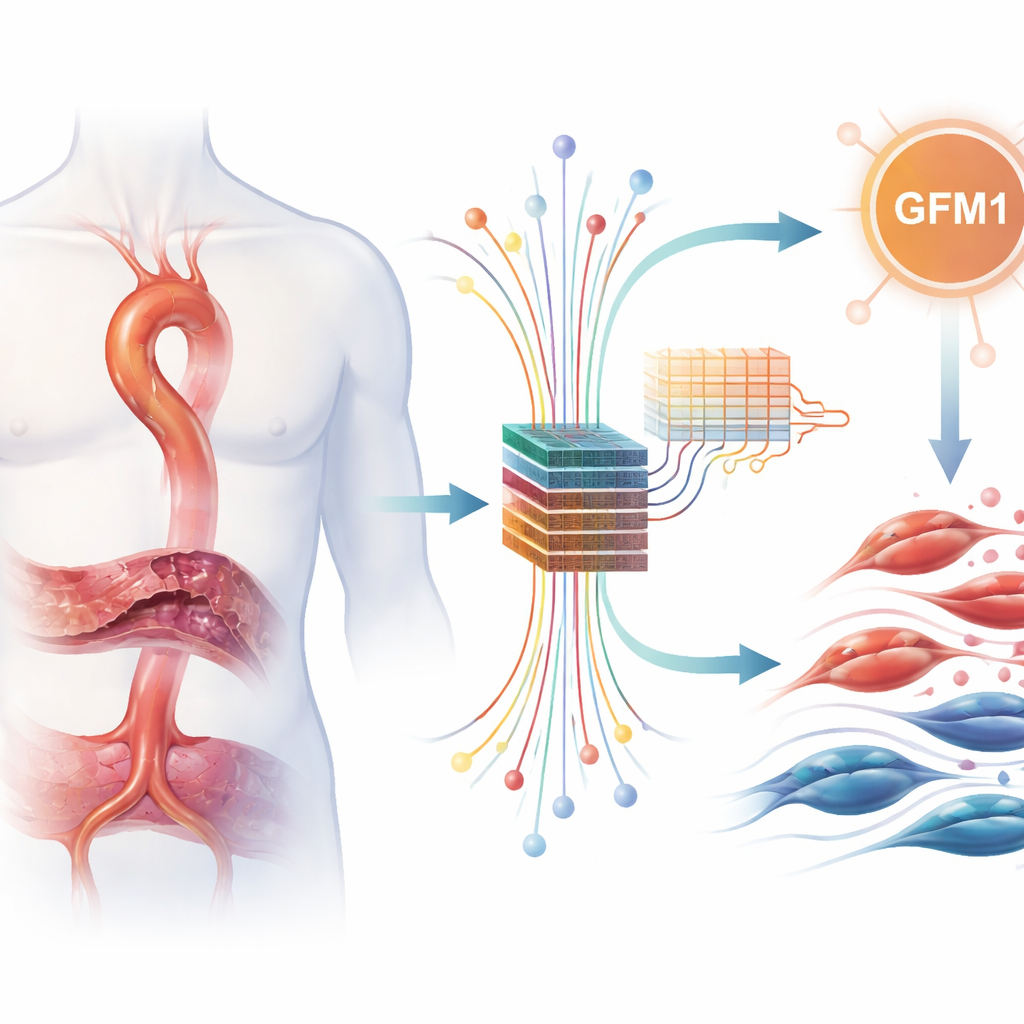
Scavare nei grandi dati con algoritmi intelligenti
Per mettere alla prova questa idea, i ricercatori hanno aggregato diversi set di dati pubblici che registrano quali geni sono attivati o repressi nel tessuto aortico. Hanno accuratamente corretto le differenze tecniche tra gli studi e poi hanno cercato geni la cui attività differisse in modo consistente tra campioni malati e sani. Tra migliaia di geni, ne hanno identificati 217 con cambiamenti netti, molti dei quali indicavano risposte immunitarie e rimodellamento della matrice che sostiene l’aorta. Successivamente si sono concentrati su un elenco curato di geni legati alla gestione del lattato e alla lattilazione e hanno identificato 11 geni che risultavano sia alterati nella dissezione aortica sia parte di questi programmi correlati al lattato.
Lasciare che le macchine votino su un sospetto chiave
Trovare 11 geni interessanti era ancora troppo per studiarli approfonditamente in laboratorio, così il gruppo ha ricorso a metodi di machine learning come sistema oggettivo di “voto”. Hanno inserito i dati di questi geni in tre diversi modelli — LASSO, Random Forest e XGBoost — comunemente usati per individuare pattern che separano al meglio i pazienti dai controlli. Ogni metodo ha evidenziato i suoi preferiti, ma un solo gene, GFM1, è stato selezionato in modo forte e coerente da tutti e tre. Questo approccio di verifica incrociata ha fatto risaltare GFM1 come un candidato particolarmente robusto, anche se i modelli sono stati usati per la classificazione dei geni e non per costruire un test diagnostico pronto all’uso.
Ingrandire sulle cellule muscolari dell’arteria
GFM1 contribuisce a regolare il modo in cui i mitocondri, le centrali energetiche della cellula, sintetizzano le proprie proteine. Poiché l’equilibrio energetico è cruciale per il comportamento delle cellule della parete arteriosa, gli autori hanno esaminato GFM1 più da vicino. Hanno confermato che i livelli di GFM1 erano più alti nei tessuti di pazienti con dissezione aortica rispetto alle aorte non malate. Poi sono passati a un sistema controllato di coltura cellulare usando cellule muscolari lisce vascolari di topo — le cellule di tipo muscolare che conferiscono resistenza all’aorta. Quando queste cellule sono state stimolate con angiotensina II, un ormone legato all’ipertensione e allo stress vascolare, hanno mostrato una maggiore tendenza a proliferare e migrare, riproducendo cambiamenti dannosi osservati nelle arterie malate. Quando i ricercatori hanno abbassato GFM1 in queste cellule usando piccoli RNA interferenti, la crescita e la migrazione indotte dall’angiotensina sono risultate notevolmente ridotte, suggerendo che GFM1 contribuisce a promuovere questi comportamenti a rischio.
Cosa significa tutto questo e cosa non dimostra ancora
Complessivamente, i risultati suggeriscono che GFM1 potrebbe agire da ponte tra il metabolismo cellulare alterato e il comportamento aggressivo delle cellule della parete arteriosa nella dissezione aortica. In termini semplici, una maggiore attività di GFM1 sembra associarsi a un’aorta più instabile e incline al danno, e ridurla in cellule coltivate in laboratorio le rende meno propense a iperproliferare e migrare. Tuttavia, gli autori sottolineano con cautela che questo lavoro è ancora a uno stadio precoce e generativo di ipotesi. Non hanno misurato direttamente la lattilazione nei tessuti né dimostrato che GFM1 sia chimicamente modificato in questo modo, e il potere predittivo dei modelli non è stato testato in gruppi indipendenti di pazienti. Studi futuri dovranno confermare questi risultati in coorti più ampie ed esplorare esattamente come GFM1 e i cambiamenti metabolici correlati indeboliscano la parete aortica. Se questi sforzi avranno successo, GFM1 o le sue vie potrebbero infine diventare bersagli per nuovi esami del sangue o trattamenti volti a prevenire questa lacerazione spesso fatale prima che si verifichi.
Citazione: Chen, J., Jiang, N., Guo, Z. et al. Machine-learning–guided transcriptomic integration identifies GFM1 as a lactylation-related candidate biomarker in aortic dissection. Sci Rep 16, 9033 (2026). https://doi.org/10.1038/s41598-026-40139-9
Parole chiave: dissezione aortica, cellule muscolari lisce vascolari, metabolismo del lattato, funzione mitocondriale, scoperta di biomarcatori