Clear Sky Science · it
Analisi multi-omica integrata identifica il gene correlato al danno al DNA CLSPN come biomarcatore nel tumore gastrico
Perché questa ricerca è importante
Il cancro allo stomaco rimane uno dei tumori più letali al mondo, in gran parte perché viene spesso rilevato in fase avanzata e mancano segnali di allarme precoci affidabili. Questo studio indaga in profondità le “impronte” genetiche lasciate dal danno al DNA e identifica un gene chiamato CLSPN come un promettente marcatore che potrebbe aiutare i medici a rilevare prima il cancro gastrico, comprendere quanto sia aggressivo e, potenzialmente, personalizzare i trattamenti in modo più preciso.
Cercare segnali di pericolo nei tumori gastrici
I ricercatori sono partiti da un’idea semplice: se il danno al DNA contribuisce allo sviluppo del cancro gastrico, allora i geni coinvolti nella risposta a quel danno potrebbero contenere indizi rilevanti su chi si ammala e su come si comporta la malattia. Per verificarlo hanno messo insieme diversi grandi set di dati. Questi includevano RNA-seq bulk, che misura l’attività genica media nei campioni tumorali; RNA-seq a singola cellula, che analizza migliaia di singole cellule una per una; e trascrittomica spaziale, che rimappa l’attività genica sul vetrino tissutale. Hanno inoltre raccolto una lunga lista di geni già collegati al danno al DNA. Usando queste risorse, hanno chiesto quali geni correlati al danno del DNA fossero più fortemente associati al cancro gastrico e alla sopravvivenza dei pazienti.
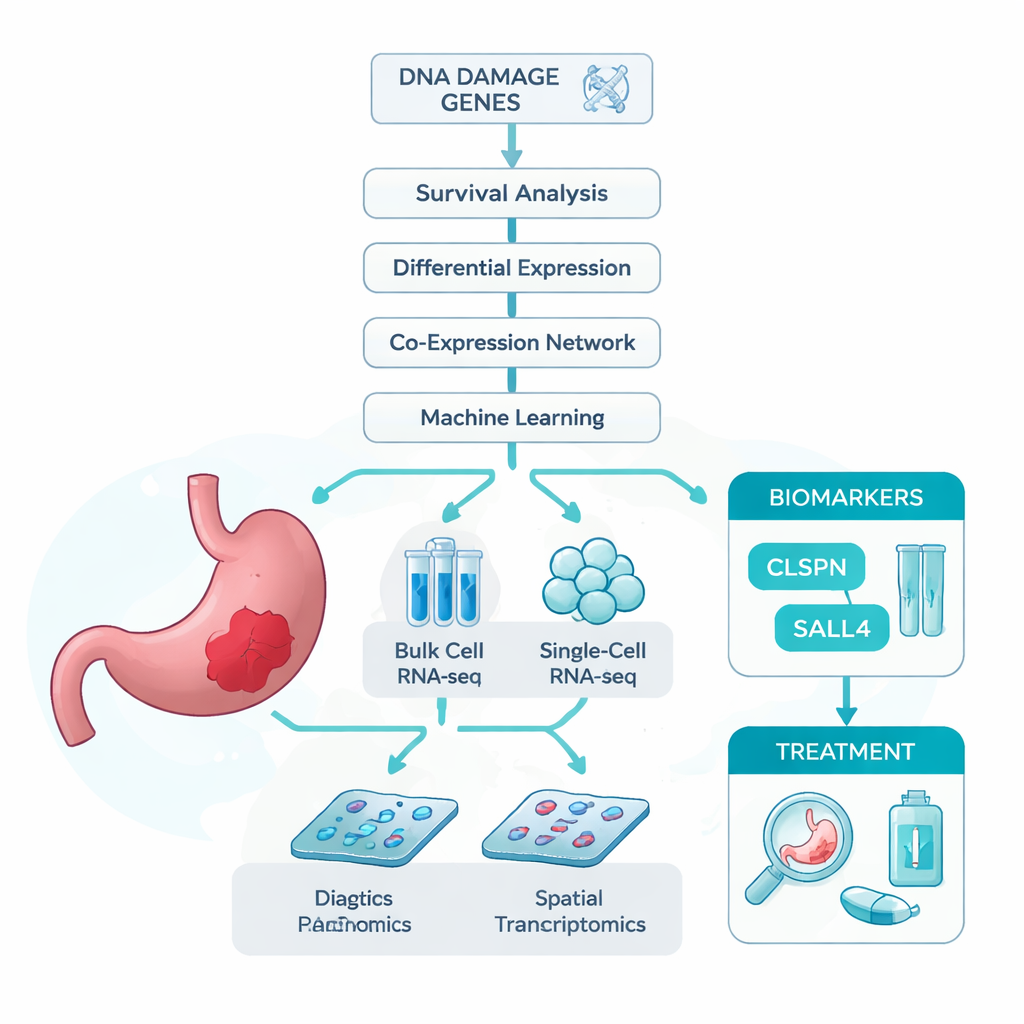
Usare algoritmi intelligenti per trovare i geni chiave
Poiché migliaia di geni variano nel cancro, il team ha utilizzato una serie di strumenti statistici e di machine learning per restringere il campo. Hanno prima filtrato i geni che risultavano sia disregolati nei tumori sia chiaramente correlati alla durata della vita dei pazienti. Poi hanno raggruppato i geni in base ai loro pattern di espressione correlata e hanno incrociato questi gruppi con la lista di geni legati al danno al DNA. Questo screening multipasso ha prodotto 13 candidati solidi. Per vedere quali di questi fossero più utili a distinguere tessuto tumorale da tessuto normale, hanno addestrato sette diversi modelli di machine learning, ciascuno dei quali ha ordinato i geni in base alla loro utilità per la classificazione. In tutti i modelli, due geni—CLSPN e SALL4—sono risultati costantemente ai primi posti, con punteggi di accuratezza vicini o superiori al 97% e aree sotto la curva ROC superiori a 0,96, suggerendo un eccellente potenziale diagnostico.
Approfondire CLSPN all’interno del tumore
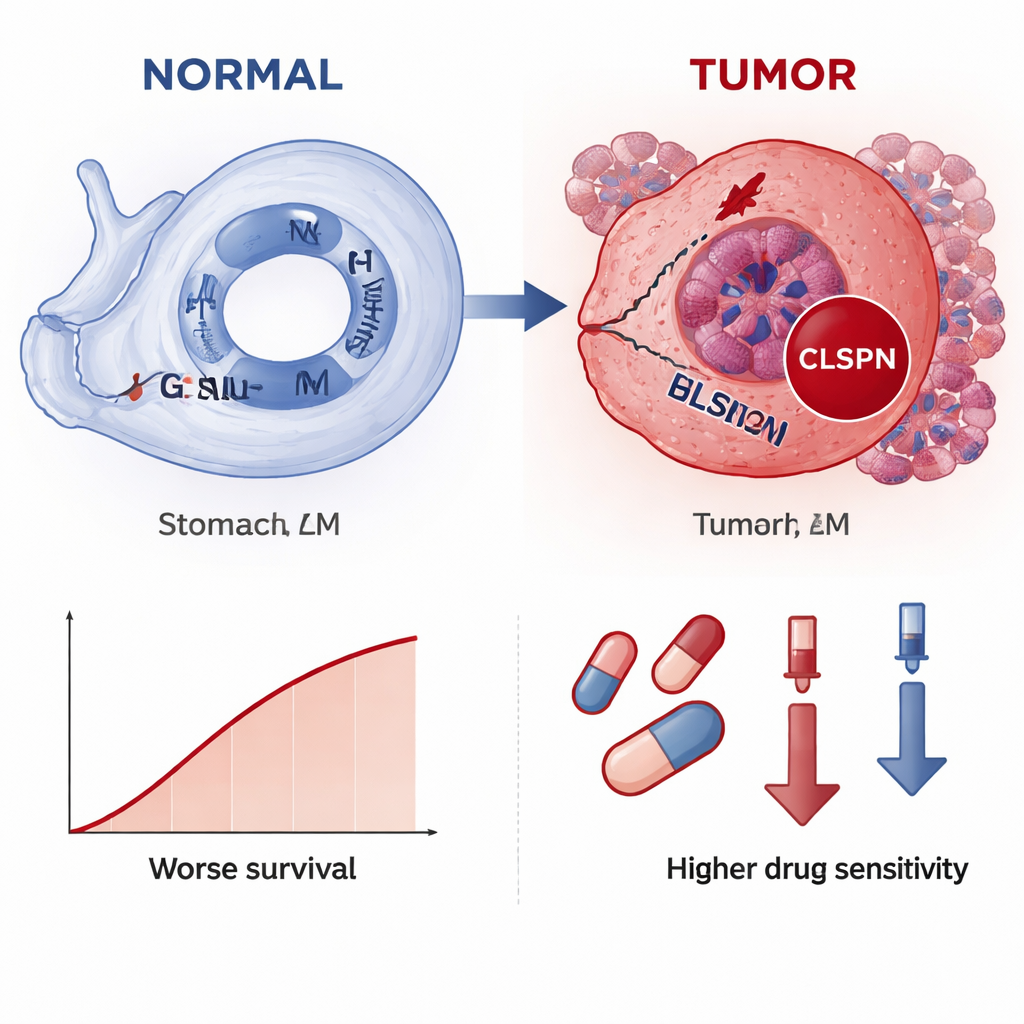
Tra i due geni principali, CLSPN si è distinto come il più informativo in generale, quindi gli autori lo hanno esaminato in maggiore dettaglio. Nei dati a singola cellula provenienti da oltre 30.000 cellule, CLSPN risultava molto più attivo nelle cellule tumorali che nelle cellule normali o di supporto adiacenti, indicando un ruolo specifico nel tumore. La mappatura spaziale delle sezioni tissutali dei pazienti ha mostrato un pattern simile: l’espressione di CLSPN si raggruppava in regioni riconosciute dai patologi come cancerose. Quando il team ha diviso le cellule tumorali in gruppi a «CLSPN alto» e «CLSPN basso», il gruppo ad alto CLSPN mostrava un’attività più forte in vie legate alla duplicazione del DNA, alla divisione cellulare e alla riparazione—processi che, se iperattivati o disdiretti, possono alimentare la crescita incontrollata. L’analisi di pseudotempo, che ricostruisce come cambiano le cellule lungo una linea temporale notionale, ha suggerito che man mano che le cellule tumorali progrediscono, i livelli di CLSPN tendono ad aumentare, insinuando che l’aumento di CLSPN potrebbe far parte dello spostamento verso uno stato più maligno.
Collegamenti con il sistema immunitario e la risposta ai trattamenti
Lo studio ha anche esplorato come CLSPN si relazioni con il microambiente tumorale e con potenziali terapie. I tumori con maggiore espressione di CLSPN presentavano composizioni diverse di cellule immunitarie, in particolare macrofagi e alcune popolazioni di cellule T e NK, suggerendo che CLSPN potrebbe contribuire a modellare un ambiente immunosoppressivo. La modellazione della sensibilità ai farmaci ha indicato che i tumori con più CLSPN potrebbero essere più vulnerabili a diversi agenti chemioterapici e mirati, poiché livelli più elevati di CLSPN sono stati associati a dosi predette più basse necessarie per inibire la crescita. Di notevole importanza, quando gli autori hanno colorato campioni tissutali reali di 70 pazienti, i livelli proteici di CLSPN risultavano chiaramente più alti nel tumore rispetto allo stomaco normale e si associavano a tumori di dimensioni maggiori, invasioni più profonde, coinvolgimento dei linfonodi e a una sopravvivenza globale più breve.
Cosa potrebbe significare per i pazienti
In termini pratici, lo studio suggerisce che CLSPN si comporta come una spia rossa per il cancro gastrico: si attiva principalmente nelle cellule tumorali, si illumina maggiormente nelle forme più avanzate della malattia e segnala un rischio più alto di esito sfavorevole. Poiché può essere rilevato sia a livello di RNA sia con metodi di colorazione standard usati in ospedale, CLSPN potrebbe diventare un biomarcatore pratico per aiutare i patologi a confermare il cancro gastrico, stratificare i pazienti per rischio e forse orientare la scelta dei farmaci. Sebbene siano necessari ulteriori test clinici prima di un uso routinario, questo lavoro evidenzia come leggere le tracce del danno al DNA su più livelli di dati possa rivelare nuovi strumenti per una diagnosi più precoce e un trattamento più personalizzato del cancro gastrico.
Citazione: Ma, Q., Yang, X., Sun, N. et al. Integrating multi-omics analysis identifies DNA damage-related gene CLSPN as a biomarker in gastric cancer. Sci Rep 16, 7789 (2026). https://doi.org/10.1038/s41598-026-39387-6
Parole chiave: cancro gastrico, danno al DNA, CLSPN, biomarcatore, analisi a singola cellula