Clear Sky Science · it
Nuovi geni marcatore per il rilevamento simultaneo di Salmonella, EHEC O157:H7 e Cronobacter
Perché questo è importante per la sicurezza alimentare di tutti i giorni
Dalle insalate agli hamburger fino alle formule per neonati, gli alimenti di cui ci fidiamo possono talvolta ospitare germi pericolosi. Tre dei colpevoli più preoccupanti — alcuni ceppi di E. coli, Salmonella e un batterio meno noto chiamato Cronobacter — possono causare malattie gravi, soprattutto nei bambini piccoli e negli adulti vulnerabili. Questo studio mostra come gli scienziati stiano usando gigantesche banche dati di DNA e test di laboratorio intelligenti per individuare tutti e tre questi rischi simultaneamente, in modo rapido e accurato, prima che il cibo contaminato arrivi sulla vostra tavola.
Pericoli nascosti negli alimenti comuni
Le malattie di origine alimentare sono aumentate nell’ultimo decennio, alimentate in parte dalle catene di approvvigionamento globali e dall’enorme volume di alimenti trasformati e pronti al consumo. L’EHEC O157:H7, una forma altamente tossica di E. coli, può provocare diarrea emorragica e insufficienza renale. La Salmonella causa milioni di casi di intossicazione alimentare ogni anno, e il Cronobacter, pur meno famoso, può essere mortale per i neonati, in particolare in relazione alle formule in polvere. I metodi di laboratorio tradizionali spesso si concentrano su un solo agente alla volta e richiedono giorni di coltura, rallentando le indagini sugli focolai e i controlli di routine. Gli autori si sono proposti di sviluppare test basati sul DNA più rapidi che possano segnalare questi tre patogeni insieme in un’unica procedura snella.
Trovare “codici a barre” in un mare di DNA
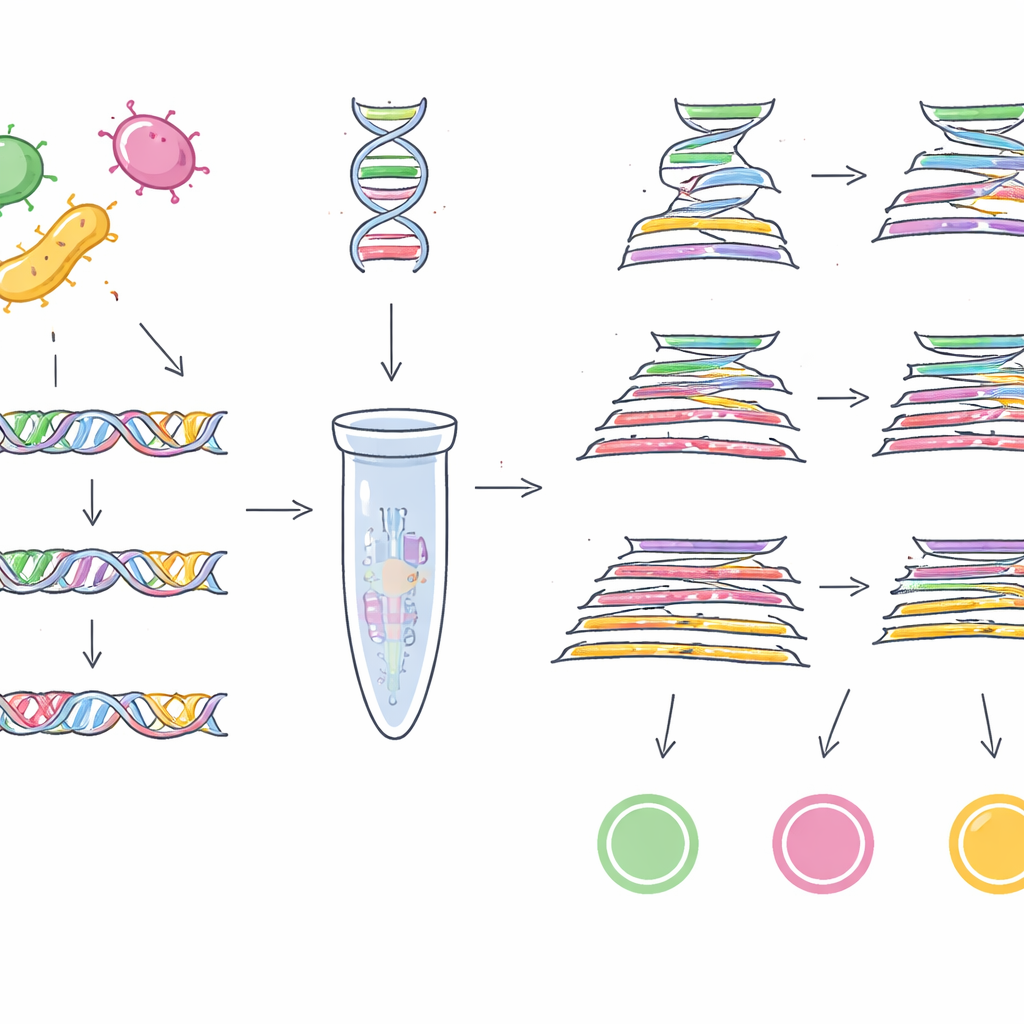
Per farlo, il team aveva prima bisogno di “codici a barre” genetici affidabili — brevi porzioni di DNA presenti in quasi tutti i ceppi di un germe target ma assenti negli altri. Invece di cercare in poche genomi, hanno utilizzato un’enorme raccolta pubblica di 1,46 milioni di genomi batterici provenienti da 50 generi differenti. Per l’EHEC O157:H7 hanno confrontato migliaia di genomi di E. coli e setacciato oltre 100.000 famiglie di geni accessori per trovare sequenze di DNA uniche per questo sottotipo pericoloso. Dopo diverse fasi di filtraggio e verifiche incrociate contro più di un milione di genomi non-E. coli, hanno individuato un gene chiamato z0340 come marcatore altamente specifico per l’EHEC O157:H7. Utilizzando una strategia simile su più di mezzo milione di genomi di Salmonella e quasi un milione di altri genomi batterici, hanno identificato un altro gene, sbcC, come marcatore affidabile per il gruppo Salmonella nel suo complesso.
Trasformare i marcatori in test pratici
Con queste due nuove “barre” genetiche — oltre a un gene specifico per Cronobacter, ygcB, che il gruppo aveva precedentemente scoperto — i ricercatori hanno progettato test di laboratorio in grado di rilevare tutti e tre i patogeni in un unico passaggio. Hanno sviluppato saggi PCR multiplex, che funzionano come fotocopiatrici molecolari mirate a tratti specifici di DNA, e una versione TaqMan qPCR più sensibile che misura in tempo reale la quantità di DNA target presente. Quando questi test sono stati messi alla prova con 23 ceppi dei tre patogeni e 100 ceppi di altri batteri comuni, hanno identificato correttamente solo i bersagli previsti ogni volta, mostrando una specificità del 100%. La PCR multiplex di base poteva rilevare quantità di DNA fino a 1 picogrammo per microlitro, mentre la versione TaqMan scendeva fino a 0,5 picogrammi, indicando un’elevata sensibilità.
Mettere i metodi alla prova sugli alimenti
L’accuratezza di laboratorio è utile solo se i test funzionano in campioni reali e complessi. Per verificarlo, gli scienziati hanno deliberatamente contaminato lattuga, carne macinata e latte in polvere per neonati con quantità note di EHEC O157:H7, Salmonella o Cronobacter. Dopo i passaggi di arricchimento standard per permettere la moltiplicazione di eventuali batteri presenti, hanno applicato i loro saggi PCR multiplex e TaqMan qPCR. In ogni caso, i metodi hanno rilevato correttamente il patogeno introdotto e non hanno prodotto falsi allarmi nei controlli negativi. La prestazione è stata consistente in tutti e tre i tipi di alimento, suggerendo che grassi, componenti vegetali o ingredienti complessi non interferivano in modo significativo con il rilevamento.
Limitazioni e possibili miglioramenti futuri
Nonostante i risultati solidi, gli autori osservano che il loro pannello di validazione rappresenta ancora solo una piccola frazione della diversità microbica presente in natura. Per esempio, in laboratorio hanno testato un solo ceppo di EHEC O157:H7, sebbene il loro screening basato sui genomi avesse coperto decine di migliaia di tali ceppi. Hanno inoltre lavorato con livelli di contaminazione relativamente elevati rispetto alle quantità estremamente basse di batteri che possono comunque causare malattia. I lavori futuri dovranno testare molti più isolati reali, esaminare alimenti contaminati naturalmente e aggiungere controlli interni per proteggere contro sostanze presenti negli alimenti che possono inibire l’amplificazione del DNA.
Cosa significa questo per i consumatori
In parole semplici, questo studio mostra che codici a barre genetici scelti con cura possono permettere ai laboratori di sicurezza alimentare di schermare più agenti ad alto rischio contemporaneamente, con alta accuratezza e in meno tempo rispetto ai metodi tradizionali basati sulla coltura. Minando milioni di genomi, i ricercatori hanno identificato tre firme genetiche — una per l’EHEC O157:H7, una per la Salmonella e una per il Cronobacter — che sembrano essere sia altamente specifiche sia stabili. I test risultanti potrebbero rafforzare il monitoraggio di routine di alimenti come insalate, carni e formule per neonati, rilevando le contaminazioni in modo più precoce e affidabile. Oltre a questi tre patogeni, lo stesso approccio “genoma-centrico” potrebbe essere usato per progettare test rapidi per molti altri microrganismi pericolosi, offrendo uno strumento potente per rendere più sicura la catena alimentare globale.
Citazione: Zhang, H., Xiong, P., Lu, Z. et al. Novel marker genes for simultaneous detection of Salmonella, EHEC O157:H7, and Cronobacter. Sci Rep 16, 9362 (2026). https://doi.org/10.1038/s41598-026-38990-x
Parole chiave: patogeni alimentari, PCR multiplex, marcatori genomici, Salmonella ed EHEC, rilevamento Cronobacter