Clear Sky Science · it
Uno studio pilota sulla coerenza del protocollo e sulla riproducibilità delle metriche di grafo nei connettomi pesati per microstruttura
Perché la mappa dei collegamenti del cervello ha bisogno di un controllo di affidabilità
Medici e scienziati guardano sempre più al cervello come a una grande mappa di cablaggi, dove le aree comunicano tra loro tramite fasci di fibre nervose. Nuovi metodi basati sulla risonanza magnetica possono trasformare questo cablaggio in reti matematiche che potrebbero rivelare segnali precoci di malattie come la sclerosi multipla o l’Alzheimer. Ma prima che tali misure possano guidare la diagnosi o il trattamento, dobbiamo sapere qualcosa di fondamentale: se scannerizziamo più volte lo stesso cervello sano, o su scanner diversi con impostazioni leggermente diverse, otteniamo sostanzialmente la stessa rete?
Dal movimento dell’acqua alle mappe delle autostrade cerebrali
Per costruire queste mappe dei collegamenti, gli autori usano una forma di risonanza magnetica che segue come le molecole d’acqua si muovono nel tessuto cerebrale. La materia bianca, dove lunghi assoni isolati corrono insieme, favorisce il movimento dell’acqua lungo la lunghezza delle fibre più che attraverso di esse. Misurando questo moto sensibile alla direzione in molte orientazioni, algoritmi informatici possono inferire gruppi di fibre e assemblare un “connettoma” – una matrice che registra quali regioni della materia grigia sono collegate da quali percorsi di materia bianca. Invece di limitarsi a contare quante fibre virtuali vengono ricostruite tra le regioni, questo studio si concentra sui connettomi “pesati per microstruttura”, in cui ogni connessione è caratterizzata dalle proprietà del tessuto stesso, come quanto ordinate sono le fibre o quanto appaiono densamente impaccate.
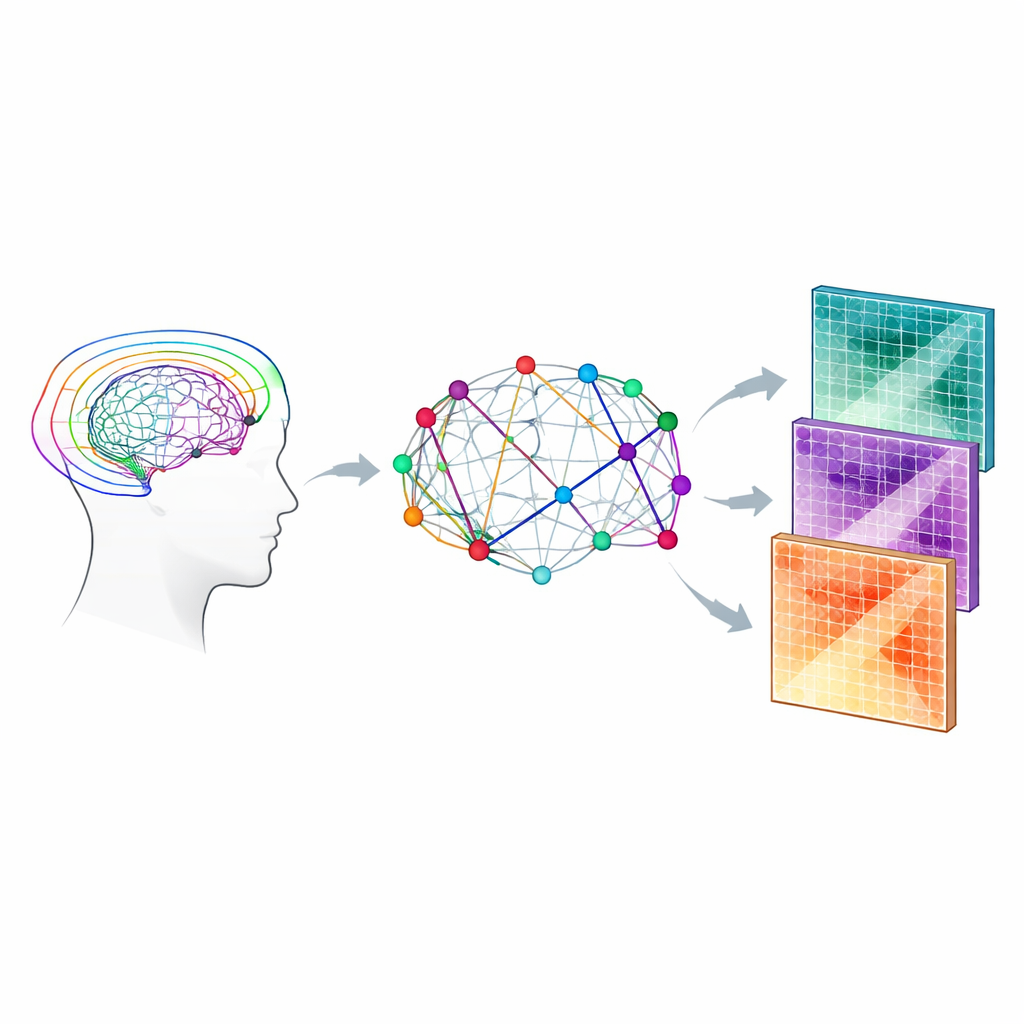
Aggiungere dettaglio biologico alla rete
Il team ha combinato due famiglie di modelli che interpretano il segnale di diffusione MRI. Il primo, l’imaging del tensore di diffusione, sintetizza quanto il moto dell’acqua sia direzionale e quanto rapidamente diffonde in media. Il secondo, chiamato Bingham-NODDI, compie un ulteriore passo stimando quanto di ciascun piccolo volume di tessuto sia costituito da acqua all’interno delle fibre nervose, all’esterno di esse o in spazi pieni di fluido. Utilizzando un protocollo di scansione relativamente ricco a “quattro shell” progettato per catturare meglio la geometria complessa delle fibre, hanno calcolato diversi parametri microstrutturali, inclusi anisotropia frazionale e diffusività media (dal modello tensore) e frazioni di volume intra-neurite ed extra-cellulare (da Bingham-NODDI). Questi parametri sono stati quindi propagati lungo ciascun fascio di fibre ricostruito e combinati per fornire un peso biologicamente informato a ogni connessione nella rete.
Mettere alla prova la pipeline
L’affidabilità è stata valutata in tre modi complementari. Primo, i ricercatori hanno scannerizzato ripetutamente un fantoccio fisico accuratamente progettato – un groviglio di fibre sintetiche in acqua salata che imita caratteristiche chiave del tessuto cerebrale – per testare quanto fossero stabili i parametri su brevi periodi. Successivamente, hanno scannerizzato quattro volontari sani in due ospedali, utilizzando la stessa marca e modello di scanner MRI e le stesse impostazioni, per sondare le differenze tra siti. Infine, hanno confrontato il protocollo a quattro shell con un protocollo più corto e convenzionale a due shell, chiedendosi se entrambi dessero valori di parametro simili. Per i dati cerebrali, hanno ricostruito più versioni del connettoma pesato da diversi parametri ed estratto misure di grafo come l’efficienza complessiva della rete, quanto sono raggruppate le connessioni e quanto fortemente ciascuna regione si connette al resto del cervello. Hanno quindi verificato quanto queste misure cambiassero da sito a sito e quanto della variazione riflettesse reali differenze tra le persone piuttosto che rumore di misura.
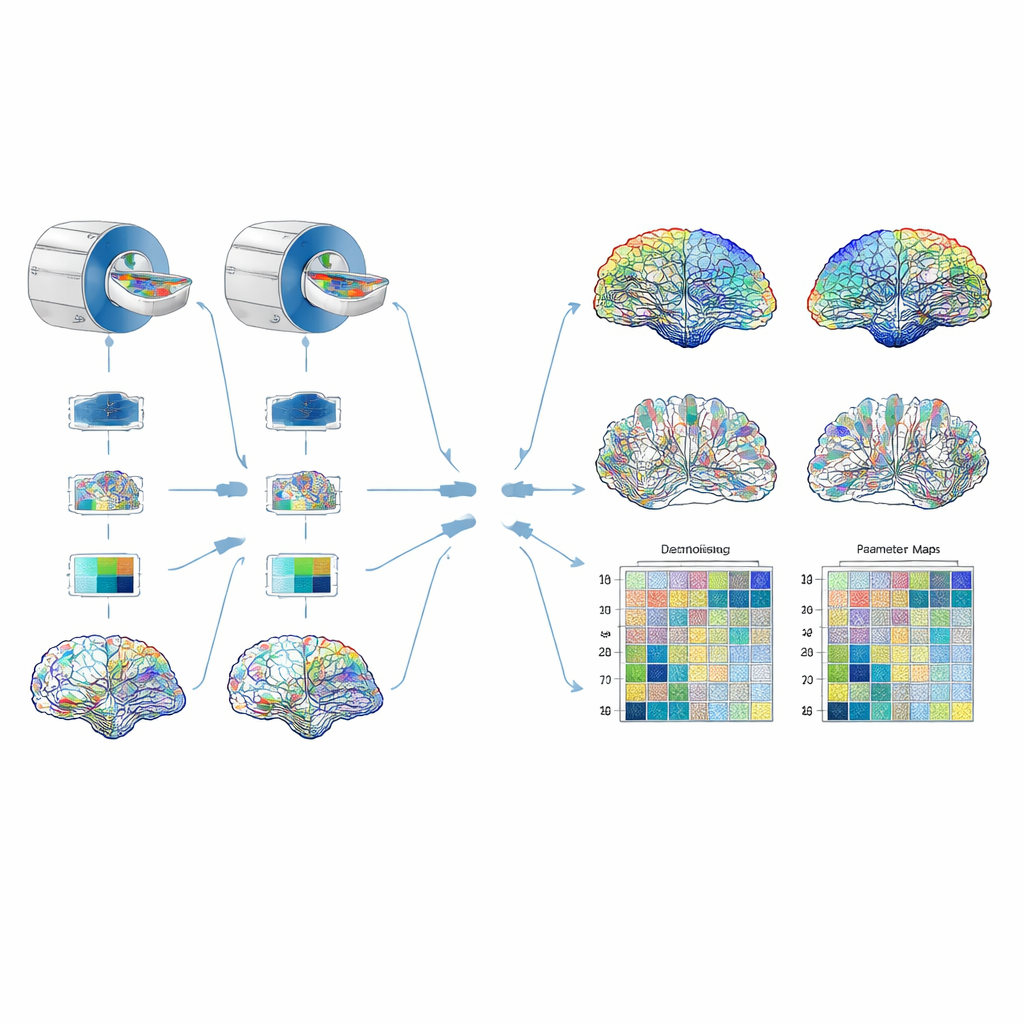
Cosa si è rivelato affidabile
Diverse misure tissutali chiave si sono dimostrate sorprendentemente coerenti. L’anisotropia frazionale, la diffusività media e le frazioni di volume intra-neurite e intra-cellulare sono variate di meno del cinque percento tra scansioni ripetute, tra siti diversi e (per la maggior parte delle regioni) tra i protocolli a due e quattro shell. Al contrario, grandezze che descrivono quanto siano disperse le orientazioni delle fibre – e un parametro correlato di “concentrazione” – sono risultate più irregolari e sono state pertanto escluse dalla costruzione della rete. Quando i ricercatori hanno costruito connettomi pesati dalle misure più stabili, molte proprietà di rete, inclusa densità, efficienza globale, clustering medio e forza media delle connessioni, sono risultate riproducibili tra i siti. Un’eccezione è stata la modularità, una misura di quanto nettamente la rete si suddivide in comunità distinte; questa è risultata particolarmente sensibile a piccoli cambiamenti nei pesi sottostanti. I connettomi pesati dalla frazione di volume extra-cellulare hanno mostrato le prestazioni peggiori in generale, con diverse misure di grafo che presentavano scarso accordo tra i siti.
Perché questo è importante per la salute cerebrale
Lo studio mostra che non basta contare le fibre ricostruite quando si cercano marcatori di malattia nella rete di collegamenti del cervello. Selezionando con cura parametri microstrutturali stabili per pesare ogni connessione, i ricercatori possono costruire reti più ricche e fondate biologicamente le cui proprietà chiave sono ripetibili tra scanner e protocolli. Nelle condizioni testate, i connettomi pesati da anisotropia frazionale, diffusività media e frazione di volume intra-neurite si sono mostrati abbastanza robusti da permettere che le loro statistiche di rete di base possano servire come potenziali biomarcatori in disturbi che alterano la connettività cerebrale. Allo stesso tempo, il lavoro segnala misure più fragili, come la modularità e alcuni indici microstrutturali avanzati, come caratteristiche da trattare con cautela finché studi più ampi e multicentrici non ne confermeranno l’affidabilità.
Citazione: Cavallo, M., Ricchi, M., Axford, A. et al. A pilot study on protocol consistency and graph metric reproducibility in microstructure-weighted connectomes. Sci Rep 16, 8288 (2026). https://doi.org/10.1038/s41598-026-38964-z
Parole chiave: connettività cerebrale, risonanza magnetica di diffusione, connettoma, riproducibilità delle reti, imaging della microstruttura