Clear Sky Science · it
Nuova rete neurale convoluzionale per l'identificazione batterica in dataset da microscopio confocale
Perché individuare i germi più rapidamente è importante
Quando i medici cercano di capire quali batteri stanno causando un'infezione, il tempo è fondamentale. I test di laboratorio tradizionali possono richiedere molte ore o addirittura giorni e richiedono esperti altamente qualificati che esaminino le immagini al microscopio a occhio nudo. Questo studio presenta un nuovo sistema di visione artificiale, chiamato CM-Net, in grado di leggere automaticamente immagini microscopiche specializzate e distinguere rapidamente due batteri comuni e di rilevanza medica, riconoscendo contemporaneamente quali cellule sono vive o morte. Il lavoro indica una strada verso una diagnostica più rapida e affidabile che un giorno potrebbe essere utilizzata in ospedali e laboratori di ricerca in tutto il mondo.
Trasformare i germi fluorescenti in immagini utili
I ricercatori hanno cominciato con uno strumento di imaging potente noto come microscopia confocale a scansione laser. In termini semplici, questo microscopio usa un laser focalizzato e coloranti fluorescenti per far brillare i batteri in colori diversi a seconda che siano vivi o morti. Le cellule vive appaiono verdi, mentre quelle morte appaiono rosse. Scansionando il campione in strati molto sottili, il microscopio costruisce immagini nitide e dettagliate dei batteri su vetrini. Il team ha lavorato con due specie ben note che spesso causano infezioni ospedaliere: il batterio a forma di bastoncello Escherichia coli e il cocco Staphylococcus aureus. Queste immagini di alta qualità costituiscono il materiale grezzo che CM-Net deve imparare a interpretare.
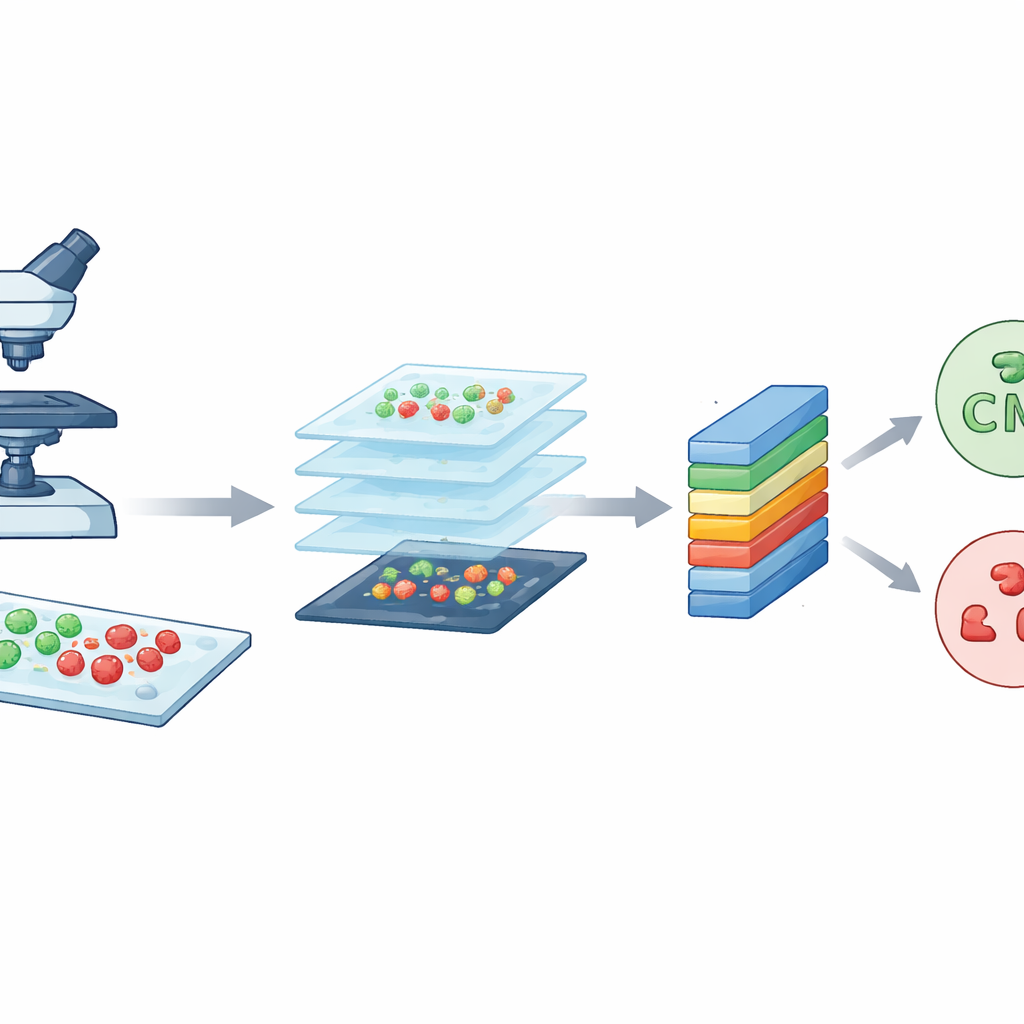
Creare molte tessere piccole a partire da immagini grandi
Benché ogni immagine confocale sia ricca di dettagli, è anche molto grande, circa 3000 per 3000 pixel. Addestrare un modello informatico direttamente su immagini così enormi sarebbe lento e richiederebbe potenza di calcolo eccessiva. Per risolvere questo problema, il team ha diviso ogni immagine grande in molte piccole tessere quadrate, ciascuna di 224 per 224 pixel, una dimensione standard nell'analisi delle immagini. Questo processo, detto data augmentation, riduce sia il carico tecnico sia moltiplica il numero di esempi di addestramento. Da un set originale di 300 immagini per tipo batterico hanno ottenuto in totale 7.066 tasselle. Queste tessere catturano modelli locali di forme, colori e texture provenienti da diverse aree dei vetrini, fornendo al modello un insieme di esempi vario ed equilibrato da cui apprendere.
Come l'osservatore digitale impara a vedere
CM-Net è un modello di deep learning progettato con cura specificamente per la microscopia batterica, anziché adattato da collezioni fotografiche generiche. È un tipo di rete neurale convoluzionale, una classe di programmi che eccelle nell'individuare pattern nelle immagini. CM-Net elabora ogni tessera attraverso una serie di stadi. Gli stadi iniziali cercano indizi visivi semplici come bordi e macchie; quelli più profondi combinano questi elementi in pattern più complessi che distinguono i bacilli dalle sfere e le cellule vive da quelle morte. La rete utilizza tecniche come la batch normalization, che mantiene i segnali interni ben bilanciati, e una versione limitata della sua funzione di attivazione, che evita risposte estreme che potrebbero destabilizzare l'apprendimento. Gli strati successivi condensano l'informazione estratta e prendono una decisione finale sul tipo di batterio e sullo stato cellulare.
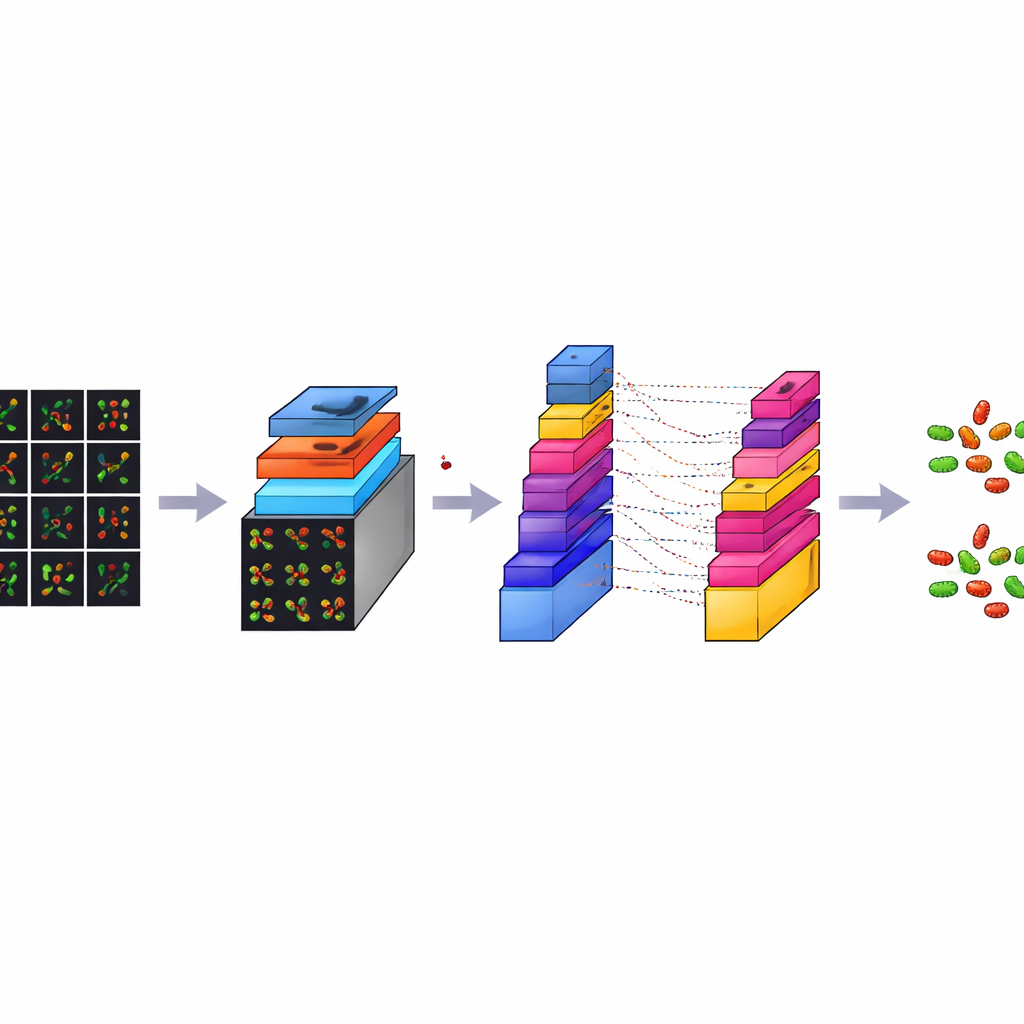
Superare modelli popolari preconfezionati
Per valutare le prestazioni di CM-Net, gli autori lo hanno addestrato e testato 30 volte, ogni volta usando una nuova suddivisione dei dati in gruppi di addestramento e test. Hanno misurato l'accuratezza, quanto spesso il modello aveva ragione nel complesso; la sensibilità, quanto bene rilevava ogni bersaglio; la specificità, quanto bene evitava falsi allarmi; e diversi altri punteggi standard. CM-Net ha raggiunto circa il 96% di accuratezza in media, con sensibilità e specificità anch'esse attorno al 96%, e un forte equilibrio tra le due classi. Richiedeva inoltre meno parametri interni e meno memoria rispetto a diversi modelli pre-addestrati largamente usati, tra cui GoogLeNet, MobileNetV2, ResNet18 e ShuffleNet, risultando comunque più veloce nell'esecuzione. Strumenti di visualizzazione hanno mostrato che CM-Net concentra la propria attenzione sui corpi batterici effettivi nelle immagini, piuttosto che su caratteristiche di sfondo casuali, sostenendo l'idea che stia imparando indizi biologicamente significativi.
Cosa significa per il lavoro di laboratorio futuro
In termini pratici, lo studio dimostra che un sistema di deep learning costruito appositamente può imparare a “leggere” immagini microscopiche complesse di batteri in modo accurato, efficiente e in linea con ciò che gli esperti umani ritengono rilevante. Per il momento, CM-Net è stato addestrato su sole due specie batteriche e su dati provenienti da un unico tipo di microscopio, quindi è necessario altro lavoro prima che possa essere impiegato come strumento diagnostico generale. Gli autori prevedono di estenderlo a più specie, diversi stati cellulari e dataset più ampi e vari. Tuttavia, i risultati suggeriscono che sistemi come CM-Net potrebbero in futuro aiutare i laboratori a identificare le infezioni più rapidamente, guidare le decisioni terapeutiche e aprire l'analisi automatizzata di esperimenti di microbiologia anche a utenti senza competenze specifiche di imaging.
Citazione: Al-Jumaili, A., Al-Jumaili, S., Alyassri, S. et al. Novel convolutional neural network for bacterial identification of confocal microscopic datasets. Sci Rep 16, 8123 (2026). https://doi.org/10.1038/s41598-026-38861-5
Parole chiave: classificazione di immagini batteriche, microscopia confocale, deep learning, reti neurali convoluzionali, diagnostica medica