Clear Sky Science · it
Il sequenziamento del genoma di Bacillus daqingensis e Alkalicoccus luteus rivela informazioni tassonomiche e meccanismi adattativi
Vivere in luoghi salati
Dai laghi salati ai suoli alcalini, alcuni microbi prosperano in condizioni che disidraterebbero e ucciderebbero la maggior parte delle altre forme di vita. Questo studio esplora il DNA di due batteri amanti del sale per comprendere come sopravvivono in ambienti estremi e per chiarire la loro collocazione nell’albero della vita. Confrontando in dettaglio i loro genomi, i ricercatori mostrano che ciò che si riteneva fossero specie batteriche distinte è in realtà lo stesso tipo di organismo, e svelano i trucchi molecolari che questi microbi utilizzano per far fronte a un forte stress salino.
Perché questi amanti del sale sono importanti
I batteri al centro di questo lavoro erano stati originariamente denominati Bacillus daqingensis e Alkalicoccus luteus. Entrambi sono stati isolati da ambienti salini e alcalini, come laghi sodici e suoli salini, dove la maggior parte delle forme di vita fa fatica. Gli scienziati sospettavano che Bacillus daqingensis potesse appartenere in realtà al genere Alkalicoccus, ma mancava la sua sequenza genomica completa, lasciando il suo status ufficiale in sospeso. Sequenziando e analizzando i genomi completi di questi microbi e confrontandoli con specie affini, gli autori si sono proposti di risolvere questo enigma tassonomico e, contemporaneamente, di capire come i membri del genere Alkalicoccus riescano a sopravvivere in condizioni così severe.
Leggere e confrontare i genomi microbici
Il team ha coltivato i batteri in laboratorio, ha estratto il loro DNA e lo ha sequenziato con metodi ad alto rendimento. Successivamente ha assemblato i milioni di piccoli frammenti di DNA in mappe genomiche quasi complete e ne ha verificato la qualità. Sia Bacillus daqingensis sia Alkalicoccus luteus si sono rivelati avere genomi di dimensioni simili, intorno a 3,4–3,5 milioni di paia di basi, con contenuti genetici quasi identici e altissima completezza. Un marcatore genetico chiave, il gene 16S rRNA, era sostanzialmente lo stesso in entrambi gli organismi: un confronto ha rilevato il 99,8 percento di identità rispetto a misurazioni di laboratorio precedenti e, cosa cruciale, le sequenze 16S dei due ceppi corrispondevano perfettamente al 100 percento l’una con l’altra.
Decifrare la sopravvivenza al sale e allo stress
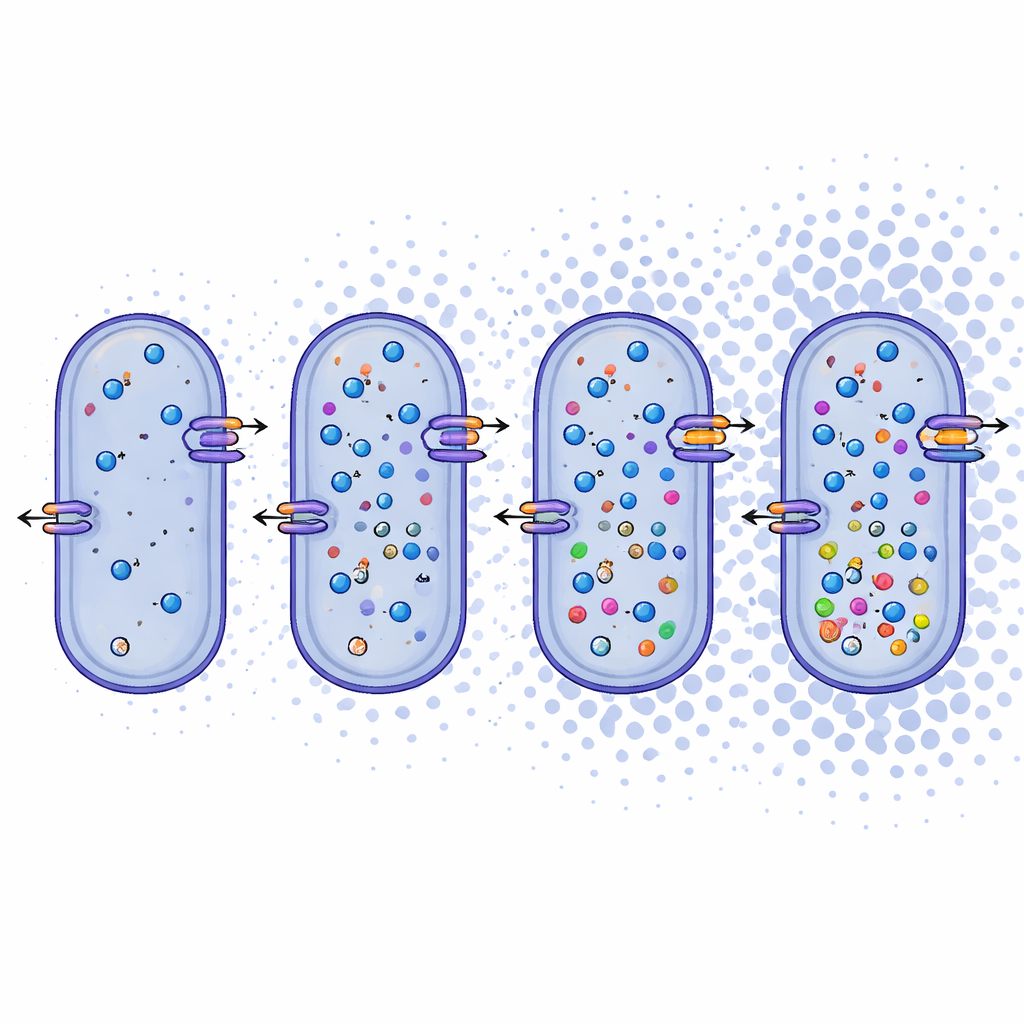
Oltre ai nomi, i ricercatori hanno esaminato cosa rivelano i genomi sui modi in cui questi microbi vivono. Hanno scoperto che Bacillus daqingensis e tutte le specie di Alkalicoccus esaminate condividono percorsi metabolici core, inclusi i normali percorsi di degradazione degli zuccheri e un ciclo modificato chiamato scissione del glicossilato (glyoxylate shunt) che aiuta a conservare il carbonio sotto stress. Più sorprendentemente, i genomi contengono un ricco arsenale per affrontare l’elevata salinità. I batteri sembrano utilizzare due tattiche complementari: sistemi “salt-in” che muovono ioni inorganici come sodio e potassio attraverso la membrana cellulare, e sistemi “salt-out” che sintetizzano o importano piccole molecole organiche, come betaina, ectoine e alcuni amminoacidi, che agiscono come ammortizzatori interni contro la disidratazione. I geni per trasportatori di ioni, antiportatori e per la biosintesi di questi soluti compatibili sono presenti in tutto il genere, indicando una risposta robusta e flessibile allo stress osmotico.
Dimostrare chi è chi
Per risolvere la questione tassonomica, gli autori hanno confrontato i genomi completi usando diversi indicatori numerici ormai standard nella sistematica microbica. L’identità nucleotidica media (ANI) misura quanto siano simili le sequenze di DNA su tutto il genoma, mentre l’identità aminoacidica media (AAI) fa lo stesso a livello proteico. Tra Bacillus daqingensis e Alkalicoccus luteus, l’ANI ha raggiunto il 98,2 percento e l’AAI il 98,5 percento—ben oltre le soglie usuali usate per definire la stessa specie e persino lo stesso genere. Alberi filogenetici costruiti a partire da molti geni, insieme al confronto dei cluster proteici condivisi, hanno mostrato che questi due ceppi si raggruppano strettamente e condividono più cluster genici tra loro che con qualsiasi altra specie di Alkalicoccus. Caratteristiche tradizionali come la forma cellulare, i profili degli acidi grassi e reazioni biochimiche chiave erano anch’esse sostanzialmente identiche tra i due.
Cosa significa per i nomi microbici
Mettendo insieme tutte le linee di evidenza, lo studio conclude che Bacillus daqingensis non rappresenta un tipo di batterio distinto. Appartiene invece al genere Alkalicoccus ed è la stessa specie di Alkalicoccus luteus, precedentemente nota come Bacillus luteus. Gli autori propongono formalmente la nuova combinazione nomenclaturale Alkalicoccus daqingensis e trattano questa denominazione, insieme al vecchio nome Bacillus, come sinonimi posteriori di Bacillus luteus/Alkalicoccus luteus. Per i non specialisti, la conclusione è che un accurato sequenziamento del genoma può rivelare quando etichette differenti indicano sostanzialmente lo stesso microbo, contribuendo a rimettere in ordine il sistema dei nomi. Allo stesso tempo, il lavoro mette in luce come questi batteri amanti del sale facciano affidamento su una combinazione di pompe ioniche e molecole protettive per sopravvivere in ambienti che altrimenti sarebbero troppo salini per la vita.
Citazione: Narsing Rao, M.P., Wang, Kk., Zhu, Ky. et al. Genome sequencing of Bacillus daqingensis and Alkalicoccus luteus reveals taxonomic insights and adaptive mechanisms. Sci Rep 16, 9720 (2026). https://doi.org/10.1038/s41598-026-38640-2
Parole chiave: batteri alofili, sequenziamento del genoma, tassonomia microbica, adattamento allo stress da sale, Alkalicoccus luteus