Clear Sky Science · it
Modifica del genoma attraverso specie di Dictyostelia consente la genetica funzionale comparativa delle amebe sociali
Come le singole cellule fanno squadra
La maggior parte del tempo le amebe sono minuscoli solitari che strisciano nel terreno nutrendosi di batteri. Tuttavia alcune di esse, chiamate amebe sociali, possono improvvisamente unirsi formando un corpo multicellulare con una primitiva “testa” e uno “stelo”. Questo stile di vita metamorfosico offre agli scienziati una rara finestra su come cellule semplici imparano a cooperare e a specializzarsi—passi chiave nell’evoluzione della vita complessa. Il nuovo studio descrive un kit per l’editing del genoma che finalmente permette ai ricercatori di sondare questi comportamenti non solo in una specie di laboratorio preferita, ma in diverse specie di amebe distanti tra loro.
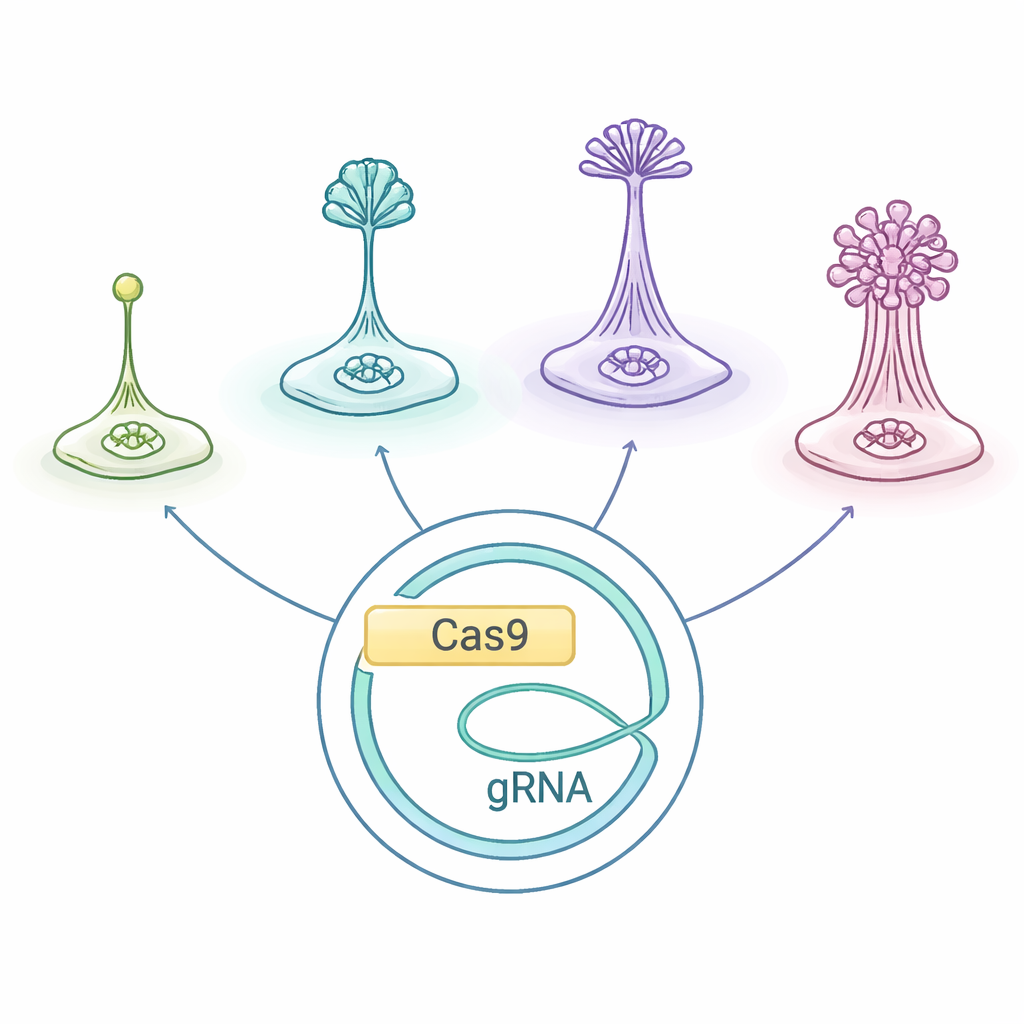
Piccole creature con grandi vite sociali
Le amebe sociali, raggruppate sotto il nome Dictyostelia, vivono come singole cellule quando il cibo è abbondante. Quando rimangono senza cibo, cominciano a emettere segnali chimici di allarme e si spostano l’una verso l’altra, raccogliendosi in un ammasso che costruisce un piccolo “corpo fruttifero”: una colonna di cellule dello stelo sacrificate che sollevano spore resistenti nell’aria. Diversi lignaggi di Dictyostelia costruiscono queste strutture in modi differenti e con insiemi diversi di tipi cellulari, rendendoli un laboratorio naturale per indagare come si evolvono i corpi multicellulari e la divisione del lavoro.
Una specie modello non bastava
Fino a oggi, quasi tutto il lavoro molecolare si è concentrato su una singola specie, Dictyostelium discoideum, perché i suoi geni sono relativamente facili da modificare. Questo ha lasciato in gran parte inesplorate oltre cento altre specie note—alcune rappresentano rami più antichi dell’albero filogenetico dei Dictyostelia. Queste specie trascurate hanno storie di vita, sistemi di segnalazione e piani corporei distinti. Per capire come la multicellularità sia cambiata nel tempo, gli scienziati devono manipolare gli stessi geni in molte di queste specie e confrontare i risultati a confronto diretto.
Portare CRISPR in una famiglia di amebe diversificata
I ricercatori hanno adattato un sistema di editing genico CRISPR/Cas9 originariamente ottimizzato per D. discoideum e hanno testato se funziona attraverso l’albero dei Dictyostelia, includendo specie a ramo precoce e specie più derivate. Hanno usato un plasmide—un piccolo pezzo circolare di DNA aggiuntivo—che porta le istruzioni per le “forbici molecolari” Cas9, l’RNA guida che indirizza Cas9 verso un gene scelto e un marcatore per la resistenza ai farmaci. Introdurre questo plasmide in diverse amebe ha permesso al gruppo di tagliare due geni ben studiati, chiamati stlA e pkaC, importanti per i segnali che coordinano l’aggregazione e la corretta formazione del corpo fruttifero. Nell’ameba del suolo Polysphondylium violaceum, questa strategia ha prodotto in modo affidabile mutanti con chiari difetti nello sviluppo, dimostrando che il sistema adattato può funzionare al di fuori del solito organismo modello.
Testare i geni attraverso le specie
Successivamente, il team è passato a specie più distantemente correlate, inclusi Heterostelium pallidum del Gruppo 2 e Cavenderia fasciculata del Gruppo 1—lignaggi che si sono separati più precocemente nell’evoluzione. Usando lo stesso design di plasmide, hanno interrotto il gene pkaC in entrambe le specie e hanno osservato che i mutanti non sono riusciti ad aggregarsi e a costruire corpi fruttiferi normali, rispecchiando i gravi difetti visti in D. discoideum. Poiché le mutazioni CRISPR generate con questo metodo non lasciano dietro cassette di selezione ingombranti, le linee risultanti erano “senza marker”. Ciò ha reso semplice reinserire una versione del gene proveniente da D. discoideum e testare se poteva sostituire la versione locale. In tutti i casi, il pkaC straniero è stato in grado di salvare la fase iniziale di aggregazione ma non la successiva modellazione di un corpo fruttifero maturo—evidenza che il repertorio di segnalazione di base è condiviso, mentre il controllo fine dei tempi e delle posizioni si è evoluto in modi specifici per specie diverse.
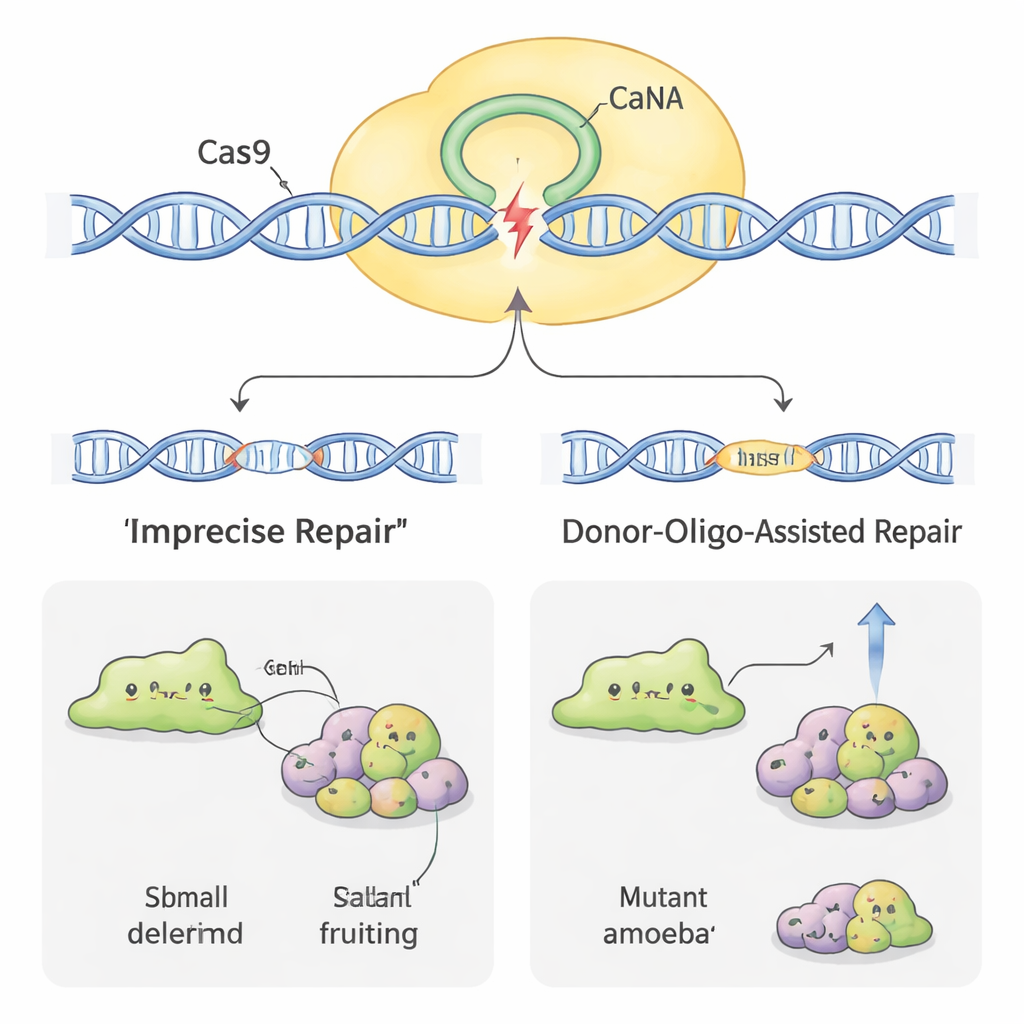
Rendere l’editing più efficiente
Non tutte le amebe hanno ceduto all’editing del genoma con la stessa facilità. In alcune specie, come H. pallidum, il tasso di successo iniziale era molto basso. Per aumentare l’efficienza, gli scienziati hanno adottato un altro trucco: aggiungere brevi frammenti di DNA “donatore” insieme al plasmide CRISPR. Questi donatori portano un piccolo tag e un segnale di stop affiancato da brevi regioni corrispondenti al gene bersaglio. Quando la cellula ripara il taglio di Cas9 usando il donatore come modello, interrompe il gene in modo riconoscibile. In D. discoideum, questo ha aumentato la quota di cloni difettosi e ha permesso al gruppo di ottenere mutanti senza l’uso di una selezione farmacologica continuativa. Nel più ostinato H. pallidum, combinare il DNA donatore con alcuni giorni di trattamento farmacologico ha aumentato i tassi di mutazione di quasi un ordine di grandezza, trasformando eventi precedentemente rari in qualcosa di vicino alla routine.
Aprire una finestra sulle origini della complessità
Per un non specialista, i dettagli sui design dei plasmidi e sui modelli di riparazione possono sembrare tecnici, ma il vantaggio è ampio: un kit CRISPR flessibile che funziona attraverso diversi rami dell’albero delle amebe sociali. Con esso, gli scienziati possono ora confrontare come lo stesso gene modella lo sviluppo in specie differenti e come cambiamenti sottili nella regolazione genica o nella struttura proteica contribuiscono a generare nuovi tipi cellulari e piani corporei. In altre parole, questo lavoro fornisce ai ricercatori gli strumenti genetici necessari per osservare, in dettaglio vivo, come l’evoluzione ha modificato organismi unicellulari per costruire società multicellulari cooperative.
Citazione: Oishi, S., Doi, S., Sekida, T. et al. Genome editing across Dictyostelia species enables comparative functional genetics of social amoebas. Sci Rep 16, 7457 (2026). https://doi.org/10.1038/s41598-026-38605-5
Parole chiave: amebe sociali, editing del genoma CRISPR, evoluzione della multicellularità, Dictyostelium, differenziazione cellulare