Clear Sky Science · it
Analisi integrata di trascrittoma e sequenziamento a singola cellula combinata con validazione sperimentale identifica biomarcatori associati alle cellule T e alla senescenza nella sepsi
Perché questa ricerca è importante per i pazienti con infezioni gravi
La sepsi è una reazione potenzialmente letale all’infezione che può trasformare una malattia o una lesione di routine in un’emergenza, spesso nel giro di poche ore. I medici non dispongono ancora di un metodo semplice e affidabile per individuare quali pazienti stanno scivolando verso l’insufficienza d’organo, e non esistono farmaci pensati specificamente per correggere il caos immunitario che la sepsi provoca. Questo studio esplora come particolari cellule immunitarie, chiamate cellule T, e l’invecchiamento di queste cellule possano guidare la sepsi — e identifica un piccolo insieme di geni che potrebbero aiutare i medici a diagnosticare la condizione prima e a orientare lo sviluppo di nuovi trattamenti.
Sepsi: quando le difese dell’organismo vanno fuori controllo
Nella sepsi il sistema immunitario esplode inizialmente in una risposta infiammatoria intensa per poi spesso virare in un pericoloso spegnimento. Le cellule T, che normalmente aiutano a eliminare le infezioni e a ricordarle, diventano meno numerose e meno efficaci nel combattere. Allo stesso tempo molte cellule immunitarie mostrano segni di “senescenza” — una sorta di invecchiamento cellulare in cui le cellule smettono di dividersi ma continuano a rilasciare segnali infiammatori. Gli autori hanno ipotizzato che se fossero riusciti a identificare geni collegati sia alle cellule T sia alla senescenza, avrebbero potuto scoprire nuovi biomarcatori in grado di rivelare chi sta sviluppando la sepsi e perché alcuni pazienti peggiorano più rapidamente di altri.
Analizzare il sangue a livello di singola cellula
Il gruppo ha combinato diversi livelli di dati provenienti da campioni di sangue di persone con e senza sepsi. Hanno prima usato dati di trascrittoma bulk (una lettura di quali geni sono attivi) per trovare quasi 10.000 geni il cui livello di espressione cambia nella sepsi. Poi, utilizzando il sequenziamento dell’RNA a singola cellula, hanno esaminato decine di migliaia di cellule ematiche individuali per identificare oltre 1.300 geni specificamente alterati nelle cellule T. Sovrapponendo questi insiemi con una lista curata di 866 geni noti per essere coinvolti nell’invecchiamento cellulare, hanno ristretto il campo a 45 candidati che si trovavano all’incrocio tra sepsi, cellule T e senescenza. 
Individuazione di quattro segnali genetici chiave
Per filtrare ulteriormente questa lista, i ricercatori hanno applicato due tecniche di apprendimento automatico che cercano le caratteristiche più informative in dati complessi. Questi approcci hanno convergono su sei geni promettenti e, quando il team ha verificato due set di dati pazienti indipendenti, quattro di essi sono emersi in modo costante: PATZ1, SIN3B, BLK e MTHFD2. Nei dati pubblici, PATZ1, SIN3B e BLK risultavano ridotti nella sepsi, mentre MTHFD2 era aumentato. In un piccolo gruppo di campioni clinici testati con un metodo sensibile chiamato RT-qPCR, i primi tre geni sono risultati nuovamente chiaramente più bassi nel sangue dei pazienti con sepsi, mentre MTHFD2 non ha mostrato una differenza netta — suggerendo che il suo ruolo potrebbe riguardare più la funzione della proteina che la quantità prodotta.
Come questi geni si collegano all’equilibrio immunitario e ai potenziali farmaci
Ulteriori analisi hanno collegato ciascun gene a percorsi biologici più ampi. PATZ1 è stato associato alla replicazione del DNA e alla segnalazione del recettore delle cellule T, processi essenziali perché le cellule T si moltiplichino e rispondano all’infezione. SIN3B è risultato collegato a un sistema di segnalazione a base lipidica che influenza la sopravvivenza cellulare e l’infiammazione. BLK, noto soprattutto nelle malattie autoimmuni, è stato associato allo sviluppo delle cellule del sangue e alle difese immunitarie intestinali, inclusa la produzione di IgA che proteggono la barriera intestinale. MTHFD2 è stato connesso alla sintesi e al ricambio delle proteine, elementi centrali per come le cellule immunitarie adattano il loro metabolismo sotto stress. Quando il team ha esaminato i modelli di “infiltrazione” delle cellule immunitarie nel sangue, livelli più alti di PATZ1 coincidevano con più cellule T CD8 e meno neutrofili, un equilibrio che potrebbe favorire un migliore controllo dell’infezione. Usando questi quattro geni, i ricercatori hanno costruito una rete neurale artificiale — un semplice modello di intelligenza artificiale — che ha distinto la sepsi dai casi non-sepsi in due dataset esterni con precisione quasi perfetta. Hanno inoltre utilizzato un database farmaco–gene e simulazioni di docking molecolare per proporre diversi composti esistenti, tra cui l’antibiotico latamoxef e le molecole emetina e diidroergotamina, come candidati che legano fortemente questi bersagli. 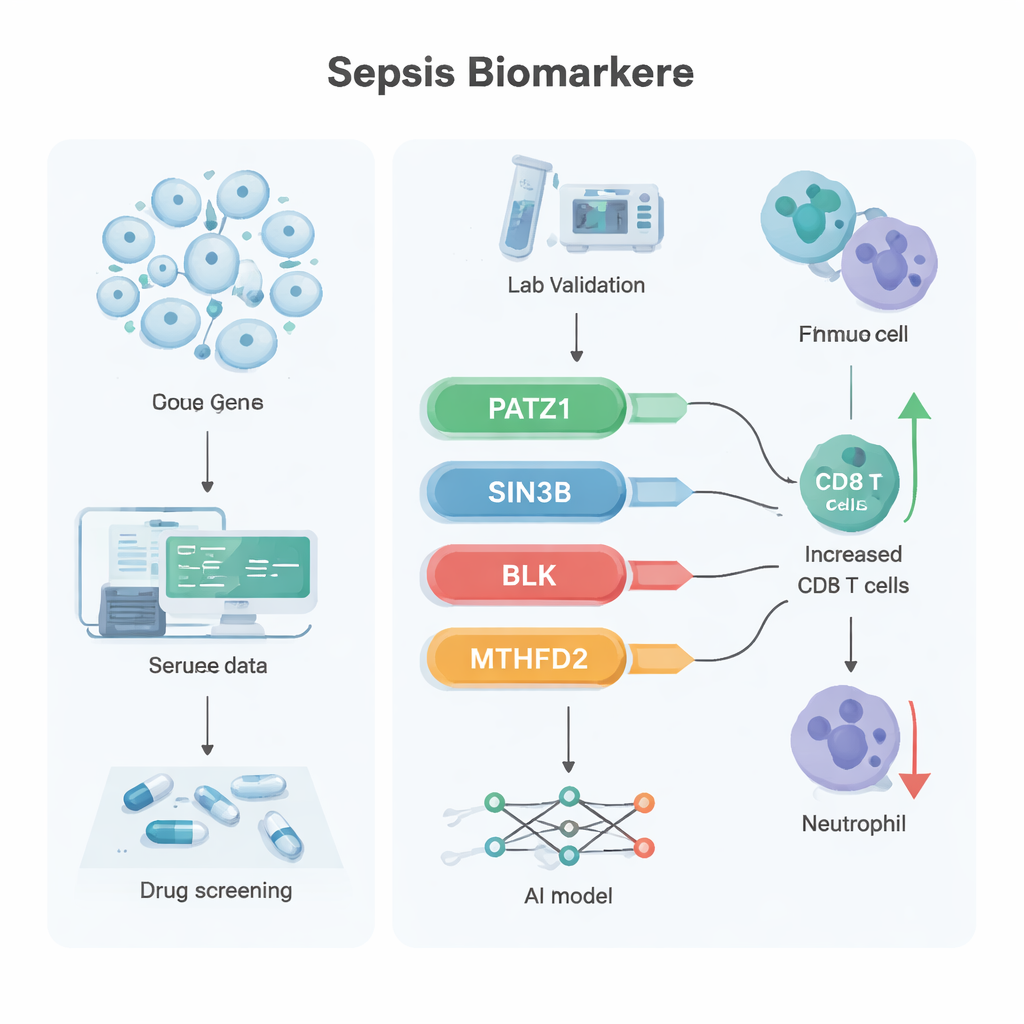
Cosa potrebbe significare per le cure future
Per il lettore non specialistico, il punto chiave è che questo studio identifica quattro geni che agiscono come segnali di allarme sulle cellule T che malfunzionano e invecchiano prematuramente durante la sepsi. Insieme, questi geni costituiscono un potenziale pannello per un esame del sangue che un giorno potrebbe aiutare i medici a diagnosticare la sepsi in modo più precoce e accurato rispetto agli strumenti attuali. Offrono anche indizi su come il metabolismo e i sistemi di riparazione del sistema immunitario si rompono, suggerendo nuove strade per farmaci mirati a ripristinare la normale funzione delle cellule T anziché limitarsi ad attenuare l’infiammazione. Sebbene siano necessari studi più ampi e esperimenti di laboratorio prima che queste scoperte possano arrivare al letto del paziente, questo lavoro traccia una strada promettente verso diagnosi e terapie della sepsi più precise e basate sulla biologia.
Citazione: Yang, K., Hu, Y., Ma, C. et al. Integrative analysis of transcriptome and single-cell sequencing combined with experimental validation identifies biomarkers associated with T cell and senescence in sepsis. Sci Rep 16, 7109 (2026). https://doi.org/10.1038/s41598-026-38559-8
Parole chiave: biomarcatori della sepsi, cellule T, senescenza immunitaria, sequenziamento a singola cellula, immunometabolismo