Clear Sky Science · it
Registrazione non rigida automatica e robusta di immagini microscopiche in sezioni seriali mediante PiCNoR
Vedere i tessuti in 3D senza perdere i dettagli
La biologia moderna spesso si basa sulla trasformazione di sottili fette di tessuto in viste 3D complete di organi e cervelli. Ma quando ogni sezione microscopica viene tagliata, colorata e acquisita, può allungarsi, lacerarsi o spostarsi. Se queste sezioni non vengono allineate correttamente, l'immagine 3D risultante può essere fuorviante. Questo articolo presenta un nuovo metodo computazionale chiamato PiCNoR che aiuta gli scienziati ad allineare tali immagini in modo più accurato e automatico, preservando così le strutture fini in ricostruzioni 3D di embrioni e cervelli.
Perché è così difficile allineare le sezioni
Per costruire una vista 3D, i ricercatori acquisiscono serie lunghe di sezioni ultra-sottili prelevate dallo stesso campione di tessuto. In teoria, ogni fetta dovrebbe combaciare perfettamente con quella precedente, come carte in un mazzo ordinato. Nella realtà, ogni sezione può deformarsi in modo leggermente diverso durante il taglio e la colorazione. I colori possono variare, le parti possono allungarsi e le caratteristiche possono spostarsi. I metodi tradizionali “rigidi” assumono che ogni intera sezione si limiti a traslare o ruotare, cosa spesso insufficiente. Esistono metodi più flessibili, “elastici”, ma possono essere lenti, richiedere una messa a punto esperta o dipendere fortemente dalla luminosità dell'immagine, che può cambiare da una sezione all'altra.
Un nuovo approccio: pezzi locali che lavorano insieme
PiCNoR adotta una visuale diversa e più locale del problema. Invece di cercare di deformare un'intera immagine in una sola volta, divide prima ogni sezione in molte regioni basate sulla distribuzione delle caratteristiche nell'immagine. All'interno di ciascuna regione, il metodo trova punti corrispondenti tra due sezioni adiacenti usando rilevatori di caratteristiche robusti e stima come quella regione debba ruotare e traslare per allinearsi. Questi movimenti locali vengono poi verificati nella plausibilità e combinati delicatamente, in modo che ogni pixel nella sezione riceva un movimento che fonde in modo graduale le informazioni dalle regioni circostanti. Il risultato è un allineamento flessibile, “non rigido”, che tuttavia si comporta in modo controllato e realistico.
Lasciare che siano i dati a scegliere la giusta complessità
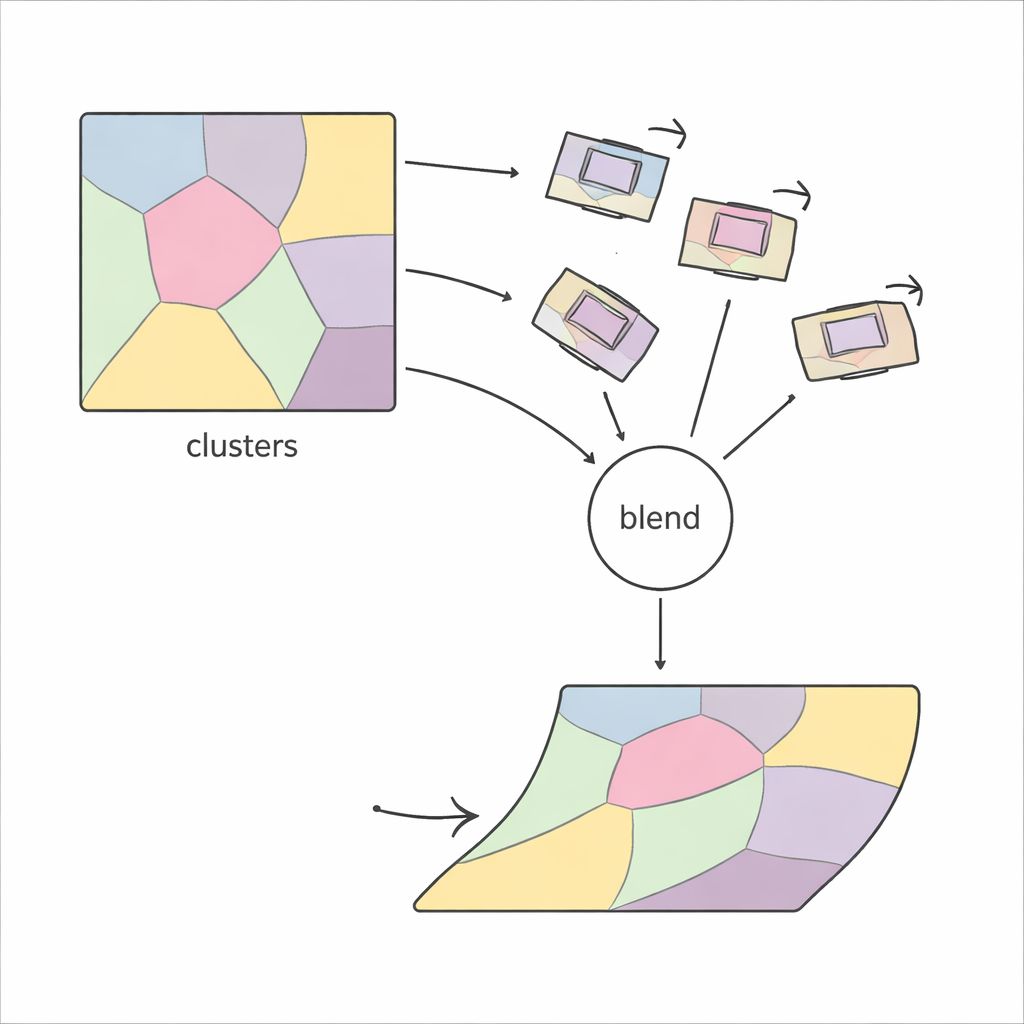
Una sfida chiave in qualsiasi metodo basato su regioni è decidere quante regioni utilizzare: troppe poche e il metodo non può correggere deformazioni sottili; troppe e diventa instabile e lento. Gli approcci precedenti spesso si basavano sul tentativo e l'errore, controllando ripetutamente la qualità visiva del risultato. PiCNoR evita questa messa a punto manuale usando uno strumento statistico chiamato criterio di informazione bayesiano, che bilancia automaticamente la quantità di dettaglio contro il rischio di overfitting. In pratica, ciò significa che l'algoritmo può decidere da solo quante regioni sono necessarie per un dato dataset, senza supervisione umana, risparmiando tempo e riducendo i bias.
Mantenere i risultati affidabili ed efficienti
Non tutti i movimenti locali stimati sono affidabili: alcuni possono essere distorti dal rumore o da corrispondenze errate. PiCNoR affronta questo rappresentando ogni regione come un nodo in un grafo, dove le regioni vicine si influenzano a vicenda. I movimenti che appaiono irrealistici in termini di rotazione o traslazione vengono sostituiti da una media pesata dei movimenti più affidabili dei vicini. Una rappresentazione matematica compatta aiuta a combinare questi spostamenti in modo efficiente. Infine, il movimento di ciascun pixel viene calcolato come una fusione ponderata dalle probabilità dei movimenti regionali, garantendo che le transizioni tra le regioni restino morbide, senza brusche pieghe o sovrapposizioni nel tessuto.
Dimostrare l'efficacia su dati biologici reali
Gli autori hanno testato PiCNoR su tre dataset molto diversi: sezioni di embrioni umani dalla collezione di Kyoto, uno stack di microscopia elettronica di un cordone nervoso della mosca della frutta e un nuovo stack da microscopia ottica dell'ippocampo di un ratto. In questi esempi, PiCNoR ha prodotto costantemente una sovrapposizione migliore tra le sezioni rispetto ai metodi rigidi standard e ad ampiamente usati metodi non rigidi. Ha mantenuto la continuità di strutture delicate nelle viste 3D ed ha evitato le distorsioni esagerate talvolta osservate con altri strumenti. È importante che lo abbia fatto usando meno regioni locali rispetto ad alcuni concorrenti e con costi computazionali ancora praticabili per pile di grandi dimensioni.
Cosa significa per la microscopia 3D futura
Per i non specialisti, la conclusione è che PiCNoR offre un modo più affidabile per trasformare pile di immagini microscopiche 2D in ricostruzioni 3D fedeli. Scegliendo automaticamente quanto dettaglio richiede l'allineamento e proteggendo contro correzioni locali errate, preserva le forme reali dei tessuti mantenendo il tempo di elaborazione gestibile. Questo rende più facile per biologi e patologi fidarsi di ciò che vedono in 3D, sia che studino lo sviluppo embrionale sia la disposizione delle cellule cerebrali, e pone le basi per analisi più accurate e automatizzate di dataset microscopici complessi.
Citazione: Adi, P.M., Shabani, H. & Mansouri, M. Automated and robust nonrigid registration of serial section microscopic images using PiCNoR. Sci Rep 16, 7559 (2026). https://doi.org/10.1038/s41598-026-38548-x
Parole chiave: microscopia 3D, registrazione di immagini, imaging cerebrale, istologia, allineamento non rigido