Clear Sky Science · it
Profilo del microbiota intestinale e del resistoma di espatriati svizzeri in Africa rivelato dalla metagenomica Nanopore
Perché i tuoi microbi intestinali cambiano quando vivi all’estero
Molte persone trascorrono mesi o anni all’estero, spesso in luoghi dove i batteri resistenti agli antibiotici sono comuni. Questo studio pone una domanda semplice ma importante: quando gli espatriati svizzeri vivono in paesi africani con un alto carico di infezioni multiresistenti, la comunità microbica e il repertorio di geni di resistenza nel loro intestino cambiano in modi che potrebbero influire sulla loro salute e sulla diffusione più ampia della resistenza antimicrobica?
La comunità invisibile dentro di noi
I nostri intestini ospitano trilioni di microrganismi, per lo più batteri, che aiutano a digerire il cibo, addestrano il sistema immunitario e tengono sotto controllo i germi dannosi. Accanto a questi microbi utili si trova il “resistoma” – la raccolta di geni che rendono i batteri resistenti agli antibiotici. Anche le persone sane portano molti di questi geni. Quando individui si trasferiscono o viaggiano in regioni dove i batteri multiresistenti sono diffusi, possono acquisire silenziosamente nuovi geni di resistenza e gli elementi di DNA mobili, chiamati plasmidi, che li diffondono. Capire come avviene questo processo è fondamentale per il controllo della resistenza antibiotica a livello globale.
Confronto tra espatriati in Europa e in Africa
I ricercatori hanno analizzato campioni di feci provenienti da 72 espatriati svizzeri in buona salute al loro rientro in Svizzera: 39 avevano vissuto in paesi africani e 33 in altri paesi europei. Invece di coltivare i batteri in laboratorio, hanno usato una tecnologia di sequenziamento del DNA a letture lunghe chiamata Nanopore shotgun metagenomics, che legge tutto il materiale genetico presente in un campione contemporaneamente. Questo ha permesso di mappare quali batteri erano presenti (il microbiota) e quali geni di resistenza agli antibiotici e plasmidi essi portavano (il resistoma e il plasmidoma). Ogni campione è stato sequenziato due volte per maggiore affidabilità e sono stati impiegati software sofisticati per identificare i gruppi batterici e i geni di resistenza e per assemblare frammenti genomici più lunghi a partire dal DNA misto.
Sorprendente stabilità dei microbi intestinali
Nonostante un maggior numero di persone nel gruppo Africa fosse risultata colonizzata da batteri intestinali multiresistenti nei test precedenti basati su coltura, la composizione complessiva del loro microbiota intestinale appariva sorprendentemente simile a quella degli espatriati che avevano vissuto in Europa. Le misure di diversità – quante diverse tipologie di batteri erano presenti e quanto uniformemente erano rappresentate – non differivano per continente, e le analisi statistiche non mostravano un raggruppamento chiaro dei campioni Africa rispetto a Europa. In entrambi i gruppi, residenti intestinali familiari come Blautia, Faecalibacterium e Bacteroides dominavano, suggerendo che una residenza prolungata all’estero non necessariamente rivoluziona la comunità batterica di base negli adulti sani.
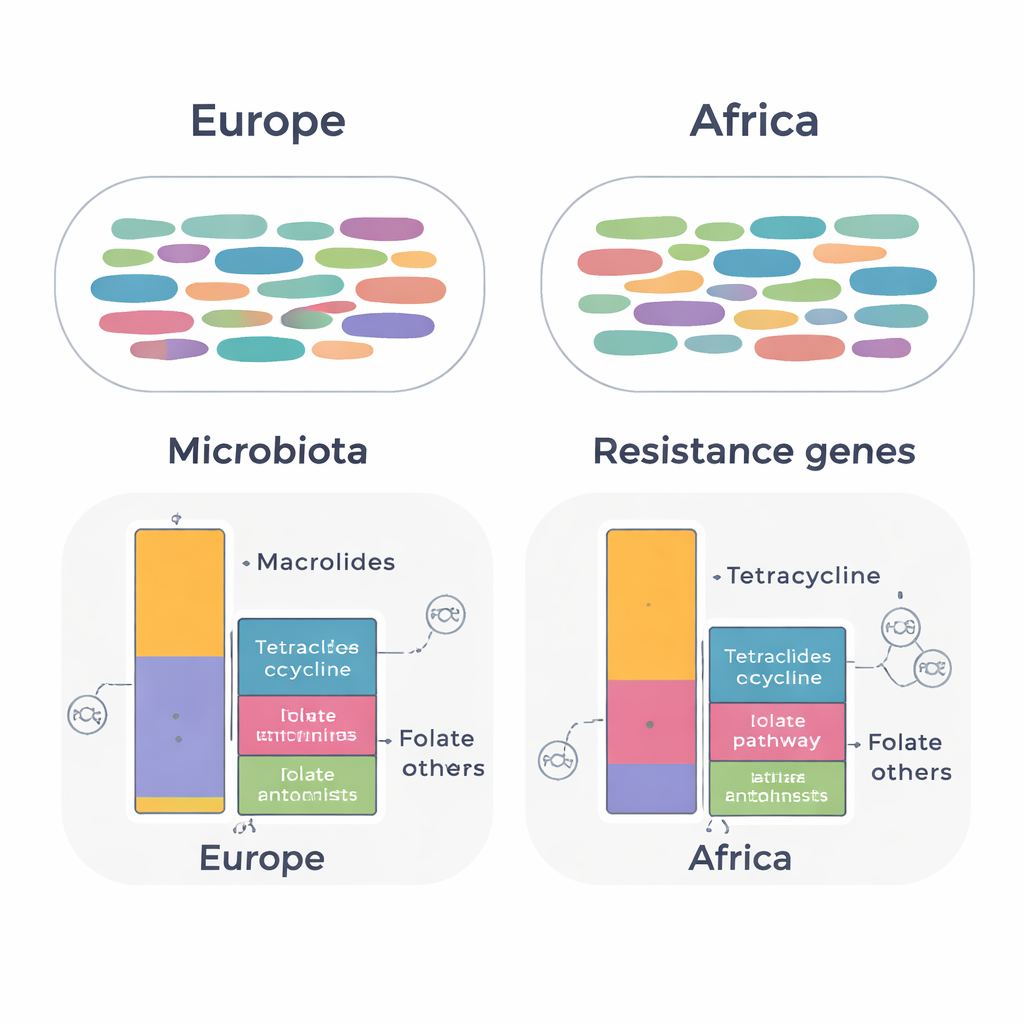
I geni di resistenza e il DNA mobile raccontano una storia diversa
Quando il team si è concentrato sui geni di resistenza, sono emerse differenze più sottili ma importanti. In tutti i campioni hanno identificato 134 geni di resistenza distinti appartenenti a 14 classi di antibiotici. Il quadro totale dei geni era in larga misura simile tra i continenti, ma gli espatriati che avevano vissuto in Africa presentavano livelli più elevati di geni che proteggono i batteri da tetracicline e da farmaci che prendono di mira la via dell’acido folico (come trimetoprim‑sulfametossazolo). Al contrario, gli espatriati dai paesi europei mostravano livelli più alti di geni che conferiscono resistenza ai macrolidi. Molti di questi geni erano collegati a batteri intestinali comuni, inclusi Ruminococcoides, Bifidobacterium e Bacteroides. Geni di rilevanza clinica, come blaCTX-M-15, che può inattivare cefalosporine avanzate, sono stati rilevati in Escherichia coli in entrambi i gruppi.
I plasmidi come navette globali della resistenza
Lo studio ha inoltre tracciato i plasmidi – piccoli cerchi di DNA spesso trasferibili che spostano geni di resistenza tra batteri e attraverso gli ambienti. Grazie alle letture di DNA lunghe, i ricercatori sono talvolta riusciti a vedere geni di resistenza e marcatori di “replicone” plasmidico sullo stesso frammento di DNA assemblato, confermando che viaggiano insieme. Hanno identificato 46 diversi tipi di plasmidi, alcuni unici per ciascun continente e altri condivisi. In modo notevole, certi plasmidi portavano più geni di resistenza e somigliavano a plasmidi noti provenienti da fonti umane, animali, alimentari e di acque reflue in diverse parti del mondo. Un tipo di plasmide comunemente associato a Enterococcus e riscontrato in pollo e acque reflue era più frequente nelle feci degli espatriati in Africa, sottolineando come cibo, animali e ambiente possano contribuire a ciò che finisce nel nostro intestino.
Cosa significa per la vita quotidiana e la salute pubblica
Per il lettore non specialista, il messaggio principale è che vivere in una regione ad alto rischio non sembra radicalmente cambiare quali batteri intestinali ospiti, ma può modificare la composizione dei geni di resistenza agli antibiotici e degli elementi di DNA mobili che li diffondono. Questi cambiamenti nascosti, influenzati in parte dai modelli locali di uso degli antibiotici, possono avere rilevanza per infezioni future e per il modo in cui i caratteri di resistenza si muovono tra persone, animali e ambiente. Il lavoro mostra anche che il sequenziamento portatile a letture lunghe può fungere da strumento di allerta precoce, rivelando come geni di resistenza e plasmidi circolino in viaggiatori ed espatriati sani prima che provochino malattia.
Citazione: Campos-Madueno, E.I., Aldeia, C. & Endimiani, A. Gut microbiota and resistome profiles of Swiss expatriates in Africa revealed by Nanopore metagenomics. Sci Rep 16, 7016 (2026). https://doi.org/10.1038/s41598-026-38302-3
Parole chiave: microbioma intestinale, resistenza agli antibiotici, espatriati, plasmidi, metagenomica