Clear Sky Science · it
Il primo genoma mitocondriale per Sterictiphorinae (Hymenoptera: Argidae) e approfondimenti sulla filogenia degli Argidae
Perché contano questi piccoli mangia‑foglie
Le sawfly della famiglia Argidae possono sembrare insignificanti, ma le loro giovani forme, simili a bruchi, possono spogliare di foglie colture e foreste, rendendole importanti fitofagi agricoli. Tuttavia, a livello del loro DNA, in particolare nei mitocondri che producono energia all’interno delle cellule, questi insetti sono stati poco studiati. Questo articolo riporta il primo genoma mitocondriale completo per una sawfly coreana, Sterictiphora koreana, e lo usa per esplorare come questa famiglia, soggetta a infestazioni, si sia evoluta nell’arco di oltre 160 milioni di anni.
Uno sguardo all’interno delle “centrali” di una sawfly
Gli autori hanno decodificato tutto il DNA mitocondriale di una singola femmina di S. koreana. Come nella maggior parte degli animali, questo piccolo genoma della “centrale” è un anello di DNA che porta 37 geni che aiutano la cellula a ricavare energia. In S. koreana l’anello è insolitamente lungo—circa 17.900 basi rispetto alle ~15.600 in tre specie affini di Argidae—principalmente perché una regione non codificante ricca di A e T si è espansa. Nonostante questa differenza di dimensione, l’organizzazione complessiva dei geni corrisponde da vicino al modello tipico osservato in altre sawfly, con la maggior parte dei geni su un filamento di DNA e un gruppo minore sull’altro filamento, e i geni per gli RNA di trasporto che si ripiegano in classiche forme a trifoglio con alcune particolarità.

Pattern di basi che suggeriscono legami familiari
Il DNA mitocondriale è fortemente sbilanciato verso le basi A e T in molti insetti, e queste sawfly non fanno eccezione. Tutte e quattro le specie di Argidae studiate hanno genomi composti per circa l’80 percento da A o T, ma l’equilibrio non è identico. Le tre specie note in precedenza, tutte della sottofamiglia Arginae, sono ancora più ricche di A+T rispetto a S. koreana, che appartiene alla sottofamiglia Sterictiphorinae. Sottigliezze negli squilibri di frequenza tra A e T, e tra G e C, differiscono tra specie e tra parti del genoma. Una specie, Arge aurora, inverte persino alcuni di questi squilibri, distinguendosi dai parenti. I ricercatori mostrano anche che alcuni amminoacidi, come leucina, isoleucina, metionina e fenilalanina, sono codificati più spesso di altri, riflettendo come questo alfabeto sbilanciato influenzi le “parole” genetiche usate dalle sawfly.
Geni rimescolati e codice che cambia lentamente
Pur essendo il progetto mitocondriale complessivo conservativo, piccoli geni chiamati tRNA tendono a spostarsi e le loro nuove posizioni possono segnare rami importanti dell’albero filogenetico delle sawfly. Nelle specie Arginae, un gene tRNA (trnW) è saltato in una nuova posizione vicino alla regione ricca di A+T. In S. koreana, un diverso insieme di tRNA (trnK, trnD, trnI e trnM) è stato riorganizzato secondo uno schema coerente. Questi riarrangiamenti distinti probabilmente segnalano che le due sottofamiglie sono lignaggi separati. Quando il team ha esaminato la velocità con cui i geni codificanti proteine accumulano cambiamenti, ha rilevato che la maggior parte delle variazioni viene eliminata dalla selezione naturale, un modello chiamato selezione purificatrice. Un gene in particolare, cox1, cambia particolarmente lentamente, confermando la sua utilità come “barcode” di DNA per distinguere le specie.
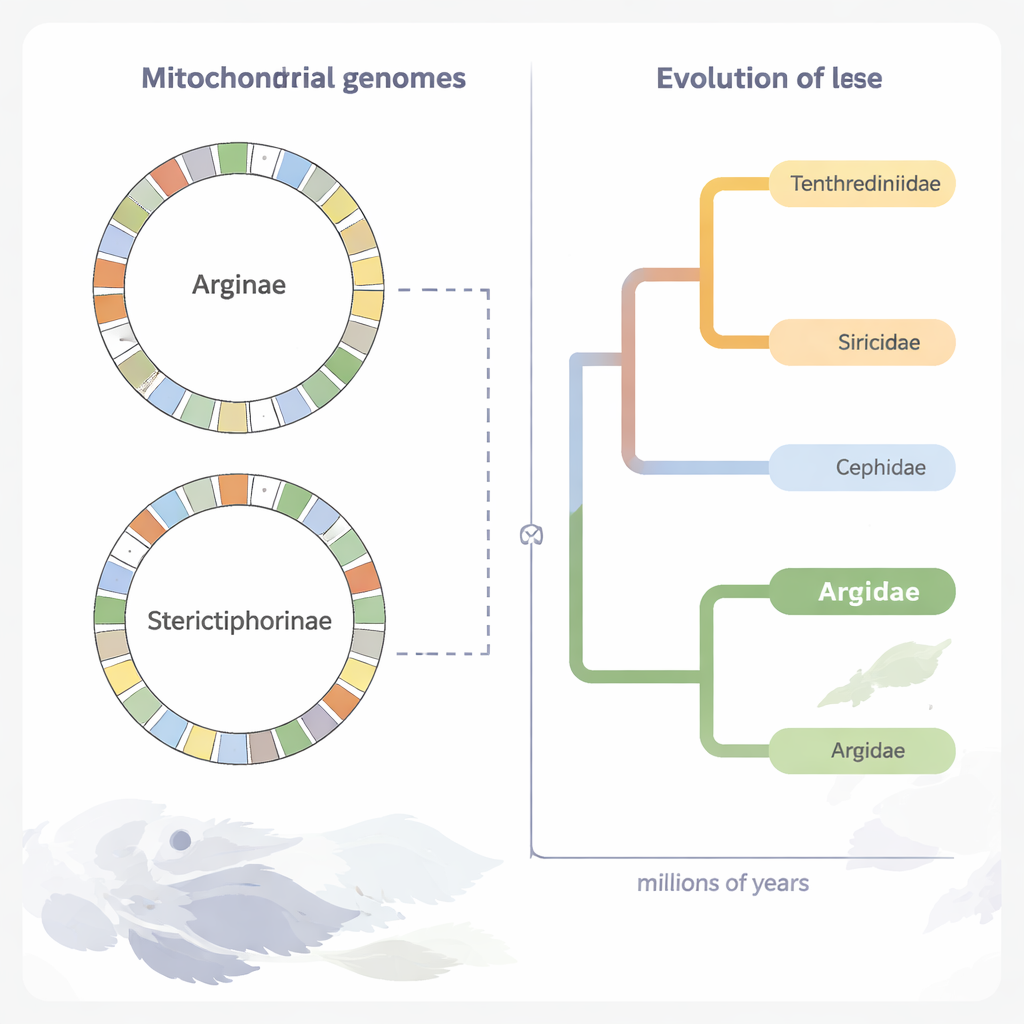
Ricostruire l’antico albero familiare delle sawfly
Utilizzando le porzioni codificanti proteine del DNA mitocondriale di 70 specie di sawfly, i ricercatori hanno ricostruito un dettagliato albero evolutivo. Le loro analisi confermano che gli Argidae formano un gruppo naturale e sono strettamente alleati con un’altra famiglia, i Pergidae, all’interno della più ampia superfamiglia delle sawfly Tenthredinoidea. Integrando le evidenze fossili, stimano che il clade Argidae–Pergidae si sia separato dalle altre famiglie di sawfly circa 206 milioni di anni fa, e che gli Argidae stessi siano comparsi approssimativamente 166 milioni di anni fa, nel Giurassico medio. Le due principali sottofamiglie di Argidae, Arginae e Sterictiphorinae, sembrano essersi separate nel Cretaceo inferiore, circa 126 milioni di anni fa, un periodo in cui anche le angiosperme si stavano diversificando.
Cosa significa per la scienza e il controllo dei parassiti
Questo primo genoma mitocondriale da Sterictiphorinae colma una lacuna importante nella nostra visione genetica degli Argidae. Dimostra che caratteristiche di dettaglio—come la lunghezza del genoma, l’ordine dei geni e gli squilibri nelle basi—possono distinguere in modo affidabile gruppi principali all’interno di questa famiglia di fitofagi e aiutarne l’ancoraggio nel più ampio albero filogenetico delle sawfly. Per i non specialisti, il messaggio è che leggendo e confrontando i piccoli anelli di DNA nelle centrali cellulari degli insetti, gli scienziati possono ricostruire le relazioni tra le sawfly che danneggiano le foglie, stimare quando sono emersi i loro lignaggi e, in ultima analisi, costruire un quadro più solido per identificare le specie e comprendere la loro diffusione nelle colture e nelle foreste.
Citazione: Park, B., Hwang, U.W. The first mitochondrial genome for Sterictiphorinae (Hymenoptera: Argidae) and insights into argid phylogeny. Sci Rep 16, 7154 (2026). https://doi.org/10.1038/s41598-026-38021-9
Parole chiave: evoluzione delle sawfly, genoma mitocondriale, filogenia degli insetti, fitofagi di foreste e colture, DNA barcoding