Clear Sky Science · it
Un quadro adattivo alla struttura del genoma per la stima dell’endogamia basata su ROH in Penaeus vannamei
Perché gli alberi genealogici dei gamberi contano per il tuo piatto
Le moderne aziende di allevamento di gamberi forniscono gran parte dei prodotti ittici consumati nel mondo, ma allevare ripetutamente le stesse linee familiari può erodere silenziosamente la loro salute. Quando si accoppiano parenti stretti, geni nocivi nascosti possono ritrovarsi in coppia, riducendo crescita, sopravvivenza e resistenza alle malattie. Questo studio pone una domanda apparentemente semplice ma dalle grandi implicazioni per l’acquacoltura globale: come possiamo misurare l’endogamia nei gamberi d’allevamento con sufficiente precisione per mantenere gli stock sani e produttivi?
Impronte genetiche nascoste dell’endogamia
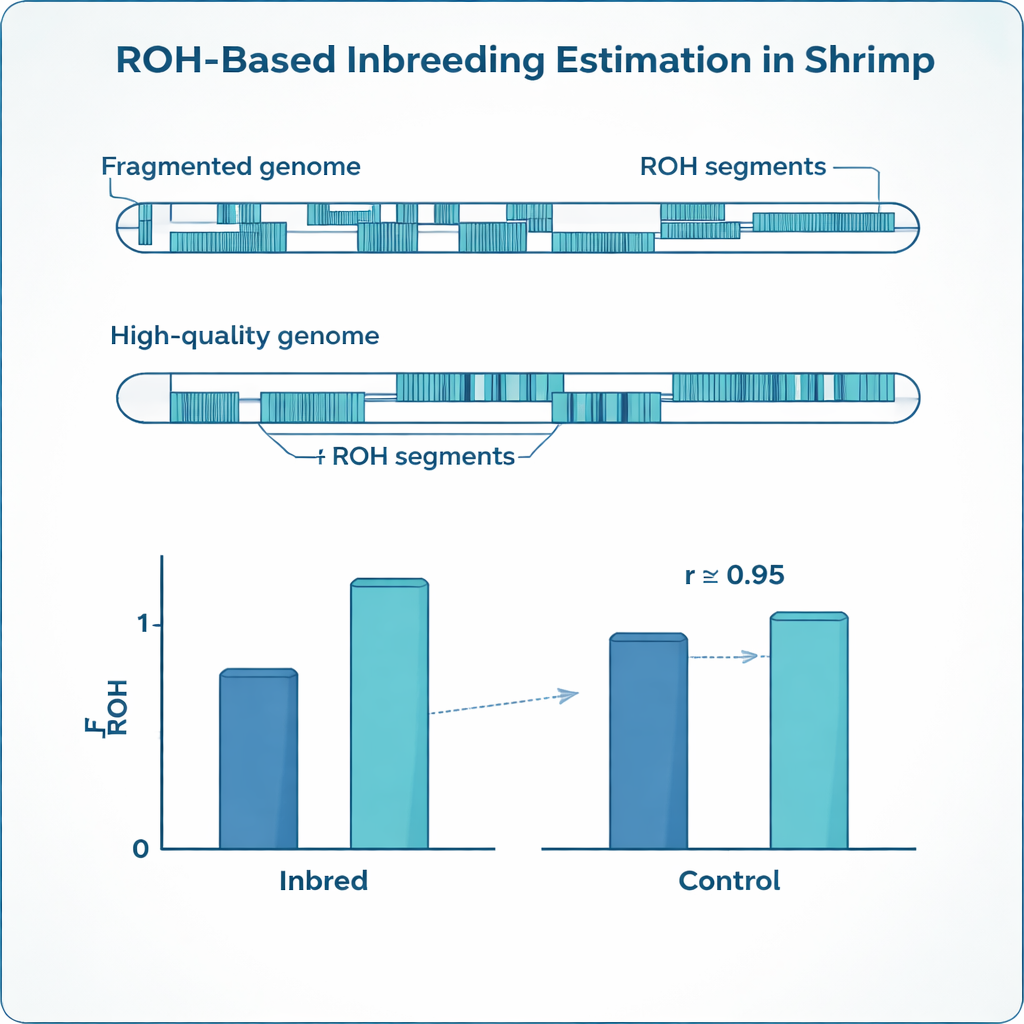
L’endogamia lascia impronte riconoscibili nel DNA. Invece di portare due versioni leggermente diverse di molti geni, gli animali endogami tendono ad avere lunghi tratti in cui entrambe le copie sono identiche. I genetisti chiamano questi tratti “run di omozigosi”, o ROH. Sommando quanto del genoma di un animale rientra in questi run, i ricercatori possono stimare il suo livello di endogamia in modo più preciso rispetto al semplice tracciamento degli alberi genealogici cartacei, spesso incompleti o affetti da errori. Questa misura basata sui ROH, nota come FROH, è diventata standard in bovini, suini e altri animali da reddito, ma i genomi dei gamberi pongono sfide speciali che rendono inaffidabili i metodi pronti all’uso.
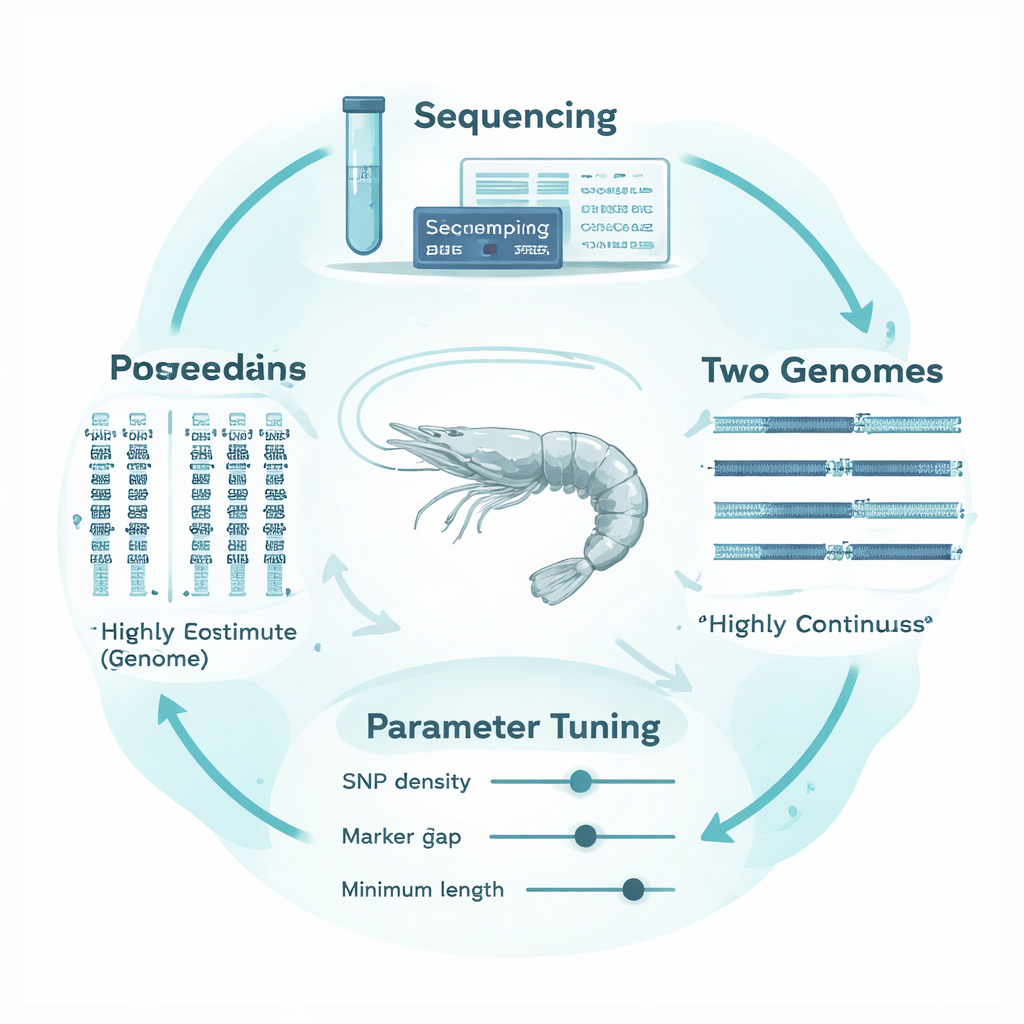
Perché i genomi dei gamberi sono particolarmente insidiosi
Il gambero bianco (Penaeus vannamei), il gambero più coltivato al mondo, possiede genomi altamente frammentati e complessi. Invece di lunghe sequenze cromosomiche continue, molte mappe genomiche disponibili sono spezzate in migliaia di frammenti più piccoli, separati da gap e regioni ripetitive. I marcatori genetici sono distribuiti in modo irregolare su questo mosaico e la specie mostra un’elevata diversità genetica. Metodi e parametri software originariamente tarati per genomi di mammiferi ben assemblati possono quindi interpretare i gap tecnici come vere interruzioni dei ROH, o confondere brevi somiglianze di background con veri segnali di endogamia. Il risultato è un alto rischio di stime errate del grado di endogamia di un gambero.
Costruire un metro di misura consapevole della struttura genomica
Per risolvere questo problema, gli autori hanno progettato un quadro «adattivo alla struttura del genoma» che adatta l’analisi dei ROH alle particolarità del DNA dei gamberi. Hanno creato tredici famiglie di gamberi altamente endogame tramite accoppiamenti controllati, poi hanno sequenziato profondamente i genomi di cinque di queste famiglie e dei loro genitori. Elemento cruciale, hanno allineato gli stessi dati di sequenziamento a due genomi di riferimento molto diversi: una vecchia assembly frammentata e una versione più recente e altamente continua. Utilizzando lo strumento di analisi comune PLINK, hanno testato sistematicamente come otto impostazioni chiave influenzassero le chiamate dei ROH, concentrandosi su tre parametri particolarmente sensibili alla struttura genomica: la densità richiesta dei marcatori, la dimensione massima del gap consentito tra marcatori all’interno di un run e la lunghezza minima perché un run venga conteggiato. Hanno costruito finestre genomiche empiriche, non sovrapposte, per monitorare la spaziatura locale dei marcatori e i dati mancanti, e hanno utilizzato la “copertura genomica” di queste finestre, insieme alla stabilità di FROH e delle lunghezze dei ROH, come guide obiettive per scegliere soglie sensate.
Diverse manopole, stesso quadro di endogamia
Le impostazioni ottimizzate si sono rivelate molto diverse per i due genomi di riferimento. Il genoma frammentato richiedeva una densità di marcatori molto più elevata, gap consentiti più brevi e lunghezze minime di run inferiori rispetto al genoma di alta qualità, per evitare che veri ROH venissero spezzati in molti pezzi piccoli. Tuttavia, dopo aver tarato questi parametri separatamente, le stime di endogamia ottenute con entrambi i riferimenti sono converse: il FROH medio nei gamberi inbred era circa 0,24 in entrambi i casi, in stretto accordo con il valore atteso dagli accoppiamenti pianificati e fortemente concordante tra loro. Allo stesso tempo, il genoma più continuo ha rivelato segmenti di ROH meno numerosi ma molto più lunghi, mentre la mappa frammentata ne spezzava molti in tratti corti. Lo studio ha inoltre messo in luce differenze marcate tra fratelli completi: anche all’interno della stessa famiglia, i livelli di endogamia variavano ampiamente, un aspetto che semplici registri genealogici non riescono a catturare.
Strumenti più affilati per stock di gamberi più sani
Per i non specialisti, il messaggio principale è semplice: misurare l’endogamia dal DNA può essere altamente accurato nei gamberi d’allevamento, ma solo se il metodo rispetta la struttura sottostante del genoma. Fornendo una ricetta pratica per tarare l’analisi dei ROH ai genomi frammentati dei crostacei, questo lavoro permette agli allevatori di monitorare l’endogamia individuo per individuo, invece di affidarsi a schede familiari imperfette. Ciò può aiutare a progettare piani di accoppiamento che mantengano la diversità genetica pur migliorando crescita e resilienza, sostenendo un’allevamento di gamberi più sostenibile e offrendo un modello applicabile ad altre specie di acquacoltura che affrontano simili ostacoli genomici.
Citazione: Zou, X., Zhou, H., Liu, M. et al. A genome-structure adaptive framework for ROH-based inbreeding estimation in Penaeus vannamei. Sci Rep 16, 6769 (2026). https://doi.org/10.1038/s41598-026-37622-8
Parole chiave: allevamento di gamberi, endogamia, selezione genomica, run di omozigosi, genetica dell’acquacoltura