Clear Sky Science · it
Probabilità che due alleli siano identici per stato in loci non osservati previste dai loci osservati nelle popolazioni bovine
Perché gli alberi genealogici dei bovini non sono più sufficienti
La moderna selezione dei bovini si basa sulla scelta dei riproduttori giusti per ottenere animali sani e produttivi. Per più di un secolo gli allevatori hanno utilizzato gli alberi genealogici, o pedigree, per evitare consanguineità stretta che può compromettere fertilità, crescita e resistenza alle malattie. Tuttavia i pedigree sono spesso incompleti o contengono errori e forniscono solo una stima di quanto gli animali possano essere simili. Questo studio pone una domanda semplice ma importante: se osserviamo direttamente il DNA invece dei registri cartacei, possiamo vedere meglio quali animali sono veramente simili dal punto di vista genetico, anche nelle porzioni del genoma che non abbiamo misurato?
Alla ricerca di gemelli genetici nascosti nel genoma
I ricercatori si sono concentrati su un concetto chiamato "identity by state" (IBS). Due basi del DNA nella stessa posizione sono IBS se appaiono identiche, indipendentemente dal fatto che provengano o meno da un antenato comune recente. In pratica, gli allevatori genotipizzano gli animali solo su un sottoinsieme di marcatori del DNA chiamati SNP, lasciando molte posizioni non osservate. Il gruppo voleva capire quanto bene diversi metodi, basati sugli SNP osservati, potessero prevedere la probabilità che animali condividano alleli corrispondenti in questi siti non osservati — in sostanza, quanto riusciamo a vedere la somiglianza genetica nascosta nel genoma.
Allevamenti simulati e dati reali di bovini
Per testare questo aspetto, gli autori hanno utilizzato due tipi di dati. Innanzitutto hanno simulato popolazioni bovine per molte generazioni, controllando fattori come la dimensione efficace della popolazione (quanti animali contribuiscono efficacemente ai geni) e se la selezione dei riproduttori fosse casuale o basata sui valori genetici stimati per un tratto. Hanno creato grandi set di SNP e poi li hanno suddivisi in marcatori “osservati” e marcatori “non osservati”. Il set non osservato ha fornito i valori di riferimento: le probabilità vere di corrispondenza degli alleli lungo il genoma. In secondo luogo, hanno ripetuto le analisi con genotipi reali ad alta densità di bovini Japanese Black, una razza da carne importante, usando un sottoinsieme di SNP come marcatori osservati e un altro sottoinsieme come punti di riferimento non osservati.
Confrontare i punteggi da pedigree con le misure basate sul DNA
Lo studio ha valutato molteplici misure basate sul DNA di consanguineità all’interno degli animali e di parentela genetica tra animali. Alcuni metodi consideravano ogni SNP indipendentemente, mentre altri raggruppavano SNP vicini in tratti più lunghi di DNA identico chiamati run di omozigosità o modellavano segmenti ereditati da un antenato comune. Per ciascuna misura il team ha calcolato quanto fortemente le sue previsioni corrispondessero ai valori di riferimento IBS nei siti non osservati, usando la correlazione come indice di accuratezza. Hanno inoltre confrontato queste misure basate sul DNA con i coefficienti di consanguineità e di relazione tradizionali derivati dai pedigree, ampiamente usati nei programmi di allevamento.
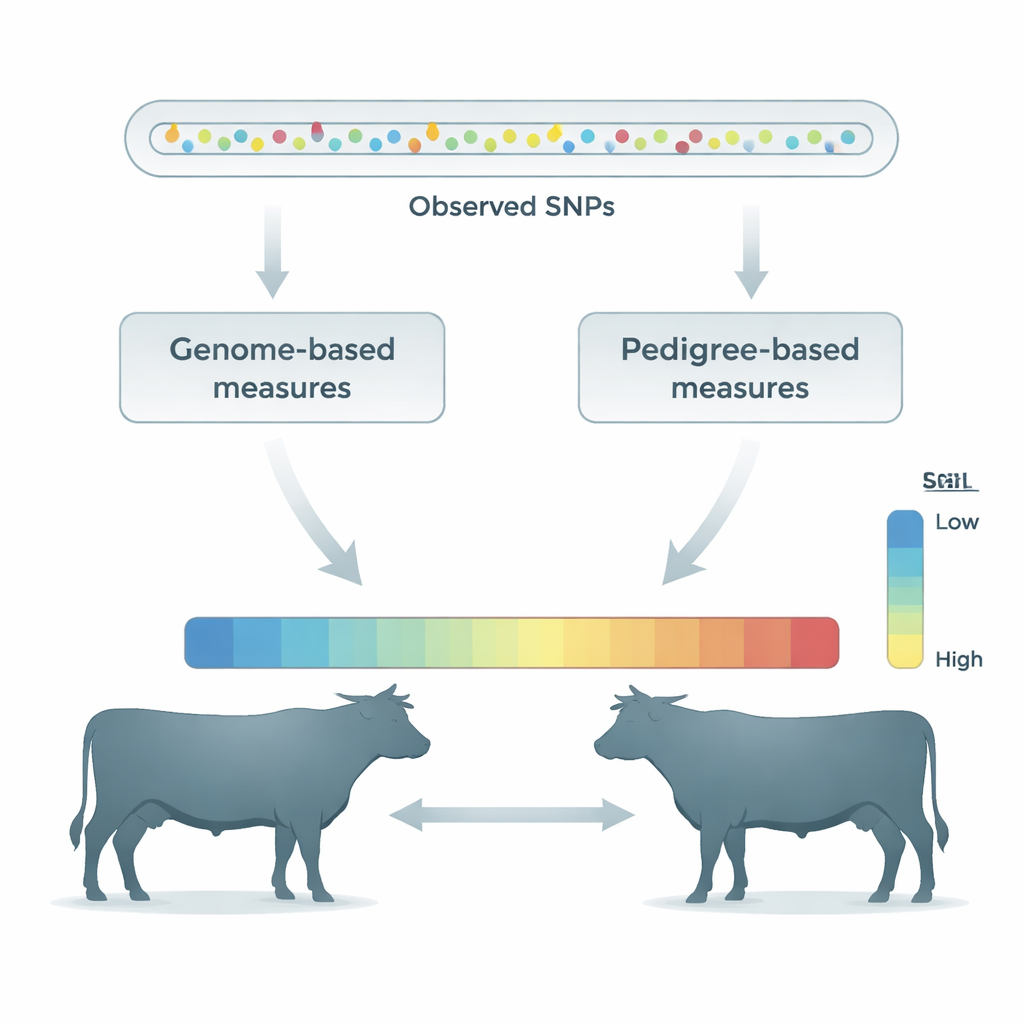
I marcatori del DNA superano chiaramente i pedigree
Sia nelle popolazioni simulate sia in quelle reali, le misure basate sul genoma hanno costantemente superato i metodi basati sui pedigree nella previsione dell’IBS nascosto. In particolare, i metodi che trattavano ogni SNP come se entrambi gli alleli avessero iniziato a una frequenza di 0,5 in una popolazione ancestrale — indicati nell’articolo come FGRMV2 e fGRMV2 — hanno mostrato un’accuratezza molto elevata. Anche le misure basate su lunghi segmenti omozigoti si sono comportate bene, specialmente quelle che modellavano segmenti ereditati da un antenato comune (FHBD) o che contavano run di omozigosità relativamente brevi su tutto il genoma (FROH4all e il corrispondente tra animali fSEG4). Queste misure top-performing sono rimaste accurate anche quando venivano applicate pressioni di selezione per molte generazioni e hanno seguito l’aumento della consanguineità in modo più affidabile rispetto alle stime basate sui pedigree.
Cosa significa per gli allevatori e la sicurezza alimentare
Per un non specialista, la conclusione è che guardare direttamente il DNA fornisce un quadro molto più chiaro di quanto i bovini siano realmente simili geneticamente rispetto a fare affidamento solo sugli alberi genealogici. Utilizzando indicatori specifici basati sul genoma, gli allevatori possono monitorare meglio la consanguineità nascosta, proteggere la diversità genetica e progettare accoppiamenti che bilancino il progresso genetico con la salute a lungo termine del gregge. Questo è importante non solo per evitare oggi la depressione da consanguineità, ma anche per mantenere sufficiente variabilità genetica per adattare i bovini a sfide future, come nuove malattie o un clima in cambiamento.
Citazione: Nagai, R., Honda, T., Satoh, M. et al. Probabilities of two alleles being identity by state at unobserved loci predicted by observed loci in cattle populations. Sci Rep 16, 7454 (2026). https://doi.org/10.1038/s41598-026-37530-x
Parole chiave: genetica bovina, consanguineità, selezione genomica, diversità genetica, marcatori SNP