Clear Sky Science · it
Quantificazione e tracciamento rapidi senza apprendimento degli organoidi con OrganoSeg2
Perché i tessuti coltivati in laboratorio in miniatura sono importanti
Nei laboratori di tutto il mondo gli scienziati coltivano ora versioni in miniatura di tessuti umani chiamate organoidi. Questi piccoli ammassi 3D di cellule possono riprodurre il comportamento di organi o tumori reali, diventando strumenti potenti per studiare le malattie e testare trattamenti. Ma esiste un collo di bottiglia: i ricercatori possono raccogliere migliaia di immagini microscopiche a bassa ingrandimento di organoidi, eppure faticano a misurare come ciascuno cresce, cambia forma o muore nel tempo. Questo articolo presenta OrganoSeg2, una versione riprogettata del software che trasforma quelle immagini in scala di grigi in misure ricche e affidabili su ogni singolo organoide—senza necessità di addestramento di intelligenza artificiale o configurazioni di imaging costose.
Un nuovo modo di interpretare immagini microscopiche affollate
Gli organoidi vengono solitamente immaginati con microscopi a campo chiaro semplici, che li mostrano come macchie tenui e sovrapposte. Delineare automaticamente ciascuna macchia—"segmentare" l’immagine—è molto più difficile di quanto sembri, specialmente quando i laboratori usano formati di coltura, illuminazione o lenti diversi. Gli autori avevano precedentemente creato OrganoSeg, un programma capace di gestire la segmentazione di base ma che rallentava e diventava scomodo con collezioni di immagini che raggiungevano le centinaia. Con OrganoSeg2 hanno ricostruito il software da zero con un’interfaccia moderna, semplificato il codice interno e reso visibili diverse impostazioni nascoste in modo che gli utenti possano regolare come il programma separa gli organoidi dallo sfondo, divide i vicini a contatto e ignora gli artefatti ai bordi dell’immagine. L’app ora conserva queste scelte come metadata in modo che le analisi siano riproducibili e condivisibili.
Velocizzare il lavoro senza sacrificare i dettagli
Oltre alla flessibilità, il team si è concentrato molto sulla velocità e sull’esperienza utente. Nelle versioni precedenti il software calcolava automaticamente ogni possibile misura per ogni organoide, anche quando erano necessarie solo poche misure. OrganoSeg2 invece calcola solo ciò che l’utente seleziona e riorganizza i calcoli correlati in modo che i passaggi che richiedono tempo siano riutilizzati in modo efficiente. Riduce anche la quantità di informazioni disegnate a schermo, mostra le etichette solo quando necessario e aggiunge scorciatoie da tastiera e strumenti interattivi per rimuovere rapidamente detriti o oggetti non organoidi. Queste scelte progettuali riducono le operazioni comuni—come segmentare immagini, visualizzare contorni ed esportare dati—di circa un fattore dieci, rendendo pratico gestire immagini grandi a mosaico e lunghi esperimenti in time‑lapse su un computer ordinario.
Superare i rivali high‑tech sui dati reali
Per testare l’efficacia di OrganoSeg2, gli autori lo hanno confrontato con diversi altri strumenti di segmentazione, inclusi sistemi di deep learning che richiedono addestramento su esempi etichettati manualmente. Hanno assemblato set di immagini provenienti da sei fonti diverse—come organoidi di colon, polmone, pancreas, cervello e mammella, oltre a corpi embrioidi—dove esperti umani avevano già tracciato i confini degli organoidi. Usando un punteggio di accuratezza standard che misura quanto i contorni automatici si sovrappongono a quelli manuali, OrganoSeg2 ha pareggiato o superato strumenti specializzati nella maggior parte dei dataset e si è nettamente distinto nelle immagini di carcinoma mammario difficili, piene di materiale estraneo e organoidi dalle forme insolite. In particolare, OrganoSeg2 ha raggiunto queste prestazioni senza necessitare di decine di migliaia di esempi di addestramento ed è risultato almeno altrettanto veloce quanto i concorrenti, anche quelli basati sull’intelligenza artificiale.
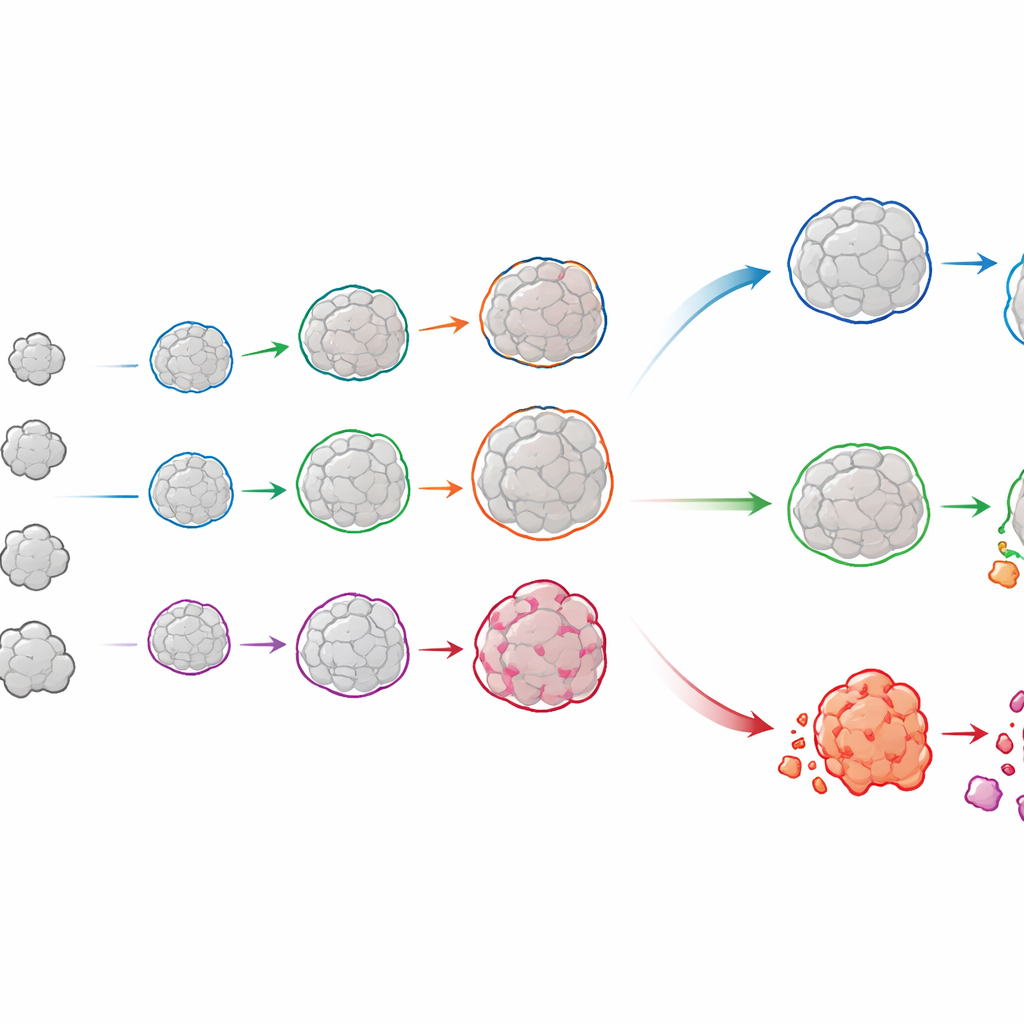
Seguire la storia di vita di ciascun organoide
OrganoSeg2 fa più che delineare gli organoidi in singoli istantanee. Può allineare immagini scattate in giorni diversi e collegare lo stesso organoide nel tempo, costruendo una storia di crescita per ciascuno. Quando gli autori hanno applicato questo a organoidi coltivati direttamente da tumori luminali della mammella dei pazienti, hanno osservato che gli organoidi individuali raramente crescevano in modo uniforme; molti rallentavano o raggiungevano un plateau, rispecchiando come i tumori reali contengano un mix di regioni a crescita rapida e lenta. Adattando queste traiettorie a un semplice modello di crescita, il team ha potuto quantificare sia la velocità di espansione di ciascun organoide sia quanto grande fosse probabile che diventasse. Confrontando questi schemi tra pazienti è emerso che tumori con crescita complessiva simile possono nascondere mescolanze molto diverse di comportamenti sottostanti—differenze che potrebbero avere importanza nella previsione della risposta al trattamento.
Osservare le cellule tumorali vivere e morire sotto le radiazioni
Il software collega anche immagini a campo chiaro con coloranti fluorescenti che segnalano lo stato di salute cellulare. In nuovi esperimenti gli autori hanno esposto organoidi di carcinoma mammario a dosi di radiazione simili a quelle cliniche e li hanno colorati con un marcatore per cellule vive che si illumina durante la morte programmata, insieme a un secondo colorante che rileva le cellule morte al tempo finale. OrganoSeg2 ha usato l’immagine a campo chiaro per definire la forma dell’organodio e poi ha misurato i segnali fluorescenti all’interno di ciascuno nel corso di molti giorni. Questo ha permesso al team di tracciare, organoide per organoide, quando la radiazione ha innescato la morte e con quale intensità. Gli organoidi di alcuni pazienti hanno risposto minimamente, mentre altri hanno mostrato alta sensibilità anche a dosi inferiori, sottolineando quanto possano variare le risposte tumorali.
Cosa significa per la ricerca e la cura futura
Nel complesso, il lavoro dimostra che un’elaborazione delle immagini accurata e regolabile può eguagliare o superare metodi complessi di deep learning per un’ampia gamma di immagini di organoidi, restando trasparente e facile da sintonizzare. OrganoSeg2 trasforma semplici filmati a bassa ingrandimento di organoidi in registri dettagliati di come ciascun piccolo tessuto cresce e sopravvive in diverse condizioni. Per i ricercatori di base offre un modo robusto per analizzare la diversità nascosta nelle colture di organoidi. Per gli studi sul cancro in particolare apre la strada all’uso di organoidi derivati da pazienti non solo per test farmacologici binari, ma per misure ricche e risolte nel tempo di crescita e morte cellulare che un giorno potrebbero aiutare a personalizzare i trattamenti con maggiore precisione.
Citazione: Wells, C.J., Labban, N., Showalter, S.L. et al. Fast learning-free organoid quantification and tracking with OrganoSeg2. Sci Rep 16, 7928 (2026). https://doi.org/10.1038/s41598-026-37526-7
Parole chiave: organoidi, analisi delle immagini, ricerca sul cancro, microscopia, risposta alle radiazioni