Clear Sky Science · it
Scoprire i potenziali MTA, i geni candidati e le reti regolatorie di microRNA coinvolte nella tolleranza allo stress da salinità indotta in Aegilops tauschii iraniana
Perché i suoli salini minacciano il nostro pane quotidiano
Con il cambiamento climatico che amplifica la siccità e l’acqua per irrigazione che diventa più salina, vaste aree agricole stanno diventando troppo salate per il grano comune. Questo riguarda chiunque dipenda dal pane come alimento fondamentale. Lo studio qui riassunto guarda a un’erba selvatica, Aegilops tauschii, diretto antenato del frumento tenero moderno, per svelare gli strumenti genetici nascosti — e le piccole molecole regolatorie — che aiutano le piante a far fronte a condizioni salmastre. Mappando queste difese naturali, i ricercatori sperano di fornire ai selezionatori nuovi modi per sviluppare varietà di frumento che restino produttive anche quando il terreno diventa salino.
Un cugino selvatico del frumento come risorsa nascosta
Aegilops tauschii cresce naturalmente nella Mezzaluna Fertile, compresa l’Iran, dove si è adattata per migliaia di anni a ambienti aridi, severi e spesso salini. Questa specie ha donato la porzione “D” del genoma che il frumento tenero moderno porta oggi. Poiché le varietà ad alto rendimento odierne sono state selezionate a partire da una base genetica relativamente ristretta, spesso mancano dell’intera gamma di tratti di tolleranza allo stress che esistono ancora nei loro parenti selvatici. Gli autori hanno raccolto 77 ecotipi iraniani di Aegilops tauschii e li hanno coltivati sia in condizioni normali sia salate allo stadio di piantina, misurando caratteristiche come lunghezza delle radici e dei germogli, peso fresco e secco, e area di foglie e radici. La salinità ha ridotto nettamente tutte queste caratteristiche, confermando che livelli elevati di sale sono dannosi per le piante giovani.
Leggere le impronte del DNA della tolleranza alla salinità
Per capire perché alcune piante selvatiche sopportavano meglio il sale rispetto ad altre, il team ha utilizzato marcatori DNA — brevi sequenze facilmente misurabili sparse nel genoma che funzionano come codici a barre per i geni vicini. Usando una combinazione di marcatori “casuali” e marcatori semi-casuali RAMP, hanno analizzato centinaia di bande di DNA e valutato quanto fosse realmente diversificata la collezione. Hanno riscontrato alti livelli di variazione genetica, con alcuni sistemi di marcatori, come ISJ9 e OPE03-Xgwm44-7DF, particolarmente efficaci nel distinguere un ecotipo dall’altro. Questa ricca diversità significa che Aegilops tauschii iraniana conserva molte varianti genetiche uniche a cui i miglioratori possono attingere. Collegando statisticamente specifiche bande di DNA ai tratti delle piantine sotto stress salino, i ricercatori hanno identificato 115 associazioni marcatore-tratto, indicando regioni genomiche che influenzano quanto bene si sviluppano radici, germogli e foglie in ambienti salini.
Da marcatori a geni operativi per la difesa dallo stress
Trovare un marcatore utile è solo il primo passo; gli autori si sono quindi chiesti quali geni effettivi si trovino vicino a quei marcatori e potrebbero essere responsabili. Utilizzando il genoma di riferimento del grano, hanno esplorato 500.000 paia di basi attorno a ciascun marcatore associato e scoperto 254 geni candidati. Molti di questi geni sono stati confermati indipendentemente da grandi dataset di RNA-seq che mostrano l’aumento o la diminuzione della loro attività quando le piante affrontano stress ambientali, inclusi freddo, calore, carenze nutritive e malattie. I geni candidati risultavano arricchiti in ruoli legati alle risposte di difesa e alla protezione da danni termici e ossidativi. Diversi codificano proteine come recettori di resistenza alle malattie, chaperoni da shock termico e proteine simili a taumatina e osmotina, che aiutano a stabilizzare le cellule quando il sale provoca perdita d’acqua e accumulo di specie reattive dell’ossigeno dannose. L’analisi dei percorsi ha evidenziato il metabolismo del glutatione, un sistema chimico centrale che le piante usano per disintossicare i prodotti derivati dallo stress.
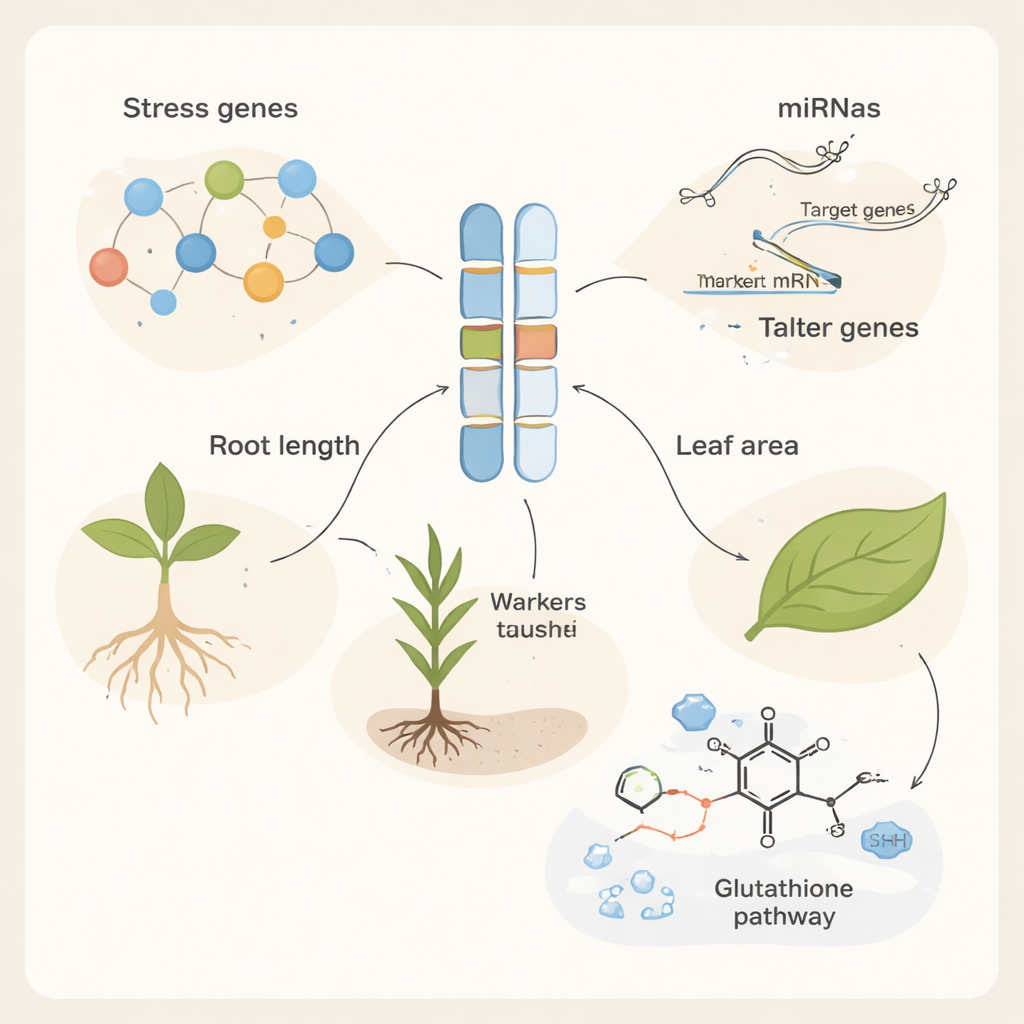
Piccoli interruttori RNA che raffinamano le risposte allo stress
I geni non agiscono da soli; sono controllati da microRNA, molecole di RNA molto corte che possono spegnere o attenuare l’attività genica. I ricercatori hanno previsto quali microRNA del grano potrebbero prendere di mira i loro geni candidati e hanno individuato 107 microRNA distinti che formano fitte reti regolatorie. Molti di questi piccoli regolatori erano già noti per rispondere a siccità, calore, metalli o salinità. Per esempio, microRNA specifici precedentemente associati alla tolleranza al sale, alla tolleranza al calore o alla “memoria dello stress” sono risultati controllare geni chiave di difesa e disintossicazione identificati in questo studio. Alcuni geni erano bersagliati da più microRNA, suggerendo che le piante sovrappongono diversi interruttori regolatori per regolare finemente la loro risposta con l’aumentare o la diminuzione dello stress.
Portare la resilienza selvatica nei campi degli agricoltori
Complessivamente, il catalogo di marcatori DNA diversificati, 254 geni candidati e 107 microRNA regolatori offre una mappa per migliorare le prestazioni del frumento su suoli salini. I miglioratori possono trasformare i marcatori più informativi in semplici test di laboratorio per selezionare rapidamente grandi numeri di piante alla ricerca di tratti di tolleranza al sale nascosti, una strategia nota come selezione assistita da marcatori. Sul lungo periodo, i geni più promettenti e i loro microRNA regolatori potrebbero essere introdotti deliberatamente o modificati nelle varietà sensibili per rafforzarne le difese naturali. Sebbene lo studio richieda ancora validazione sperimentale in piante vive sotto salinità, mostra chiaramente che il parente selvatico Aegilops tauschii possiede potenti strumenti genetici che, se usati con attenzione, possono aiutare a proteggere i raccolti di grano man mano che la salinità e le pressioni climatiche aumentano.
Citazione: Sabouri, H., Nikkhah, N., Kazerani, B. et al. Uncovering the potential MTAs, candidate genes and microRNAs regulatory networks involved in salinity stress tolerance triggered in Iranian Aegilops tauschii. Sci Rep 16, 6877 (2026). https://doi.org/10.1038/s41598-026-37365-6
Parole chiave: tolleranza alla salinità, miglioramento del grano, Aegilops tauschii, geni responsivi allo stress, microRNA vegetali