Clear Sky Science · it
Un framework tri-omico e di machine learning identifica biomarcatori prognostici e firme metaboliche nella sepsi
Perché questo è importante per le persone con infezioni gravi
La sepsi è una reazione potenzialmente letale a un’infezione che può mandare il sistema immunitario in sovraattivazione e causare il cedimento degli organi. I medici sanno che individuare la sepsi precocemente e adattare il trattamento a ciascun paziente può salvare vite, ma gli esami del sangue attuali sono strumenti grossolani: spesso dicono poco su chi migliorerà e chi è a rischio più elevato. Questo studio utilizza una potente combinazione di tre tipi di misurazioni molecolari e il machine learning moderno per cercare segnali d’allarme più precisi nel sangue dei pazienti con sepsi.
Osservare il sangue attraverso tre prospettive diverse
Invece di concentrarsi su un solo tipo di molecola, i ricercatori hanno profilato gli stessi pazienti in tre modi contemporaneamente. Hanno misurato quali geni erano attivati o spenti (trascrittomica), quali proteine erano effettivamente presenti e attive (proteomica) e quali piccoli metaboliti circolavano (metabolomica). Hanno raccolto campioni di sangue da 21 pazienti con sepsi e 10 volontari sani e hanno usato statistiche avanzate per capire come questi tre livelli cambiassero insieme nella malattia. Questa visione “tri-omica” aiuta a superare un problema chiave: nella sepsi l’attività genica e i livelli proteici possono disaccoppiarsi, quindi guardare solo un livello può essere fuorviante.
Addestrare gli algoritmi a individuare pattern ad alto rischio
Da migliaia di geni e proteine, il gruppo ha prima utilizzato un metodo di rete per trovare gruppi che si muovessero insieme nella sepsi. Hanno poi incrociato quei gruppi con le proteine che differivano nettamente tra pazienti e controlli sani, ottenendo 32 candidati solidi. Per restringere ulteriormente la lista hanno utilizzato il machine learning, impiegando due algoritmi complementari per eliminare segnali più deboli e mantenere solo quelli più informativi. Testando come i geni rimasti si correlavano con la sopravvivenza in un ampio dataset pubblico sulla sepsi, due geni sono emersi in modo evidente: TPR ed ERN1. I pazienti con livelli più elevati di TPR tendevano a sopravvivere più a lungo, mentre livelli più alti di ERN1 erano associati a esiti peggiori.
Collegare le cellule immunitarie al metabolismo alterato
Lo studio non si è fermato a geni e proteine. Analizzando migliaia di metaboliti nel sangue dei pazienti, i ricercatori hanno identificato 136 piccole molecole che seguivano da vicino TPR ed ERN1. Molte appartenevano a vie metaboliche che gestiscono i lipidi di membrana e gli acidi grassi, elementi chiave per la segnalazione delle cellule immunitarie e la diffusione dell’infiammazione. Contemporaneamente, un’analisi a singola cellula — che esamina le cellule immunitarie del sangue una per una invece di mescolarle — ha mostrato che TPR ed ERN1 sono particolarmente attivi in monociti, macrofagi e cellule natural killer. Nel complesso, questi risultati suggeriscono che i due marcatori si trovano al crocevia tra le cellule che combattono le infezioni e il modo in cui tali cellule utilizzano e rimodellano lipidi ed energia durante la sepsi.
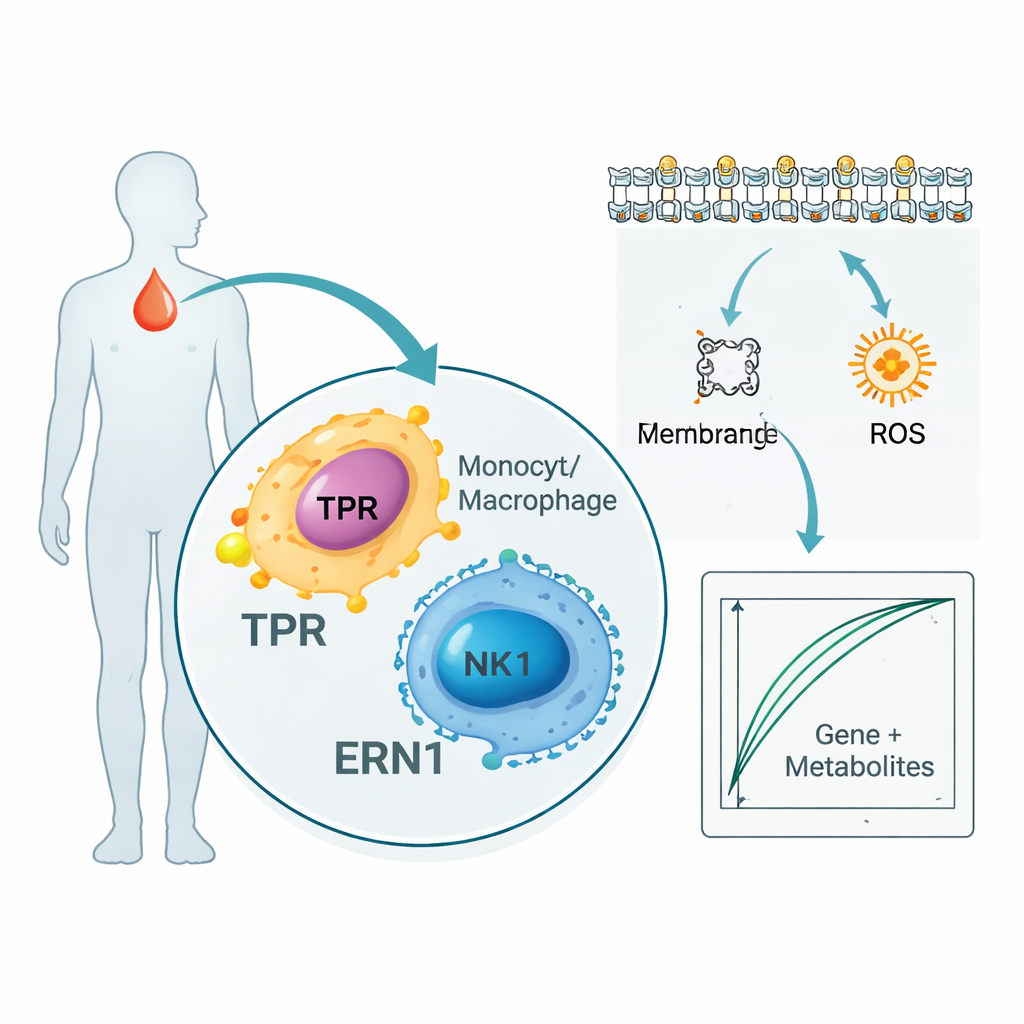
Costruire un test del sangue proof‑of‑concept
Per esplorare come queste scoperte potrebbero tradursi in pratica, gli autori hanno combinato i due geni con cinque dei metaboliti più informativi per addestrare semplici modelli computazionali in grado di distinguere i pazienti con sepsi dai soggetti sani. Nel loro piccolo dataset interno, queste firme combinate “gene-plus-metabolite” riuscivano quasi perfettamente a identificare chi aveva la sepsi. I ricercatori hanno inoltre consultato grandi database pubblici che collegano proteine plasmatiche a rischio di malattia in decine di migliaia di persone e hanno trovato che i livelli proteici di TPR ed ERN1 erano costantemente associati a condizioni correlate alla sepsi, fornendo un ulteriore livello di supporto. Rimane comunque il fatto che gli autori sottolineano: questi modelli sono strumenti in fase iniziale pensati per generare ipotesi, non test pronti per l’uso clinico al letto del paziente.
Composti vegetali come indizi iniziali, non cure
In un passo finale, il gruppo ha indagato se qualche molecola naturale potesse influenzare TPR o ERN1. Hanno consultato un database specializzato di quasi 500 composti purificati provenienti dalla medicina tradizionale cinese, ciascuno con il proprio profilo di attività genica. Diversi composti sembravano modulare fortemente questi due geni in cellule coltivate in laboratorio, suggerendo che un giorno potrebbero aiutare i ricercatori a sondare la biologia della sepsi o a progettare nuovi farmaci. Tuttavia questi risultati derivano solo da corrispondenze computazionali: non dimostrano che tali sostanze siano sicure o efficaci per le persone con sepsi.
Cosa ci dice davvero questo lavoro
Questo studio fornisce più una mappa dettagliata che una soluzione definitiva. Intrecciando tre livelli molecolari, dati a singola cellula e machine learning, gli autori mettono in luce TPR ed ERN1 — e i cambiamenti metabolici a essi connessi — come segnali promettenti di come il sistema immunitario e il metabolismo si sbilanciano nella sepsi. Per il pubblico generale, il messaggio chiave è che la sepsi non è una singola malattia ma un pattern in continua evoluzione di stati immunitari e metabolici, e che test del sangue più intelligenti potrebbero un giorno aiutare i medici a capire in quale stato si trovi un paziente e ad adattare di conseguenza il trattamento. Prima che ciò avvenga, questi segnali preliminari devono essere testati e confermati in gruppi di pazienti molto più ampi e diversi e in esperimenti di laboratorio che possano provare causalità ed effetto.
Citazione: Li, X., Ke, G., Hu, Y. et al. A tri-omics and machine learning framework identifies prognostic biomarkers and metabolic signatures in sepsis. Sci Rep 16, 6648 (2026). https://doi.org/10.1038/s41598-026-37342-z
Parole chiave: biomarcatori della sepsi, multi-omica, machine learning in medicina, metabolismo immunitario, diagnostica di precisione