Clear Sky Science · it
Analisi comparativa del cariotipo di undici specie di Lilium dalla Cina mediante FISH con sonde oligonucleotidiche per rDNA
Perché i cromosomi dei gigli contano oltre il laboratorio
I gigli da giardino sono più di fiori belli e rimedi tradizionali: sono anche modelli genetici che aiutano gli scienziati a comprendere come nascono nuove specie vegetali e come classificarle correttamente. Questo studio osserva all’interno delle cellule undici specie di giglio cinesi, molte usate come alimento o medicinale, per verificare come sono disposti e marcati i loro cromosomi. Confrontando queste strutture nascoste, gli autori chiariscono quali gigli sono davvero parenti stretti e forniscono prove per risolvere dibattiti di lunga data sugli alberi filogenetici dei gigli.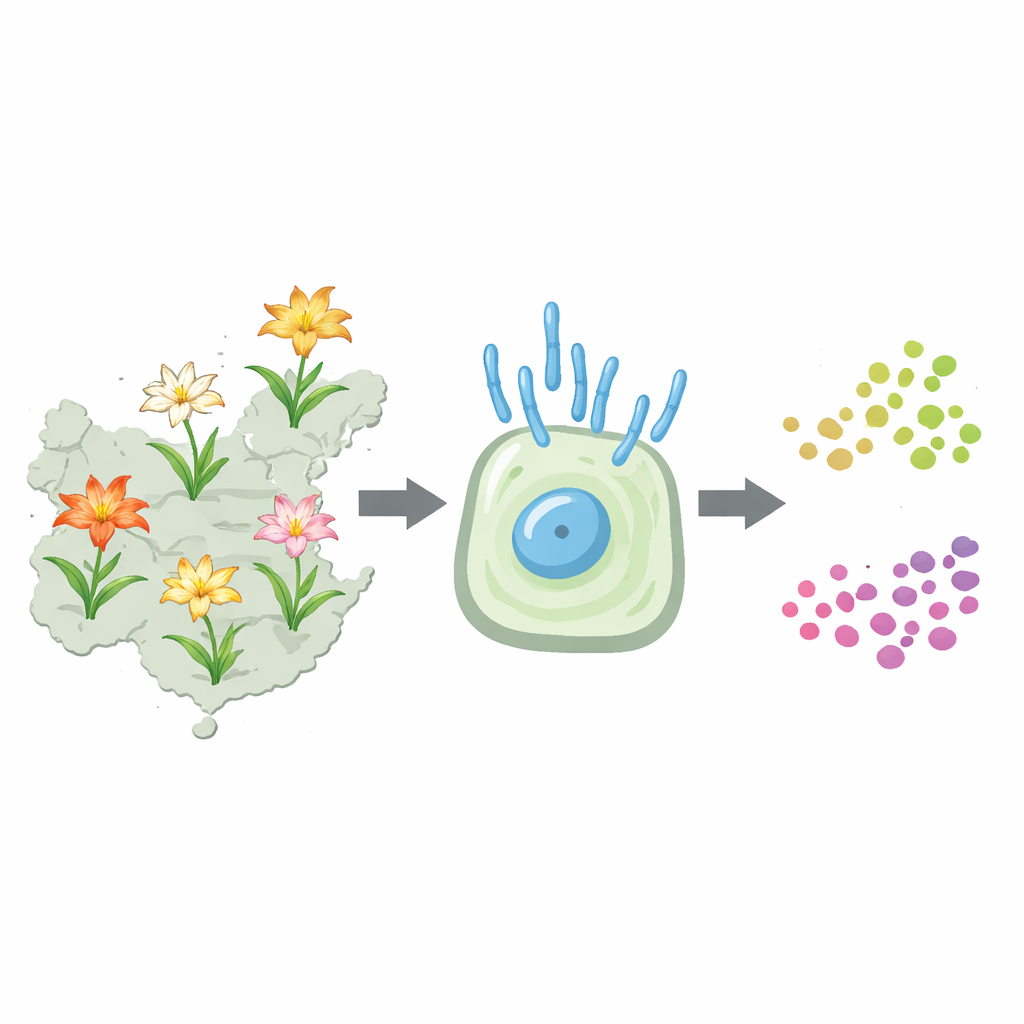
Districare un albero filogenetico dei gigli confuso
Il genere Lilium comprende circa 125 specie diffuse nell’emisfero settentrionale, con la Cina come uno dei principali centri di diversità. Per più di un secolo i botanici hanno cercato di raggruppare queste specie in sezioni naturali basandosi in gran parte su tratti visibili come la forma dei fiori. Ma fiori simili non significano sempre parentela stretta, e studi genetici di cloroplasti e nuclei talvolta hanno fornito risposte contrastanti sulle relazioni tra i gigli. In particolare, un gruppo denominato Leucolirion e le sue due sottosezioni (6a e 6b), oltre ad alcune specie del sud-ovest e del centro della Cina, sono state difficili da collocare con sicurezza.
Leggere i codici a barre sui cromosomi
Per affrontare questo problema, gli autori si sono rivolti alla citogenetica, lo studio dei cromosomi. Tutte e undici le specie esaminate condividono lo stesso corredo fondamentale di dodici cromosomi, solitamente presenti come 24 nei diploidi; due popolazioni di Lilium lancifolium erano triploidi con 36 cromosomi. Al microscopio ogni specie mostra due cromosomi più grandi e dieci più piccoli, ma sottili differenze di forma e lunghezza possono essere difficili da vedere a occhio nudo. Il team ha quindi misurato con precisione le dimensioni cromosomiche e ha utilizzato una tecnica chiamata ibridazione fluorescente in situ (FISH) per legare marche di DNA fluorescenti a specifiche regioni di DNA ribosomiale (rDNA), che agiscono come codici a barre luminosi lungo ogni cromosoma.
Trovare schemi nei genomi dei gigli
I ricercatori hanno mappato due tipi di rDNA—5S e 35S—sui cromosomi di ciascuna specie. La maggior parte dei gigli presentava un sito 5S e tra due e sei siti 35S, spesso in posizioni caratteristiche. Per esempio, quattro specie tradizionalmente collocate nella sottosezione Leucolirion 6a (L. leucanthum, L. sargentiae, L. sulphureum e L. regale) condividevano schemi molto simili di marcature rDNA sugli stessi paia di cromosomi, indicando una stretta parentela, sebbene L. regale mostrasse alcuni cambiamenti aggiuntivi. Al contrario, le specie della sottosezione sorella 6b e alcuni gigli del gruppo Sinomartagon mostravano disposizioni rDNA nettamente diverse, sottolineando una reale separazione tra questi due gruppi. Al di fuori di Leucolirion, schemi fortemente condivisi collegavano il largamente coltivato L. lancifolium a L. pumilum e L. davidii, in accordo con precedenti studi sulle sequenze di DNA che li avevano raggruppati insieme.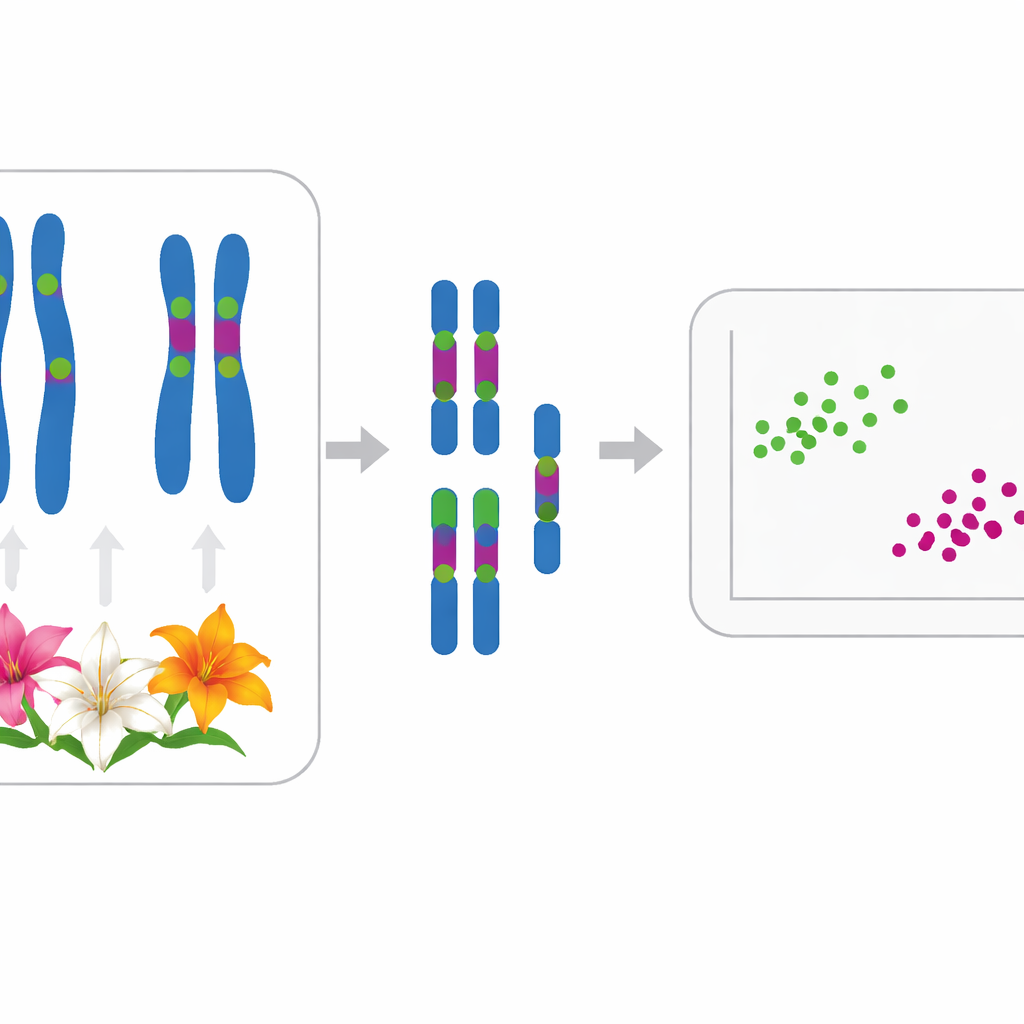
Trasformare le misure in una mappa delle relazioni
Oltre alle posizioni dei codici a barre, il team ha quantificato quanto fosse irregolare ciascun cariotipo—sia nelle posizioni dei centromeri (la “vita” del cromosoma) sia nelle lunghezze cromosomiche. Hanno utilizzato due indici statistici, MCA e CVCL, per catturare queste caratteristiche e hanno tracciato le undici specie in un grafico bidimensionale. Ogni specie occupava una propria posizione distinta, mostrando che anche cariotipi apparentemente simili possono essere distinti quando misurati con cura. Un’analisi statistica più ampia (analisi delle coordinate principali) ha quindi raggruppato i gigli in due ammassi principali che corrispondono bene alla loro storia evolutiva presunta. Un gruppo conteneva L. pumilum, L. jinfushanense, L. brownii var. viridulum, L. regale e le forme di L. lancifolium e L. davidii; l’altro raggruppava L. leucanthum, L. sargentiae, L. sulphureum, L. henryi e L. rosthornii.
Cosa significa questo per la denominazione e l’uso dei gigli
Combinando misurazioni cromosomiche dettagliate con mappe a codice a barre rDNA, questo studio mostra che le specie di giglio differiscono più nei loro cariotipi di quanto si pensasse e che queste differenze portano un chiaro segnale evolutivo. In termini pratici, il lavoro sostiene il riconoscimento della sottosezione Leucolirion 6a come gruppo naturale e ben definito all’interno del genere Lilium, in linea con recenti proposte di classificazione. Per gli allevatori, i fitoterapeuti e i pianificatori della conservazione, avere un quadro più accurato delle relazioni tra i gigli può guidare gli incroci, salvaguardare la diversità genetica e garantire che le varietà medicinali ed edibili siano identificate e utilizzate correttamente.
Citazione: Yang, YD., Jiang, XH., Zhang, BY. et al. Comparative karyotype analysis of eleven species of Lilium from China using FISH with rDNA oligo-probes. Sci Rep 16, 9446 (2026). https://doi.org/10.1038/s41598-026-37297-1
Parole chiave: Lilium, cromosomi, ibridazione fluorescente in situ, evoluzione delle piante, cariotassonomia