Clear Sky Science · it
Sviluppo e valutazione preliminare di saggi PCR in tempo reale per sei batteri lattici
Microrganismi amici dietro i cibi di ogni giorno
Molti degli alimenti sugli scaffali dei supermercati — dallo yogurt e i formaggi ai sottaceti e alle verdure fermentate — devono il loro sapore e i potenziali benefici per la salute a batteri «amici» noti come probiotici. Ma per sfruttare questi «buoni» in modo sicuro e affidabile, le aziende devono essere assolutamente certe di quali specie batteriche siano effettivamente presenti nei loro prodotti. Questo studio descrive nuovi test di laboratorio che possono identificare rapidamente e con precisione sei promettenti batteri probiotici impiegati negli alimenti, contribuendo a colmare il divario tra la microbiologia d’avanguardia e i cibi che consumiamo ogni giorno.
Perché questi batteri probiotici sono importanti
I sei batteri al centro di questo lavoro appartengono a un gruppo più ampio chiamato batteri lattici, usati da lungo tempo nelle fermentazioni. Ricerche recenti suggeriscono che possono fare molto più che acidificare latte o cavoli. Alcuni ceppi di Ligilactobacillus agilis e Ligilactobacillus salivarius potrebbero contribuire a contrastare germi intestinali dannosi, attenuare l’infiammazione e sostenere una barriera intestinale sana. Limosilactobacillus fermentum è stato associato a un migliore controllo della pressione sanguigna e ad effetti antiossidanti in studi su animali. Lactobacillus johnsonii sembra aiutare a riequilibrare il microbiota intestinale in modi che potrebbero proteggere diversi organi. Pediococcus pentosaceus e Weissella cibaria mostrano potenziale nel ridurre il colesterolo, combattere il deterioramento degli alimenti e persino sostenere la salute orale. Con una gamma così ampia di benefici potenziali, l’industria alimentare è desiderosa di utilizzare queste specie più diffusamente — ma solo se possono essere identificate con sicurezza.
La sfida di distinguere microrganismi simili
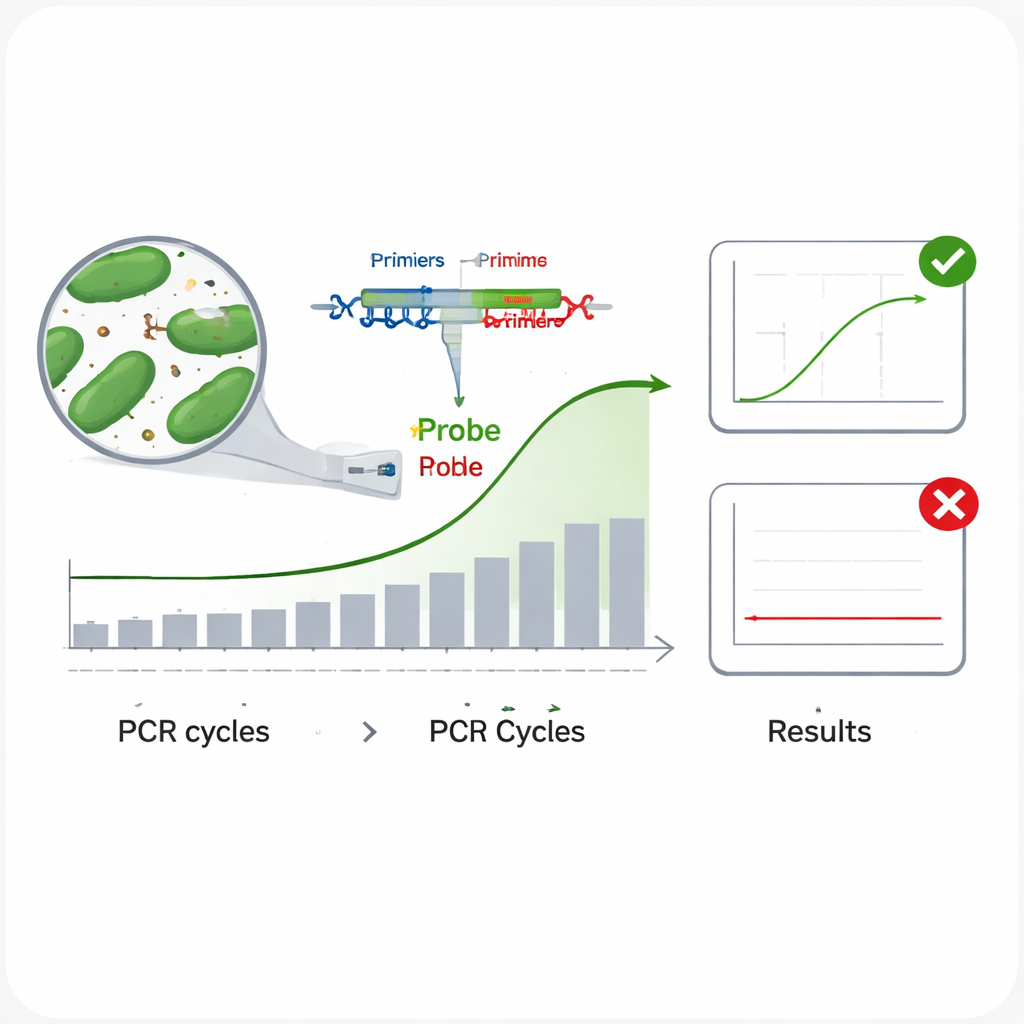
I metodi tradizionali per identificare i batteri — coltivarli in laboratorio ed eseguire test biochimici — sono lenti e richiedono molto lavoro. I metodi moderni basati sul DNA, in particolare la PCR in tempo reale, sono molto più rapidi. Nella PCR in tempo reale, brevi frammenti di DNA chiamati primer e una sonda fluorescente si legano a uno specifico tratto del codice genetico del microrganismo; quando è presente il microrganismo giusto, la macchina rileva un segnale luminoso man mano che il DNA viene copiato ciclo dopo ciclo. Il problema è che batteri strettamente correlati possono condividere DNA molto simile, quindi regioni genetiche comunemente usate come il gene 16S rRNA a volte non riescono a distinguere una specie dall’altra. Questo può portare a test che non individuano il bersaglio (falsi negativi) o che si attivano per la specie sbagliata (falsi positivi), entrambi inaccettabili per l’etichettatura dei prodotti e la sicurezza.
Progettare «codici a barre» molecolari più precisi
Per superare questo problema, i ricercatori hanno esaminato sequenze genomiche complete per trovare brevi regioni di DNA che fossero altamente conservate all’interno di ciascuna specie target e chiaramente diverse dagli altri batteri. Per ciascuno dei sei probiotici hanno progettato una coppia di primer e una sonda abbinata con lunghezza, composizione basica, temperatura di fusione e minima tendenza ad autoappaiarsi o ad appaiarsi tra loro attentamente ottimizzate. Verifiche informatiche usando il database BLAST e software di allineamento delle sequenze hanno confermato che le regioni di DNA selezionate erano stabili all’interno delle specie e distintive rispetto ai non‑bersagli. Il gruppo ha quindi messo a punto un mix di reazione standard e un programma di riscaldamento in modo che tutti i test potessero essere eseguiti in condizioni coerenti e pratiche sullo stesso tipo di strumento per PCR in tempo reale.
Mettere alla prova i nuovi saggi
Gli scienziati hanno quindi valutato come ciascun saggio si comportasse in pratica. Per testare l’inclusività — se un test può rilevare molti ceppi diversi della stessa specie — hanno eseguito ogni saggio su più campioni di DNA provenienti dal batterio target. In tutti i casi, tutti i ceppi testati hanno prodotto una chiara curva di amplificazione, suggerendo un basso rischio di non rilevare bersagli genuini. Per verificare la specificità — se il saggio ignora le specie non target — hanno sfidato ciascun test con DNA di 13 altri batteri intestinali, inclusi batteri lattici correlati e microrganismi intestinali comuni come Escherichia coli. Nessuno di questi ha prodotto un segnale, indicando un rischio molto basso di falsi allarmi. Il team ha anche esaminato l’efficienza di amplificazione eseguendo una serie di diluizioni decimali del DNA e ha confermato che tutti e sei i saggi replicavano i loro bersagli a un’efficienza di circa 95–100%, vicino all’ideale. Infine hanno misurato la precisione ripetendo le prove a due livelli di DNA e hanno riscontrato che le piccole variazioni tra ripetizioni e tra esperimenti distinti restavano ben al di sotto dei limiti accettati.
Cosa significa per i cibi del futuro
In termini semplici, gli autori hanno sviluppato sei test di “impronta” del DNA finemente calibrati che possono distinguere rapidamente, con precisione e affidabilità le specie probiotiche chiave. Pur sottolineando che sono necessari ulteriori test su più ceppi, più specie non target e su ulteriori strumenti per PCR prima di un’adozione industriale routinaria, i risultati preliminari sono incoraggianti. Per i consumatori, progressi come questo aiutano a garantire che gli alimenti pubblicizzati come contenenti probiotici specifici contengano davvero i microrganismi giusti, favorendo etichette oneste, un migliore controllo della qualità e ricerche più affidabili su come questi piccoli partner influenzano la nostra salute.
Citazione: Li, SJ., Cui, B., Li, W. et al. Development and preliminary evaluation of real-time PCR assays for six lactic acid bacteria. Sci Rep 16, 6165 (2026). https://doi.org/10.1038/s41598-026-37047-3
Parole chiave: probiotici, batteri lattici, PCR in tempo reale, microbiologia degli alimenti, identificazione microbica