Clear Sky Science · it
Predire la sopravvivenza del graft renale con un modello di machine learning basato sulla trascrittomica di biopsie “for-cause”
Perché è importante per i pazienti trapiantati
Per le persone con insufficienza renale, un trapianto può fare la differenza tra la vita in dialisi e il ritorno alle attività quotidiane. Eppure molti reni trapiantati guastano ancora anni dopo l’intervento, spesso perché il sistema immunitario del corpo attacca lentamente il nuovo organo. Questo studio esplora se i modelli di attività genica rilevati in biopsie renali di routine possano essere combinati con il machine learning moderno per individuare quali graft sono realmente in pericolo molto prima che i test standard mostrino segnali di guasto.
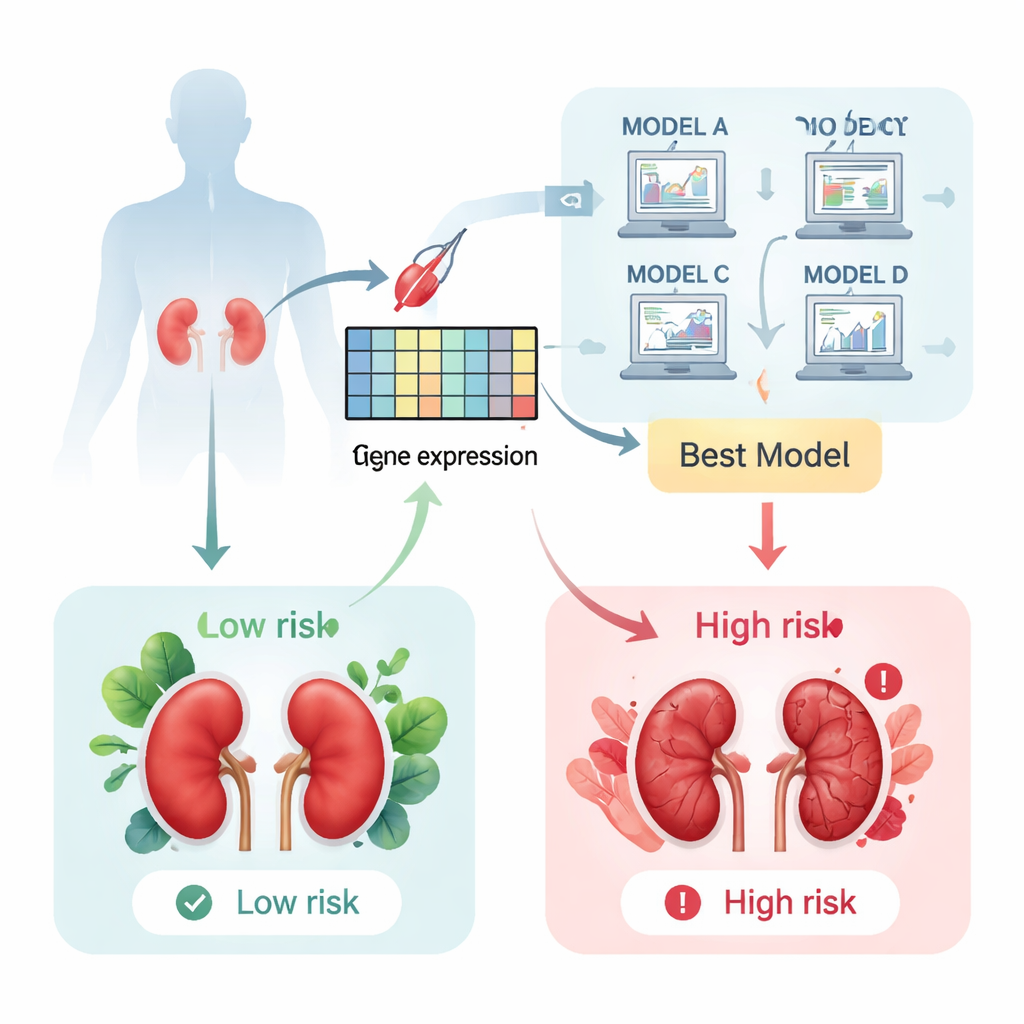
Osservare il trapianto a livello molecolare
Dopo un trapianto di rene, i medici talvolta eseguono una biopsia “for cause” quando esami del sangue o delle urine suggeriscono che l’organo potrebbe essere sotto stress. Tradizionalmente, i patologi esaminano questi campioni al microscopio per valutare il grado di danno. Gli autori di questo lavoro si sono posti una domanda diversa: i geni attivati all’interno di quei campioni di biopsia potrebbero rivelare un segnale di allarme più chiaro e più precoce di un futuro fallimento del graft? Per rispondere hanno raccolto dati di attività genica da più di 1.200 biopsie provenienti da sei collezioni di ricerca internazionali e si sono concentrati su pazienti i cui graft o sono sopravvissuti o hanno successivamente fallito.
Trovare un segnale di allarme basato su 11 geni
I ricercatori hanno prima confrontato i campioni di biopsia di pazienti che in seguito hanno perso il rene trapiantato con quelli di pazienti che hanno mantenuto una buona funzione. Hanno esaminato migliaia di geni e identificato un piccolo gruppo di 11 che risultavano costantemente più attivi nei graft destinati a fallire. Questi geni erano fortemente associati ad attivazione immunitaria e infiammazione, incluse le segnali che richiamano i globuli bianchi nel rene e ne facilitano l’attacco ai tessuti. In altre parole, le biopsie di reni che in seguito avrebbero fallito erano già “accese” da una firma immunitaria aggressiva, anche quando le misure tradizionali potevano ancora apparire accettabili.
Addestrare le macchine a prevedere la sopravvivenza del graft
Successivamente, il gruppo ha inserito i livelli di attività di questi 11 geni in una vasta gamma di approcci di machine learning progettati per prevedere per quanto tempo un rene trapiantato avrebbe continuato a funzionare. Hanno testato 117 configurazioni di modelli differenti e le hanno valutate su quanto accuratamente riuscivano a ordinare i pazienti dal rischio più basso al più alto di perdita del graft. Un tipo di algoritmo chiamato Gradient Boosting Machine è emerso come vincitore indiscusso, ordinando correttamente i pazienti con un alto grado di accuratezza. Quando il modello assegnava un punteggio di alto rischio, quei pazienti avevano una probabilità molto maggiore di perdere il graft nei successivi anni rispetto ai pazienti con punteggi bassi, come mostrato da curve di sopravvivenza che si separavano nettamente nel tempo.
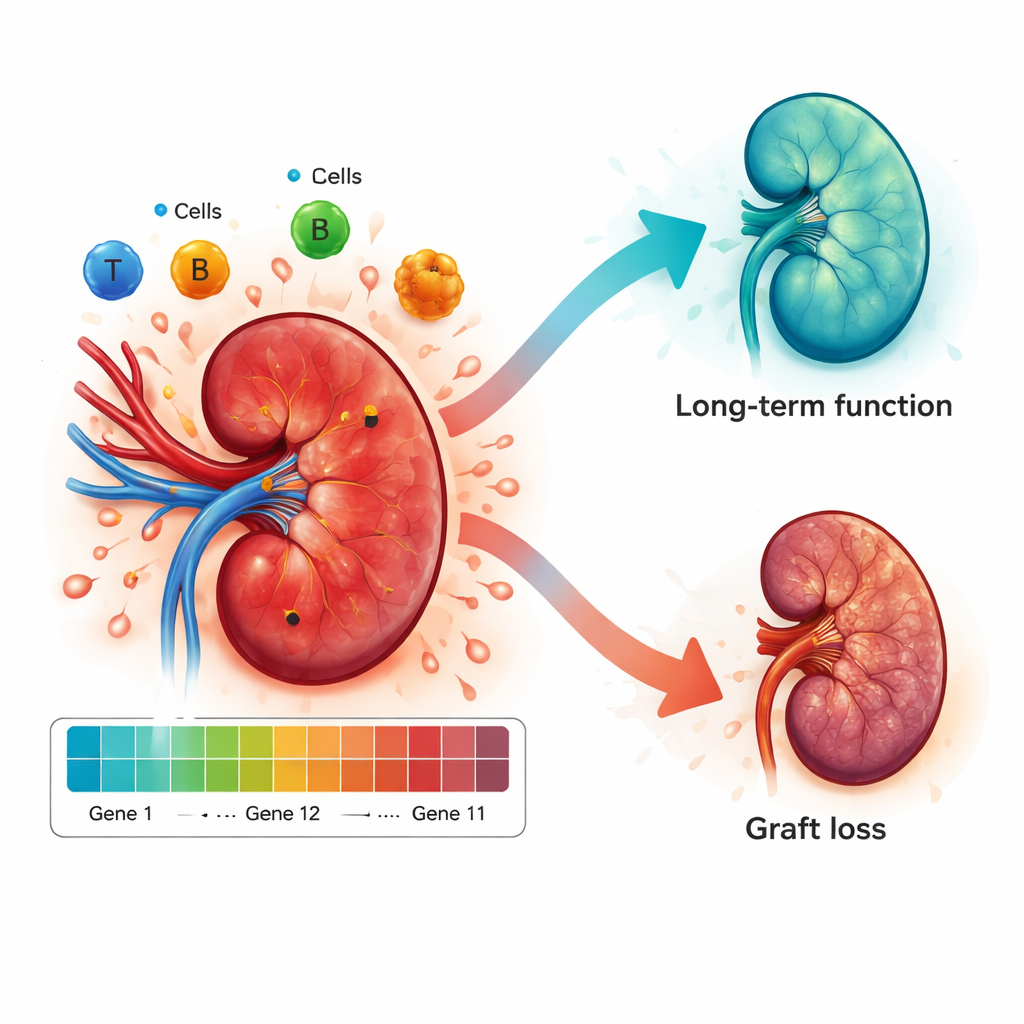
Verificare le prestazioni in nuovi gruppi di pazienti
Per essere utile in clinica, uno strumento di rischio deve funzionare oltre i dati su cui è stato costruito. Gli autori hanno quindi applicato il loro modello a 11 geni a quattro collezioni di biopsie completamente indipendenti provenienti da altri centri. In questi gruppi i tempi dettagliati di sopravvivenza non erano sempre disponibili, ma gli esperti avevano classificato ogni biopsia come indicativa di rigetto o non rigetto. Lo stesso punteggio basato sui geni si è dimostrato efficace nel distinguere il rigetto dai graft stabili, con misure di accuratezza confrontabili a molti test medici usati nella pratica. In uno studio separato in cui ai pazienti erano previste biopsie programmate a 0, 6 e 24 mesi dopo il trapianto, quelli che successivamente svilupparono danno cronico avevano già punteggi di rischio più elevati mesi prima che il danno fosse evidente al microscopio.
Cosa rivela il modello sulla battaglia immunitaria
Oltre alla previsione, i ricercatori hanno usato i pattern genici per dare uno sguardo sul paesaggio immunitario all’interno del rene. Le biopsie con punteggi di rischio elevati mostravano tipi cellulari immunitari più aggressivi, come certe popolazioni di macrofagi e cellule T, e una maggiore presenza di segnali chimici che ne favoriscono l’afflusso nell’organo. Le biopsie a basso rischio, al contrario, erano più ricche di tipi cellulari associati alla modulazione dell’infiammazione e alla promozione della riparazione tissutale. Questo suggerisce che il modello non è solo una scatola nera: il suo punteggio di rischio rispecchia processi biologici reali che spingono il rene verso il rigetto o favoriscono una pace a lungo termine tra l’organo e il sistema immunitario del ricevente.
Come questo potrebbe cambiare l’assistenza trapiantologica
Lo studio conclude che un punteggio basato su 11 geni e supportato dal machine learning, ricavato da biopsie renali di routine, può prevedere in modo affidabile quali graft sono più propensi a fallire e può segnalare problemi prima dei metodi standard. Per pazienti e clinici, uno strumento del genere potrebbe un giorno guidare cure personalizzate: gli individui ad alto rischio potrebbero ricevere monitoraggio più ravvicinato o aggiustamenti farmacologici mirati, mentre i pazienti a basso rischio potrebbero evitare procedure non necessarie. Poiché la firma utilizza solo un piccolo insieme di geni, potrebbe essere tradotta in test di laboratorio pratici con le tecnologie esistenti. Sebbene siano necessari ulteriori trial prospettici prima che entri nella pratica quotidiana, questo lavoro indica una direzione in cui letture molecolari e intelligenza artificiale aiutano a proteggere a lungo termine i reni trapiantati.
Citazione: Filho, V.O.C., Passos, P.R.C., de Andrade, L.G.M. et al. Predicting kidney graft survival with a machine learning model based on for-cause biopsy transcriptomics. Sci Rep 16, 6157 (2026). https://doi.org/10.1038/s41598-026-37038-4
Parole chiave: trapianto di rene, sopravvivenza del graft, machine learning, espressione genica da biopsia, rigetto immunitario