Clear Sky Science · it
Identificatore integrato su chip per BSI tramite corrispondenza approssimativa di k-mer
Perché la rilevazione rapida dei germi è importante
Per i pazienti sottoposti a trapianti di cellule staminali salvavita, le infezioni del flusso sanguigno possono trasformare il recupero in un’emergenza medica nel giro di poche ore. I medici sanno che ogni minuto conta, ma gli strumenti di laboratorio attuali per individuare i batteri responsabili possono essere lenti o richiedere computer potenti. Questo studio presenta un piccolo chip computerizzato a bassa energia — chiamato PC-CAM — che può scansionare rapidamente il DNA dei campioni dei pazienti e segnalare in tempo reale batteri pericolosi, potenzialmente a livello del letto del paziente in ospedale.
Il rischio di infezione dopo un trattamento che salva l’intestino
Alcuni pazienti trapiantati sviluppano una complicazione grave in cui le cellule immunitarie donate attaccano l’intestino del paziente. Un trattamento promettente è il trapianto di microbiota fecale, in cui microbi intestinali sani di un donatore vengono introdotti nel paziente. Pur potendo salvare l’intestino, questo intervento talvolta comporta un pericolo aggiuntivo: batteri dannosi dall’intestino possono fuggire nel flusso sanguigno, causando infezioni potenzialmente letali. Per curare efficacemente queste infezioni, i medici devono identificare rapidamente quali specie batteriche sono presenti, ma i test tradizionali possono richiedere ore o giorni e potrebbero non rilevare ceppi non familiari.
Dalla ricostruzione lenta dei genomi ai frammenti di DNA veloci
I moderni sequenziatori di DNA possono leggere il materiale genetico direttamente da campioni di sangue o feci in tempo quasi reale. Il collo di bottiglia non è più la lettura del DNA, ma la sua interpretazione. I metodi convenzionali cercano prima di ricostruire interi genomi da milioni di brevi frammenti di DNA e poi confrontare questi genomi assemblati con una libreria di riferimento — un processo computazionalmente gravoso. Gli autori lo sostituiscono con una strategia più semplice: spezzettano il DNA in pezzi brevi di lunghezza fissa, chiamati k-mer, e cercano direttamente questi frammenti in un database di sequenze batteriche note. Invece di richiedere una corrispondenza perfetta lettera per lettera, il loro sistema tollera un certo numero di differenze, il che gli permette di gestire gli inevitabili errori del sequenziamento e le mutazioni naturali. 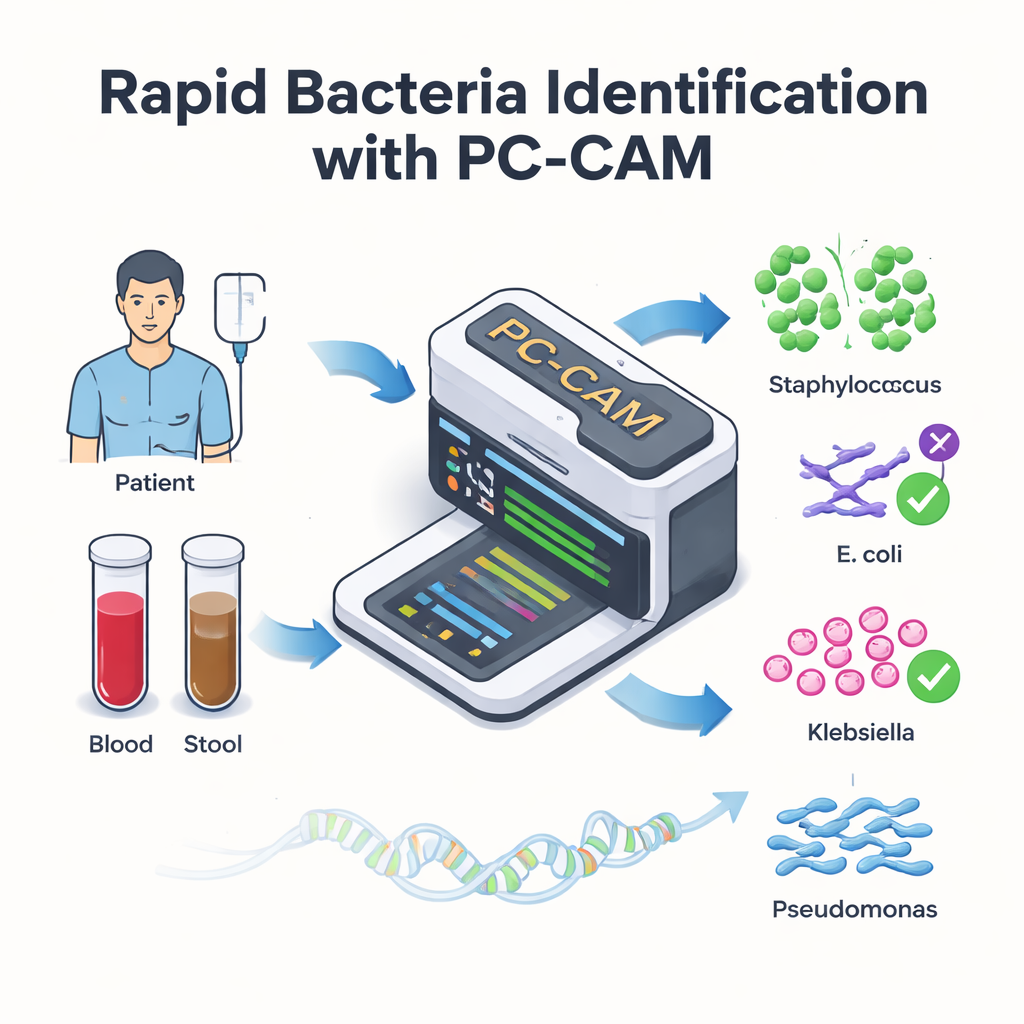
Un chip di memoria intelligente progettato per la ricerca nel DNA
Al cuore di PC-CAM c’è un tipo specializzato di memoria chiamata content-addressable memory, che può confrontare i dati in ingresso con tutto ciò che contiene simultaneamente. I ricercatori hanno progettato una versione di questa memoria per la «ricerca approssimativa» (ACAM) che può essere tarata per accettare corrispondenze vicine invece di quelle esatte. Ogni breve frammento di DNA viene codificato e memorizzato come una riga in questa memoria. Quando arriva un nuovo frammento dal campione del paziente, il chip attiva una linea di ricerca attraverso tutte le righe simultaneamente e misura la velocità con cui minuscoli segnali elettrici si scaricano. Regolando due tensioni di controllo, il sistema imposta una soglia per il numero di discrepanze che tollererà, fissando in pratica quanto deve essere permissiva la corrispondenza. Questo confronto a livello hardware permette al chip di setacciare i pattern molto più rapidamente e con meno energia rispetto a un computer general-purpose.
Quanto bene il chip trova i batteri reali
Il team ha testato PC-CAM su set di dati reali provenienti da pazienti sottoposti a trapianto di microbiota fecale, confrontando i batteri rilevati nel loro sangue e nelle feci con i risultati di un’analisi genomica completa basata su software. Anche quando il chip memorizzava solo un piccolo sottoinsieme selezionato di frammenti di DNA di ogni genoma batterico, concordava in larga misura con il metodo più dispendioso in termini computazionali, identificando correttamente agenti patogeni chiave in più pazienti. In esperimenti estesi usando letture simulate di DNA da vari batteri e diversi tassi di errore, la sensibilità del chip (la sua capacità di catturare corrispondenze vere) aumentava all’aumentare della tolleranza alle differenze, mentre la specificità (la capacità di evitare falsi allarmi) diminuiva a livelli di tolleranza molto elevati. Gli autori mostrano che semplici passaggi di post-elaborazione — come richiedere più frammenti concordanti o scartare corrispondenze deboli — possono ridurre questi falsi positivi. 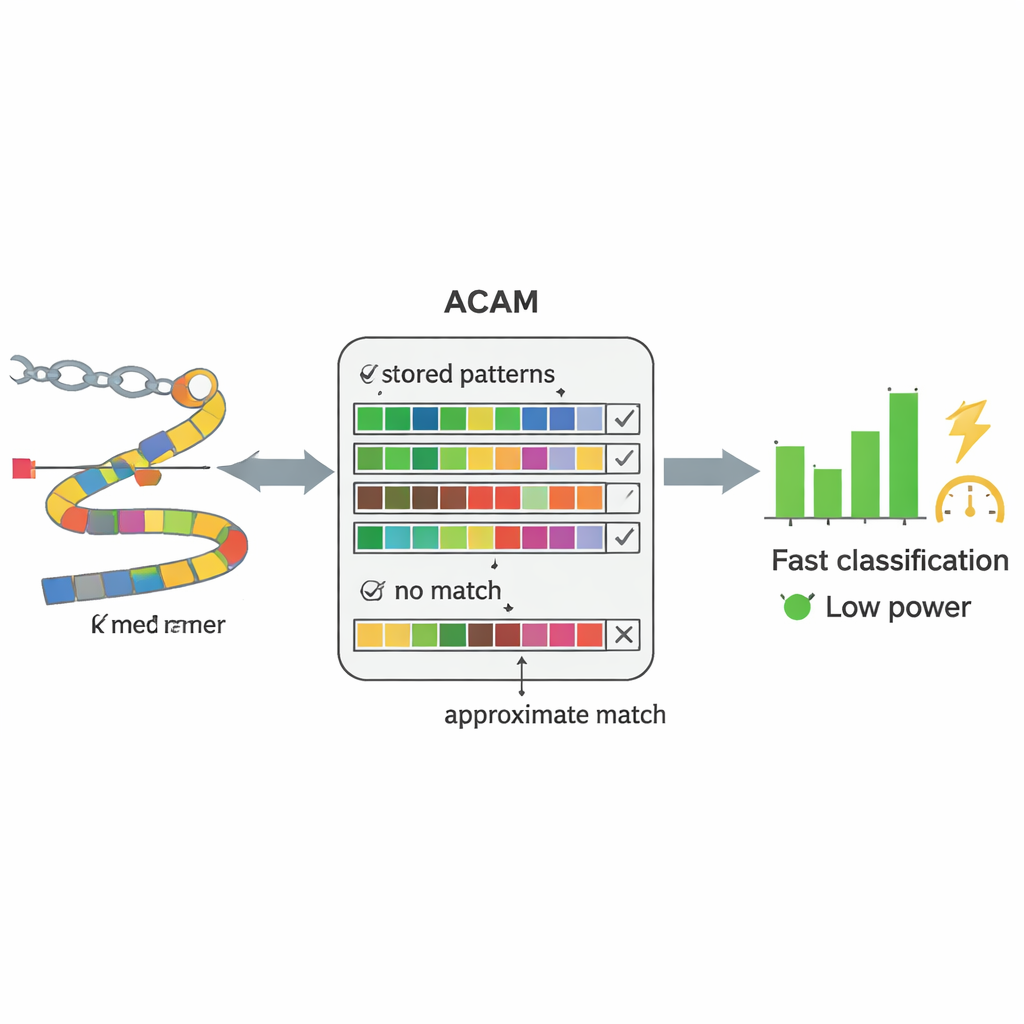
Hardware minuscolo con grande velocità e basso consumo
PC-CAM integra la memoria ACAM con un piccolo processore RISC-V su un chip di pochi millimetri quadrati, fabbricato con una tecnologia standard a 65 nanometri. Le misure su hardware reale mostrano che può classificare circa 960.000 brevi letture di DNA ogni secondo consumando intorno a 1,27 milliwatt di potenza — meno di molti orologi digitali da polso. Rispetto a un noto strumento software eseguito su un processore desktop di fascia alta, il chip è risultato circa 1.900 volte più veloce per questo tipo di attività di classificazione. Sebbene la sua accuratezza sia moderatamente ridotta dal fatto che memorizza una versione diluita di ogni genoma, gli autori sostengono che questo compromesso è accettabile quando velocità e consumo energetico sono i vincoli primari, come nelle cure d’emergenza o nei dispositivi portatili.
Cosa significa per i pazienti e oltre
In parole semplici, lo studio dimostra che un chip minuscolo e a basso consumo può fungere da motore di ricerca specializzato per il DNA batterico, individuando germi pericolosi in campioni di sangue o feci quasi istantaneamente. Pur non sostituendo un’analisi genetica completa in un laboratorio di grandi dimensioni, può fornire indicazioni rapide e sul posto su quali batteri siano presenti, aiutando i medici a scegliere antibiotici prima e con maggiore precisione. Lo stesso approccio potrebbe essere esteso al monitoraggio della resistenza agli antibiotici, al controllo di alimenti e acqua per contaminazioni o alla sorveglianza delle malattie delle colture — il tutto usando hardware compatto che porta analisi sofisticate del DNA fuori dal centro dati e più vicino ai luoghi in cui devono essere prese le decisioni.
Citazione: Garzón, E., Galindo, V., Harary, Y. et al. Integrated BSI bacteria identifier-on-chip using approximate k-mer matching. Sci Rep 16, 5722 (2026). https://doi.org/10.1038/s41598-026-36497-z
Parole chiave: infezione del flusso sanguigno, rilevamento rapido dei patogeni, sequenziamento del DNA, lab-on-a-chip, microbioma