Clear Sky Science · it
Assemblaggio del trascrittoma a lunghezza intera e sviluppo di marcatori SSR per Spinibarbus hollandi usando il sequenziamento PacBio SMRT
Perché un modesto pesce di fiume conta
Lungo i fiumi del sud della Cina nuota Spinibarbus hollandi, un pesce simile alla carpa apprezzato sia come alimento sia come specie ornamentale. Gli allevatori vorrebbero crescerlo in modo più efficiente, ma il pesce cresce lentamente, raggiunge la maturità tardi e produce relativamente poche uova. Lo studio descritto qui usa strumenti di sequenziamento del DNA e dell'RNA all'avanguardia per costruire una dettagliata “lista dei componenti” genetici per questa specie. Queste informazioni genetiche possono infine aiutare gli allevatori a selezionare esemplari più robusti e a crescita più rapida e sostenere la conservazione delle popolazioni selvatiche.
Trasformare molti tessuti in una mappa genetica
Per catturare quante più informazioni genetiche possibile, i ricercatori hanno prelevato sei diversi tessuti — cuore, branchia, cervello, pinna, fegato e gonade — da sei maschi e femmine adulti. Da questi tessuti hanno estratto l'RNA, la molecola che porta copie dei geni attivi all'interno delle cellule. Utilizzando una tecnologia chiamata PacBio SMRT, che legge tratti molto lunghi di copie di RNA, hanno assemblato il primo trascrittoma a lunghezza intera per S. hollandi. In termini semplici, hanno costruito un catalogo ad alta risoluzione di 15.197 geni distinti e 23.403 sequenze trascrizionali, la maggior parte delle quali molto più lunghe e complete rispetto a quanto possono produrre i metodi più vecchi a letture corte.
Ciò che i geni rivelano sul pesce
Successivamente, il team ha chiesto cosa fanno effettivamente questi geni. Hanno confrontato ciascuna sequenza con grandi banche dati pubbliche che raggruppano i geni per funzione. Più del 95% dei geni è stato associato a voci note, un tasso di successo molto elevato che indica buona qualità dei dati. Molti geni rientravano in categorie legate ad attività cellulari di base come il metabolismo, la trasmissione di segnali e lo sviluppo, e la maggior parte somigliava particolarmente a geni di altri pesci della famiglia delle carpe. Questo conferma che il nuovo trascrittoma è biologicamente valido e fornisce una base per individuare geni legati a tratti come tasso di crescita, tolleranza allo stress e riproduzione in S. hollandi.
Strati nascosti di controllo nell'RNA
Oltre a identificare i geni, gli scienziati hanno anche esaminato come questi geni siano regolati. Hanno trovato 373 casi di splicing alternativo, in cui lo stesso gene viene tagliato e ricombinato in modi diversi per creare messaggi di RNA distinti. Il modello più comune conservava porzioni di RNA che spesso vengono rimosse in altre specie, suggerendo un modo particolare con cui questo pesce affina le sue proteine. Hanno anche scoperto 2.397 RNA lunghi non codificanti — molecole di RNA che non producono proteine ma possono regolare quando e dove altri geni si attivano. Insieme, questi risultati mostrano che S. hollandi utilizza un ricco insieme di controlli a livello di RNA che potrebbero influenzare la crescita, la maturazione sessuale e l'adattamento agli ambienti locali.
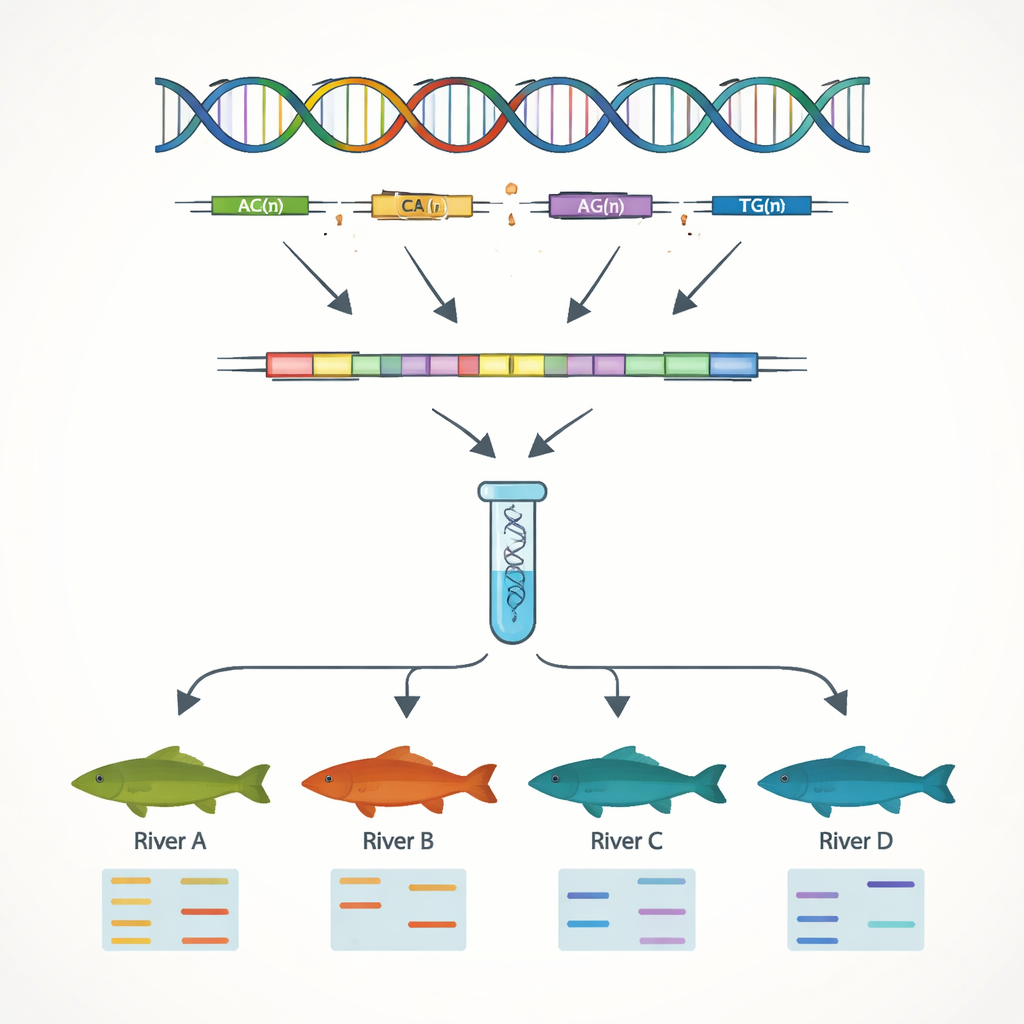
Costruire punti di riferimento del DNA per allevamento e conservazione
Un obiettivo principale del lavoro era sviluppare marcatori di DNA semplici che possano distinguere individui e popolazioni. Concentrandosi sulle sequenze geniche, gli autori hanno ricercato ripetizioni di sequenze semplici, o SSR — brevi motivi di DNA come “AC” o “AAT” ripetuti molte volte di seguito. Questi tratti tendono a variare tra gli individui, rendendoli utili come codici genetici. Hanno individuato 7.449 siti SSR e progettato decine di primers brevi per amplificarli in laboratorio. Tredici di questi marcatori si sono rivelati altamente variabili e affidabili quando testati su 51 pesci provenienti da quattro bacini fluviali. Utilizzando solo questi 13 marcatori, il team ha potuto rilevare chiaramente differenze genetiche tra le popolazioni del Fiume Azzurro (Yangtze) e quelle del Fiume Perla, a riflesso delle catene montuose che limitano il mescolamento naturale tra i bacini.
Cosa significa per gli allevatori e i fiumi
Per i non specialisti, la conclusione chiave è che gli autori hanno creato un riferimento genetico dettagliato e di alta qualità per S. hollandi e un insieme di marcatori di DNA pratici. Questo kit di strumenti aiuterà i ricercatori a individuare i geni alla base della crescita lenta o della bassa fertilità, assisterà gli allevatori nella selezione di riproduttori con tratti desiderabili e permetterà ai conservazionisti di monitorare la diversità genetica tra i sistemi fluviali. Pur essendo necessario ulteriore lavoro per collegare geni specifici alle prestazioni in vasca o in natura, questo studio pone le basi molecolari per trasformare un tradizionale pesce di fiume in una specie di acquacoltura moderna e gestita in modo sostenibile.
Citazione: Li, S., Lai, J., Wu, M. et al. Full-Length transcriptome assembly and SSR marker development for Spinibarbus hollandi using PacBio SMRT sequencing. Sci Rep 16, 5629 (2026). https://doi.org/10.1038/s41598-026-36468-4
Parole chiave: Spinibarbus hollandi, trascrittoma di pesce, sequenziamento PacBio, marcatori microsatellite, genetica dell'acquacoltura